2016 Dr. Walter F. de Azevedo Jr.
|
|
|
- Clara Álvaro Mendonça
- 6 Há anos
- Visualizações:
Transcrição
1 2016 Dr. Walter F. de Azevedo Jr
2 Trabalho 1 o Abaixo temos uma lista de programas a serem desenvolvidos na aula de hoje. Os programas são aplicações diretas de equações, assim o programa bhaskara.py, visto na aula 1, pode ser usado como protótipo para o desenvolvimento deles. Os conceitos de física e biologia apresentados são normalmente discutidos em cursos introdutórios de graduação. A partir do estudo dos pseudocódigos apresentados, é relativamente simples a implementação do código em Python. Programas para o Trabalho 1 1) Área acessível ao solvente de proteínas (versão 1) (programa: asa1.py) 2) Área acessível ao solvente de proteínas (versão 2) (programa: asa2.py) 3) Energia livre de Gibbs para o sistema proteína-ligante (programa: freeenergy.py) 2
3 Trabalho 1 o Para desenvolvermos os programas freeenergy.py temos que fazer uso de métodos matemáticos disponíveis no módulo math da linguagem Python. Para o uso desses métodos matemáticos, precisamos chamar o módulo math, com o comando import indicado abaixo. import math A linha acima tem que aparecer antes de qualquer uso dos métodos matemáticos do módulo math. Por convenção, colocamos a linha acima logo após a última linha do cabeçalho do programa, se este existir. A descrição completa das funções disponíveis módulo math podem ser acessadas em: < >. Acesso em 14 de agosto de
4 Trabalho 1 o A seguir temos a lista das principais funções matemáticas do módulo math. Funções matemáticas Funções do módulo math Exemplos de implementação Arco-seno, arco-cosseno, arcotangente Funções trigonométricas hiperbólicas Inversas das funções trigonométricas hiperbólicas math.asin(x), math.acos(x), math.atan(x) math.sinh(x), math.cosh(x), math.tanh(x) math.asinh(x), math.acosh(x), math.atanh(x) function1 = math.asin(x) function2 = math.acos(x) function3 = math.atan(x) function1 = math.sinh(x) function2 = math.cosh(x) function3 = math.tanh(x) function1 = math.asinh(x) function2 = math.acosh(x) function3 = math.atanh(x) Número de Euler math.e function1 = math.e Potência na base e math.exp(x) function1 = math.exp(x) Logaritmo na base y math.log(x,y) function1 = math.log(x,y) 4
5 Programa: asa1.py Área acessível ao solvente de proteínas (versão 1) Programa: asa1.py Resumo O programa asa1.py usa uma equação empírica para o cálculo aproximado da área acessível ao solvente de uma proteína. A entrada é a massa molecular da proteína em Daltons, variável (molweight). A saída é área acessível ao solvente em Å2, variável area. O cálculo é uma aproximação válida para proteínas monoméricas, publicada em: LESK Arthur M. Introduction to Protein Architecture. Oxford: Oxford University Press, página 27. A equação em Python para o cálculo da ASA é a seguinte: area= 11.1*(molWeight)**(2/3). 5
6 Programa: asa1.py Diversos programas gráficos permitem a visualização molecular, como a representada abaixo para o aminoácido alanina. A representação da figura é chamada CPK, referente aos nomes dos cientistas que a propuseram (Corey, Pauling e Koltun) (COREY e PAULING, 1953; KOLTUN, 1965). A figura abaixo foi gerada com o programa VMD (visual molecular dynamics, disponível em: )(HUMPHREY et al, 1996). As esferas em ciano representam os átomos de carbono, em branco os átomos de hidrogênio, vermelho para oxigênio e azul para o nitrogênio. Os bastões são ligações covalentes entre os átomos. VMD é o acrônimo para visual molecular dynamics. 6
7 Programa: asa1.py Abaixo temos a representação de van der Waals do aminoácido alanina, onde os átomos são desenhados como esferas com o raio de van der Waals. Esta representação mostra a superfície de van der Waals, definida pela área contínua das superfícies esféricas. A tabela abaixo mostra os raios de van der Waals dos principais átomos encontrados em moléculas biológicas. Átomo Raio de van der Waals (Å) H 1,20 C 1,85 N 1,54 O 1,40 P 1,90 S 1,85 Na figura as esferas representam átomos, onde o raio de cada esfera é o raio de van der Waals. O código de cores é o mesmo usado para representação CPK. 7
8 Programa: asa1.py A superfície molecular é a superfície de van der Waals suavizada nas reentrâncias, pois consideramos uma molécula de água esférica rolando sobre a superfície de van der Waals. Esta molécula de água é chamada sonda. Quando aplicada à uma proteína permite a visualização de cavidades na superfície proteica. Superfície molecular A superfície molecular do aminoácido alanina. O código de cores é o mesmo usado para representação CPK. Simplificação da representação da molécula de água, como uma esfera de raio de 1,4 Å. 8
9 Programa: asa1.py As proteínas em solução permitem a interação de moléculas de água com sua estrutura. A área acessível ao solvente (ASA, para accessible surface area) é um parâmetro geométrico usado para analisar a interação de ligantes e água com a superfície da proteína. O conceito de tal parâmetro é relativamente simples. Imagine uma molécula de água deslizando sobre a superfície da proteína, uma molécula esférica com um raio 1,4 Å é usada na representação, como mostrado abaixo. Esta forma esférica para a molécula de água não é realista, mas é uma boa aproximação para nossos propósitos. A superfície acessível ao solvente é traçada pelo movimento do centro da esfera do solvente, indicada pela linha tracejada. Superfície acessível ao solvente Molécula de água Simplificação da representação da molécula de água, como uma esfera de raio de 1,4 Å. Cada átomo está representado por uma esfera, onde o raio é o de van der Waals. Superfície molecular ASA é o acrônimo em inglês para accessible surface area. 9
10 Programa: asa1.py Há uma equação simples (LESK, 2001), que relaciona a massa molecular em Daltons (MM) de uma proteína monomérica, com sua área acessível ao solvente (ASA), esta equação é uma aproximação, mas pode ser usada para termos uma ideia preliminar da ASA. O resultado sai em angstroms ao quadrado (Å 2 ). ASA = 11,1 (MM) 2/3 Superfície acessível ao solvente Cada átomo está representado por uma esfera, onde o raio é o de van der Waals. Molécula de água Superfície molecular Simplificação da representação da molécula de água, como uma esfera de raio de 1,4 Å. Referência para a equação da área acessível ao solvente: LESK A. M. Introduction to Protein Architecture. Oxford University Press, Oxford UK, 2001, página
11 Programa: asa1.py Vamos preparar o pseudocódigo para o cálculo da área acessível ao solvente de uma proteína, para a qual sabemos a massa molecular (MM). O algoritmo é bem simples, temos como variável independente o MM (molweight) e a saída é a área acessível ao solvente (area). A equação fica da seguinte forma: area = 11,1 (molweight) 2/3 O pseudocódigo está no quadro abaixo. O cálculo só é efetuado se a massa molecular for maior que zero, caso contrário é mostrada uma mensagem de erro. Início Fim Leia (molweight) Se (molweight > 0) area = 11.1*(molWeight)**(2/3) Escreva \nárea acessível ao solvente :, area, A^2 \n Senão Escreva Erro! A massa molecular deve ser > 0! 11
12 Programa: asa1.py Teste o seu programa para os valores de massas moleculares indicados abaixo. Na tabela temos as massas moleculares em Daltons e a área acessível ao solvente em Å 2. Os números estão em notação inglesa, ou seja, com ponto decimal. Proteína Fonte Massa molecular (Daltons) * ASA (Å 2 ) Mioglobina Physeter catodon CDK2 Homo sapiens Protease (monômetro) Chiquimato quinase HIV Mycobacterium tuberculosis A informação sobre as massas moleculares (MW) das proteínas foi obtida da base de dados Protein Data Bank (PDB)( ). 12
13 Programa: asa1.py Referências relacionadas ao programa asa1.py -COREY, RB; PAULING L. Molecular models of amino acids, peptides and proteins. Review of Scientific Instruments, Nova York, v. 24, n.8, p , HUMPHREY W; DALKE A; SCHULTEN K. VMD - Visual Molecular Dynamics. Journal of Molecular Graphics, Amsterdã, v.14, p.33-38, KOLTUN WL. Precision space-filling atomic models. Biopolymers, Hoboken, v.3, n.6, p , LESK, Arthur. M. Introduction to Protein Architecture. Oxford: Oxford University Press, p. -Proteopedia. Disponível em: < >. Acesso em 14 de agosto de
14 Programa: asa2.py Área acessível ao solvente de proteínas (versão 2) Programa: asa2.py Resumo O programa asa2.py calcula a área acessível ao solvente de uma proteína de forma similar ao programa asa1.py. A modificação ocorre na entrada, que agora é o número de resíduos de aminoácidos. A massa molecular da proteína é calculada multiplicando-se o número de resíduos por 118,89 Daltons, que é a massa molecular média de cada aminoácido. A saída é área acessível ao solvente em Å 2. O cálculo é uma aproximação válida para proteína monoméricas, publicada em: LESK Arthur. M. Introduction to Protein Architecture. Oxford: Oxford University Press, página 27. A equação em Python para o cálculo da ASA é a seguinte: area= 11.1*(molWeight)**(2/3). 14
15 Programa: asa2.py O programa anterior (asa1.py) calcula a área acessível ao solvente de proteínas, a partir do conhecimento da massa molecular. Podemos modificar o programa asa1.py para que o novo programa (asa2.py) considere o número de resíduos de aminoácidos como entrada. Normalmente usamos a unidade Dalton (Da) para medir a massa molecular de aminoácidos e moléculas biológicas em geral. Um Dalton equivale à massa de 1/12 do átomo de carbono 12. Para proteínas usamos o kilodalton (kda), 1 kda = 10 3 Da. Na figura ao lado, temos o aminoácido alanina, que apresenta uma massa molecular de 89,09 Da, e uma proteína chamada lisozima, que apresenta uma massa molecular de 14331,20 Da. Usaremos o símbolo MM para representarmos a massa molecular. Alanina (MM= 89,09 Da) Lisozima de ovo de galinha (MM = 14331,20 Da ou 14,331 kda). Código PDB: 6LYZ. As figuras não estão na mesma escala. 15
16 Programa: asa2.py Considerando-se a massa molecular de cada resíduo de aminoácido, temos uma massa molecular média de 118,89 Da. Este valor médio é útil na estimativa da massa molecular aproximada de proteínas e peptídeos, a partir do conhecimento do número de resíduos de aminoácidos presentes na molécula. A equação abaixo indica a massa molecular aproximada (MM), MM = 118,89. N aa onde N aa é o número de resíduos de aminoácidos presentes na molécula. No exemplo ao lado temos a CDK2 (cyclindependente kinase)(quinase dependente de ciclina 2), com massa molecular de 34331,25 Da e 298 resíduos de aminoácidos. CDK2 humana (MW = 34331,25 Da ) Código PDB: 2A4L. A massa molecular calculada pela equação, é de MM = 35429,22 Da, aproximadamente 3,2 % maior que a massa molecular precisa da proteína. A equação é útil para aproximações. 16
17 Programa: asa2.py A nova versão do programa, usa como entrada o número de resíduos de aminoácidos da proteína (vale para peptídeos também). Vamos preparar o pseudocódigo para o cálculo da área acessível ao solvente de uma proteína, para a qual sabemos número de resíduos de aminoácidos (numres). Temos como variável independente o numres e a saída é a área acessível ao solvente (area). Assim temos que incluir uma linha adicional de código para calcular a massa molecular (molweight), como na equação indicada abaixo: molweight = *numRes A equação para a área acessível ao solvente é a mesma: area = 11.1 (molweight) 2/3 O pseudocódigo está no quadro abaixo. O cálculo só é efetuado se o número de resíduos for maior que zero, caso contrário é mostrada uma mensagem de erro. Início Fim Leia (numres) Se (numres> 0) molweight = *numRes area = 11.1*(molWeight)**(2/3) Escreva Área acessível ao solvente :, area, A^2 \n Senão Escreva O número de resíduos de aa deve ser > 0! 17
18 Programa: asa2.py Teste o seu programa para os valores de número de resíduos de aminoácidos mostrados abaixo. Na tabela temos o número de resíduos de aminoácidos para cada proteína e a área acessível ao solvente em Å 2. Os números estão em notação inglesa, ou seja, com ponto decimal. Proteína Fonte Número de resíduos de aa * ASA (Å 2 ) Mioglobina Physeter catodon CDK2 Homo sapiens Protease HIV Chiquimato quinase Mycobacterium tuberculosis A informação sobre os números de resíduos de aminoácidos das proteínas foi obtida da base de dados Protein Data Bank (PDB)( ). 18
19 Programa: asa2.py Referências relacionadas ao programa asa2.py -COREY, RB; PAULING L. Molecular models of amino acids, peptides and proteins. Review of Scientific Instruments, Nova York, v. 24, n.8, p , HUMPHREY W; DALKE A; SCHULTEN K. VMD - Visual Molecular Dynamics. Journal of Molecular Graphics, Amsterdã, v.14, p.33-38, KOLTUN WL. Precision space-filling atomic models. Biopolymers, Hoboken, v.3, n.6, p , LESK Arthur. M. Introduction to Protein Architecture. Oxford: Oxford University Press, p. -VOET Donald; VOET Judith G.; PRATT Charlotte W. Fundamentos de Bioquímica. Porto Alegre: Artmed Editora SA, p. 19
20 Programa: freeenergy.py Energia livre de Gibbs para o sistema proteínaligante Programa: freeenergy.py Resumo Programa para calcular a energia livre de Gibbs de ligação. O foco é no uso para o estudo da interação proteína-ligante. Os dados de entrada são a temperatura em Celsius (tempcelsius) e a constante de dissociação (Kd) em molar, chamada de variável dissconst. A saída é a energia livre de Gibbs em J/mol (deltag). A equação da energia livre de Gibbs usa a constante dos gases. O valor foi obtido da base de dados NIST, e vale gasconst= J mol -1 K -1, disponível em: < >. Acesso em 14 de agosto de 2016 A energia livre de Gibbs (deltag) é dada pela seguinte equação: deltag= gasconst*tempkelvin*math.log(dissconst). 20
21 Programa: freeenergy.py Consideremos um sistema biológico formado por uma proteína (P) e um ligante (L) em solução, sendo que o ligante é uma pequena molécula que apresenta afinidade pela proteína, por exemplo, o fármaco indinavir que inibe a protease do HIV-1, o agente causador da AIDS. Tal sistema possibilita a formação de um complexo binário proteína-ligante (PL), com constante de reação indicada por k 1 e constante reversa de reação dada por k -1, ambos descritos na equação reversível abaixo, P + L k 1 k -1 PL A reação pode ser caracterizada pela constante de equilíbrio (K eq ). Na prática são usadas as constantes de dissociação (K d ) e inibição (K i ). Formação do complexo proteína (P) com ligante (L), complexo proteína-ligante (PL). A estrutura em destaque é o complexo protease do HIV-1 (P) e o fármaco indinavir (L), usado no tratamento contra a AIDS. 21
22 Programa: freeenergy.py As interações entre o inibidor de CDK2 (Cyclin-Dependent Kinase) (roscovitine mostrado ao lado) e a proteína alvo (CDK2) são não covalentes. Tais contatos intermoleculares apresentam uma interação energética favorável, o que leva o equilíbrio da reação química para o lado da formação do complexo binário (PL). P + L k 1 k -1 PL A análise da energia da interação proteína-ligante, indica a formação de um composto de transição, onde a energia do sistema é elevada e o composto formado instável. Tal estado é chamado estado de transição, e a reação caminha para uma menor energia, com a formação do complexo binário PL, mostrada no próximo slide. Estrutura molecular do inibidor de CDK2 roscovitine. A figura foi gerada com o programa VMD e a opção CPK. As coordenadas foram extraídas do arquivo PDB: 2a4l. 22
23 Energia Programa: freeenergy.py + Proteína + Ligante Estado de transição Complexo proteína-ligante E a = Energia de ativação para associação E d = Energia de ativação para dissociação E a E = Variação total da energia E d E Coordenada da interação 23
24 Programa: freeenergy.py Podemos representar a formação do complexo proteína-ligante (PL), a partir dos componentes proteína (P) e ligante (L), como esquematizado abaixo. Temos a proteína (P) e o ligante (L) em solução, no caso do ligante apresentar afinidade pela proteína, o equilíbrio da reação será favorável à formação do complexo proteínaligante (PL). P + L PL k 1 k -1 24
25 Programa: freeenergy.py No caso do complexo binário proteínaligante (PL) apresentar uma energia menor que as moléculas livres (proteína e ligante sem interação), a formação do complexo proteína-ligante ocorrerá de forma espontânea, ou seja, sem a necessidade de fornecimento de energia para que ocorra a formação. Uma forma de estudar a formação do complexo binário, é a partir da avaliação da variação de energia livre de Gibbs ( G), definida pela seguinte equação, P PL G = H -T S onde H é a entalpia do sistema proteínaligante, T é a temperatura e S é a variação da entropia do sistema. Na figura acima temos a formação espontânea de um complexo binário proteína-ligante, pois este apresenta energia menor que das moléculas livres (proteína 25 e ligante sem interação) L
26 Programa: freeenergy.py O termo H indica a entalpia do sistema, que representa as forças moleculares envolvidas nas interações proteínaligante. O termo S é a variação da entropia do sistema, que pode ser entendida como a quantidade de energia que não pode ser convertida em trabalho. Na equação anterior, o produto da temperatura absoluta (T) pela variação da entropia ( S), indica que um aumento da entropia favorece a formação do complexo binário. P Se G < 0 PL Um valor negativo de G indica formação espontânea do complexo. G = H -T S Se G > 0 Com G > 0 a reação não é favorável à formação do complexo, como na figura inferior. Com G < 0 temos uma reação favorável à formação do complexo, como 26 na figura superior. L
27 Programa: freeenergy.py Quando o sistema proteína-ligante está em equilíbrio, a formação do complexo binário e a dissociação ocorrem, assim a constante de equilíbrio (K eq ) da reação é dada por, K eq k k 1 1 PL P L onde os termos [P], [L], [PL] indicam as concentrações molares da proteína, ligante e complexo proteína-ligante, respectivamente. A partir da análise dimensional da constante de equilíbrio, vemos claramente que sua unidade é M -1. Estrutura do complexo entre a proteína quinase dependente de ciclina 2 (Cyclin-Dependent Kinase 2, CDK2) e o inibidor roscovitine. 27
28 Programa: freeenergy.py A variação da energia livre de Gibbs da interação intermolecular entre proteína e ligante é dada pela seguinte equação, G G o [PL] RT ln( ) [P][L] onde G o é a variação da energia livre de Gibbs padrão, ou seja, a variação em G que acompanha a formação do complexo no estado padrão de equilíbrio (temperatura de 25 o C, pressão de 100 kpa). Estrutura cristalográfica da protease do HIV-1 em complexo com inibidor. 28
29 Programa: freeenergy.py No equilíbrio termodinâmico temos G = 0 (estado estacionário), assim a equação fica da seguinte forma, 0 G G o o RT ln( [PL] RT ln( ) [P][L] [PL] ) [P][L] O termo G o é chamado variação na energia livre de Gibbs da ligação ( G binding ), assim temos, G binding RT ln( [PL] ) [P][L] 29
30 Programa: freeenergy.py De uma forma geral, podemos expressar a afinidade proteína-ligante pela variação da energia livre de Gibbs ( G binding ), quanto menor a energia, maior a afinidade do ligante pela proteína. Tal grandeza física depende das concentrações do complexo proteínaligante [PL], das concentrações da proteína [P] e do ligante [L], bem como da temperatura. O R (R=1,99 cal/mol.k = 8, J/mol.K)( na equação indica a constante dos gases). G G G binding binding binding [ PL] RTln( ) [ P][ L] 1 RTln( K RTln( K A constante de dissociação (K d ) é dada por: d [ P][ L] K d [ PL] Podemos calcular a energia livre de uma interação proteína-ligante, a partir da constante de dissociação determinada experimentalmente. d ) ) RTln( K Fonte da informação sobre as constantes físicas: Acesso em 14 de agosto de d )
31 Programa: freeenergy.py Vamos considerar o estudo do desenvolvimento de fármacos contra o HIV. Vimos que um alvo para o desenho de fármacos contra HIV é a protease do HIV-1. Os dados sobre a constante de dissociação (K d ) de 4 inibidores da protease 1 estão indicados na tabela abaixo, todos tomados na temperatura de 25 º C. As estruturas são mostradas ao lado. A partir dessa informação, calcularemos a variação na energia livre de Gibbs da ligação ( G binding ). Inibidor K d (nm) G binding (kj/mol) Indinavir 1,07 Saquinavir 0,31 Ritonavir 0,6 Nelfinavir 0,0122 Estruturas de alguns inibidores da protease do HIV.-1 A) Indinavir. B) Saquinavir. C) Ritonavir. D) Nelfinavir. 31
32 Programa: freeenergy.py Estudo do indinavir. As constantes de dissociação foram determinadas a uma temperatura de 25 º C, para converter para Kelvin é só somar 273,15, assim temos T= 298,15 K G R.T.ln(K ) 8, ,15. ln 1, ,9569. ln 1,07.10 G G binding binding binding d 2478, ,2 kj/mol.(-20,6556) ,342 J/mol Inibidor K d (nm) G binding (kj/mol) Indinavir 1,07-51,2 Saquinavir 0,31 Ritonavir 0,6 Nelfinavir 0,0122 Estrutura molecular do fármaco indinavir. A figura foi gerada com o programa VMD e a opção CPK. As coordenadas foram extraídas do arquivo PDB: 1hsg. 32
33 Programa: freeenergy.py Repetindo o cálculo para os outros inibidores, chegamos à tabela abaixo. A partir da análise desta tabela vemos que o inibidor que apresenta menor energia livre de Gibbs de ligação é o nelfinavir, cujo a estrutura do complexo proteína-ligante está mostrada abaixo. Inibidor K d (nm) G binding (kj/mol) Indinavir 1,07-51,2 Saquinavir 0,31-54,3 Ritonavir 0,6-52,6 Nelfinavir 0, ,3 33
34 Programa: freeenergy.py Para implementar a equação para energia livre de Gibbs, usamos como entrada a temperatura em graus Celsius (tempcelsius) e a constante de dissociação (dissconst) em molar. Temos que inicialmente converter a temperatura em Celsius para Kelvin, como segue: tempkelvin = tempcelsius A equação para a energia livre de Gibbs (deltag) fica da seguinte forma: deltag= gasconst*tempkelvin*math.log(dissconst) O resultado será em J/mol. O valor da constante molar dos gases foi obtido de (Acesso em 16 de março de 2015). 34
35 Programa: freeenergy.py O pseudocódigo está no quadro abaixo. Escreva o seu código fonte e teste para os 4 valores de constante de dissociação indicados nos slides anteriores. Lembre-se que a constante de dissociação está em nanomolar, ou seja, para entrar os dados temos que usar notação científica, por exemplo: 1,07 nm = 1.07e-9. Usaremos o método math.log(x) para o logaritmo natural. Só efetuamos o cálculo da energia livre de Gibbs, se a constante de dissociação for maior que zero e a temperatura em Celsius for maior que , caso contrário mostramos uma mensagem de erro. Início Chama módulo math Definição da constante: gasconst= Leia (tempcelsius, dissconst) Fim Se dissconst>0 and tempcelsius >= tempkelvin = tempcelsius deltag= gasconst*tempkelvin*math.log(dissconst) Escreva "\nenergia livre de Gibbs = ", deltag, " J/mol." Senão Escreva Erro! Kd tem que ser > 0 e temperatura tem que ser > C! 35
36 Programa: freeenergy.py Referências relacionadas ao programa freeenergy.py -FERSHT, Alan. Structure and Mechanism in Protein Science. A Guide to Enzyme Catalysis and Protein Folding. Nova York: W. H. Freeman and Company, p. -VOET, Donald; VOET, Judith G; PRATT, Charlotte W. Fundamentos de Bioquímica. Porto Alegre: Artmed Editora SA, p. -TINOCO, Ignacio Jr.; SAUER, Kenneth.; WANG, James C. Physical Chemistry. Principles and Applications in Biological Sciences. 3 a Ed. Nova Jersey: Prentice Hall, Inc., p. -VAN HOLDE, Kensal Edward; JOHNSON, W. Curtis; HO P. Shing. Principles of Physical Biochemistry. Nova Jersey: Prentice Hall, Inc., p. 36
37 Referências ALBERTS, B. et al. Biologia Molecular da Célula. 4a edição. Porto Alegre: Artmed editora, Porto Alegre, BRESSERT, Eli. SciPy and NumPy. Sebastopol: O Reilly Media, Inc., p. -DAWSON, Michael. Python Programming, for the absolute beginner. 3ed. Boston: Course Technology, p. -HETLAND, Magnus Lie. Python Algorithms. Mastering Basic Algorithms in the Python Language. Nova York: Springer Science+Business Media LLC, p. -IDRIS, Ivan. NumPy 1.5. An action-packed guide dor the easy-to-use, high performance, Python based free open source NumPy mathematical library using real-world examples. Beginner s Guide. Birmingham: Packt Publishing Ltd., p. -KIUSALAAS, Jaan. Numerical Methods in Engineering with Python. 2ed. Nova York: Cambridge University Press, p. -LANDAU, Rubin H. A First Course in Scientific Computing: Symbolic, Graphic, and Numeric Modeling Using Maple, Java, Mathematica, and Fortran90. Princeton: Princeton University Press, p. -LANDAU, Rubin H., PÁEZ, Manuel José, BORDEIANU, Cristian C. A Survey of Computational Physics. Introductory Computational Physics. Princeton: Princeton University Press, p. -LUTZ, Mark. Programming Python. 4ed. Sebastopol: O Reilly Media, Inc., p. -MODEL, Mitchell L. Bioinformatics Programming Using Python. Sebastopol: O Reilly Media, Inc., p. -TOSI, Sandro. Matplotlib for Python Developers. Birmingham: Packt Publishing Ltd., p. Última atualização: 14 de agosto de
2015 Dr. Walter F. de Azevedo Jr. www.python.org
 2015 Dr. Walter F. de Azevedo Jr. 000000000000000000000000000000000000000 000000000000000000000000000000000000000 000000000000111111111110001100000000000 000000000001111111111111111111000000001 000000000111111111111111111111111000000
2015 Dr. Walter F. de Azevedo Jr. 000000000000000000000000000000000000000 000000000000000000000000000000000000000 000000000000111111111110001100000000000 000000000001111111111111111111000000001 000000000111111111111111111111111000000
Bioinformática Aplicada
 000000000000000000000000000000000000000 000000000000000000000000000000000000000 000000000000111111111110001100000000000 000000000001111111111111111111000000001 000000000111111111111111111111111000000 000000000111111111111111111111111000000
000000000000000000000000000000000000000 000000000000000000000000000000000000000 000000000000111111111110001100000000000 000000000001111111111111111111000000001 000000000111111111111111111111111000000 000000000111111111111111111111111000000
Fisica do Corpo Humano ( ) Prof. Adriano Mesquita Alencar Dep. Física Geral Instituto de Física da USP B01. Temperatura Aula 5 e 1/2 da 6
 Fisica do Corpo Humano (4300325) Prof. Adriano Mesquita Alencar Dep. Física Geral Instituto de Física da USP B01 Temperatura Aula 5 e 1/2 da 6 1. Existem em torno de uma centena de átomos 2. Cada átomo
Fisica do Corpo Humano (4300325) Prof. Adriano Mesquita Alencar Dep. Física Geral Instituto de Física da USP B01 Temperatura Aula 5 e 1/2 da 6 1. Existem em torno de uma centena de átomos 2. Cada átomo
FFI0750 Biologia Molecular Estrutural
 Objetivos FFI0750 Biologia Molecular Estrutural Visualização de estruturas de macromoléculas Representação de estruturas de macromoléculas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 02 Bacharelado
Objetivos FFI0750 Biologia Molecular Estrutural Visualização de estruturas de macromoléculas Representação de estruturas de macromoléculas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 02 Bacharelado
Profª Eleonora Slide de aula. Revisão: Termodinâmica e Bioenergética
 Revisão: Termodinâmica e Bioenergética Revisão:Termodinâmica As leis da termodinâmica governam o comportamento de s bioquímicos As leis da termodinâmica são princípios gerais aplicados a todos os processos
Revisão: Termodinâmica e Bioenergética Revisão:Termodinâmica As leis da termodinâmica governam o comportamento de s bioquímicos As leis da termodinâmica são princípios gerais aplicados a todos os processos
Dois exercícios desta lista entrarão na primeira prova teórica
 Dois exercícios desta lista entrarão na primeira prova teórica 01. Quais são os três estados físicos da matéria? Quais as diferenças entre eles do ponto de vista de movimentação de moléculas e interações
Dois exercícios desta lista entrarão na primeira prova teórica 01. Quais são os três estados físicos da matéria? Quais as diferenças entre eles do ponto de vista de movimentação de moléculas e interações
Aula 14 Equilíbrio de Fases: Substâncias Puras
 Aula 14 Equilíbrio de Fases: Substâncias Puras 1. A condição de estabilidade Inicialmente precisamos estabelecer a importância da energia de Gibbs molar na discussão das transições de fase. A energia de
Aula 14 Equilíbrio de Fases: Substâncias Puras 1. A condição de estabilidade Inicialmente precisamos estabelecer a importância da energia de Gibbs molar na discussão das transições de fase. A energia de
Macromoléculas Biológicas
 Macromoléculas Biológicas Objetivos Visualizar a estrutura tridimensional de peptídeos e proteínas, usando-se recursos computacionais. Montar modelos estruturais de proteínas, usando-se kit de plástico.
Macromoléculas Biológicas Objetivos Visualizar a estrutura tridimensional de peptídeos e proteínas, usando-se recursos computacionais. Montar modelos estruturais de proteínas, usando-se kit de plástico.
TERMODINÂMICA QUÍMICA
 TERMODINÂMICA QUÍMICA Processos Espontâneos 1ª Lei da termodinâmica: Energia de um sistema é conservada ΔE = variação da energia interna q = calor absorvido pelo sistema w = trabalho realizado pela vizinhança
TERMODINÂMICA QUÍMICA Processos Espontâneos 1ª Lei da termodinâmica: Energia de um sistema é conservada ΔE = variação da energia interna q = calor absorvido pelo sistema w = trabalho realizado pela vizinhança
CAPÍTULO 1 Quantidades e Unidades 1. CAPÍTULO 2 Massa Atômica e Molecular; Massa Molar 16. CAPÍTULO 3 O Cálculo de Fórmulas e de Composições 26
 Sumário CAPÍTULO 1 Quantidades e Unidades 1 Introdução 1 Os sistemas de medida 1 O Sistema Internacional de Unidades (SI) 1 A temperatura 2 Outras escalas de temperatura 3 O uso e o mau uso das unidades
Sumário CAPÍTULO 1 Quantidades e Unidades 1 Introdução 1 Os sistemas de medida 1 O Sistema Internacional de Unidades (SI) 1 A temperatura 2 Outras escalas de temperatura 3 O uso e o mau uso das unidades
CQ110 : Princípios de FQ
 CQ 110 Princípios de Físico Química Curso: Farmácia 1º semestre de 2011 Quartas / Quintas: 9:30 11:30 Prof. Dr. Marcio Vidotti www.quimica.ufpr.br/mvidotti mvidotti@ufpr.br criação de modelos CQ110 : Princípios
CQ 110 Princípios de Físico Química Curso: Farmácia 1º semestre de 2011 Quartas / Quintas: 9:30 11:30 Prof. Dr. Marcio Vidotti www.quimica.ufpr.br/mvidotti mvidotti@ufpr.br criação de modelos CQ110 : Princípios
Interações de van der Waals. Interações de van der Waals. Interações de van der Waals.
 Interações de van der Waals aandrico@if.sc.usp.br Também conhecidas como forças de dispersão de London, caracterizam-se pelo momento de dipolo induzido e ocorrem entre todos os átomos. Apesar de moléculas
Interações de van der Waals aandrico@if.sc.usp.br Também conhecidas como forças de dispersão de London, caracterizam-se pelo momento de dipolo induzido e ocorrem entre todos os átomos. Apesar de moléculas
FFI0750 BIOLOGIA MOLECULAR ESTRUTURAL
 AULA PRÁTICA 1 VISUALIZAÇÃO E REPRESENTAÇÃO MOLECULAR Os programas disponíveis para representação molecular variam em função da finalidade desejada. Por exemplo, as ferramentas necessárias para estudos
AULA PRÁTICA 1 VISUALIZAÇÃO E REPRESENTAÇÃO MOLECULAR Os programas disponíveis para representação molecular variam em função da finalidade desejada. Por exemplo, as ferramentas necessárias para estudos
LICENCIATURA EM QUÍMICA QUÍMICA
 Programa de Disciplina Nome: Química Geral II IQ Código: IQG 120 Categoria: Carga Horária Semanal: CARACTERÍSTICAS Número de Semanas Previstas para a Disciplina: 15 Número de Créditos da Disciplina: 4
Programa de Disciplina Nome: Química Geral II IQ Código: IQG 120 Categoria: Carga Horária Semanal: CARACTERÍSTICAS Número de Semanas Previstas para a Disciplina: 15 Número de Créditos da Disciplina: 4
Equações-chave FUNDAMENTOS. Seção A. Seção E. Seção F. Seção G. mv 2. E c E P. mgh. Energia total energia cinética energia potencial, ou E E c.
 Equações-chave FUNDAMENTOS Seção A 3 A energia cinética de uma partícula de massa m relaciona-se com sua velocidade v, por: E c mv 2 4 Um corpo de massa m que está a uma altura h da Terra tem energia potencial
Equações-chave FUNDAMENTOS Seção A 3 A energia cinética de uma partícula de massa m relaciona-se com sua velocidade v, por: E c mv 2 4 Um corpo de massa m que está a uma altura h da Terra tem energia potencial
Biologia Estrutural. Qualidade de modelos estruturais Prof. Dr. Walter F. de Azevedo Jr. wfdaj.sites.uol.com.br Dr. Walter F. de Azevedo Jr.
 Biologia Estrutural Qualidade de modelos estruturais Prof. Dr. Walter F. de Azevedo Jr. Biologia Estrutural Resumo SCOP Modelagem molecular SCOP A primeira versão do SCOP foi liberada em 29 de outubro
Biologia Estrutural Qualidade de modelos estruturais Prof. Dr. Walter F. de Azevedo Jr. Biologia Estrutural Resumo SCOP Modelagem molecular SCOP A primeira versão do SCOP foi liberada em 29 de outubro
Sumário. 1 Introdução: matéria e medidas 1. 2 Átomos, moléculas e íons Estequiometria: cálculos com fórmulas e equações químicas 67
 Prefácio 1 Introdução: matéria e medidas 1 1.1 O estudo da química 1 1.2 Classificações da matéria 3 1.3 Propriedades da matéria 8 1.4 Unidades de medida 12 1.5 Incerteza na medida 18 1.6 Análise dimensional
Prefácio 1 Introdução: matéria e medidas 1 1.1 O estudo da química 1 1.2 Classificações da matéria 3 1.3 Propriedades da matéria 8 1.4 Unidades de medida 12 1.5 Incerteza na medida 18 1.6 Análise dimensional
Equilíbrio de misturas gasosas
 Martim Kurauchi e Neusa lonso-falleiros 2012 1 Equilíbrio de misturas gasosas Quando mais de um componente estiver presente em uma fase, o sistema não estará completamente definido a não ser que sejam
Martim Kurauchi e Neusa lonso-falleiros 2012 1 Equilíbrio de misturas gasosas Quando mais de um componente estiver presente em uma fase, o sistema não estará completamente definido a não ser que sejam
FUNÇÕES DE ESTADO TERMODINÂMICAS: ENTALPIA E ENERGIA LIVRE Parte 1
 FUNÇÕES DE ESTADO TERMODINÂMICAS: ENTALPIA E ENERGIA LIVRE Parte 1 [texto baseado nas seções 2.5 (a e b) e 2.7 de Physical Chemistry, P. Atkins e J. de Paula, Freeman 2006] Funções de estado termodinâmico
FUNÇÕES DE ESTADO TERMODINÂMICAS: ENTALPIA E ENERGIA LIVRE Parte 1 [texto baseado nas seções 2.5 (a e b) e 2.7 de Physical Chemistry, P. Atkins e J. de Paula, Freeman 2006] Funções de estado termodinâmico
Scoring Functions (MolDock Score) Prof. Dr. Walter F. de Azevedo Jr. walter.junior@pucrs.br ou walter.filgueira@hotmail.com
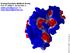 2015 Dr. Walter F. de Azevedo Jr. Scoring Functions (MolDock Score) Prof. Dr. Walter F. de Azevedo Jr. walter.junior@pucrs.br ou walter.filgueira@hotmail.com 1 O que é desenho de fármacos baseado em computador?
2015 Dr. Walter F. de Azevedo Jr. Scoring Functions (MolDock Score) Prof. Dr. Walter F. de Azevedo Jr. walter.junior@pucrs.br ou walter.filgueira@hotmail.com 1 O que é desenho de fármacos baseado em computador?
Termodinâmica em Bioquímica
 Instituto de Química de São Carlos IQSC Universidade de São Paulo Termodinâmica em Bioquímica Disciplina: Bioquímica I Docente: Profa. Dra. Fernanda Canduri Sugestão de leitura: Cap. 1 do Lehninger A vida
Instituto de Química de São Carlos IQSC Universidade de São Paulo Termodinâmica em Bioquímica Disciplina: Bioquímica I Docente: Profa. Dra. Fernanda Canduri Sugestão de leitura: Cap. 1 do Lehninger A vida
Módulo II: A visão clássica da ligação covalente
 Módulo II: A visão clássica da ligação covalente Aula 3: Eletronegatividade de Pauling e o caráter iônico das ligações químicas 4. Eletronegatividade de Pauling e o caráter iônico das ligações covalentes
Módulo II: A visão clássica da ligação covalente Aula 3: Eletronegatividade de Pauling e o caráter iônico das ligações químicas 4. Eletronegatividade de Pauling e o caráter iônico das ligações covalentes
Torneio Virtual de Química 2016
 Torneio Virtual de Química 2016 2ª Fase 4 Conjunto Início: 8/10 Término: 15/10 LEIA ATENTAMENTE ÀS INSTRUÇÕES ABAIXO: 01) Esta prova contém 2 questões, apenas uma deve ser escolhida e respondida; 02) As
Torneio Virtual de Química 2016 2ª Fase 4 Conjunto Início: 8/10 Término: 15/10 LEIA ATENTAMENTE ÀS INSTRUÇÕES ABAIXO: 01) Esta prova contém 2 questões, apenas uma deve ser escolhida e respondida; 02) As
ADSORÇÃO. Adsorção é a fixação de uma substância em uma interface, seja ela sólido-gás, sólido-líquido, líquido-gás (vapor).
 ADSORÇÃO Adsorção é a fixação de uma substância em uma interface, seja ela sólido-gás, sólido-líquido, líquido-gás (vapor). Adsorção física não ocorre ligação química entre substrato e adsorbato. O adsorbato
ADSORÇÃO Adsorção é a fixação de uma substância em uma interface, seja ela sólido-gás, sólido-líquido, líquido-gás (vapor). Adsorção física não ocorre ligação química entre substrato e adsorbato. O adsorbato
EXERCÍCIOS DE ELETROQUÍMICA
 Aula EXERCÍCIOS DE ELETROQUÍMICA META Apresentar os conceitos relacionados a misturas de substâncias simples através da resolução de exercícios comentados. OBJETIVOS Ao nal desta aula, o aluno deverá:
Aula EXERCÍCIOS DE ELETROQUÍMICA META Apresentar os conceitos relacionados a misturas de substâncias simples através da resolução de exercícios comentados. OBJETIVOS Ao nal desta aula, o aluno deverá:
L. G. Oliveira, S. P. Nascimento, T. D. Romão, J. A. Cavalcante, N. A. Costa
 APLICATIVO EXCEL/VBA PARA ESTIMATIVAS DE COEFICIENTES DE ATIVIDADES A DILUIÇÃO INFINITA ATRAVÉS DO MODELO MOSCED E VERIFICAÇÃO DE AZEOTROPIA DE MISTURAS BINÁRIAS L. G. Oliveira, S. P. Nascimento, T. D.
APLICATIVO EXCEL/VBA PARA ESTIMATIVAS DE COEFICIENTES DE ATIVIDADES A DILUIÇÃO INFINITA ATRAVÉS DO MODELO MOSCED E VERIFICAÇÃO DE AZEOTROPIA DE MISTURAS BINÁRIAS L. G. Oliveira, S. P. Nascimento, T. D.
P4 - PROVA DE QUÍMICA GERAL 30/06/12
 P4 - POVA DE QUÍMICA GEAL 30/06/ Nome: Nº de Matrícula: GABAITO Turma: Assinatura: Questão Valor Grau evisão a,5 a,5 3 a,5 4 a,5 Total 0,0 Constantes e equações: 73,5 K = 0 C = 0,08 atm L mol - K - = 8,345
P4 - POVA DE QUÍMICA GEAL 30/06/ Nome: Nº de Matrícula: GABAITO Turma: Assinatura: Questão Valor Grau evisão a,5 a,5 3 a,5 4 a,5 Total 0,0 Constantes e equações: 73,5 K = 0 C = 0,08 atm L mol - K - = 8,345
6/Mar/2013 Aula 7 Entropia Variação da entropia em processos reversíveis Entropia e os gases ideais
 6/Mar/01 Aula 7 Entropia ariação da entropia em processos reversíveis Entropia e os gases ideais Entropia no ciclo de Carnot e em qualquer ciclo reversível ariação da entropia em processos irreversíveis
6/Mar/01 Aula 7 Entropia ariação da entropia em processos reversíveis Entropia e os gases ideais Entropia no ciclo de Carnot e em qualquer ciclo reversível ariação da entropia em processos irreversíveis
TEORIA DO ESTADO ESTACIONÁRIO E SIMULAÇÃO COMPUTACIONAL.
 EXERCÍCIOS SOBRE: TEORIA DA COLISÃO, TEORIA DO ESTADO ESTACIONÁRIO E SIMULAÇÃO COMPUTACIONAL. Glauber Silva Godoi META Desenvolver no aluno a capacidade de extrair os parâmetros cinéticos de uma reação
EXERCÍCIOS SOBRE: TEORIA DA COLISÃO, TEORIA DO ESTADO ESTACIONÁRIO E SIMULAÇÃO COMPUTACIONAL. Glauber Silva Godoi META Desenvolver no aluno a capacidade de extrair os parâmetros cinéticos de uma reação
META Estudar o comportamento de reações químicas que envolvem mais de uma etapa.
 EQUÇÕES CINÉTICS COMPOSTS Camilo ndrea ngelucci ula MET Estudar o comportamento de reações químicas que envolvem mais de uma etapa. OBJETIVOS o fi nal desta aula, o aluno deverá: compreender e determinar
EQUÇÕES CINÉTICS COMPOSTS Camilo ndrea ngelucci ula MET Estudar o comportamento de reações químicas que envolvem mais de uma etapa. OBJETIVOS o fi nal desta aula, o aluno deverá: compreender e determinar
2015 Dr. Walter F. de Azevedo Jr. www.python.org
 2015 Dr. Walter F. de Azevedo Jr. 000000000000000000000000000000000000000 000000000000000000000000000000000000000 000000000000111111111110001100000000000 000000000001111111111111111111000000001 000000000111111111111111111111111000000
2015 Dr. Walter F. de Azevedo Jr. 000000000000000000000000000000000000000 000000000000000000000000000000000000000 000000000000111111111110001100000000000 000000000001111111111111111111000000001 000000000111111111111111111111111000000
Aula 2 - Introdução à Bioquímica
 Aula 2 - Introdução à Bioquímica -Interações intermoleculares: interação eletrostática, interações de van der Waals -Solubilidade de compostos polares em água -Solubilidade de compostos apolares em água
Aula 2 - Introdução à Bioquímica -Interações intermoleculares: interação eletrostática, interações de van der Waals -Solubilidade de compostos polares em água -Solubilidade de compostos apolares em água
2.1 Princípios gerais da ligação química. Ligações químicas
 2.1 Princípios gerais da ligação química Ligações químicas A associação de átomos formando moléculas, ou em agregados de maiores dimensões como, por exemplo, nos metais, é possível pelo estabelecimento
2.1 Princípios gerais da ligação química Ligações químicas A associação de átomos formando moléculas, ou em agregados de maiores dimensões como, por exemplo, nos metais, é possível pelo estabelecimento
Entropia e energia livre de Gibbs. Prof. Leandro Zatta
 Entropia e energia livre de Gibbs Prof. Leandro Zatta 1 Segunda e a terceira leis Ideias importantes Sentido Natural Desordem Medido por Energia livre de Gibbs 2 Chave para compreensão da ocorrência ou
Entropia e energia livre de Gibbs Prof. Leandro Zatta 1 Segunda e a terceira leis Ideias importantes Sentido Natural Desordem Medido por Energia livre de Gibbs 2 Chave para compreensão da ocorrência ou
Escola Secundária de Lagoa. Ficha de Trabalho 16. Exercícios. Física e Química A 11º Ano Paula Melo Silva
 Escola Secundária de Lagoa Física e Química A 11º Ano Paula Melo Silva Exercícios Ficha de Trabalho 16 Global 1. Um certo ião negativo, X 3-, tem um número total de eletrões de 18 e o seu número de massa
Escola Secundária de Lagoa Física e Química A 11º Ano Paula Melo Silva Exercícios Ficha de Trabalho 16 Global 1. Um certo ião negativo, X 3-, tem um número total de eletrões de 18 e o seu número de massa
Docking (ou atracamento) Molecular. Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia 9 de outubro de 2014
 Docking (ou atracamento) Molecular Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia rafaelasf@gmail.com 9 de outubro de 2014 O ATRACAMENTO MOLECULAR PERMITE ESTIMAR COMO DUAS MOLÉCULAS INTERAGEM
Docking (ou atracamento) Molecular Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia rafaelasf@gmail.com 9 de outubro de 2014 O ATRACAMENTO MOLECULAR PERMITE ESTIMAR COMO DUAS MOLÉCULAS INTERAGEM
BIK0102: ESTRUTURA DA MATÉRIA. Crédito: Sprace GASES. Professor Hugo B. Suffredini Site:
 BIK0102: ESTRUTURA DA MATÉRIA Crédito: Sprace GASES Professor Hugo B. Suffredini hugo.suffredini@ufabc.edu.br Site: www.suffredini.com.br Pressão Atmosférica A pressão é a força atuando em um objeto por
BIK0102: ESTRUTURA DA MATÉRIA Crédito: Sprace GASES Professor Hugo B. Suffredini hugo.suffredini@ufabc.edu.br Site: www.suffredini.com.br Pressão Atmosférica A pressão é a força atuando em um objeto por
ocorridas na concentração dos participantes das reações em função do tempo:
 CINÉTICA QUÍMICA Fala Gás Nobre! Preparado para reagir? Então vamos para mais um resumo de química! Você já parou pra pensar, que a velocidade com que as reações químicas acontecem, podem estar relacionadas
CINÉTICA QUÍMICA Fala Gás Nobre! Preparado para reagir? Então vamos para mais um resumo de química! Você já parou pra pensar, que a velocidade com que as reações químicas acontecem, podem estar relacionadas
Biologia Estrutural. Cálculo da Densidade Eletrônica. Prof. Dr. Walter Filgueira de Azevedo Jr. wfdaj.sites.uol.com.br
 Biologia Estrutural Cálculo da Densidade Eletrônica Prof. Dr. Walter Filgueira de Azevedo Jr. Resumo Introdução Cálculo da densidade eletrônica Densidade eletrônica de um cristal unidimensional Densidade
Biologia Estrutural Cálculo da Densidade Eletrônica Prof. Dr. Walter Filgueira de Azevedo Jr. Resumo Introdução Cálculo da densidade eletrônica Densidade eletrônica de um cristal unidimensional Densidade
CQ049 FQ Eletroquímica
 CQ049 FQ Eletroquímica prof. Dr. Marcio Vidotti LEAP Laboratório de Eletroquímica e Polímeros mvidotti@ufpr.br www.quimica.ufpr.br/mvidotti criação de modelos Modelos são criados para explicar os fenômenos
CQ049 FQ Eletroquímica prof. Dr. Marcio Vidotti LEAP Laboratório de Eletroquímica e Polímeros mvidotti@ufpr.br www.quimica.ufpr.br/mvidotti criação de modelos Modelos são criados para explicar os fenômenos
ESTUDO DO COMPORTAMENTO DE UM GÁS POR DINÂMICA MOLECULAR.
 ESTUDO DO COMPORTAMENTO DE UM GÁS POR DINÂMICA MOLECULAR. João Paulo Smykaluk (ICV-UNICENTRO), Eduardo Vicentini (Orientador), e-mail: evicentini@unicentro.br. Universidade Estadual do Centro-Oeste, Setor
ESTUDO DO COMPORTAMENTO DE UM GÁS POR DINÂMICA MOLECULAR. João Paulo Smykaluk (ICV-UNICENTRO), Eduardo Vicentini (Orientador), e-mail: evicentini@unicentro.br. Universidade Estadual do Centro-Oeste, Setor
Apresentar as aplicações conjuntas do primeiro e do segundo princípio; apresentar as equações fundamentais da termodinâmica.
 ENERGIA LIVRE E POTENCIAL QUÍMICO Metas Apresentar as aplicações conjuntas do primeiro e do segundo princípio; apresentar as equações fundamentais da termodinâmica. Objetivos Ao final desta aula, o aluno
ENERGIA LIVRE E POTENCIAL QUÍMICO Metas Apresentar as aplicações conjuntas do primeiro e do segundo princípio; apresentar as equações fundamentais da termodinâmica. Objetivos Ao final desta aula, o aluno
Características dos gases
 Gases Características dos gases Os gases são altamente compressíveis e ocupam o volume total de seus recipientes. Quando um gás é submetido à pressão, seu volume diminui. Os gases sempre formam misturas
Gases Características dos gases Os gases são altamente compressíveis e ocupam o volume total de seus recipientes. Quando um gás é submetido à pressão, seu volume diminui. Os gases sempre formam misturas
QUÍMICA MÓDULO 18 RELAÇÕES NUMÉRICAS. Professor Edson Cruz
 QUÍMICA Professor Edson Cruz MÓDULO 18 RELAÇÕES NUMÉRICAS INTRODUÇÃO Precisamos compreender que houve uma necessidade de se definir uma nova unidade de massa para átomos e moléculas. É importante que você
QUÍMICA Professor Edson Cruz MÓDULO 18 RELAÇÕES NUMÉRICAS INTRODUÇÃO Precisamos compreender que houve uma necessidade de se definir uma nova unidade de massa para átomos e moléculas. É importante que você
Aula de Bioquímica I. Tema: Água. Prof. Dr. Júlio César Borges
 Aula de Bioquímica I Tema: Água Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: borgesjc@iqsc.usp.br
Aula de Bioquímica I Tema: Água Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: borgesjc@iqsc.usp.br
E-books PCNA. Vol. 1 QUÍMICA ELEMENTAR CAPÍTULO 4 ESTEQUIOMETRIA
 E-books PCNA Vol. 1 QUÍMICA ELEMENTAR CAPÍTULO 4 ESTEQUIOMETRIA 1 QUÍMICA ELEMENTAR CAPÍTULO 4 SUMÁRIO Apresentação -------------------------------------------- 2 Capítulo 4 ------------------------------------------------
E-books PCNA Vol. 1 QUÍMICA ELEMENTAR CAPÍTULO 4 ESTEQUIOMETRIA 1 QUÍMICA ELEMENTAR CAPÍTULO 4 SUMÁRIO Apresentação -------------------------------------------- 2 Capítulo 4 ------------------------------------------------
Diagramas de Energia
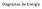 Diagramas de Energia 1.1- Análise Gráfica Reação exotérmica Reação endotérmica (a) Energia de ativação (Ea) para a reação inversa (b) Energia de ativação (Ea) para a reação direta (c) ΔH 1.2- Entropia
Diagramas de Energia 1.1- Análise Gráfica Reação exotérmica Reação endotérmica (a) Energia de ativação (Ea) para a reação inversa (b) Energia de ativação (Ea) para a reação direta (c) ΔH 1.2- Entropia
Gás Ideal (1) PMT2305 Físico-Química para Metalurgia e Materiais I César Yuji Narita e Neusa Alonso-Falleiros 2012
 Gás Ideal (1) Para um gás, uma equação de estado é uma relação entre pressão (P), volume (V), temperatura (T) e composição ou número de mols (n). O primeiro passo para a determinação de uma equação de
Gás Ideal (1) Para um gás, uma equação de estado é uma relação entre pressão (P), volume (V), temperatura (T) e composição ou número de mols (n). O primeiro passo para a determinação de uma equação de
EQUILÍBRIO QUÍMICO Equilíbrio químico numa mistura:
 Equilíbrio químico numa mistura: Considere a seguinte reação: A + B C a) Se G mist < 0 reação expontânea (ocorre até atingir o equilíbrio G min ) b) Se G mist > 0 reação ocorre no sentido inverso. Para
Equilíbrio químico numa mistura: Considere a seguinte reação: A + B C a) Se G mist < 0 reação expontânea (ocorre até atingir o equilíbrio G min ) b) Se G mist > 0 reação ocorre no sentido inverso. Para
Conceitos Básicos sobre gases
 Conceitos Básicos sobre gases ara este estudo não vamos fazer distinção entre gás e vapor, desta forma neste capítulo, o estado gasoso (gás ou vapor) será sempre referido como gás... ressão dos gases Suponha
Conceitos Básicos sobre gases ara este estudo não vamos fazer distinção entre gás e vapor, desta forma neste capítulo, o estado gasoso (gás ou vapor) será sempre referido como gás... ressão dos gases Suponha
AULA 5 Adsorção, isotermas e filmes monomoleculares. Prof a Elenice Schons
 AULA 5 Adsorção, isotermas e filmes monomoleculares Prof a Elenice Schons ADSORÇÃO É um processo de acumulação e concentração seletiva de um ou mais constituintes contidos num gás ou líquido sobre superfícies
AULA 5 Adsorção, isotermas e filmes monomoleculares Prof a Elenice Schons ADSORÇÃO É um processo de acumulação e concentração seletiva de um ou mais constituintes contidos num gás ou líquido sobre superfícies
Entropia. Energia de Gibbs e Equilíbrio
 Entropia Energia de Gibbs e Equilíbrio Mestrado integrado em Engenharia Biológica Disciplina Química II, 2º semestre 2009/10 Professsora Ana Margarida Martins TRANSFORMAÇÕES ESPONTÂNEAS Uma reacção diz-se
Entropia Energia de Gibbs e Equilíbrio Mestrado integrado em Engenharia Biológica Disciplina Química II, 2º semestre 2009/10 Professsora Ana Margarida Martins TRANSFORMAÇÕES ESPONTÂNEAS Uma reacção diz-se
INTRODUÇÃO À QUÍMICA FÍSICA
 FACULDADE DE CIÊNCIAS E TECNOLOGIA DEPARTAMENTO DE QUÍMICA, BIOQUÍMICA E FARMÁCIA Orientação tutorial INTRODUÇÃO À QUÍMICA FÍSICA 1º Ano Q/BQ/CF/F/MIEB/BT Ano Lectivo: 2008 / 2009 (5º Módulo) 2009 IQF
FACULDADE DE CIÊNCIAS E TECNOLOGIA DEPARTAMENTO DE QUÍMICA, BIOQUÍMICA E FARMÁCIA Orientação tutorial INTRODUÇÃO À QUÍMICA FÍSICA 1º Ano Q/BQ/CF/F/MIEB/BT Ano Lectivo: 2008 / 2009 (5º Módulo) 2009 IQF
Aula 13 A Energia de Gibbs
 Aula 13 A Energia de Gibbs 1. Introdução: Um dos problemas ao se considerar a entropia já deve ter ficado claro: temos que trabalhar com duas variações de entropia, a variação no sistema e a variação nas
Aula 13 A Energia de Gibbs 1. Introdução: Um dos problemas ao se considerar a entropia já deve ter ficado claro: temos que trabalhar com duas variações de entropia, a variação no sistema e a variação nas
1
 Resolução da Prova de Química Vestibular Verão UPF/2003 Professor Emiliano Chemello www.quimica.net/emiliano emiliano@quimica.net Questões Resolução Resolução: D A afirmação III é falsa, pois as forças
Resolução da Prova de Química Vestibular Verão UPF/2003 Professor Emiliano Chemello www.quimica.net/emiliano emiliano@quimica.net Questões Resolução Resolução: D A afirmação III é falsa, pois as forças
CQ110 : Princípios de FQ. Imagens de Rorschach
 Imagens de Rorschach 1 Leis de velocidade Velocidade de uma reação química: Variação de reagentes / produtos em função do tempo: a A+ b B produtos v = k [A] x [B] y Lei de velocidade k: constante de velocidade
Imagens de Rorschach 1 Leis de velocidade Velocidade de uma reação química: Variação de reagentes / produtos em função do tempo: a A+ b B produtos v = k [A] x [B] y Lei de velocidade k: constante de velocidade
(QHUJLD/LYUHGH0LVWXUDH$WLYLGDGH
 8))7HUPRGLQkPLFD$SOLFDGDD$FLDULD (TXLOtEULRHP6LVWHPDV5HDWLYRV (QHUJLD/LYUHGHLVWXUDH$WLYLGDGH 5HODo}HV([SHULPHQWDLVHP6ROXo}HV As relações experimentais entre atividade e concentração apresentadas anteriormente
8))7HUPRGLQkPLFD$SOLFDGDD$FLDULD (TXLOtEULRHP6LVWHPDV5HDWLYRV (QHUJLD/LYUHGHLVWXUDH$WLYLGDGH 5HODo}HV([SHULPHQWDLVHP6ROXo}HV As relações experimentais entre atividade e concentração apresentadas anteriormente
META Compreender os conceitos relacionado a lei de arrhenius e seus modelos matematicos. Compreender as aplicações catálise e seus fundamentos.
 ATIVIDADS SOBR LI D ARHHNIUS CATÁLIS Aula 7 MTA Compreender os conceitos relacionado a lei de arrhenius e seus modelos matematicos. Compreender as aplicações catálise e seus fundamentos. OBJTIVOS Ao fi
ATIVIDADS SOBR LI D ARHHNIUS CATÁLIS Aula 7 MTA Compreender os conceitos relacionado a lei de arrhenius e seus modelos matematicos. Compreender as aplicações catálise e seus fundamentos. OBJTIVOS Ao fi
ENSINO MÉDIO QUÍMICA
 ENSINO MÉDIO QUÍMICA TERMOQUÍMICA TERMOQUÍMICA Termoquímica é a parte da química que estuda o calor associado a uma reação química. A unidade usada para medir a energia liberada ou absorvida por um sistema
ENSINO MÉDIO QUÍMICA TERMOQUÍMICA TERMOQUÍMICA Termoquímica é a parte da química que estuda o calor associado a uma reação química. A unidade usada para medir a energia liberada ou absorvida por um sistema
Calcule o valor mínimo de M para permitir o degelo (e recongelação) do bloco à medida que é atravessado pela barra.
 Termodinâmica Aplicada (PF: comunicar eventuais erros para pmmiranda@fc.ul.pt) Exercícios 7. Uma barra metálica rectangular fina, com 0 cm de comprimento e mm de largura, está assente num bloco de gelo
Termodinâmica Aplicada (PF: comunicar eventuais erros para pmmiranda@fc.ul.pt) Exercícios 7. Uma barra metálica rectangular fina, com 0 cm de comprimento e mm de largura, está assente num bloco de gelo
FUNDAÇÃO CARMELITANA MÁRIO PALMÉRIO FACIHUS - FACULDADE DE CIÊNCIAS HUMANAS E SOCIAIS. Enzimas. Prof. Me. Cássio Resende de Morais
 FUNDAÇÃO CARMELITANA MÁRIO PALMÉRIO FACIHUS - FACULDADE DE CIÊNCIAS HUMANAS E SOCIAIS Enzimas Prof. Me. Cássio Resende de Morais Enzimas Catalisadores biológicos: substâncias de origem biológica que aceleram
FUNDAÇÃO CARMELITANA MÁRIO PALMÉRIO FACIHUS - FACULDADE DE CIÊNCIAS HUMANAS E SOCIAIS Enzimas Prof. Me. Cássio Resende de Morais Enzimas Catalisadores biológicos: substâncias de origem biológica que aceleram
sat 1 = 431 Pa e sat sat
 Modelos Baseados no Conceito de Composição Local 85 Exemplo 9. Para o sistema n-pentanol ()/n-hexano () as constantes da equação de Wilson são Λ = 0.0700 e Λ = 0.69. Admitindo que a fase vapor é ideal,
Modelos Baseados no Conceito de Composição Local 85 Exemplo 9. Para o sistema n-pentanol ()/n-hexano () as constantes da equação de Wilson são Λ = 0.0700 e Λ = 0.69. Admitindo que a fase vapor é ideal,
OBJETIVOS BIBLIOGRAFIA ENZIMAS E INIBIDORES ENZIMÁTICOS
 OBJETIVOS Enzimas: Funções, Nomenclatura e Propriedades Fundamentos da Cinética Enzimática Cinética Enzimática: Michaelis-Menten Ensaios Cinéticos: Padronização e Validação Parâmetros Cinéticos: vo, KM,
OBJETIVOS Enzimas: Funções, Nomenclatura e Propriedades Fundamentos da Cinética Enzimática Cinética Enzimática: Michaelis-Menten Ensaios Cinéticos: Padronização e Validação Parâmetros Cinéticos: vo, KM,
Vamos iniciar o estudo da unidade fundamental que constitui todos os organismos vivos: a célula.
 Aula 01 Composição química de uma célula O que é uma célula? Vamos iniciar o estudo da unidade fundamental que constitui todos os organismos vivos: a célula. Toda célula possui a capacidade de crescer,
Aula 01 Composição química de uma célula O que é uma célula? Vamos iniciar o estudo da unidade fundamental que constitui todos os organismos vivos: a célula. Toda célula possui a capacidade de crescer,
QUÍMICA. Professores: Andréia, Herval, Thiago
 QUÍMICA Professores: Andréia, Herval, Thiago Comentário Geral A prova de química deste ano foi abrangente, porém, infelizmente, faltaram alguns assuntos relevantes: atomística, tabela periódica, hibridação
QUÍMICA Professores: Andréia, Herval, Thiago Comentário Geral A prova de química deste ano foi abrangente, porém, infelizmente, faltaram alguns assuntos relevantes: atomística, tabela periódica, hibridação
Volume Parcial Molar
 Volume Parcial Molar 1. Introdução O volume molar é definido como o volume ocupado por 1 mol de uma substância pura. Por exemplo, o volume molar da água pura é 18 cm 3 /mol, conforme mostrado no cálculo
Volume Parcial Molar 1. Introdução O volume molar é definido como o volume ocupado por 1 mol de uma substância pura. Por exemplo, o volume molar da água pura é 18 cm 3 /mol, conforme mostrado no cálculo
ESTUDO COMPARATIVO DE MODELOS DE COEFICIENTES DE ATIVIDADE DA FASE LÍQUIDA PARA SEPARAÇÃO DA MISTURA ETANOL-ÁGUA
 ESTUDO COMPARATIVO DE MODELOS DE COEFICIENTES DE ATIVIDADE DA FASE LÍQUIDA PARA SEPARAÇÃO DA MISTURA ETANOL-ÁGUA A. APIO 1 e N. P. G. SALAU Universidade Federal de Santa Maria, Departamento de Engenharia
ESTUDO COMPARATIVO DE MODELOS DE COEFICIENTES DE ATIVIDADE DA FASE LÍQUIDA PARA SEPARAÇÃO DA MISTURA ETANOL-ÁGUA A. APIO 1 e N. P. G. SALAU Universidade Federal de Santa Maria, Departamento de Engenharia
Vamos aos Gritos. Quem são os números quânticos? Os números quânticos são as soluções da equação de Schrondinger que
 Disciplina de Física e Química A 10ºAno Ano lectivo 2014/2015 Vamos aos Gritos Números Quânticos!!! Quem são os números quânticos? Os números quânticos são as soluções da equação de Schrondinger que indicam
Disciplina de Física e Química A 10ºAno Ano lectivo 2014/2015 Vamos aos Gritos Números Quânticos!!! Quem são os números quânticos? Os números quânticos são as soluções da equação de Schrondinger que indicam
Apresentar os conceitos fundamentais da termodinâmica estatística e como aplicá-los as propriedades termodinâmicas vista até então.
 Introdução À Termodinâmica Estatística Aula 15 Meta Apresentar os conceitos fundamentais da termodinâmica estatística e como aplicá-los as propriedades termodinâmicas vista até então. Objetivos Ao final
Introdução À Termodinâmica Estatística Aula 15 Meta Apresentar os conceitos fundamentais da termodinâmica estatística e como aplicá-los as propriedades termodinâmicas vista até então. Objetivos Ao final
ESTUDO E ANÁLISE DA MISTURA DE ÁGUA E ETANOL ATRAVÉS DE EQUAÇÕES DE ESTADO.
 ESTUDO E ANÁLISE DA MISTURA DE ÁGUA E ETANOL ATRAVÉS DE EQUAÇÕES DE ESTADO. S. F. VASCONCELOS 1, F. J. F. CHAVES 1, C. V. FERNANDES 1, N. SILVA 1, H. BISPO 1 1 Universidade Federal de Campina Grande, Unidade
ESTUDO E ANÁLISE DA MISTURA DE ÁGUA E ETANOL ATRAVÉS DE EQUAÇÕES DE ESTADO. S. F. VASCONCELOS 1, F. J. F. CHAVES 1, C. V. FERNANDES 1, N. SILVA 1, H. BISPO 1 1 Universidade Federal de Campina Grande, Unidade
Disciplina de BIOQUÍMICA do Ciclo Básico de MEDICINA Universidade dos Açores 1º Ano ENSINO PRÁTICO 4ª AULA PRÁTICA
 Disciplina de BIOQUÍMICA do Ciclo Básico de MEDICINA Universidade dos Açores 1º Ano ENSINO PRÁTICO 4ª AULA PRÁTICA CONCEITO DE SOLUÇÕES TAMPÃO, ph E pk 1. Conceito de soluções tampão (ph e pk) 2. Principais
Disciplina de BIOQUÍMICA do Ciclo Básico de MEDICINA Universidade dos Açores 1º Ano ENSINO PRÁTICO 4ª AULA PRÁTICA CONCEITO DE SOLUÇÕES TAMPÃO, ph E pk 1. Conceito de soluções tampão (ph e pk) 2. Principais
CINÉTICA QUÍMICA. Profa. Loraine Jacobs DAQBI.
 CINÉTICA QUÍMICA Profa. Loraine Jacobs DAQBI lorainejacobs@utfpr.edu.br http://paginapessoal.utfpr.edu.br/lorainejacobs Cinética Química Lei de Velocidade Integrada Mostra a variação das concentrações
CINÉTICA QUÍMICA Profa. Loraine Jacobs DAQBI lorainejacobs@utfpr.edu.br http://paginapessoal.utfpr.edu.br/lorainejacobs Cinética Química Lei de Velocidade Integrada Mostra a variação das concentrações
Ácidos, Bases, ph e Solução Tampão: Antonio Rodrigues Instituto de Física da USP
 Ácidos, Bases, ph e Solução Tampão: Antonio Rodrigues Instituto de Física da USP Reações ácido-base 1 O que são ácidos e bases? Um ácido é uma substância que, quando dissolvida em água, libera prótons
Ácidos, Bases, ph e Solução Tampão: Antonio Rodrigues Instituto de Física da USP Reações ácido-base 1 O que são ácidos e bases? Um ácido é uma substância que, quando dissolvida em água, libera prótons
CINÉTICA QUÍMICA Conceito de velocidade de reação
 CINÉTICA QUÍMICA 1 1. Conceito de velocidade de reação Cinética química é o estudo da velocidade das reações, de como a velocidade varia em função das diferentes condições e quais os mecanismos de desenvolvimento
CINÉTICA QUÍMICA 1 1. Conceito de velocidade de reação Cinética química é o estudo da velocidade das reações, de como a velocidade varia em função das diferentes condições e quais os mecanismos de desenvolvimento
Notas de aula - Profa. Zélia Aulas 07,08,09 e 10. Capítulo 3 Relações formais e sistemas amostrais (exemplares)
 Notas de aula - Profa. Zélia Aulas 07,08,09 e 10 Livro texto: Thermodynamics and an Introduction to Thermostatistics (2nd edition) H. B. Callen. Capítulo 3 Relações formais e sistemas amostrais (exemplares)
Notas de aula - Profa. Zélia Aulas 07,08,09 e 10 Livro texto: Thermodynamics and an Introduction to Thermostatistics (2nd edition) H. B. Callen. Capítulo 3 Relações formais e sistemas amostrais (exemplares)
Universidade Tecnológica Federal do Paraná Departamento Acadêmico de Química e Biologia. Aula Interlúdio molecular
 Universidade Tecnológica Federal do Paraná Departamento Acadêmico de Química e Biologia Aula Interlúdio molecular Energia Interna somatório de energias (cinética + potencial) Energia cinética relacionada
Universidade Tecnológica Federal do Paraná Departamento Acadêmico de Química e Biologia Aula Interlúdio molecular Energia Interna somatório de energias (cinética + potencial) Energia cinética relacionada
GASES. https://www.youtube.com/watch?v=wtmmvs3uiv0. David P. White. QUÍMICA: A Ciência Central 9ª Edição Capítulo by Pearson Education
 GASES PV nrt https://www.youtube.com/watch?v=wtmmvs3uiv0 David P. White QUÍMICA: A Ciência Central 9ª Edição volume, pressão e temperatura Um gás consiste em átomos (individualmente ou ligados formando
GASES PV nrt https://www.youtube.com/watch?v=wtmmvs3uiv0 David P. White QUÍMICA: A Ciência Central 9ª Edição volume, pressão e temperatura Um gás consiste em átomos (individualmente ou ligados formando
EXAME DE SELEÇÃO PARA O PROGRAMA DE PÓS-GRADUAÇÃO EM QUÍMICA DA UNIVERSIDADE FEDERAL DE RORAIMA/ MESTRADO
 UNIVERSIDADE FEDERAL DE RORAIMA PRÓ-REITORIA DE PESQUISA E PÓS-GRADUAÇÃO PROGRAMA DE PÓS-GRADUAÇÃO EM QUÍMICA EXAME DE SELEÇÃO PARA O PROGRAMA DE PÓS-GRADUAÇÃO EM QUÍMICA DA UNIVERSIDADE FEDERAL DE RORAIMA/2016.1
UNIVERSIDADE FEDERAL DE RORAIMA PRÓ-REITORIA DE PESQUISA E PÓS-GRADUAÇÃO PROGRAMA DE PÓS-GRADUAÇÃO EM QUÍMICA EXAME DE SELEÇÃO PARA O PROGRAMA DE PÓS-GRADUAÇÃO EM QUÍMICA DA UNIVERSIDADE FEDERAL DE RORAIMA/2016.1
Aula INTRODUÇÃO À ESTEQUIOMETRIA META OBJETIVOS PRÉ-REQUISITOS
 INTRODUÇÃO À ESTEQUIOMETRIA Aula 9 META Apresentar o estudo das equações usadas para representar as mudanças químicas e utilizar essas equações para definir as quantidades relativas de elementos combinados
INTRODUÇÃO À ESTEQUIOMETRIA Aula 9 META Apresentar o estudo das equações usadas para representar as mudanças químicas e utilizar essas equações para definir as quantidades relativas de elementos combinados
Aula 8 Entropia e espontaneidade
 Universidade Tecnológica Federal do Paraná Departamento Acadêmico de Química e Biologia Aula 8 Entropia e espontaneidade Dr. Tiago P. Camargo Reações químicas e espontaneidade Ocorrer ou não ocorrer...
Universidade Tecnológica Federal do Paraná Departamento Acadêmico de Química e Biologia Aula 8 Entropia e espontaneidade Dr. Tiago P. Camargo Reações químicas e espontaneidade Ocorrer ou não ocorrer...
Física Geral II. Aula 1 - Teoria cinética dos gases. D. Valin 1. Universidade do Estado de Mato Grosso. Sinop-MT, April 25, 2017
 Física Geral II Aula 1 - Teoria cinética dos gases D. Valin 1 1 Faculdade de Ciências Exatas - FACET Universidade do Estado de Mato Grosso Sinop-MT, April 25, 2017 D. Valin (Universidade do Estado de Mato
Física Geral II Aula 1 - Teoria cinética dos gases D. Valin 1 1 Faculdade de Ciências Exatas - FACET Universidade do Estado de Mato Grosso Sinop-MT, April 25, 2017 D. Valin (Universidade do Estado de Mato
DISCIPLINA DE QUÍMICA
 DISCIPLINA DE QUÍMICA OBJETIVOS: 1ª série Traduzir linguagens químicas em linguagens discursivas e linguagem discursiva em outras linguagens usadas em Química tais como gráficos, tabelas e relações matemáticas,
DISCIPLINA DE QUÍMICA OBJETIVOS: 1ª série Traduzir linguagens químicas em linguagens discursivas e linguagem discursiva em outras linguagens usadas em Química tais como gráficos, tabelas e relações matemáticas,
TERMODINÂMICA TERMOQUÍMICA
 TERMODINÂMICA TERMOQUÍMICA Termodinâmica é a ciência que estuda as transformações de energia nas quais as variações de temperatura são importantes. A maioria das transformações químicas resulta em alterações
TERMODINÂMICA TERMOQUÍMICA Termodinâmica é a ciência que estuda as transformações de energia nas quais as variações de temperatura são importantes. A maioria das transformações químicas resulta em alterações
Universidade de São Paulo Instituto de Física Energia em Sistemas Biológicos Edi Carlos Sousa
 Universidade de São Paulo Instituto de Física Energia em Sistemas Biológicos Edi Carlos Sousa edisousa@if.usp.br Metabolismo Celular Cada reação que ocorre em um organismo vivo requer o uso de energia
Universidade de São Paulo Instituto de Física Energia em Sistemas Biológicos Edi Carlos Sousa edisousa@if.usp.br Metabolismo Celular Cada reação que ocorre em um organismo vivo requer o uso de energia
LCB208 BIOQUÍMICA DEPARTAMENTO DE CIÊNCIAS BIOLÓGICAS BIOENERGÉTICA
 LCB208 BIOQUÍMICA DEPARTAMENTO DE CIÊNCIAS BIOLÓGICAS BIOENERGÉTICA + NH 4 + (CO 2, Esq. C, NH 4+, H 2 O) ATP A moeda Energética das Células INTRODUÇÃO Os organismos vivos, para manterem sua intrincada
LCB208 BIOQUÍMICA DEPARTAMENTO DE CIÊNCIAS BIOLÓGICAS BIOENERGÉTICA + NH 4 + (CO 2, Esq. C, NH 4+, H 2 O) ATP A moeda Energética das Células INTRODUÇÃO Os organismos vivos, para manterem sua intrincada
CINÉTICA QUÍMICA. Obs.: a variação da quantidade deverá ser sempre um valor positivo, então ela deverá ser em módulo. 1.
 CINÉTICA QUÍMICA 1. Introdução O Conhecimento e o estudo da velocidade das reações, além de ser muito importante em termos industriais, também está relacionado ao nosso dia-adia, verificamos que há algumas
CINÉTICA QUÍMICA 1. Introdução O Conhecimento e o estudo da velocidade das reações, além de ser muito importante em termos industriais, também está relacionado ao nosso dia-adia, verificamos que há algumas
Físico-Química I. Profa. Dra. Carla Dalmolin. Misturas Simples. Físico-Química, cap. 5: Transformações Físicas de Substâncias Puras
 Físico-Química I Profa. Dra. Carla Dalmolin Misturas Simples Físico-Química, cap. 5: Transformações Físicas de Substâncias Puras Misturas Simples Misturas de substâncias que não reagem Modelo simples para
Físico-Química I Profa. Dra. Carla Dalmolin Misturas Simples Físico-Química, cap. 5: Transformações Físicas de Substâncias Puras Misturas Simples Misturas de substâncias que não reagem Modelo simples para
VERSÃO DE TRABALHO. Exame Final Nacional de Física e Química A Prova ª Fase Ensino Secundário º Ano de Escolaridade
 Exame Final Nacional de Física e Química A Prova 715 1.ª Fase Ensino Secundário 2017 11.º Ano de Escolaridade Decreto-Lei n.º 139/2012, de 5 de julho Critérios de Classificação 11 Páginas Prova 715/1.ª
Exame Final Nacional de Física e Química A Prova 715 1.ª Fase Ensino Secundário 2017 11.º Ano de Escolaridade Decreto-Lei n.º 139/2012, de 5 de julho Critérios de Classificação 11 Páginas Prova 715/1.ª
Química Orgânica I Profa. Dra. Alceni Augusta Werle Profa. Dra. Tania Márcia do Sacramento Melo
 Química Orgânica I Profa. Dra. Alceni Augusta Werle Profa. Dra. Tania Márcia do Sacramento Melo Formas de representação e interações intermoleculares Aula 3 1- Fórmula química Maneira que os químicos possuem
Química Orgânica I Profa. Dra. Alceni Augusta Werle Profa. Dra. Tania Márcia do Sacramento Melo Formas de representação e interações intermoleculares Aula 3 1- Fórmula química Maneira que os químicos possuem
AULA 03 GASES Cap. 4 Russel PROF. MARCELL MARIANO CORRÊA MACENO
 AULA 03 GASES Cap. 4 Russel PROF. MARCELL MARIANO CORRÊA MACENO Características dos gases Os gases são altamente compressíveis e ocupam o volume total de seus recipientes. Quando um gás é submetido à pressão,
AULA 03 GASES Cap. 4 Russel PROF. MARCELL MARIANO CORRÊA MACENO Características dos gases Os gases são altamente compressíveis e ocupam o volume total de seus recipientes. Quando um gás é submetido à pressão,
11/Mar/2016 Aula 7 Entropia Variação da entropia em processos reversíveis Entropia e os gases ideais
 11/Mar/016 Aula 7 Entropia ariação da entropia em processos reversíveis Entropia e os gases ideais Entropia no ciclo de Carnot e em qualquer ciclo reversível ariação da entropia em processos irreversíveis
11/Mar/016 Aula 7 Entropia ariação da entropia em processos reversíveis Entropia e os gases ideais Entropia no ciclo de Carnot e em qualquer ciclo reversível ariação da entropia em processos irreversíveis
LCE0182 Química Analítica Quantitativa. Equilíbrio Químico. Wanessa Melchert Mattos
 LCE0182 Química Analítica Quantitativa Equilíbrio Químico Wanessa Melchert Mattos Equilíbrio Químico Estalactites: CaCO 3 (s) + CO 2 (aq) + H 2 O (l) Ca 2+ (aq) + 2 HCO 3- (aq) Estalagmites: Ca 2+ (aq)
LCE0182 Química Analítica Quantitativa Equilíbrio Químico Wanessa Melchert Mattos Equilíbrio Químico Estalactites: CaCO 3 (s) + CO 2 (aq) + H 2 O (l) Ca 2+ (aq) + 2 HCO 3- (aq) Estalagmites: Ca 2+ (aq)
Estudo Físico-Químico dos Gases
 Estudo Físico-Químico dos Gases Prof. Alex Fabiano C. Campos Fases de Agregação da Matéria Sublimação (sólido em gás ou gás em sólido) Gás Evaporação (líquido em gás) Condensação (gás em líquido) Sólido
Estudo Físico-Químico dos Gases Prof. Alex Fabiano C. Campos Fases de Agregação da Matéria Sublimação (sólido em gás ou gás em sólido) Gás Evaporação (líquido em gás) Condensação (gás em líquido) Sólido
Pontifícia Universidade Católica de Goiás Departamento de Biologia Bioquímica Metabólica ENZIMAS
 Pontifícia Universidade Católica de Goiás Departamento de Biologia Bioquímica Metabólica ENZIMAS Origem das proteínas e de suas estruturas Níveis de Estrutura Protéica Estrutura das proteínas Conformação
Pontifícia Universidade Católica de Goiás Departamento de Biologia Bioquímica Metabólica ENZIMAS Origem das proteínas e de suas estruturas Níveis de Estrutura Protéica Estrutura das proteínas Conformação
TERMODINÂMICA TERMOQUÍMICA
 TERMODINÂMICA TERMOQUÍMICA Termodinâmica é a ciência que estuda as transformações de energia nas quais as variações de temperatura são importantes. A maioria das transformações químicas resulta em alterações
TERMODINÂMICA TERMOQUÍMICA Termodinâmica é a ciência que estuda as transformações de energia nas quais as variações de temperatura são importantes. A maioria das transformações químicas resulta em alterações
Exame Final Nacional de Física e Química A Prova ª Fase Ensino Secundário º Ano de Escolaridade. Critérios de Classificação.
 Exame Final Nacional de Física e Química A Prova 715 1.ª Fase Ensino Secundário 2017 11.º Ano de Escolaridade Decreto-Lei n.º 139/2012, de 5 de julho Critérios de Classificação 11 Páginas Prova 715/1.ª
Exame Final Nacional de Física e Química A Prova 715 1.ª Fase Ensino Secundário 2017 11.º Ano de Escolaridade Decreto-Lei n.º 139/2012, de 5 de julho Critérios de Classificação 11 Páginas Prova 715/1.ª
ANEXO XIV. A) Alternativas de composição do Ciclo de Born-Haber para o CaF2, e. Proposta 1-A. Proposta 2-A
 ANEXO XIV Departamento Acadêmico, Questão 01: (Valor 0,00 a 2,00 pts) - [Cada um dos itens (A) e (B) vale 1,00 ponto]. A) Alternativas de composição do Ciclo de Born-Haber para o CaF2, e Proposta 1-A Proposta
ANEXO XIV Departamento Acadêmico, Questão 01: (Valor 0,00 a 2,00 pts) - [Cada um dos itens (A) e (B) vale 1,00 ponto]. A) Alternativas de composição do Ciclo de Born-Haber para o CaF2, e Proposta 1-A Proposta
Estudo Físico-Químico dos Gases
 19/08/009 Estudo Físico-Químico dos Gases Prof. Alex Fabiano C. Campos Gás e Vapor Diagrama de Fase Gás Vapor Gás: fluido elástico que não pode ser condensado apenas por aumento de pressão, pois requer
19/08/009 Estudo Físico-Químico dos Gases Prof. Alex Fabiano C. Campos Gás e Vapor Diagrama de Fase Gás Vapor Gás: fluido elástico que não pode ser condensado apenas por aumento de pressão, pois requer
Aula de Bioquímica I. Tema: Enzimas. Prof. Dr. Júlio César Borges
 Aula de Bioquímica I Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: borgesjc@iqsc.usp.br
Aula de Bioquímica I Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: borgesjc@iqsc.usp.br
P3 - PROVA DE QUÍMICA GERAL - 18/06/07
 P3 - PROVA DE QUÍMICA GERAL - 8/06/07 Nome: Nº de Matrícula: GABARITO Turma: Assinatura: Questão Valor Grau Revisão Dados gerais: G = - n F E o a,5 a,5 3 a,5 4 a,5 Total 0,0 RT ΔE = ΔE lnq nf G = G o +
P3 - PROVA DE QUÍMICA GERAL - 8/06/07 Nome: Nº de Matrícula: GABARITO Turma: Assinatura: Questão Valor Grau Revisão Dados gerais: G = - n F E o a,5 a,5 3 a,5 4 a,5 Total 0,0 RT ΔE = ΔE lnq nf G = G o +
