- HIBRIDAÇÃO DE SOUTHERN UTILIZANDO SONDAS NÃO RADIOACTIVAS 1ª
|
|
|
- Rui Godoi Van Der Vinne
- 7 Há anos
- Visualizações:
Transcrição
1 TP3 e TP4 - HIBRIDAÇÃO DE SOUTHERN UTILIZANDO SONDAS NÃO RADIOACTIVAS 1ª Parte: A- Separação em gel de agarose e visualização do DNA cromossómico de S. elodea ATCC após hidrólise com BamHI, EcoRI, HindIII ou PstI; B- Depurinação, desnaturação e neutralização do DNA no gel de agarose; C- Transferência por capilaridade do DNA cromossómico do gel de agarose para uma membrana de nylon com carga positive e fixação do DNA à membrana. 2ª Parte D- Preparação e marcação com digoxigenina do fragmento de DNA a utilizar como sonda (obtido no TP2_B, C, D); E- Pré-hibridação e Hibridação; F- Lavagens restringentes; G- Detecção dos sinais de hibridação. Introdução A técnica de hibridação dos ácidos nucleicos é uma das mais usadas em Biologia Molecular, mas também em diagnóstico clínico e na identificação de agentes patogénicos em produtos alimentares. Por esta razão, nos últimos anos, tem-se intensificado a procura de métodos de marcação de ácidos nucleicos que não utilizem radioisótopos, de modo a poderem ser usados sem qualquer limitação em rotina. Num protocolo básico de hibridação de ácidos nucleicos, a sonda marcada liga-se a uma sequência complementar alvo de DNA ou RNA, sequência esta que se pode encontrar em solução ou imobilizada a um suporte inerte. A sonda marcada é usada para pesquisar a presença ou ausência de determinada sequência alvo na mistura de reacção. Segue-se a detecção do híbrido sonda-molécula alvo, usando um sistema que deve apresentar um alto grau de sensibilidade e selectividade. Neste trabalho, pretende-se detectar e visualizar fragmentos do DNA cromossómico de S. elodea ATCC que contem o gene pgmg com base na técnica de hibridação de Southern. Será usado como sonda o fragmento de DNA que foi amplificado por PCR usando como molde o cromossoma de S. elodea (no TP2). A molécula-alvo será o DNA cromossómico de S. elodea previamente digerido com as enzimas de restrição BamHI, HindIII, PstI ou EcoRI. Utilizar-se-à o sistema comercial DIG High Prime DNA Labeling
2 and Detection Starter Kit I (Roche Applied Science). Este sistema usa digoxigenina (DIG) para marcar a sonda de DNA e a subsequente detecção colorimétrica dos híbridos DNA alvo-sonda com base num ensaio imunoenzimático. Procedimento experimental 1ª parte: A- Separação em gel de agarose e visualização do DNA cromossómico de S. elodea ATCC hidrolisado com BamHI, HindIII, PstI e EcoRI. 1. Usar alíquotas contendo 10 μg de DNA cromossómico que foi sujeito a hidrólise com as enzimas de restrição BamHI, HindIII, PstI e EcoRI num volume total de 20 μl contendo 10 U de enzima. 2. Proceder à sua separação electroforética de acordo com o descrito no ponto C do TP2. 3. Registar os resultados com um sistema de aquisição de imagem para documentação de géis (Bio-Rad; programa Quantity One ). O gel contendo os fragmentos resultantes da hidrólise do DNA cromossómico de S. elodea, separados por electroforese, será em seguida tratado (parte B) e os fragmentos serão transferidos para uma membrana de Nylon (parte C). Esta será posteriormente sujeita ao procedimento de hibridação com a sonda de DNA marcada com digoxigenina (parte E). B- Depurinação, desnaturação e neutralização do DNA no gel de agarose 1. Colocar o gel numa solução 0.25 M HCl, durante 10 minutos à temperatura ambiente, com agitação suave constante. 2. Colocar o gel numa solução 1.5 M NaCl/0.5 M NaOH durante 20 minutos, à temperatura ambiente e com agitação constante. 3. Colocar o gel numa solução 1M Tris.Cl ph 8.0/1.5M NaCl durante 25 minutos à temperatura ambiente e com agitação constante.
3 C- Transferência por capilaridade do DNA cromossómico do gel de agarose para uma membrana de nylon 1. Montar um sistema como o ilustrado na figura 1. Figura 1- Transferência do DNA do gel de agarose para a membrana de nylon. 2. Para transferência do DNA do gel de agarose para a membrana (membrana de nylon carregado positivamente - Boehringer Mannheim) colocar num tabuleiro com fundo plano 4 borrachas da mesma altura de modo a servir de base à colocação de uma placa de vidro com 20x20 cm. 3. Adicionar tampão 10xSSC (preparado com base em tampão 20xSSC = 3M NaCl, 0.3M Na3 Citrato.2H2O, ph 7.0) até atingir o nível da placa de vidro. 4. Colocar sobre a placa de vidro uma folha de papel "Whatman 3MM", de modo a que as extremidades fiquem embebidas no tampão. Ter o cuidado de não deixar bolhas de ar entre o vidro e o papel. 5. Colocar o gel em posição invertida sobre a folha de papel "Whatman 3 MM".
4 6. Passar a membrana de nylon por uma solução 2xSSC durante 2-3 minutos e colocar a membrana sobre o gel. 7. Referenciar as amostras na membrana não esquecendo que o gel foi colocado em posição invertida. 8. Sobre a membrana, colocar duas folhas de papel "Whatman 3 MM" que previamente foram embebidas em tampão 2xSSC. 9. Colocar papel absorvente (8-10 cm de altura) e, por último, um peso de aproximadamente 500 g. Com base neste sistema, a transferência do DNA do gel de agarose para a membrana prolongar-se-á por horas. 10. Remover o papel absorvente e colocar a membrana numa solução 6xSSC durante 5 minutos. 11. Remover o excesso de solução 6xSSC, colocando a membrana entre duas folhas de papel "Whatman 3MM". 12. Fixar o DNA à membrana por exposição à luz ultravioleta, num transiluminador UV, durante 3 minutos. 13. Secar a membrana à temperatura ambientee guardar até posterior utilização.
5 2ª parte: D- Preparação e marcação com digoxigenina (DIG) do fragmento de DNA a utilizar como sonda O fragmento de DNA utilizado como sonda neste trabalho foi obtido por amplificação por PCR a partir de uma região do genoma de S. elodea ATCC 31461, correspondente a parte do gene pgmg que codifica para uma proteína bifuncional com actividades de PGM/PMM (TP 2; v. pag. 58). A marcação do DNA que se pretende utilizar como sonda será efectuada por método enzimático, por ligação de DIG (grupo modificador) (Fig. 2). Para esse fim utilizar-se-á o sistema comercial DIG High Prime DNA Labeling (Roche Applied Science). Este sistema foi construído para marcar sondas de DNA por extensão de iniciadores com sequências aleatórias, em que esses oligonucleótidos hibridam com o DNA desnaturado permitindo a síntese de uma cadeia com uma sequência complementar à deste, por acção de uma DNA polimerase. A presença de um nucleótido marcado com digoxigenina (DIG-dUTP) durante a polimerização, resulta na sua incorporação nas cadeias em formação, originando uma sonda idêntica ao DNA inicial mas com digoxigenina incorporada. Template DNA Primer DIG-dUTP Figura 2- Diagrama representativo da marcação de um fragmento de DNA utilizando iniciadores com sequências aleatórias ("Multi-primer").
6 Técnica: 1. Adicionar num microtubo os seguintes componentes para um volume final de 20 μl: - 1 µg de DNA (proveniente de TP2_secção D) desnaturado pelo calor (5 minutos em água a ferver) Nota: estimar o volume necessário de solução do fragmento de DNA obtido no TP2_D, com base na determinação espectrofotométrica da respectiva concentração no sistema NanoDrop. - água desionizada estéril, de modo a perfazer 16 µl - 4 µl da mistura DIG-High Prime 5x concentrada, fornecida no kit comercial; esta mistura contém concentrações óptimas de: - nucleótidos (DIG-dUTP, datp, dctp, dgtp, dttp); - iniciadores (nonâmeros) aleatórios; - enzima (fragmento Klenow da DNA polimerase I de E. coli); - MgCl 2 e componentes do tampão (ph 7.8). 2. Incubar a mistura à temperatura de 37ºC durante a noite (~ 20 h) (ver Fig. 3). 3. Parar a reacção através da adição de 2 µl de uma solução de EDTA a 0.2 M (ph 8) ou por aquecimento a 65ºC durante 10 minutos. 4. Congelar a solução até posterior utilização, ou colocar o microtubo contendo o DNA num banho de água em ebulição durante 5 minutos, para desnaturar a sonda, e incubar em gelo (se se prosseguir de imediato para a hibridação). Nota: - A marcação da sonda será efectuada pelo docente.
7 - Procede-se também à marcação com digoxigenina de uma mistura de fragmentos padrão 1 Kbp DNA ladder (esta será adicionada à mistura de hibridação em conjunto com a sonda marcada (secção E) e permitirá visualizar os fragmentos de DNA padrão de tamanho conhecido, na membrana de hibridação). Figura 3. Rendimento de DNA marcado com DIG obtido a partir de diferentes quantidades de DNA molde após 1 ou 20h de incubação da mistura de reacção DIG High Prime a 37ºC (publicado no Manual de instruções DIG High Prime DNA Labeling and Detection Starter Kit I; Roche Applied Science). Por exemplo, partindo-se de 1000 ng de DNA molde, é de esperar obter aproximadamente 850 ng ou 2300 ng de DNA marcado com DIG se a reacção for conduzida durante 1 ou 20 h, respectivamente.
8 E- Pré-hibridação e Hibridação A membrana de Nylon com o DNA imobilizado será submetido a uma pré-hibridação de modo a minimizar a ligação não específica da sonda, antes de ser sujeita à hibridação com a sonda marcada. Nota: A hibridação será iniciada pelo docente no dia anterior à realização da aula. Técnica: 1. Preparar o tampão de pré-hibridação DIG Easy Hyb de acordo com as instruções do fornecedor, isto é, adicionar cuidadosamente 64 ml de água desionisada estéril (em 2 porções) aos grânulos DIG Easy Hyb e dissolver imediatamente através de agitação durante 5 min a 37ºC. Nota 1: Usar (10 ml / 100 cm 2 de membrana, para a pré-hibridação, e 3.5 ml/100 cm 2 de membrana, para a hibridação) Nota 2: o tampão de pré-hibridação comercial DIG Easy Hyb contém concentrações adequadas de: - solução SSC - dodecil sulfato de sódio (SDS) - líquido de bloqueio - DNA heterólogo de esperma de salmão 2. Aquecer o tampão de pré-hibridação a 55ºC. 3. Passar a membrana de Nylon contendo o DNA fixado (secção C) durante 2 minutos numa solução de 2xSSC. 4. Colocar a membrana no interior de um frasco de hibridação. 5. Adicionar ao frasco contendo a membrana 8 ml de tampão de pré-hibridação previamente aquecido (nota: para membrana com cerca de 7.7 x 10.4 cm, i.e. 80 cm 2 ).
9 6. Incubar durante 30 minutos, com agitação suave, a 55ºC, numa estufa de hibridação (TECHNE, Hybridiser HB-1D). 7. Entretanto, desnaturar pelo calor (5 minutos em banho de água a ferver) a sonda de DNA e a mistura de fragmentos DNA padrão marcados com DIG (secção D) e arrefecer rapidamente no gelo. (nota: cerca de 25 ng de sonda marcada / ml de tampão de hibridação) 8. Remover o tampão de pré-hibridação e adicionar 3 ml de mistura de hibridação constituida por tampão de pré-hibridação fresco ao qual foi adicionada a sonda de DNA desnaturada (nota: misturar bem, mas evitar a formação de bolhas). 9. Incubar durante a noite a 55ºC (ver Nota A), com agitação suave numa estufa de hibridação (TECHNE, Hybridiser HB-1D). Nota A Cálculo da Temperatura de Hibridação apropriada para o sistema DIG Easy Hyb (de acordo com o fornecedor): T optima = T m - 20 to 25ºC T m = (%G+C) (600 / l) l comprimento do hibrido em pares de bases % G+C (gene pgmg) = 66% l = 839 pb Pelo que, T opt = 51 a 56 ºC Nota B: o tampão DIG Easy Hyb contendo a sonda marcada com DIG pode ser armazenada a -15 a -20ºC e ser reutilizada várias vezes, quando desnaturada a 68ºC durante 10 minutos imediatamente antes da sua reutilização. IMPORTANTE - não ferva o tampão DIG Easy Hyb.
10 F- Lavagens restringentes 1. Terminada a hibridação, retirar o tampão e transferir a membrana para uma solução SSC 2x, SDS 0.1%, à temperatura ambiente. Lavar 2 x 5 min, com agitação suave. 2. Incubar 15 minutos com agitação moderada, a 60ºC. 3. Realizar uma nova lavagem a 60ºC, durante 15 minutos, com solução pré-aquecida de SSC 0.5x; SDS 0.1 %. G- Detecção dos sinais de hibridação A detecção de híbridos de DNA resultantes da ligação da sonda a sequências homólogas do DNA cromossómico imobilizado na membrana da nylon, será efectuada por um processo de imunodetecção enzimática, de acordo com o sistema comercial usado. Aos híbridos formados irá ligar-se um anticorpo conjugado, anti-dig-fosfatase alcalina (AP). A enzima repórter fosfatase alcalina irá catalisar a formação de cor a partir dos substratos colorimétricos NBT/BCIP, permitindo a visualização na membrana dos fragmentos do DNA cromossómico de S. elodea ATCC que contém o gene pgmg. Técnica: Todas as incubações devem ser realizadas à temperatura ambiente (15-25ºC). 1. Após as lavagens restringentes, lavar a membrana brevemente (1-5 min) no tampão de lavagem (NaCl 150 mm; Ácido maleico 100 mm, ph 7.5, Tween %(v/v)). 2. Incubar durante 30 minutos em 80 ml de solução de bloqueio (100 ml/100 cm 2 de membrana); preparar a solução de bloqueio no momento, por diluição 1:10 da solução de bloqueio 10x concentrada fornecida no sistema comercial, em tampão M (NaCl 150 mm; Ácido maleico 100 mm, ajustado a ph 7.5 com NaOH (sólido)). 3. Incubar durante 30 minutos em 16 ml de solução de anticorpo (20 ml/100 cm 2 de membrana); para preparar a solução de anticorpo, centrifugar a solução de anti- DIG-AP fornecida no sistema comercial, durante 5 min a rpm no microtubo
11 original, e pipetar o volume necessário cuidadosamente da superfície (diluir a solução anti-dig-ap 1:5000 em solução de bloqueio). 4. Lavar (2x15 min) com 80 ml de tampão de lavagem (NaCl 150 mm; Ácido maleico 100 mm, ph 7.5, Tween %(v/v)). 5. Equilibrar (2-5 min) em 16 ml de tampão de detecção (20 ml/100 cm 2 de membrana; 100 mm Tris-HCl, 100 mm NaCl, ph 9.5). 6. Incubar a membrana em 10 ml de solução de desenvolvimento de cor (200 μl da solução stock de NBT/BCIP em 10 ml de tampão de detecção), preparada imediatamente antes do início da reacção de detecção. Não agitar e manter no escuro (a membrana pode ser exposta à luz momentanemanete para monitorizar o desenvolvimento da cor). 7. Parar a reacção quando a intensidade do sinal/cor for a desejada, através da lavagem da membrana durante 5 min em 50 ml de água desionisada esterilizada ou tampão TE (10 mm Tris-HCl, 1 mm EDTA, ph 8.0). 8. Secar a membrana à temperatura ambiente. MANUAIS DE TÉCNICAS DE MANIPULAÇÃO GENÉTICA Ausubel, F.M., Brent, R., Kingston, R.E., Moore, D.D., Seidman, J.G., Smith, J.A. e Struhl, K., "Current Protocols in Molecular Biology", John Wiley & Sons, New York, Berger, S.L. and Kimmel, A.R." Guide to Molecular Cloning Techniques", Methods in Enzymology, 152, Academic Press, Inc., San Diego, Sambrook, J. and Maniatis, T. Molecular Cloning : A laboratory Manual, (3ª Ed.) Cold Spring Harbor Lab. Press, New York, 1989.
Estudo de um Polimorfismo no Gene da Cadeia Pesada β da Miosina (CPβM)
 Estudo de um Polimorfismo no Gene da Cadeia Pesada β da Miosina (CPβM) Ana Luísa Carvalho Departamento de Zoologia, Universidade de Coimbra Introdução: Neste trabalho pretende-se analisar um polimorfismo
Estudo de um Polimorfismo no Gene da Cadeia Pesada β da Miosina (CPβM) Ana Luísa Carvalho Departamento de Zoologia, Universidade de Coimbra Introdução: Neste trabalho pretende-se analisar um polimorfismo
Hibridação in situ por fluorescência FISH
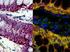 Universidade Estadual de Londrina Departamento de Biologia Geral Laboratório de Citogenética Animal - LACA Hibridação in situ por fluorescência FISH O protocolo descrito a seguir foi baseado nos procedimentos
Universidade Estadual de Londrina Departamento de Biologia Geral Laboratório de Citogenética Animal - LACA Hibridação in situ por fluorescência FISH O protocolo descrito a seguir foi baseado nos procedimentos
FISH. Tratamento com Pepsina (opcional pular para passo 8) Fluorescence in situ hybridization Protocolo p/ 10 lâminas
 FISH Fluorescence in situ hybridization Protocolo p/ 10 lâminas Tratamento com RNAse 1. Lavar as lâminas em tampão PBS 1x durante 5 min. em temperatura ambiente (shaker); 2. Desidratar as lâminas em série
FISH Fluorescence in situ hybridization Protocolo p/ 10 lâminas Tratamento com RNAse 1. Lavar as lâminas em tampão PBS 1x durante 5 min. em temperatura ambiente (shaker); 2. Desidratar as lâminas em série
Exercício 1. Calcule a concentração dos reagentes listados abaixo em mol L -1 Tabela 1. Propriedades de ácidos inorgânicos e hidróxido de amônio.
 ATIVIDADE 2 - CÁLCULO DE CONCENTRAÇÃO Exercício 1. Calcule a concentração dos reagentes listados abaixo em mol L -1 Tabela 1. Propriedades de ácidos inorgânicos e hidróxido de amônio. Exercício 2. Calcule
ATIVIDADE 2 - CÁLCULO DE CONCENTRAÇÃO Exercício 1. Calcule a concentração dos reagentes listados abaixo em mol L -1 Tabela 1. Propriedades de ácidos inorgânicos e hidróxido de amônio. Exercício 2. Calcule
Departamento de Biologia. Mestrado em Bioempreendedorismo e Biotecnologia de PAM
 Departamento de Biologia Mestrado em Bioempreendedorismo e Biotecnologia de PAM Protocolos das aulas práticas Docente: Rui Oliveira Construção de um plasmídeo com o gene da GFP sob regulação do promotor
Departamento de Biologia Mestrado em Bioempreendedorismo e Biotecnologia de PAM Protocolos das aulas práticas Docente: Rui Oliveira Construção de um plasmídeo com o gene da GFP sob regulação do promotor
Extracção de ADN de mancha de sangue por Chelex 100. Protocolo experimental:
 Extracção de ADN de mancha de sangue por Chelex 100 1. Num tubo eppendorf misturar 1ml de água desionizada estéril com uma mancha de sangue com aproximadamente 3mm²; 2. Incubar à temperatura ambiente no
Extracção de ADN de mancha de sangue por Chelex 100 1. Num tubo eppendorf misturar 1ml de água desionizada estéril com uma mancha de sangue com aproximadamente 3mm²; 2. Incubar à temperatura ambiente no
Preparação do gel de poliacrilamida
 Preparação do gel de poliacrilamida Materiais: - álcool 70% (limpeza) - SDS 10% - água Milli-Q - APS 10% - acrilamida/ bisacrilamida 40% - TEMED - tampão Tris-HCl, ph 8,8 e 6,8 - vidros 1º Limpar os vidros
Preparação do gel de poliacrilamida Materiais: - álcool 70% (limpeza) - SDS 10% - água Milli-Q - APS 10% - acrilamida/ bisacrilamida 40% - TEMED - tampão Tris-HCl, ph 8,8 e 6,8 - vidros 1º Limpar os vidros
Tecnologia do DNA recombinante. John Wiley & Sons, Inc.
 Tecnologia do DNA recombinante John Wiley & Sons, Inc. Tópicos Técnicas básicas usadas para identificar, amplificar e clonar genes Construção e triagem de bibliotecas de DNA Análise molecular de DNA, RNA
Tecnologia do DNA recombinante John Wiley & Sons, Inc. Tópicos Técnicas básicas usadas para identificar, amplificar e clonar genes Construção e triagem de bibliotecas de DNA Análise molecular de DNA, RNA
EXTRAÇÃO DE DNA DE SANGUE (LEUCÓCITOS)
 EXTRAÇÃO DE DNA DE SANGUE (LEUCÓCITOS) A) Obtenção de Leucócitos 1. Coletar 5mL de sangue em tubos contendo EDTA potássio (50uL de EDTA (k 3) a 15%). O EDTA é uma substância anticoagulante. Existem outras
EXTRAÇÃO DE DNA DE SANGUE (LEUCÓCITOS) A) Obtenção de Leucócitos 1. Coletar 5mL de sangue em tubos contendo EDTA potássio (50uL de EDTA (k 3) a 15%). O EDTA é uma substância anticoagulante. Existem outras
Apostila de aula prática REAÇÃO EM CADEIA PELA POLIMERASE (PCR)
 1 Universidade Federal Fluminense Instituto Biomédico Departamento de Microbiologia e Parasitologia Curso: Medicina Veterinária Disciplina: Virologia III (MIP00071) Apostila de aula prática REAÇÃO EM CADEIA
1 Universidade Federal Fluminense Instituto Biomédico Departamento de Microbiologia e Parasitologia Curso: Medicina Veterinária Disciplina: Virologia III (MIP00071) Apostila de aula prática REAÇÃO EM CADEIA
PCR Reação de Polimerase em Cadeia. Termociclador
 PCR Reação de Polimerase em Cadeia Termociclador REAÇÃO EM CADEIA DA POLIMERASE (PCR) Técnica que permite a amplificação da quantidade de DNA específico utilizando a enzima Taq DNA polimerase, sequências
PCR Reação de Polimerase em Cadeia Termociclador REAÇÃO EM CADEIA DA POLIMERASE (PCR) Técnica que permite a amplificação da quantidade de DNA específico utilizando a enzima Taq DNA polimerase, sequências
Departamento de Biologia. Mestrado em Bioempreendedorismo e Biotecnologia de PAM
 Departamento de Biologia Mestrado em Bioempreendedorismo e Biotecnologia de PAM Protocolos das aulas práticas Docente: Rui Oliveira P1-Análise da actividade do promotor CTA1 com o gene repórter GFP Ligação
Departamento de Biologia Mestrado em Bioempreendedorismo e Biotecnologia de PAM Protocolos das aulas práticas Docente: Rui Oliveira P1-Análise da actividade do promotor CTA1 com o gene repórter GFP Ligação
Molecular para Diagnóstico Clínico Western blotting. Prof. Dra. Marieta Torres de Abreu Assis
 Técnicas em Biologia Molecular para Diagnóstico Clínico Western blotting Prof. Dra. Marieta Torres de Abreu Assis Email: marietapitagoras@yahoo.com.br Western blotting ou Immunoblotting Ø Permite que proteínas
Técnicas em Biologia Molecular para Diagnóstico Clínico Western blotting Prof. Dra. Marieta Torres de Abreu Assis Email: marietapitagoras@yahoo.com.br Western blotting ou Immunoblotting Ø Permite que proteínas
BIBLIOTECAS DE DNA E HIBRIDIZAÇÃO. FABIANA SEIXAS
 BIBLIOTECAS DE DNA E HIBRIDIZAÇÃO FABIANA SEIXAS email: fabianak@ufpel.edu.br ABORDAGENS... BIBLIOTECAS DE DNA -Bibliotecas de DNA Genômico -Bibliotecas de cdna TÉCNICAS DE HIBIDIZAÇÃO -Hibidização em
BIBLIOTECAS DE DNA E HIBRIDIZAÇÃO FABIANA SEIXAS email: fabianak@ufpel.edu.br ABORDAGENS... BIBLIOTECAS DE DNA -Bibliotecas de DNA Genômico -Bibliotecas de cdna TÉCNICAS DE HIBIDIZAÇÃO -Hibidização em
Para 1L de meio triptona ou peptona 16g (1,6%) extrato de levedura 10g (1%) NaCl 5g (0,5%)
 Preparação de meio líquido - triptona ou peptona - extrato de levedura 1º Dissolver a triptona e o extrato; 2º Acrescentar o cloreto de sódio e acertar o volume; 3º Após tudo dissolvido e com volume correto,
Preparação de meio líquido - triptona ou peptona - extrato de levedura 1º Dissolver a triptona e o extrato; 2º Acrescentar o cloreto de sódio e acertar o volume; 3º Após tudo dissolvido e com volume correto,
Departamento de Biologia da Universidade do Minho
 Departamento de Biologia da Universidade do Minho Mestrado em Bioempreendedorismo e Biotecnologia em Plantas Aromáticas e Medicinais Ano lectivo de 2007/2008 Protocolos das aulas práticas Rui Oliveira
Departamento de Biologia da Universidade do Minho Mestrado em Bioempreendedorismo e Biotecnologia em Plantas Aromáticas e Medicinais Ano lectivo de 2007/2008 Protocolos das aulas práticas Rui Oliveira
Análises moleculares - DNA
 Análises moleculares - DNA Como o mapeamento genético contribui para a genética médica? A caracterização de um gene e suas mutações aumenta a compreensão da doença Aplicações: -Desenvolvimento de diagnóstico
Análises moleculares - DNA Como o mapeamento genético contribui para a genética médica? A caracterização de um gene e suas mutações aumenta a compreensão da doença Aplicações: -Desenvolvimento de diagnóstico
Kit de Clonagem Flex-C
 Kit de Clonagem Flex-C Instruções de Uso DESCRIÇÃO O Kit de Clonagem Flex-C é altamente eficiente, rápido e de fácil uso para clonagem por PCR. A enzima Flex-C permite a clonagem direta de qualquer fragmento
Kit de Clonagem Flex-C Instruções de Uso DESCRIÇÃO O Kit de Clonagem Flex-C é altamente eficiente, rápido e de fácil uso para clonagem por PCR. A enzima Flex-C permite a clonagem direta de qualquer fragmento
Hibridação de ácidos nucleicos. de cromossomo a chip de DNA
 Hibridação de ácidos nucleicos de cromossomo a chip de DNA Hibridação de ácidos nucleicos Pareamento complementar de bases entre duas fitas simples de ácido nucleico DNA DNA RNA RNA DNA - RNA Hibridação
Hibridação de ácidos nucleicos de cromossomo a chip de DNA Hibridação de ácidos nucleicos Pareamento complementar de bases entre duas fitas simples de ácido nucleico DNA DNA RNA RNA DNA - RNA Hibridação
MARCADORES MOLECULARES: AFLP E RFLP
 Universidade Federal de Pelotas Programa de Pós Graduação em Agronomia Disciplina de Biotecnologia Aplicada ao Melhoramento MARCADORES MOLECULARES: AFLP E RFLP Prof. PhD. Antonio Costa de Oliveira Gabriela
Universidade Federal de Pelotas Programa de Pós Graduação em Agronomia Disciplina de Biotecnologia Aplicada ao Melhoramento MARCADORES MOLECULARES: AFLP E RFLP Prof. PhD. Antonio Costa de Oliveira Gabriela
NextGeneration ECO One-Step RT-qPCR Kit
 DNA EXPRESS BIOTECNOLOGIA NextGeneration ECO One-Step RT-qPCR Kit Kit para uso em RT-PCR em tempo real quantitativo (RT-qPCR) em único tubo contendo NextGeneration Transcriptase Reversa M-MLV RNAse Minus
DNA EXPRESS BIOTECNOLOGIA NextGeneration ECO One-Step RT-qPCR Kit Kit para uso em RT-PCR em tempo real quantitativo (RT-qPCR) em único tubo contendo NextGeneration Transcriptase Reversa M-MLV RNAse Minus
PCR Prof. Dr. Fábio Gregori
 PCR Prof. Dr. Fábio Gregori Laboratório de Biologia Molecular Aplicada e Sorologia VPS-FMVZ-USP 1 Reação em Cadeia pela Polimerase Amplificação in vitro de DNA BANDA DNA (amplificado) DNA Agente infeccioso
PCR Prof. Dr. Fábio Gregori Laboratório de Biologia Molecular Aplicada e Sorologia VPS-FMVZ-USP 1 Reação em Cadeia pela Polimerase Amplificação in vitro de DNA BANDA DNA (amplificado) DNA Agente infeccioso
Procedimento Operacional Padrão - POP
 Página 1 de 10 IMT-POP-BB-0 Biobanco Procedimento Operacional Padrão para: Extração de DNA de sangue total POP: V. 1.0 Nome: Extração de DNA em sangue total Efetiva: dezembro, 22 autora: Erika Regina Manuli
Página 1 de 10 IMT-POP-BB-0 Biobanco Procedimento Operacional Padrão para: Extração de DNA de sangue total POP: V. 1.0 Nome: Extração de DNA em sangue total Efetiva: dezembro, 22 autora: Erika Regina Manuli
Hibridação in situ fluorescente em corte histológico (Câncer de Próstata)
 Hibridação in situ fluorescente em corte histológico (Câncer de Próstata) FISH em tecido incluído em parafina: Four Colour PTEN Deletion Probe O protocolo de FISH descrito abaixo é recomendado para cortes
Hibridação in situ fluorescente em corte histológico (Câncer de Próstata) FISH em tecido incluído em parafina: Four Colour PTEN Deletion Probe O protocolo de FISH descrito abaixo é recomendado para cortes
Cargo: D-41 Técnico Laboratório - Biotecnologia - Análise de Proteínas
 da Prova Prática QUESTÃO 1: Cargo: D-41 Técnico Laboratório - Biotecnologia - Análise de Proteínas Apresenta-se abaixo um protocolo para preparação de géis SDS-PAGE a ser utilizado em uma análise de confirmação
da Prova Prática QUESTÃO 1: Cargo: D-41 Técnico Laboratório - Biotecnologia - Análise de Proteínas Apresenta-se abaixo um protocolo para preparação de géis SDS-PAGE a ser utilizado em uma análise de confirmação
Hibridação in situ fluorescente em corte histológico (Câncer de Próstata)
 Hibridação in situ fluorescente em corte histológico (Câncer de Próstata) FISH em tecido incluído em parafina: Four Colour PTEN Deletion Probe O protocolo de FISH descrito abaixo é recomendado para cortes
Hibridação in situ fluorescente em corte histológico (Câncer de Próstata) FISH em tecido incluído em parafina: Four Colour PTEN Deletion Probe O protocolo de FISH descrito abaixo é recomendado para cortes
Detecção de IL-1 por ELISA sanduíche. Andréa Calado
 Detecção de IL-1 por ELISA sanduíche Andréa Calado andreabelfort@hotmail.com ELISA O teste identifica e quantifica Ag ou Ac, utilizando um dos dois conjugados com enzimas; PRINCIPAIS TIPOS: INDIRETO:
Detecção de IL-1 por ELISA sanduíche Andréa Calado andreabelfort@hotmail.com ELISA O teste identifica e quantifica Ag ou Ac, utilizando um dos dois conjugados com enzimas; PRINCIPAIS TIPOS: INDIRETO:
Diagnóstico Virológico
 Diagnóstico Virológico Para que serve? Importância do Diagnóstico Laboratorial Diferenciação de agentes que causam a mesma síndrome clínica Identificação de patógenos novos Diferenciação de fases de doença
Diagnóstico Virológico Para que serve? Importância do Diagnóstico Laboratorial Diferenciação de agentes que causam a mesma síndrome clínica Identificação de patógenos novos Diferenciação de fases de doença
PREPARAÇÃO DE CÉLULAS COMPETENTES DE Escherichia coli HB101
 PREPARAÇÃO DE CÉLULAS COMPETENTES DE Escherichia coli HB101 OBJECTIVO Obtenção de células competentes de Escherichia coli através de um método químico, para transformação de DNA plasmídico INTRODUÇÃO O
PREPARAÇÃO DE CÉLULAS COMPETENTES DE Escherichia coli HB101 OBJECTIVO Obtenção de células competentes de Escherichia coli através de um método químico, para transformação de DNA plasmídico INTRODUÇÃO O
Em nossos experimento serão utilizadas células SH SY5Y, uma sublinhagem de células de neuroblastoma SK-N-SH, figura 1.
 Procedimentos Em nossos experimento serão utilizadas células SH SY5Y, uma sublinhagem de células de neuroblastoma SK-N-SH, figura 1. As células serão submetidas a estresse oxidativo por meio do tratamento
Procedimentos Em nossos experimento serão utilizadas células SH SY5Y, uma sublinhagem de células de neuroblastoma SK-N-SH, figura 1. As células serão submetidas a estresse oxidativo por meio do tratamento
Alunos: Carlos Guilherme Reis, Roberta Silveira Professora: Fabiana Seixas Disciplina: Biologia Molecular
 Alunos: Carlos Guilherme Reis, Roberta Silveira Professora: Fabiana Seixas Disciplina: Biologia Molecular O que é PCR? Aplicações Técnicas: -Nested-PCR e artigos relacionados -PCR-Elisa e artigos relacionados
Alunos: Carlos Guilherme Reis, Roberta Silveira Professora: Fabiana Seixas Disciplina: Biologia Molecular O que é PCR? Aplicações Técnicas: -Nested-PCR e artigos relacionados -PCR-Elisa e artigos relacionados
GENÉTICA HUMANA LICENCIATURA EM CIÊNCIAS DA SAÚDE
 GENÉTICA HUMANA LICENCIATURA EM CIÊNCIAS DA SAÚDE PROTOCOLOS LABORATORIAIS 3º Ano - 1º Semestre 2013 / 2014 1 EXTRACÇÃO DE DNA GENÓMICO ESFREGAÇO BUCAL Citogene Buccal Kit Esfregar 10 vezes a mucosa bucal
GENÉTICA HUMANA LICENCIATURA EM CIÊNCIAS DA SAÚDE PROTOCOLOS LABORATORIAIS 3º Ano - 1º Semestre 2013 / 2014 1 EXTRACÇÃO DE DNA GENÓMICO ESFREGAÇO BUCAL Citogene Buccal Kit Esfregar 10 vezes a mucosa bucal
HEMOCENTRO RP TÉCNICA
 P. 1/9 1. OBJETIVO Genotipar os Alelos HLA em alta resolução. 2. APLICAÇÃO Aplica-se a amostras de DNA de pacientes e doadores. 3. RESPONSABILIDADE Assistentes de Laboratório, Técnicos, Aprimorandos, Bolsistas
P. 1/9 1. OBJETIVO Genotipar os Alelos HLA em alta resolução. 2. APLICAÇÃO Aplica-se a amostras de DNA de pacientes e doadores. 3. RESPONSABILIDADE Assistentes de Laboratório, Técnicos, Aprimorandos, Bolsistas
Universidade de Évora ICAAM Laboratório de Microbiologia do Solo 18/07/ /07/2011
 Universidade de Évora ICAAM Laboratório de Microbiologia do Solo Ana Neves José Neto 18/07/2011-22/07/2011 Responsável: Solange Oliveira Investigadoras: Marta Laranjo Ana Alexandre Rizóbios são bactérias
Universidade de Évora ICAAM Laboratório de Microbiologia do Solo Ana Neves José Neto 18/07/2011-22/07/2011 Responsável: Solange Oliveira Investigadoras: Marta Laranjo Ana Alexandre Rizóbios são bactérias
CONSTRUÇÃO DE BACTÉRIAS VERDES FLUORESCENTES PARA USO DIDÁTICO
 UNIVERSIDADE FEDERAL DE MINAS GERAIS INSTITUTO DE CIENCIAS BIOLOGICAS PROJETO DE BIOLOGIA MOLECULAR CONSTRUÇÃO DE BACTÉRIAS VERDES FLUORESCENTES PARA USO DIDÁTICO Débora do Vale Gabriela Modenesi Gabriela
UNIVERSIDADE FEDERAL DE MINAS GERAIS INSTITUTO DE CIENCIAS BIOLOGICAS PROJETO DE BIOLOGIA MOLECULAR CONSTRUÇÃO DE BACTÉRIAS VERDES FLUORESCENTES PARA USO DIDÁTICO Débora do Vale Gabriela Modenesi Gabriela
ZytoDot CEN 7 Probe. Para a deteção dos satélites alfa humanos do cromossoma 7 por meio de hibridação in situ cromogénica (CISH)
 ZytoDot CEN 7 Probe C-3008-400 40 (0,4 ml) Para a deteção dos satélites alfa humanos do cromossoma 7 por meio de hibridação in situ cromogénica (CISH).... Para utilização em diagnóstico in vitro em conformidade
ZytoDot CEN 7 Probe C-3008-400 40 (0,4 ml) Para a deteção dos satélites alfa humanos do cromossoma 7 por meio de hibridação in situ cromogénica (CISH).... Para utilização em diagnóstico in vitro em conformidade
ZytoDot. Para a deteção dos satélites alfa humanos do cromossoma 17 por meio de hibridação in situ cromogénica (CISH)
 ZytoDot CEN 17 Probe C-3006-400 40 (0,4 ml) Para a deteção dos satélites alfa humanos do cromossoma 17 por meio de hibridação in situ cromogénica (CISH).... Para utilização em diagnóstico in vitro em conformidade
ZytoDot CEN 17 Probe C-3006-400 40 (0,4 ml) Para a deteção dos satélites alfa humanos do cromossoma 17 por meio de hibridação in situ cromogénica (CISH).... Para utilização em diagnóstico in vitro em conformidade
MF-612.R-3 - MÉTODO DE DETERMINAÇÃO DE NITRATOS EM SUSPENSÃO NO AR POR COLORIMETRIA
 MF-612.R-3 - MÉTODO DE DETERMINAÇÃO DE NITRATOS EM SUSPENSÃO NO AR POR COLORIMETRIA 1. OBJETIVO Definir o método de determinação de nitratos em suspensão no ar, por colorimetria, utilizando 2,4 dimetilfenol
MF-612.R-3 - MÉTODO DE DETERMINAÇÃO DE NITRATOS EM SUSPENSÃO NO AR POR COLORIMETRIA 1. OBJETIVO Definir o método de determinação de nitratos em suspensão no ar, por colorimetria, utilizando 2,4 dimetilfenol
SUBSTÂNCIAS E MISTURAS
 Universidade de São Paulo Instituto de Química de São Carlos Departamento de Físico-Química SUBSTÂNCIAS E MISTURAS Prof. Dr. Edson Antonio Ticianelli edsont@iqsc.usp.br Monitor: Dr. Wanderson Oliveira
Universidade de São Paulo Instituto de Química de São Carlos Departamento de Físico-Química SUBSTÂNCIAS E MISTURAS Prof. Dr. Edson Antonio Ticianelli edsont@iqsc.usp.br Monitor: Dr. Wanderson Oliveira
BIOLOGIA MOLECULAR PARA O BACHARELADO BIO 0307 Sequenciamento de genoma
 BIOLOGIA MOLECULAR PARA O BACHARELADO BIO 0307 Sequenciamento de genoma - 2017 Etapas consecutivas, em comum para o sequenciamento massivo, em paralelo de DNA total de um genoma (métodos diferentes): 1)
BIOLOGIA MOLECULAR PARA O BACHARELADO BIO 0307 Sequenciamento de genoma - 2017 Etapas consecutivas, em comum para o sequenciamento massivo, em paralelo de DNA total de um genoma (métodos diferentes): 1)
Protocolo de extração de DNA de tecido vegetal: (Doyle & Doyle, 1987)
 Protocolo de extração de DNA de tecido vegetal: (Doyle & Doyle, 1987) PROCEDIMENTOS 1. Preparo do Material» Primeiro verifique se todas as soluções estão preparadas;» Ligue o banho-maria a 65ºC;» Prepare
Protocolo de extração de DNA de tecido vegetal: (Doyle & Doyle, 1987) PROCEDIMENTOS 1. Preparo do Material» Primeiro verifique se todas as soluções estão preparadas;» Ligue o banho-maria a 65ºC;» Prepare
Detecção de Seqüências Específicas de DNA
 Detecção de Seqüências Específicas de DNA Parte 1. Procurando um gene Imagine que você é um cientista e acabou de extrair um DNA. Você precisa saber se este DNA contém o gene para fibrose cística. Você
Detecção de Seqüências Específicas de DNA Parte 1. Procurando um gene Imagine que você é um cientista e acabou de extrair um DNA. Você precisa saber se este DNA contém o gene para fibrose cística. Você
Princípios e Aplicações da Técnica de PCR
 Universidade Federal de Santa Catarina Centro de Ciências Biológicas XVIII Semana Acadêmica da Biologia- UFSC Curso teórico-prático Princípios e Aplicações da Técnica de PCR Prof. Dr. Rafael D Rosa Departamento
Universidade Federal de Santa Catarina Centro de Ciências Biológicas XVIII Semana Acadêmica da Biologia- UFSC Curso teórico-prático Princípios e Aplicações da Técnica de PCR Prof. Dr. Rafael D Rosa Departamento
Sessão 1: Os Princípios e as Técnicas da Biologia Molecular do Séc XXI
 Sessão 1: Os Princípios e as Técnicas da Biologia Molecular do Séc XXI Menu do dia: -DNA RNA proteína - Sequenciação de genomas (Clonagem, electroforese em gel) - Transcritoma (Microarrays) - Organismos
Sessão 1: Os Princípios e as Técnicas da Biologia Molecular do Séc XXI Menu do dia: -DNA RNA proteína - Sequenciação de genomas (Clonagem, electroforese em gel) - Transcritoma (Microarrays) - Organismos
Procedimento Operacional Padrão - POP
 Página 1 de 10 Biobanco Procedimento Operacional Padrão para: Extração de RNA total de sangue POP: V. 1.0 Nome: Extração de RNA total de sangue Efetiva: dezembro, 22 autora: Erika Regina Manuli Aprovação
Página 1 de 10 Biobanco Procedimento Operacional Padrão para: Extração de RNA total de sangue POP: V. 1.0 Nome: Extração de RNA total de sangue Efetiva: dezembro, 22 autora: Erika Regina Manuli Aprovação
Extração de DNA/RNA Viral. Instruções de uso K204
 Extração de DNA/RNA Viral Instruções de uso K204 Revisão: Novembro/2018 ÍNDICE Finalidade... 3 Princípio de Ação... 3 Apresentação... 3 Reagentes... 4 Equipamentos e Insumos Operacionais... 4 Condições
Extração de DNA/RNA Viral Instruções de uso K204 Revisão: Novembro/2018 ÍNDICE Finalidade... 3 Princípio de Ação... 3 Apresentação... 3 Reagentes... 4 Equipamentos e Insumos Operacionais... 4 Condições
Actividade prática: Constrói os teus Kits de Genética!
 Actividade prática: Constrói os teus Kits de Genética! Mais uma vez vais vestir a tua bata de cientista e investigador e preparar o teu dia a dia no laboratório. Hoje é um dia especial, vais receber a
Actividade prática: Constrói os teus Kits de Genética! Mais uma vez vais vestir a tua bata de cientista e investigador e preparar o teu dia a dia no laboratório. Hoje é um dia especial, vais receber a
Polimerase Chain Reaction PCR
 Polimerase Chain Reaction PCR Reação em cadeia da polimerase Técnica in vitro utilizada para sintetizar muitas cópias de DNA Amplificar uma seqüência alvo específica Termociclador DNA molde dntp DNA polimerase
Polimerase Chain Reaction PCR Reação em cadeia da polimerase Técnica in vitro utilizada para sintetizar muitas cópias de DNA Amplificar uma seqüência alvo específica Termociclador DNA molde dntp DNA polimerase
CATÁLOGO DE KITS DE EXTRAÇÃO
 CATÁLOGO DE KITS DE EXTRAÇÃO KITS DE EXTRAÇÃO BIOPUR A extração de DNA é o primeiro passo para diferentes procedimentos na Biologia Molecular. Este processo é parte fundamental para se obter alta eficiência
CATÁLOGO DE KITS DE EXTRAÇÃO KITS DE EXTRAÇÃO BIOPUR A extração de DNA é o primeiro passo para diferentes procedimentos na Biologia Molecular. Este processo é parte fundamental para se obter alta eficiência
AULA PRÁTICA N 15: DETERMINAÇÃO DE PERÓXIDO DE HIDROGÊNIO NA ÁGUA OXIGENADA Volumetria de oxirredução permanganimetria volumetria direta
 3 AULA PRÁTICA N 15: DETERMINAÇÃO DE PERÓXIDO DE HIDROGÊNIO NA ÁGUA OXIGENADA Volumetria de oxirredução permanganimetria volumetria direta REAGENTES: Solução de permanganato de potássio 0,02 mol L -1,
3 AULA PRÁTICA N 15: DETERMINAÇÃO DE PERÓXIDO DE HIDROGÊNIO NA ÁGUA OXIGENADA Volumetria de oxirredução permanganimetria volumetria direta REAGENTES: Solução de permanganato de potássio 0,02 mol L -1,
Aprender a preparar soluções aquosas, realizar diluições e determinar suas concentrações.
 EXPERIMENTO 2 Preparação e Padronização de Soluções OBJETIVOS Rever os conceitos de concentração de soluções. Aprender a preparar soluções aquosas, realizar diluições e determinar suas concentrações. Exercitar
EXPERIMENTO 2 Preparação e Padronização de Soluções OBJETIVOS Rever os conceitos de concentração de soluções. Aprender a preparar soluções aquosas, realizar diluições e determinar suas concentrações. Exercitar
Técnicas de biologia molecular. da análise de genes e produtos gênicos únicos a abordagens em larga escala
 Técnicas de biologia molecular da análise de genes e produtos gênicos únicos a abordagens em larga escala os mesmos genes, qual a diferença? Dogma central Localizando alvos Técnicas iniciais para evidenciar
Técnicas de biologia molecular da análise de genes e produtos gênicos únicos a abordagens em larga escala os mesmos genes, qual a diferença? Dogma central Localizando alvos Técnicas iniciais para evidenciar
Catálogo de Kits de Extração
 Catálogo de Kits de Extração Kits de Extração Biopur A extração de DNA é o primeiro passo para diferentes procedimentos na Biologia Molecular. Este processo é parte fundamental para se obter alta eficiência
Catálogo de Kits de Extração Kits de Extração Biopur A extração de DNA é o primeiro passo para diferentes procedimentos na Biologia Molecular. Este processo é parte fundamental para se obter alta eficiência
DNA recombinante. Nilce M. Martinez Rossi Depto de Genética
 DNA recombinante Nilce M. Martinez Rossi Depto de Genética Descobertas marcantes 1962 Arber, Nathans e Smith Enzimas de restrição 1966 Niremberg, Ochoa e Khorana Elucidaram o código genético 1961 Marmur
DNA recombinante Nilce M. Martinez Rossi Depto de Genética Descobertas marcantes 1962 Arber, Nathans e Smith Enzimas de restrição 1966 Niremberg, Ochoa e Khorana Elucidaram o código genético 1961 Marmur
Biologia Celular e Molecular
 DEPARTAMENTO DE ZOOLOGIA FACULDADE DE CIÊNCIAS E TECNOLOGIA UNIVERSIDADE DE COIMBRA Biologia Celular e Molecular Detecção da presença de organismos geneticamente modificados em alimento por PCR 2007-2008
DEPARTAMENTO DE ZOOLOGIA FACULDADE DE CIÊNCIAS E TECNOLOGIA UNIVERSIDADE DE COIMBRA Biologia Celular e Molecular Detecção da presença de organismos geneticamente modificados em alimento por PCR 2007-2008
Estudo Estudo da Química
 Estudo Estudo da Química Prof. Railander Borges Fale com o Professor: Email: rayllander.silva.borges@gmail.com Instagram: @rayllanderborges Facebook: Raylander Borges Aula 16 CONCENTRAÇÃO DE SOLUÇÕES 1.
Estudo Estudo da Química Prof. Railander Borges Fale com o Professor: Email: rayllander.silva.borges@gmail.com Instagram: @rayllanderborges Facebook: Raylander Borges Aula 16 CONCENTRAÇÃO DE SOLUÇÕES 1.
Técnicas Moleculares: PCR, Sequenciamento e Southern Blot Técnicas Sorológicas
 UNIVERSIDADE FEDERAL DO PARANÁ SETOR DE CIÊNCIAS AGRÁRIAS DEPARTAMENTO DE FITOTECNIA E FITOSSANITARISMO AF 073- Biotecnologia Vegetal Técnicas Moleculares: PCR, Sequenciamento e Southern Blot Técnicas
UNIVERSIDADE FEDERAL DO PARANÁ SETOR DE CIÊNCIAS AGRÁRIAS DEPARTAMENTO DE FITOTECNIA E FITOSSANITARISMO AF 073- Biotecnologia Vegetal Técnicas Moleculares: PCR, Sequenciamento e Southern Blot Técnicas
Aplicações. Enzimas de restrição
 Engenharia genética - Capacidade de manipular ácidos núcleicos de forma bem definida e controlada. As ferramentas que o permitem são as enzimas capazes de actuarem sobre ácidos núcleicos. Enzimas de restrição
Engenharia genética - Capacidade de manipular ácidos núcleicos de forma bem definida e controlada. As ferramentas que o permitem são as enzimas capazes de actuarem sobre ácidos núcleicos. Enzimas de restrição
Ministério da Educação Universidade Federal do Paraná Setor Palotina. Soluções e cálculos de soluções
 Ministério da Educação Universidade Federal do Paraná Setor Palotina Aula Soluções e cálculos de soluções Prof. Isac G. Rosset Isac G. Rosset -UFPR Mistura vs Composto Mistura Os componentes podem ser
Ministério da Educação Universidade Federal do Paraná Setor Palotina Aula Soluções e cálculos de soluções Prof. Isac G. Rosset Isac G. Rosset -UFPR Mistura vs Composto Mistura Os componentes podem ser
PROTOCOLO DE UTILIZAÇAO
 PROTOCOLO DE UTILIZAÇAO Hibridação para cortes de tecidos preservados em parafina Materiais fornecidos: DNA marcado com moléculas fluorescentes (sonda). Buffer(tampão) de Hibridação Reativos para preparar
PROTOCOLO DE UTILIZAÇAO Hibridação para cortes de tecidos preservados em parafina Materiais fornecidos: DNA marcado com moléculas fluorescentes (sonda). Buffer(tampão) de Hibridação Reativos para preparar
mundo inteiro com uma variedade de aplicações como clonagem, genotipagem e sequenciamento.
 mundo inteiro com uma variedade de aplicações como clonagem, genotipagem e sequenciamento. necessária para que você possa alcançar o melhor desempenho nesta técnica. AGAROSE A agarose é um polissacarídeo
mundo inteiro com uma variedade de aplicações como clonagem, genotipagem e sequenciamento. necessária para que você possa alcançar o melhor desempenho nesta técnica. AGAROSE A agarose é um polissacarídeo
Análise Cromatográfica em Camada Delgada
 Seminário de Orgânica Experimental I Análise Cromatográfica em Camada Delgada - Rafael Antonino Joaquim Ingino - Tathiana Mayumi Arakaki Adsorventes Para realizarmos uma cromatografia em camada delgada,
Seminário de Orgânica Experimental I Análise Cromatográfica em Camada Delgada - Rafael Antonino Joaquim Ingino - Tathiana Mayumi Arakaki Adsorventes Para realizarmos uma cromatografia em camada delgada,
II - ELECTROFORESE DE AMINOÁCIDOS
 II - ELECTROFORESE DE AMINOÁCIDOS Introdução Muitas moléculas biológicas apresentam carga eléctrica cujo valor e sinal depende das suas características e também do ph e da composição do meio em que se
II - ELECTROFORESE DE AMINOÁCIDOS Introdução Muitas moléculas biológicas apresentam carga eléctrica cujo valor e sinal depende das suas características e também do ph e da composição do meio em que se
Electroforese de ácidos nucleicos
 Electroforese de ácidos nucleicos 1 A electroforese consiste em fazer migrar biomoléculas por uma matriz, sob a influência de um campo eléctrico, permitindo separá-las segundo as suas propriedades fisicoquímicas
Electroforese de ácidos nucleicos 1 A electroforese consiste em fazer migrar biomoléculas por uma matriz, sob a influência de um campo eléctrico, permitindo separá-las segundo as suas propriedades fisicoquímicas
Ficha de protocolo do QIAsymphony SP
 Fevereiro de 2017 Ficha de protocolo do QIAsymphony SP circdna_2000_dsp_v1 e circdna_4000_dsp_v1 Este documento é a ficha de protocolo do QIAsymphony circdna_2000_dsp_v1 e circdna_4000_dsp_v1, versão 1,
Fevereiro de 2017 Ficha de protocolo do QIAsymphony SP circdna_2000_dsp_v1 e circdna_4000_dsp_v1 Este documento é a ficha de protocolo do QIAsymphony circdna_2000_dsp_v1 e circdna_4000_dsp_v1, versão 1,
1 º Exame Engenharia Genética 11 de Janeiro de 2013 Duração: 2h30min.
 Nome: Curso: Nº 1 º Exame Engenharia Genética 11 de Janeiro de 2013 Duração: 2h30min. A bactéria Edwardsiella tarda causa septicémia hemorrágica em peixes bem como infecções gastrointestinais em humanos.
Nome: Curso: Nº 1 º Exame Engenharia Genética 11 de Janeiro de 2013 Duração: 2h30min. A bactéria Edwardsiella tarda causa septicémia hemorrágica em peixes bem como infecções gastrointestinais em humanos.
AMPLIFICAÇÃO DO GENE DA PROTEÍNA E DO VÍRUS DENV ATRAVÉS DA TÉCNICA DE REAÇÃO EM CADEIA DA POLIMERASE (PCR)
 AMPLIFICAÇÃO DO GENE DA PROTEÍNA E DO VÍRUS DENV ATRAVÉS DA TÉCNICA DE REAÇÃO EM CADEIA DA POLIMERASE (PCR) Beatriz Dantas Guimarães (1); Lucas Linhares de Locio (2); Herbert Crisóstomo dos Santos Araújo
AMPLIFICAÇÃO DO GENE DA PROTEÍNA E DO VÍRUS DENV ATRAVÉS DA TÉCNICA DE REAÇÃO EM CADEIA DA POLIMERASE (PCR) Beatriz Dantas Guimarães (1); Lucas Linhares de Locio (2); Herbert Crisóstomo dos Santos Araújo
Aplicações de anticorpos em métodos diagnósticos
 Aula Prática Demonstrativa: Aplicações de anticorpos em métodos diagnósticos Introdução Profa. Cristina MED- 2017 Detecção de anticorpos (diagnóstico sorológico) Exemplo: detecção de anticorpos em jovem
Aula Prática Demonstrativa: Aplicações de anticorpos em métodos diagnósticos Introdução Profa. Cristina MED- 2017 Detecção de anticorpos (diagnóstico sorológico) Exemplo: detecção de anticorpos em jovem
4 O anticoagulante mais utilizado na coleta de sangue para a extração de DNA é:
 CONCURSO PARA VAGA DE TÉCNICO DE LABORATÓRIO PROVA ESPECÍFICA 1ª FASE NOME: RG: DATA: 1 A extração de DNA é possível na seguinte condição: 2 - Um rastro fragmentado de DNA em gel de agarose indica: 3 A
CONCURSO PARA VAGA DE TÉCNICO DE LABORATÓRIO PROVA ESPECÍFICA 1ª FASE NOME: RG: DATA: 1 A extração de DNA é possível na seguinte condição: 2 - Um rastro fragmentado de DNA em gel de agarose indica: 3 A
IDENTIFICAÇÃO DE SEQUÊNCIAS POR HIBRIDIZAÇÃO E SEQUENCIAMENTO. Aula 5. Maria Carolina Quecine Departamento de Genética
 IDENTIFICAÇÃO DE SEQUÊNCIAS POR HIBRIDIZAÇÃO E SEQUENCIAMENTO Aula 5 LGN232 Genética Molecular Maria Carolina Quecine Departamento de Genética mquecine@usp.br LEMBRANDO O DOGMA CENTRAL DA BIOLOGIA MOLECULAR
IDENTIFICAÇÃO DE SEQUÊNCIAS POR HIBRIDIZAÇÃO E SEQUENCIAMENTO Aula 5 LGN232 Genética Molecular Maria Carolina Quecine Departamento de Genética mquecine@usp.br LEMBRANDO O DOGMA CENTRAL DA BIOLOGIA MOLECULAR
FISIOLOGIA ANIMAL II
 DEPARTAMENTO DE ZOOLOGIA FACULDADE DE CIÊNCIAS E TECNOLOGIA UNIVERSIDADE DE COIMBRA FISIOLOGIA ANIMAL II AULA 5 Teste ELISA para o VIH PAULO SANTOS 2006 1 OBJECTIVOS Consolidar conhecimentos relativos
DEPARTAMENTO DE ZOOLOGIA FACULDADE DE CIÊNCIAS E TECNOLOGIA UNIVERSIDADE DE COIMBRA FISIOLOGIA ANIMAL II AULA 5 Teste ELISA para o VIH PAULO SANTOS 2006 1 OBJECTIVOS Consolidar conhecimentos relativos
Eletroforese de DNA. Gabriel M. Matos Nicolas Conceição
 Eletroforese de DNA Gabriel M. Matos Nicolas Conceição Eletroforese Usada para separar, identificar e purificar fragmentos de DNA; Bastante sensível, capaz de detectar até 20 pg de DNA; Permite a recuperação
Eletroforese de DNA Gabriel M. Matos Nicolas Conceição Eletroforese Usada para separar, identificar e purificar fragmentos de DNA; Bastante sensível, capaz de detectar até 20 pg de DNA; Permite a recuperação
Preparação e padronização de soluções
 INSTITUTO POLITÉCNICO DE TOMAR ESCOLA SUPERIOR DE TECNOLOGIA Departamento de Engenharia Química e do Ambiente QUÍMICA I (1º Ano 1º Semestre) Trabalho Prático nº 2 Preparação e padronização de soluções
INSTITUTO POLITÉCNICO DE TOMAR ESCOLA SUPERIOR DE TECNOLOGIA Departamento de Engenharia Química e do Ambiente QUÍMICA I (1º Ano 1º Semestre) Trabalho Prático nº 2 Preparação e padronização de soluções
Amplificação, Detecção e Quantificação. Daniela Cochicho Luís Martins
 Amplificação, Detecção e Quantificação PCR em Tempo Real Daniela Cochicho Luís Martins I curso de Virologia Molecular em Oncologia PCR Clássico The polymerase chain reaction (PCR) is one of the most powerful
Amplificação, Detecção e Quantificação PCR em Tempo Real Daniela Cochicho Luís Martins I curso de Virologia Molecular em Oncologia PCR Clássico The polymerase chain reaction (PCR) is one of the most powerful
Concurso Público Edital nº 342/2013. Técnico de Laboratório Biotecnologia - Análise de Proteínas. Leia com atenção as Instruções
 D-41 Concurso Público 2014 - Edital nº 342/2013 Técnico de Laboratório prova prática/discursiva Leia com atenção as Instruções 1. Você recebeu do fi scal um caderno de respostas da prova prática/discursiva
D-41 Concurso Público 2014 - Edital nº 342/2013 Técnico de Laboratório prova prática/discursiva Leia com atenção as Instruções 1. Você recebeu do fi scal um caderno de respostas da prova prática/discursiva
MF-431.R-1 - MÉTODO TURBIDIMÉTRICO PARA DETERMINAÇÃO DE SULFATO
 MF-431.R-1 - MÉTODO TURBIDIMÉTRICO PARA DETERMINAÇÃO DE SULFATO Notas: Revisão aprovada pela Deliberação CECA nº 0102, de 04 de setembro de 1980. Publicada no DOERJ de 18 de setembro de 1980. 1. OBJETIVO
MF-431.R-1 - MÉTODO TURBIDIMÉTRICO PARA DETERMINAÇÃO DE SULFATO Notas: Revisão aprovada pela Deliberação CECA nº 0102, de 04 de setembro de 1980. Publicada no DOERJ de 18 de setembro de 1980. 1. OBJETIVO
Ajustar o ph para 7,4. Filtrar o meio em 0,22 µm no fluxo e depois acrescentar o antibiótico/antimicótico. Armazenar de 2ºC a 8ºC.
 ANEXO I - SOLUÇÕES A Para expansão dos hibridomas Meio de cultura (solução-estoque) Meio RPMI - Roswell Park Memorial 10,4 g Institute (Gibco, Invitrogen) NaHCO 3 2 g HEPES 4,68 g Antibiótico/antimicótico
ANEXO I - SOLUÇÕES A Para expansão dos hibridomas Meio de cultura (solução-estoque) Meio RPMI - Roswell Park Memorial 10,4 g Institute (Gibco, Invitrogen) NaHCO 3 2 g HEPES 4,68 g Antibiótico/antimicótico
PCR (Polymerase chain reaction) Reação em cadeia da DNA polimerase. e suas aplicações
 PCR (Polymerase chain reaction) Reação em cadeia da DNA polimerase e suas aplicações Bianca Zingales zingales@iq.usp.br PCR é uma Técnica - Desenvolvida por Kary Mullis e colaboradores em 1983 - É um método
PCR (Polymerase chain reaction) Reação em cadeia da DNA polimerase e suas aplicações Bianca Zingales zingales@iq.usp.br PCR é uma Técnica - Desenvolvida por Kary Mullis e colaboradores em 1983 - É um método
Identificação de sementes de soja geneticamente modificadas utilizando a técnica de PCR convencional
 Identificação de sementes de soja geneticamente modificadas utilizando a técnica de PCR convencional HONNA,P.T. 1 ; GIROTTO, L. 2 ; SOLDERA, M.C.A. 2 ; KANAMORI, N. 3 ;MARCELINO-GUIMARAES, F. C. 4 ; YAMAGUCHI-SHINOZAKI,
Identificação de sementes de soja geneticamente modificadas utilizando a técnica de PCR convencional HONNA,P.T. 1 ; GIROTTO, L. 2 ; SOLDERA, M.C.A. 2 ; KANAMORI, N. 3 ;MARCELINO-GUIMARAES, F. C. 4 ; YAMAGUCHI-SHINOZAKI,
Síntese do acetato de n-butilo ou etanoato de n-butilo
 Síntese do acetato de n-butilo ou etanoato de n-butilo Realização experimental a microescala (baseado no protocolo de Williamson 1 ) A reacção entre o butan-1-ol e o ácido acético glacial (ou ácido etanoico)
Síntese do acetato de n-butilo ou etanoato de n-butilo Realização experimental a microescala (baseado no protocolo de Williamson 1 ) A reacção entre o butan-1-ol e o ácido acético glacial (ou ácido etanoico)
SÍNTESE DO SULFATO DE TETRAAMINA COBRE (II) MONO HIDRATADO
 SÍNTESE DO SULFATO DE TETRAAMINA COBRE (II) MONO HIDRATADO O que se pretende Realizar laboratorialmente a síntese do sal sulfato de tetraaminacobre (II) monohidratado, uma substância usado como fungicida
SÍNTESE DO SULFATO DE TETRAAMINA COBRE (II) MONO HIDRATADO O que se pretende Realizar laboratorialmente a síntese do sal sulfato de tetraaminacobre (II) monohidratado, uma substância usado como fungicida
Cargo: D-43 - Tecnólogo Laboratório Meio ambiente
 da Prova Prática QUESTÃO 1: Cargo: D-43 - Tecnólogo Laboratório Meio ambiente A titulometria volumétrica envolve a medida de volume de uma solução de concentração conhecida, necessária para reagir essencial
da Prova Prática QUESTÃO 1: Cargo: D-43 - Tecnólogo Laboratório Meio ambiente A titulometria volumétrica envolve a medida de volume de uma solução de concentração conhecida, necessária para reagir essencial
Southern blotting análise de DNA. Northern blotting análise de RNA. Western blotting análise de proteínas
 Southern blotting análise de DNA Northern blotting análise de RNA Western blotting análise de proteínas Southern blotting Hibridação DNA-DNA em membrana Southern blot Digestão enzimática Eletroforese em
Southern blotting análise de DNA Northern blotting análise de RNA Western blotting análise de proteínas Southern blotting Hibridação DNA-DNA em membrana Southern blot Digestão enzimática Eletroforese em
BacBio. Crescimento, Renovação Celular e Reprodução: da teoria à prática. Coimbra, 2012/2013. Sandra Gamboa Andreia Quaresma Fernando Delgado
 BacBio Crescimento, Renovação Celular e Reprodução: da teoria à prática Coimbra, 2012/2013 Sandra Gamboa Andreia Quaresma Fernando Delgado Escolher Ciência PEC282 ESCOLA SUPERIOR AGRÁRIA DE COIMBRA BacBio
BacBio Crescimento, Renovação Celular e Reprodução: da teoria à prática Coimbra, 2012/2013 Sandra Gamboa Andreia Quaresma Fernando Delgado Escolher Ciência PEC282 ESCOLA SUPERIOR AGRÁRIA DE COIMBRA BacBio
Escola Secundária / 3º CEB da Batalha ACTIVIDADE LABORATORIAL DE FÍSICA E QUÍMICA A FORMAÇÃO ESPECÍFICA ENSINO SECUNDÁRIO. Ano de Escolaridade : 11
 Escola Secundária / 3º CEB da Batalha ACTIVIDADE LABORATORIAL DE FÍSICA E QUÍMICA A FORMAÇÃO ESPECÍFICA ENSINO SECUNDÁRIO Ano de Escolaridade : 11 AL 2.5 Solubilidade: solutos e solventes Apesar da água
Escola Secundária / 3º CEB da Batalha ACTIVIDADE LABORATORIAL DE FÍSICA E QUÍMICA A FORMAÇÃO ESPECÍFICA ENSINO SECUNDÁRIO Ano de Escolaridade : 11 AL 2.5 Solubilidade: solutos e solventes Apesar da água
Métodos Analíticos de Controle de Alergênicos em Alimentos Juliana Ramos - R-Biopharm Brasil
 Reunião de vendas II/14 Campinas SP 26. 28. de Agosto 2014 Métodos Analíticos de Controle de Alergênicos em Alimentos Juliana Ramos - R-Biopharm Brasil Alergias Alimentares Alergias Alimentares 170 alimentos
Reunião de vendas II/14 Campinas SP 26. 28. de Agosto 2014 Métodos Analíticos de Controle de Alergênicos em Alimentos Juliana Ramos - R-Biopharm Brasil Alergias Alimentares Alergias Alimentares 170 alimentos
Extração de DNA e Amplificação por PCR
 Universidade Federal de São Carlos Departamento de Genética e Evolução Disciplina Práticas de Genética Extração de DNA e Amplificação por PCR Érique de Castro 405523, Victor Martyn 405612, Wilson Lau Júnior
Universidade Federal de São Carlos Departamento de Genética e Evolução Disciplina Práticas de Genética Extração de DNA e Amplificação por PCR Érique de Castro 405523, Victor Martyn 405612, Wilson Lau Júnior
Perguntas para o roteiro de aula. 1) Descreva as principais características estruturais gerais das moléculas de DNA e
 Perguntas para o roteiro de aula Professora: Drª Marilda S. Gonçalves Propriedades físico-químicas dos ácidos nucléicos 1) Descreva as principais características estruturais gerais das moléculas de DNA
Perguntas para o roteiro de aula Professora: Drª Marilda S. Gonçalves Propriedades físico-químicas dos ácidos nucléicos 1) Descreva as principais características estruturais gerais das moléculas de DNA
ACÇÃO DE FORMAÇÃO GUIÃO DE ACTIVIDADE PRÁTICA. (Versão Professor)
 Escola Secundária Marques de Castilho ÁGUEDA ACÇÃO DE FORMAÇÃO UTILIZAÇÃO DOS NOVOS LABORATÓRIOS ESCOLARES GUIÃO DE ACTIVIDADE PRÁTICA FUNCIONAMENTO DE UM SISTEMA TAMPÃO (Versão Professor) Formando: Henrique
Escola Secundária Marques de Castilho ÁGUEDA ACÇÃO DE FORMAÇÃO UTILIZAÇÃO DOS NOVOS LABORATÓRIOS ESCOLARES GUIÃO DE ACTIVIDADE PRÁTICA FUNCIONAMENTO DE UM SISTEMA TAMPÃO (Versão Professor) Formando: Henrique
ÁCIDO ÚRICO. REAGENTES Primary Inject (A): Reagente de Cor O reagente está pronto para uso. Aconselhamos a leitura das Instruções de Uso.
 ÁCIDO ÚRICO Primary Inject (A): Reagente de Cor O reagente está pronto para uso. Aconselhamos a leitura das Instruções de Uso. # Usar os calibrador protéico da Katal. Verificar os parâmetros da aplicação
ÁCIDO ÚRICO Primary Inject (A): Reagente de Cor O reagente está pronto para uso. Aconselhamos a leitura das Instruções de Uso. # Usar os calibrador protéico da Katal. Verificar os parâmetros da aplicação
Preparação do cloreto de t-butila. Carina de Freitas Vellosa Daiane Cristina Romanini
 Preparação do cloreto de t-butila Carina de Freitas Vellosa Daiane Cristina Romanini Técnicas e Materiais Utilizados Funil de separação: serve para extrair duas soluções imiscíveis. A fase orgânica pode
Preparação do cloreto de t-butila Carina de Freitas Vellosa Daiane Cristina Romanini Técnicas e Materiais Utilizados Funil de separação: serve para extrair duas soluções imiscíveis. A fase orgânica pode
BIOQUÍMICA EXPERIMENTAL
 Departamento de Bioquímica Instituto de Química USP Apostila de protocolos Parte A BIOQUÍMICA EXPERIMENTAL QBQ 036N 05 Professores Carlos T. Hotta Ronaldo B. Quaggio Esta apostila foi desenvolvida originalmente
Departamento de Bioquímica Instituto de Química USP Apostila de protocolos Parte A BIOQUÍMICA EXPERIMENTAL QBQ 036N 05 Professores Carlos T. Hotta Ronaldo B. Quaggio Esta apostila foi desenvolvida originalmente
SOLUBILIDADE DE SÓLIDOS EM LÍQUIDOS
 EXPERIMENTO 4 SOLUBILIDADE DE SÓLIDOS EM LÍQUIDOS OBJETIVOS Observar soluções insaturadas, saturadas e supersaturadas; Construir a curva de solubilidade de um sal inorgânico. INTRODUÇÃO Os depósitos naturais
EXPERIMENTO 4 SOLUBILIDADE DE SÓLIDOS EM LÍQUIDOS OBJETIVOS Observar soluções insaturadas, saturadas e supersaturadas; Construir a curva de solubilidade de um sal inorgânico. INTRODUÇÃO Os depósitos naturais
TÍTULO: ANÁLISE TITRIMÉTRICA (Volumétrica)
 Componente Curricular: Química dos Alimentos Prof. Barbosa e Prof. Daniel 4º Módulo de Química Procedimento de Prática Experimental Competências: Identificar as propriedades dos alimentos. Identificar
Componente Curricular: Química dos Alimentos Prof. Barbosa e Prof. Daniel 4º Módulo de Química Procedimento de Prática Experimental Competências: Identificar as propriedades dos alimentos. Identificar
ELECTROPHORESIS 4 detecção electroforética de DNA
 ÍNDICE USO PREVISTO pág. 1 PRINCÍPIO DO MÉTODO pág. 2 DESCRIÇÃO DO KIT pág. 2 MATERIAL INCLUÍDO NO KIT pág. 2 MATERIAL NECESSÁRIO NÃO INCLUÍDO NO KIT pág. 3 OTROS PRODUTOS REQUERIDO pág. 3 ADVERTÊNCIAS
ÍNDICE USO PREVISTO pág. 1 PRINCÍPIO DO MÉTODO pág. 2 DESCRIÇÃO DO KIT pág. 2 MATERIAL INCLUÍDO NO KIT pág. 2 MATERIAL NECESSÁRIO NÃO INCLUÍDO NO KIT pág. 3 OTROS PRODUTOS REQUERIDO pág. 3 ADVERTÊNCIAS
ESCOLA SECUNDÁRIA DE S. LOURENÇO EM PORTALEGRE ACTIVIDADE LABORATORIAL QUÍMICA 11º ANO TITULAÇÃO ÁCIDO-BASE. Versão professor. Algumas notas prévias
 ESCOLA SECUNDÁRIA DE S. LOURENÇO EM PORTALEGRE ACTIVIDADE LABORATORIAL QUÍMICA 11º ANO TITULAÇÃO ÁCIDO-BASE Versão professor O que se pretende: Conhecer processos para neutralizar resíduos de ácidos/bases
ESCOLA SECUNDÁRIA DE S. LOURENÇO EM PORTALEGRE ACTIVIDADE LABORATORIAL QUÍMICA 11º ANO TITULAÇÃO ÁCIDO-BASE Versão professor O que se pretende: Conhecer processos para neutralizar resíduos de ácidos/bases
Transiluminador. Características
 Produtos para PCR pcr A PCR - Reação em Cadeia da Polimerase - é uma técnica de biologia molecular que permite a replicação in vitro do DNA de maneira eficiente, utilizando amostras que podem ser amplificadas
Produtos para PCR pcr A PCR - Reação em Cadeia da Polimerase - é uma técnica de biologia molecular que permite a replicação in vitro do DNA de maneira eficiente, utilizando amostras que podem ser amplificadas
Produtos não passíveis de regulamentação na ANVISA.
 Produtos para PCR PCR A PCR - Reação em Cadeia da Polimerase - é uma técnica de biologia molecular que permite a replicação in vitro do DNA de maneira eficiente, utilizando amostras que podem ser amplificadas
Produtos para PCR PCR A PCR - Reação em Cadeia da Polimerase - é uma técnica de biologia molecular que permite a replicação in vitro do DNA de maneira eficiente, utilizando amostras que podem ser amplificadas
fmvz-unesp FACULDADE DE MEDICINA VETERINÁRIA E ZOOTECNIA - BOTUCATU Curso de Pós-Graduação em Zootecnia Nutrição e Produção Animal
 fmvz-unesp FACULDADE DE MEDICINA VETERINÁRIA E ZOOTECNIA - BOTUCATU Curso de Pós-Graduação em Zootecnia Nutrição e Produção Animal MÉTODOS DE DETERMINAÇÃO DE AMINOÁCIDOS NOS ALIMENTOS Kátia Sardinha Bisinato
fmvz-unesp FACULDADE DE MEDICINA VETERINÁRIA E ZOOTECNIA - BOTUCATU Curso de Pós-Graduação em Zootecnia Nutrição e Produção Animal MÉTODOS DE DETERMINAÇÃO DE AMINOÁCIDOS NOS ALIMENTOS Kátia Sardinha Bisinato
IDENTIFICAÇÃO DE SUBSTÂNCIAS E AVALIAÇÃO DA SUA PUREZA
 IDENTIFICAÇÃO DE SUBSTÂNCIAS E AVALIAÇÃO DA SUA PUREZA O que se pretende Utilizar técnicas experimentais de determinação de propriedades físicas características das substâncias como métodos de identificação
IDENTIFICAÇÃO DE SUBSTÂNCIAS E AVALIAÇÃO DA SUA PUREZA O que se pretende Utilizar técnicas experimentais de determinação de propriedades físicas características das substâncias como métodos de identificação
