Mecanismo de Inibição de Enzimas Preparação de Micro e Macromoléculas Docagem Molecular Exemplo de Aplicação
|
|
|
- David Bentes Tavares
- 6 Há anos
- Visualizações:
Transcrição
1 bjetivos FFI0776 Modelagem e Engenharia de Proteínas Mecanismo de Inibição de Enzimas Preparação de Micro e Macromoléculas M l Docagem Molecular Exemplo de Aplicação Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Bacharelado em Ciências Físicas e Biomoleculares em e Biomoleculares Instituto de Física de São Carlos USP Mecanismo de inibição Sítio de ligação Inibidor competitivo GAPDH Leishmania mexicana IC 50 = 4 µm inibidor competitivo Suresh et al J Mol Biol
2 Sítio de de ligação Inibidor não-competitivo Mecanismo de inibição RA Polimerase vírus hepatite C Sítio catalítico = V max [I] = 9 µm K M 1/V [I] = 5 µm [I] = 3 µm Sítio de ligação [I] = 0 µm IC 50 =093µM =0,93 inibidor não competitivo L t l J Vi l /[substrato] Inibidor competitivo Identificação da cavidade de ligação Preparação de macro e micromoléculas para docagem molecular molecular Análise de complexos cristalográficos Ligante-macromolécula Análise estrutural t comparativa membro conhecido da superfamília da macromolécula em complexo com um ligante
3 Seleção da geometria Macromoléculas possuem alto grau de liberdade interno Flexibilidade determina o fenômeno conhecido como mudança conformacional Local envolvem apenas as cadeias laterais de resíduos de aminoácidos (e.g., rotâmeros estruturais) Mudança conformacional GAPDH Global - rearranjo tetrâmero conformacional da estrutura GAPDH terciária da monômero macromolécula GAPDH Domínio de ligação do AD + Domínio de ligação do substrato Moléculas de água Moléculaslas de água possuem papel importante em sistemas macromoleculares, estando presentes em aproximadamente 70% dos complexos cristalográficos Ligantes Preparação de ligantes moléculas pequenas que se ligam nas cavidades de interação de macromoléculas Estruturas t 3D dos ligantes devem ser submetidas a um processo de minimização de energia conformacional
4 Validação dos resultados Estruturas cristalográficas de receptores alvo em complexo com ligantes podem ser empregadas no processo de validação do modo de interação proposto pelo método de docagem molecular Valores de rmsd menores que 2 Å são considerados satisfatórios Docagem molecular Método que consiste na predição do modo de ligação de pequenas moléculas no sítio de ligação de macromoléculas alvo com subseqüente avaliação e classificação dos modos de ligação propostos. Docagem molecular A docagem molecular foi introduzida no início da década de 80, e desde d então tem encontrado ampla aplicação em química medicinal i e biologia estrutural, sendo, portanto, uma ferramenta de grande valor em projetos de planejamento de fármacos Kuntz, I. D.; Blaney, J. M.; atley, S. J.; Langridge, R.; Ferrin, T. E. A geometric approach to macromolecule ligand interactions. J. Mol. Biol., 161, , 1982
5 Docagem molecular Criação de modelos de interação entre o compostos líder e o receptor timização de compostos líderes cujo modo de interação é conhecido Identificação de novos compostos (Triagem virtual) Programas para docagem molecular Uma das etapas mais importantes desta estratégia de é a escolha do programa de docagem ~ 30 programas disponíveis Uso acadêmico livre: DCK 6.0 Autodock FTDCK (MULTIDCK) ZDCK Uso acadêmico pago; GLD FlexX FlexE DockVision Docagem molecular Docagem molecular processo de docagem molecular pode ser dividido em duas etapas fundamentais determinação do modo de ligação predição da afinidade do ligante pelo sítio de interação predição da afinidade Classificação Pontuação Amostragem Complementaridade Estéreo 6 Química 3 4 modo de ligação ligante sítio de ligação
6 Determinação do modo de ligação Função de busca Modo de interação Métodos de amostragem atribuem flexibilidade as moléculas gerar todos os complexos possíveis s programas de docagem molecular, l em geral, consideram que a molécula do receptor é rígida, enquanto que a molécula do ligante pode ter uma flexibilidade parcial; Essa flexibilidade é traduzida através da variação dos ângulos torsionais do ligante; (i) métodos sistemáticos construção incremental, amostragem conformacional (ii) métodos aleatórios ou estocásticos Monte Carlo, algoritmo genético (iii) métodos de simulação dinâmica molecular e minimização de energia ângulos torsionais docagem Função de busca minimizada Função de busca biotiva processo de reconhecimento molecular é um processo tridimensional Mínima energia bioativa
7 Predição da afinidade de ligação Mecânica molecular Funções de pontuação avaliam e classificam os modos de ligação propostos Funções de pontuação que levam em conta as interações intermoleculares descritas por termos clássicos da mecânica molecular (i) campos de força métodos de mecânica molecular capazes de quantificar a energia proveniente das interações ligante-receptor t (ii) empíricas ajuste teórico de equações (regressão linear) que reproduzem dados experimentais (iii) com base no conhecimento funções que utilizam dados estatísticos dos potenciais de pares atômicos de interação distância de ligação ângulo de ligação ângulo torsional Interação de van der Waals Interação eletrostática Métodos empíricos Dados ajustados a partir de um conjunto de complexos cristalográficos cujo K i foi determinado experimentalmente; ligante-enzima proteína-proteína p antígeno-anticorpo Com base no conhecimento Funções que utilizam dados estatísticos dos potenciais de ç q p pares atômicos de interação, os quais são derivados de conjuntos de dados provenientes de complexos cristalográficos entre ligantes e proteínas G= G vdw (A ij /r ij 12 B ij /R ij6 ) + G hbond E(t) (C ij /r ij 12 D ij /r ij 10 ) + GG G G ( elet q i q j / (r ij )r ij + G tor tor + G sol (S i V j + S j V i )e (-r/2 ) função de energia baseada no campo de força AMBER (AUTDCK)
8 Validação dos resultados Estruturas cristalográficas de receptores alvo em complexo com ligantes podem ser empregadas no processo de validação do modo de interação proposto pelo método de docagem molecular Valores de rmsd menores que 2 Å são considerados satisfatórios Tuberculose Tuberculose Proteína Tirosina Fosfatase A (PtPA) Impacto Global Distribuição Mortes: 2 milhões/ano Global Agente Etiológico Micobacterium tuberculosis s Tratamento Parcialmente eficaz; Diversas limitações: falta de adesão do paciente longos regimes prescritos resistência toxicidade rifampicina H H 3CC H H H 3 C H H (a) H 2 (b) (c) H 2 H pirazinamida isoniazida MM = 18 kda Fator de virulência do M. tuberculosis Molécula essencial para o l l desenvolvimento intracelular A inibição da PtpA determina redução significativa na taxa de na taxa de crescimento do M. tuberculosis
9 Identificação de Inibidores Mecanismo de Inibição K i = 3 µm K i = 5 µm K i = 15 µm K i = 3 µm Inibidores Competitivos K i =13 µm K i = 10 µm Mascarello et al Bioorg Med Chem Modelagem Molecular Atividade in vitroin vitro Macrófagos THP-1 infectados com a cepa de M. tuberculosis H37Rv 5a K i = 3 μm 4a K i = 15 μm Mascarello et al Bioorg Med Chem Mascarello et al Bioorg Med Chem
Docking (ou atracamento) Molecular. Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia 9 de outubro de 2014
 Docking (ou atracamento) Molecular Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia rafaelasf@gmail.com 9 de outubro de 2014 O ATRACAMENTO MOLECULAR PERMITE ESTIMAR COMO DUAS MOLÉCULAS INTERAGEM
Docking (ou atracamento) Molecular Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia rafaelasf@gmail.com 9 de outubro de 2014 O ATRACAMENTO MOLECULAR PERMITE ESTIMAR COMO DUAS MOLÉCULAS INTERAGEM
QSAR 3D Planejamento de NCEs QSAR 3D. O processo de reconhecimento molecular é um processo tridimensional. Conformação bioativa.
 QSAR 3D Interação Fármaco-Receptor AULA 5 a maioria dos casos, a ação dos fármacos está ligada a interação fármaco-receptor, receptor, através de uma associação do tipo reversível e não- covalente Agonistas
QSAR 3D Interação Fármaco-Receptor AULA 5 a maioria dos casos, a ação dos fármacos está ligada a interação fármaco-receptor, receptor, através de uma associação do tipo reversível e não- covalente Agonistas
OBJETIVOS INTERAÇÕES INTERMOLECULARES INTERAÇÕES INTERMOLECULARES.
 OBJETIVOS aandrico@if.sc.usp.br Interações Intermoleculares Mecanismo de Ação Modo de Ligação Complexos Recetor-Ligante Exemplos e Exercícios INTERAÇÕES INTERMOLECULARES INTERAÇÕES INTERMOLECULARES O processo
OBJETIVOS aandrico@if.sc.usp.br Interações Intermoleculares Mecanismo de Ação Modo de Ligação Complexos Recetor-Ligante Exemplos e Exercícios INTERAÇÕES INTERMOLECULARES INTERAÇÕES INTERMOLECULARES O processo
OBJETIVOS AULA 10 DESENVOLVIMENTO DESCOBERTA. ¾ Otimização de Moléculas Bioativas. ¾ Integração com o processo de HTS
 AULA 10 2 DESCOBERTA DESENVOLVIMENTO Pesquisa Básica (Pré-clínica) (Fases Clínicas I IV) Identificação do alvo molecular Triagens clínicas conduzidas em humanos: avaliação da segurança, impacto no estado
AULA 10 2 DESCOBERTA DESENVOLVIMENTO Pesquisa Básica (Pré-clínica) (Fases Clínicas I IV) Identificação do alvo molecular Triagens clínicas conduzidas em humanos: avaliação da segurança, impacto no estado
Mecânica Molecular. Dinâmica Molecular. Exemplos de aplicação. é um método relativamente. energia e conformação de micro ou macromoléculas
 Objetivos FFI0776 Modelagem e Engenharia de Proteínas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 04 Mecânica Molecular Campo de força Exemplos de Campo de Força Dinâmica Molecular Etapas envolvidas
Objetivos FFI0776 Modelagem e Engenharia de Proteínas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 04 Mecânica Molecular Campo de força Exemplos de Campo de Força Dinâmica Molecular Etapas envolvidas
Interações de van der Waals. Interações de van der Waals. Interações de van der Waals.
 Interações de van der Waals aandrico@if.sc.usp.br Também conhecidas como forças de dispersão de London, caracterizam-se pelo momento de dipolo induzido e ocorrem entre todos os átomos. Apesar de moléculas
Interações de van der Waals aandrico@if.sc.usp.br Também conhecidas como forças de dispersão de London, caracterizam-se pelo momento de dipolo induzido e ocorrem entre todos os átomos. Apesar de moléculas
ATRACAMENTO MOLECULAR
 UNIVERSIDADE FEDERAL DO ESPÍRITO SANTO CENTRO DE CIÊNCIAS DA SAÚDE PROGRAMA DE PÓS-GRADUAÇÃO EM BIOTECNOLOGIA BIOINFORMÁTICA ATRACAMENTO MOLECULAR VITÓRIA 2018 Ivana Alece Arantes Moreno Júlia de Assis
UNIVERSIDADE FEDERAL DO ESPÍRITO SANTO CENTRO DE CIÊNCIAS DA SAÚDE PROGRAMA DE PÓS-GRADUAÇÃO EM BIOTECNOLOGIA BIOINFORMÁTICA ATRACAMENTO MOLECULAR VITÓRIA 2018 Ivana Alece Arantes Moreno Júlia de Assis
Características AULA 11. Características e Propriedades. drug-like (fármaco-similar) Bioativo-similar
 AULA 11 rganização e gerenciamento de bases de dados padrões Emprego de pré-filtros: otimização das bases de dados (e.g., seleção por tipo de átomo: C,,,, S, F, Cl, Br, P) Características e Propriedades
AULA 11 rganização e gerenciamento de bases de dados padrões Emprego de pré-filtros: otimização das bases de dados (e.g., seleção por tipo de átomo: C,,,, S, F, Cl, Br, P) Características e Propriedades
AULA 7. Cálculo das energias de interação estereoquímicas e eletrostáticas entre as moléculas do conjunto de
 Análise Comparativa dos Campos Moleculares AULA 7 Análise Comparativa dos Campos Moleculares A contribuição devido às forças de dispersão entre moléculas é descrita pelo potencial de Lennard-Jones e as
Análise Comparativa dos Campos Moleculares AULA 7 Análise Comparativa dos Campos Moleculares A contribuição devido às forças de dispersão entre moléculas é descrita pelo potencial de Lennard-Jones e as
FFI0750 Biologia Molecular Estrutural
 Objetivos FFI0750 Biologia Molecular Estrutural Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Estrutura de proteínas Estrutura primária Estrutura secundária Estrutura terciária Estrutura quaternária Aula
Objetivos FFI0750 Biologia Molecular Estrutural Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Estrutura de proteínas Estrutura primária Estrutura secundária Estrutura terciária Estrutura quaternária Aula
Quiminformática e o planejamento de fármacos
 Quiminformática e o planejamento de fármacos Banco de Dados Otimização do Matriz Análise e Modelagem Estatística Quiminformática Carlos Montanari NEQUIMED/DQFM/IQSC/USP montana@iqsc.usp.br Evolução do
Quiminformática e o planejamento de fármacos Banco de Dados Otimização do Matriz Análise e Modelagem Estatística Quiminformática Carlos Montanari NEQUIMED/DQFM/IQSC/USP montana@iqsc.usp.br Evolução do
Métodos de Química Computacional
 Universidade Federal de Ouro Preto Instituto de Ciências Exatas e Biológicas Departamento de Química Métodos de Química Computacional Professora: Melissa Soares Caetano Mecânica Molecular Mecânica Molecular
Universidade Federal de Ouro Preto Instituto de Ciências Exatas e Biológicas Departamento de Química Métodos de Química Computacional Professora: Melissa Soares Caetano Mecânica Molecular Mecânica Molecular
FFI0750 Biologia Molecular Estrutural
 Objetivos FFI0750 Biologia Molecular Estrutural Visualização de estruturas de macromoléculas Representação de estruturas de macromoléculas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 02 Bacharelado
Objetivos FFI0750 Biologia Molecular Estrutural Visualização de estruturas de macromoléculas Representação de estruturas de macromoléculas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 02 Bacharelado
ENSAIO VIRTUAL E A IDENTIFICAÇÃO DE MOLÉCULAS BIOATIVAS
 ENSAIO VIRTUAL E A IDENTIFICAÇÃO DE MOLÉCULAS BIOATIVAS 1. Introdução A fantástica evolução da Química Medicinal nas últimas décadas foi acompanhada por avanços científicos significativos que levaram a
ENSAIO VIRTUAL E A IDENTIFICAÇÃO DE MOLÉCULAS BIOATIVAS 1. Introdução A fantástica evolução da Química Medicinal nas últimas décadas foi acompanhada por avanços científicos significativos que levaram a
RELAÇÕES ENTRE A ESTRUTURA E ATIVIDADE. Relações entre a estrutura e atividade (SAR) Requerimentos para estudos de QSAR
 BJETIVS AULA 3 Relações entre a estrutura e atividade (SAR) Requerimentos para estudos de QSAR Propriedade biológica Descritores moleculares Conjunto de dados Parâmetros estatísticos RELAÇÕES ETRE A ESTRUTURA
BJETIVS AULA 3 Relações entre a estrutura e atividade (SAR) Requerimentos para estudos de QSAR Propriedade biológica Descritores moleculares Conjunto de dados Parâmetros estatísticos RELAÇÕES ETRE A ESTRUTURA
Modelagem Comparativa de Proteínas
 Modelagem Comparativa de Proteínas Bioinformática Estrutural Aula 3 3 de Junho de 2013 Paula Kuser Falcão Laboratório de Bioinformática Aplicada Embrapa Informática Agropecuária Por que predizer a estrutura?
Modelagem Comparativa de Proteínas Bioinformática Estrutural Aula 3 3 de Junho de 2013 Paula Kuser Falcão Laboratório de Bioinformática Aplicada Embrapa Informática Agropecuária Por que predizer a estrutura?
Funções Escores (MolDock Score) Prof. Dr. Walter F. de Azevedo Jr. ou
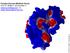 205 Dr. Walter F. de zevedo Jr. Funções Escores (MolDock Score) Prof. Dr. Walter F. de zevedo Jr. walter.junior@pucrs.br ou walter.filgueira@hotmail.com Função MolDock Score função ajuste ou escore, usada
205 Dr. Walter F. de zevedo Jr. Funções Escores (MolDock Score) Prof. Dr. Walter F. de zevedo Jr. walter.junior@pucrs.br ou walter.filgueira@hotmail.com Função MolDock Score função ajuste ou escore, usada
Métodos de Química Computacional
 Universidade Federal de Ouro Preto Instituto de Ciências Exatas e Biológicas Departamento de Química Métodos de Química Computacional Professora: Melissa Soares Caetano Dinâmica molecular Conhecendo posições
Universidade Federal de Ouro Preto Instituto de Ciências Exatas e Biológicas Departamento de Química Métodos de Química Computacional Professora: Melissa Soares Caetano Dinâmica molecular Conhecendo posições
Triagem Virtual em Larga Escala. Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia 10 de outubro de 2014
 Triagem Virtual em Larga Escala Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia rafaelasf@gmail.com 10 de outubro de 2014 1 O que é triagem virtual? Grande conjunto de compostos Estratégia
Triagem Virtual em Larga Escala Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia rafaelasf@gmail.com 10 de outubro de 2014 1 O que é triagem virtual? Grande conjunto de compostos Estratégia
FUNDAÇÃO CARMELITANA MÁRIO PALMÉRIO FACIHUS - FACULDADE DE CIÊNCIAS HUMANAS E SOCIAIS. Enzimas. Prof. Me. Cássio Resende de Morais
 FUNDAÇÃO CARMELITANA MÁRIO PALMÉRIO FACIHUS - FACULDADE DE CIÊNCIAS HUMANAS E SOCIAIS Enzimas Prof. Me. Cássio Resende de Morais Enzimas Catalisadores biológicos: substâncias de origem biológica que aceleram
FUNDAÇÃO CARMELITANA MÁRIO PALMÉRIO FACIHUS - FACULDADE DE CIÊNCIAS HUMANAS E SOCIAIS Enzimas Prof. Me. Cássio Resende de Morais Enzimas Catalisadores biológicos: substâncias de origem biológica que aceleram
Estrutura e Função de Proteínas O NMR tem a vantagem de puder apresentar mais do que uma estrura possivel
 Vamos trabalhar com a neurominidase. A m-glutinina liga o virs à celula. A neurominidasez o contrario e permite que o virus de despegue dessa celula e consegue ir infetar mais virus. O centro ativo mantem
Vamos trabalhar com a neurominidase. A m-glutinina liga o virs à celula. A neurominidasez o contrario e permite que o virus de despegue dessa celula e consegue ir infetar mais virus. O centro ativo mantem
Alinhamento de Sequências de Proteínas. Modelagem por homologia Estratégia/aplicação Etapas do processo Exemplo
 Objetivos FFI0776 Modelagem e Engenharia de Proteínas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 06 Alinhamento de Sequências de Proteínas Determinação da sequência de aa Características do alinhamento
Objetivos FFI0776 Modelagem e Engenharia de Proteínas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 06 Alinhamento de Sequências de Proteínas Determinação da sequência de aa Características do alinhamento
Função proteica envolve a ligação reversível com outras moléculas O ligante se liga na proteína e um sítio específico, chamado SÍTIO DE LIGAÇÃO.
 Estrutura Função 1. Função proteica envolve a ligação reversível com outras moléculas. A molécula que se liga reversivelmente à proteina LIGANTE 2. O ligante se liga na proteína e um sítio específico,
Estrutura Função 1. Função proteica envolve a ligação reversível com outras moléculas. A molécula que se liga reversivelmente à proteina LIGANTE 2. O ligante se liga na proteína e um sítio específico,
OBJETIVOS BIBLIOGRAFIA ENZIMAS E INIBIDORES ENZIMÁTICOS
 OBJETIVOS Enzimas: Funções, Nomenclatura e Propriedades Fundamentos da Cinética Enzimática Cinética Enzimática: Michaelis-Menten Ensaios Cinéticos: Padronização e Validação Parâmetros Cinéticos: vo, KM,
OBJETIVOS Enzimas: Funções, Nomenclatura e Propriedades Fundamentos da Cinética Enzimática Cinética Enzimática: Michaelis-Menten Ensaios Cinéticos: Padronização e Validação Parâmetros Cinéticos: vo, KM,
1164 BIOLOGIA ESTRUTURAL Aula 4 Prof. Dr. Valmir Fadel
 Apesar da grande quantidade de seqüências determinadas (260.175 seqüências e 3.874.166 transcrições no UniProtKB/TrEMBL em 06/03/2007) a quantidade de estruturas tridimensionais determinadas é significativamente
Apesar da grande quantidade de seqüências determinadas (260.175 seqüências e 3.874.166 transcrições no UniProtKB/TrEMBL em 06/03/2007) a quantidade de estruturas tridimensionais determinadas é significativamente
Cinética em fase homogênea
 Cinética em fase homogênea Hipótese chave-fechadura Centro ativo complementar em tamanho, forma e natureza química à molécula do substrato, ou seja, uma cavidade geometricamente rígida. Emil Fischer (1894)
Cinética em fase homogênea Hipótese chave-fechadura Centro ativo complementar em tamanho, forma e natureza química à molécula do substrato, ou seja, uma cavidade geometricamente rígida. Emil Fischer (1894)
Fundamentos da modelagem Molecular - 1
 Fundamentos da modelagem Molecular - 1 Departamento de Física UFPel ufpellogo Introdução Rotas para a pesquisa Conexão entre experimento, simulação e teoria Sistema real Fazer modelos do sistema Fazer
Fundamentos da modelagem Molecular - 1 Departamento de Física UFPel ufpellogo Introdução Rotas para a pesquisa Conexão entre experimento, simulação e teoria Sistema real Fazer modelos do sistema Fazer
Caracterização e classificação de proteínas. Desafio de Paracelsus
 Objetivos FFI0776 Modelagem e Engenharia de Proteínas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 05 Caracterização e classificação de proteínas Proteínas homólogas Base de dados SCOP CATH Desafio
Objetivos FFI0776 Modelagem e Engenharia de Proteínas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 05 Caracterização e classificação de proteínas Proteínas homólogas Base de dados SCOP CATH Desafio
Determinação da Estrutura de Proteínas
 Centro Brasileiro-Argentino de Biotecnologia Introdução à Biologia Computacional Determinação da Estrutura de Proteínas Paulo enrique C. Godoi Bioinformática objetivo principal é determinar a função de
Centro Brasileiro-Argentino de Biotecnologia Introdução à Biologia Computacional Determinação da Estrutura de Proteínas Paulo enrique C. Godoi Bioinformática objetivo principal é determinar a função de
Mutação aleatória. DNA shuffling Apresentação em Fagos (Phage Display) Exemplos de Aplicação. Error prone
 Objetivos FFI0776 Modelagem e Engenharia de Proteínas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 09 Mutação aleatória Error prone PCR Apresentação em Fagos (Phage Display) Exemplos de Aplicação
Objetivos FFI0776 Modelagem e Engenharia de Proteínas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 09 Mutação aleatória Error prone PCR Apresentação em Fagos (Phage Display) Exemplos de Aplicação
Estudo estrutural da Chiquimato Quinase de Mycobacterium tuberculosis
 Estudo estrutural da Chiquimato Quinase de Mycobacterium tuberculosis Laboratório Sistemas Biomoleculares José Henrique Pereira Introdução Modelagem Molecular Estudo cristalográfico Introdução Aproximadamente
Estudo estrutural da Chiquimato Quinase de Mycobacterium tuberculosis Laboratório Sistemas Biomoleculares José Henrique Pereira Introdução Modelagem Molecular Estudo cristalográfico Introdução Aproximadamente
Princípios básicos da modelagem molecular e sua aplicação no desenvolvimento de novos fármacos
 II JRADA DE IVER DA QUÍMICA Princípios básicos da modelagem molecular e sua aplicação no desenvolvimento de novos fármacos Ana Carolina de liveira Introdução MDELAGEM MLECULAR DEFIIÇÃ: Trata da investigação
II JRADA DE IVER DA QUÍMICA Princípios básicos da modelagem molecular e sua aplicação no desenvolvimento de novos fármacos Ana Carolina de liveira Introdução MDELAGEM MLECULAR DEFIIÇÃ: Trata da investigação
Estudo da velocidade da reação enzimática e como ela se altera em função de diferentes parâmetros
 Estudo da velocidade da reação enzimática e como ela se altera em função de diferentes parâmetros Importante abordagem para o entendimento do mecanismo de ação de uma enzima. Vários fatores afetam a atividade
Estudo da velocidade da reação enzimática e como ela se altera em função de diferentes parâmetros Importante abordagem para o entendimento do mecanismo de ação de uma enzima. Vários fatores afetam a atividade
Aula de Bioquímica Avançada. Tema: Enzimas. Prof. Dr. Júlio César Borges
 Aula de Bioquímica Avançada Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: borgesjc@iqsc.usp.br
Aula de Bioquímica Avançada Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: borgesjc@iqsc.usp.br
Pontifícia Universidade Católica de Goiás Departamento de Biologia Bioquímica Metabólica ENZIMAS
 Pontifícia Universidade Católica de Goiás Departamento de Biologia Bioquímica Metabólica ENZIMAS Origem das proteínas e de suas estruturas Níveis de Estrutura Protéica Estrutura das proteínas Conformação
Pontifícia Universidade Católica de Goiás Departamento de Biologia Bioquímica Metabólica ENZIMAS Origem das proteínas e de suas estruturas Níveis de Estrutura Protéica Estrutura das proteínas Conformação
Fundamentos da modelagem Molecular - 1
 Fundamentos da modelagem Molecular - 1 Departamento de Física UFPel Introdução Rotas para a pesquisa Conexão entre experimento, simulação e teoria Sistema real Fazer modelos do sistema Fazer experimentos
Fundamentos da modelagem Molecular - 1 Departamento de Física UFPel Introdução Rotas para a pesquisa Conexão entre experimento, simulação e teoria Sistema real Fazer modelos do sistema Fazer experimentos
Aula de Bioquímica I. Tema: Enzimas. Prof. Dr. Júlio César Borges
 Aula de Bioquímica I Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: borgesjc@iqsc.usp.br
Aula de Bioquímica I Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: borgesjc@iqsc.usp.br
Resposta Imunológica celular. Alessandra Barone
 Resposta Imunológica celular Alessandra Barone Resposta mediada pelos linfócitos T: TCD4 e TCD8 Resposta contra microrganismos que estão localizados no interior de fagócitos e de células não fagocíticas
Resposta Imunológica celular Alessandra Barone Resposta mediada pelos linfócitos T: TCD4 e TCD8 Resposta contra microrganismos que estão localizados no interior de fagócitos e de células não fagocíticas
Estudo da velocidade da reação enzimática e como ela se altera em função de diferentes parâmetros
 Estudo da velocidade da reação enzimática e como ela se altera em função de diferentes parâmetros Importante abordagem para o entendimento do mecanismo de ação de uma enzima. Vários fatores afetam a atividade
Estudo da velocidade da reação enzimática e como ela se altera em função de diferentes parâmetros Importante abordagem para o entendimento do mecanismo de ação de uma enzima. Vários fatores afetam a atividade
SAR Estratégias de Otimização Molecular
 SAR aandrico@ifsc.usp.br SAR Estratégias de timização Molecular - Variação de substituintes - Aumento da estrutura molecular - Extensão/contração de cadeias - Variação de anéis, padrão de substituição
SAR aandrico@ifsc.usp.br SAR Estratégias de timização Molecular - Variação de substituintes - Aumento da estrutura molecular - Extensão/contração de cadeias - Variação de anéis, padrão de substituição
Métodos de Química Computacional
 Universidade Federal de Ouro Preto Instituto de Ciências Exatas e Biológicas Departamento de Química Métodos de Química Computacional Professora: Melissa Soares Caetano Química Medicinal Matemática Química
Universidade Federal de Ouro Preto Instituto de Ciências Exatas e Biológicas Departamento de Química Métodos de Química Computacional Professora: Melissa Soares Caetano Química Medicinal Matemática Química
INTRODUÇÃO Á BIOQUÍMICA
 INTRODUÇÃO Á BIOQUÍMICA BIOQUÍMICA ENFERMAGEM FIO Faculdades Integradas de Ourinhos. Prof. Esp. Roberto Venerando Fundação Educacional Miguel Mofarrej. FIO robertovenerando@fio.edu.br 1 - Introdução à
INTRODUÇÃO Á BIOQUÍMICA BIOQUÍMICA ENFERMAGEM FIO Faculdades Integradas de Ourinhos. Prof. Esp. Roberto Venerando Fundação Educacional Miguel Mofarrej. FIO robertovenerando@fio.edu.br 1 - Introdução à
Rafael Mesquita. Proteínas. Estrutura
 Proteínas Estrutura Ligação peptídica Ligação peptídica - Rígida e plana - Ligação simples com caráter de dupla ligação Ângulos Φ e Ψ Ligação peptídica limitações estruturais Limitações estruturais impostas
Proteínas Estrutura Ligação peptídica Ligação peptídica - Rígida e plana - Ligação simples com caráter de dupla ligação Ângulos Φ e Ψ Ligação peptídica limitações estruturais Limitações estruturais impostas
Introdução à Engenharia de Proteínas. Enovelamento e Desnaturação
 Objetivos FFI0776 Modelagem e Engenharia de Proteínas Enovelamento e Desnaturação de Proteínas Introdução à Engenharia de Proteínas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br usp Aula 07 Bacharelado
Objetivos FFI0776 Modelagem e Engenharia de Proteínas Enovelamento e Desnaturação de Proteínas Introdução à Engenharia de Proteínas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br usp Aula 07 Bacharelado
Gabriela Sehnem Heck 1,2, Prof. Dr. Walter F. de Azevedo Jr 2. (orientador)
 Pontifícia Universidade Católica do Rio Grande do Sul Gabriela Sehnem Heck 1,2, Prof. Dr. Walter F. de Azevedo Jr 2. (orientador) 1 Acadêmica de Curso de Ciêncas Biológicas da PUCRS, 2 Laboratório de Bioquímica
Pontifícia Universidade Católica do Rio Grande do Sul Gabriela Sehnem Heck 1,2, Prof. Dr. Walter F. de Azevedo Jr 2. (orientador) 1 Acadêmica de Curso de Ciêncas Biológicas da PUCRS, 2 Laboratório de Bioquímica
Referência: Primeira parte Docking nativo do composto co-cristalizado
 Tutorial Docking utilizando AUTODOCK Vina Profa. Rafaela Salgado Ferreira Departamento de Bioquímica e Imunologia - Universidade Federal de Minas Gerais Referência: AutoDockVina - Trott O, Olson AJ. AutoDock
Tutorial Docking utilizando AUTODOCK Vina Profa. Rafaela Salgado Ferreira Departamento de Bioquímica e Imunologia - Universidade Federal de Minas Gerais Referência: AutoDockVina - Trott O, Olson AJ. AutoDock
Aula 12: Enzimas Introdução e Cinética
 Disciplina de Bioquímica Estrutural Curso de Biologia Aula 12: Enzimas Introdução e Cinética Prof. Marcos Túlio de Oliveira mtoliveira@fcav.unesp.br Faculdade de Ciências Agrárias e Veterinárias de Jaboticabal
Disciplina de Bioquímica Estrutural Curso de Biologia Aula 12: Enzimas Introdução e Cinética Prof. Marcos Túlio de Oliveira mtoliveira@fcav.unesp.br Faculdade de Ciências Agrárias e Veterinárias de Jaboticabal
MODELAGEM DE PROTEÍNAS COM IMPORTÂNCIA FARMACÊUTICA E BIOMÉDICA POR MEIO DE SIMULAÇÃO COMPUTACIONAL
 MODELAGEM DE PROTEÍNAS COM IMPORTÂNCIA FARMACÊUTICA E BIOMÉDICA POR MEIO DE SIMULAÇÃO COMPUTACIONAL Ronaldo Correia da SILVA SILVA, Ronaldo Correia da. Modelagem de proteínas com importância farmacêutica
MODELAGEM DE PROTEÍNAS COM IMPORTÂNCIA FARMACÊUTICA E BIOMÉDICA POR MEIO DE SIMULAÇÃO COMPUTACIONAL Ronaldo Correia da SILVA SILVA, Ronaldo Correia da. Modelagem de proteínas com importância farmacêutica
UNIVERSIDADE FEDERAL DE SERGIPE PRÓ-REITORIA DE PÓS-GRADUAÇÃO E PESQUISA PROGRAMA DE PÓS-GRADUAÇÃO EM QUÍMICA ANTÔNIO LUIZ SILVEIRA VILANOVA COSTA
 UNIVERSIDADE FEDERAL DE SERGIPE PRÓ-REITORIA DE PÓS-GRADUAÇÃO E PESQUISA PROGRAMA DE PÓS-GRADUAÇÃO EM QUÍMICA ANTÔNIO LUIZ SILVEIRA VILANOVA COSTA DOCAGEM MOLECULAR UTILIZANDO MÉTODOS SEMIEMPÍRICOS QUÂNTICOS
UNIVERSIDADE FEDERAL DE SERGIPE PRÓ-REITORIA DE PÓS-GRADUAÇÃO E PESQUISA PROGRAMA DE PÓS-GRADUAÇÃO EM QUÍMICA ANTÔNIO LUIZ SILVEIRA VILANOVA COSTA DOCAGEM MOLECULAR UTILIZANDO MÉTODOS SEMIEMPÍRICOS QUÂNTICOS
Aula 1. Referência. Bancos de Dados. Linguagem x Informação. Introdução a Bioquímica: Biomoléculas. Introdução ao Curso: Aminoácidos.
 Introdução a Bioquímica: Biomoléculas Aula 1 Introdução ao urso: Aminoácidos eferência Autores: Ignez aracelli e Julio Zukerman-Schpector Editora: EdUFSar Ignez aracelli BioMat DF UNESP/Bauru Julio Zukerman
Introdução a Bioquímica: Biomoléculas Aula 1 Introdução ao urso: Aminoácidos eferência Autores: Ignez aracelli e Julio Zukerman-Schpector Editora: EdUFSar Ignez aracelli BioMat DF UNESP/Bauru Julio Zukerman
FÁRMACO. Fármacos X Drogas. Caráter ilícito. Substância química com efeito psicotrópico que pode levar o usuário à dependência física e/ou psíquica.
 Fármacos X Drogas UL 1 Caráter ilícito Substância química com efeito psicotrópico que pode levar o usuário à dependência física e/ou psíquica Substância química (molécula) que constitui o princípio ativo
Fármacos X Drogas UL 1 Caráter ilícito Substância química com efeito psicotrópico que pode levar o usuário à dependência física e/ou psíquica Substância química (molécula) que constitui o princípio ativo
DROGA. Acção FÁRMACO. Efeito MEDICAMENTO
 FARMACODINAMIA DROGA Acção FÁRMACO Efeito MEDICAMENTO RECETORES Estruturas macromoleculares funcionais do organismo INTERAÇÃO FÁRMACO-RECETOR Resposta farmacológica Possíveis LOCAIS DE AÇÃO dos fármacos
FARMACODINAMIA DROGA Acção FÁRMACO Efeito MEDICAMENTO RECETORES Estruturas macromoleculares funcionais do organismo INTERAÇÃO FÁRMACO-RECETOR Resposta farmacológica Possíveis LOCAIS DE AÇÃO dos fármacos
Cinética Enzimática. Prof Karine P. Naidek Novembro/2016
 UNIVERSIDADE DO ESTADO DE SANTA CATARINA CENTRO DE CIÊNCIAS TECNOLÓGICAS DEPARTAMENTO DE QUÍMICA DQMC BIOQUÍMICA BIO0001 Cinética Enzimática Prof Karine P. Naidek Novembro/2016 Cinética das Reações Bioquímicas
UNIVERSIDADE DO ESTADO DE SANTA CATARINA CENTRO DE CIÊNCIAS TECNOLÓGICAS DEPARTAMENTO DE QUÍMICA DQMC BIOQUÍMICA BIO0001 Cinética Enzimática Prof Karine P. Naidek Novembro/2016 Cinética das Reações Bioquímicas
2018 Dr. Walter F. de Azevedo Jr. Biofísica. Prof. Dr. Walter F. de Azevedo Jr.
 2018 Dr. Walter F. de Azevedo Jr. Biofísica Prof. Dr. Walter F. de Azevedo Jr. 1 Ao lado temos a estrutura de um peptídeo formado pelos aminoácidos Arginina - Prolina - Alanina - Tirosina - Serina, coloridos
2018 Dr. Walter F. de Azevedo Jr. Biofísica Prof. Dr. Walter F. de Azevedo Jr. 1 Ao lado temos a estrutura de um peptídeo formado pelos aminoácidos Arginina - Prolina - Alanina - Tirosina - Serina, coloridos
Metaloproteínas e modelagem biomimética. Prof. Fernando R. Xavier
 Metaloproteínas e modelagem biomimética Prof. Fernando R. Xavier UDESC 2018 Resumindo temos: Enzimas cofator orgânico inorgânico coenzima metaloenzima Proteínas Sítio ativo Complexos altamente Elaborados!!!
Metaloproteínas e modelagem biomimética Prof. Fernando R. Xavier UDESC 2018 Resumindo temos: Enzimas cofator orgânico inorgânico coenzima metaloenzima Proteínas Sítio ativo Complexos altamente Elaborados!!!
Molecular Co. Visualizador de Moléculas
 Molecular Co. Visualizador de Moléculas David Macedo da Conceição n o USP : 3681479 Fernando Waitman n o USP : 4951109 Gabriel H. Pugliese n o USP : 5639061 Leonardo Ventura n o USP : 5382607 Ricardo A.
Molecular Co. Visualizador de Moléculas David Macedo da Conceição n o USP : 3681479 Fernando Waitman n o USP : 4951109 Gabriel H. Pugliese n o USP : 5639061 Leonardo Ventura n o USP : 5382607 Ricardo A.
5 Metodologia Utilizada no Trabalho
 68 5 Metodologia Utilizada no Trabalho 5.1 Modelagem das Moléculas 5.1.1 Dendrímeros Foram simuladas estruturas da geração 0 (G0) até a geração 4 (G4) para três estados de protonação, foram construídas
68 5 Metodologia Utilizada no Trabalho 5.1 Modelagem das Moléculas 5.1.1 Dendrímeros Foram simuladas estruturas da geração 0 (G0) até a geração 4 (G4) para três estados de protonação, foram construídas
Visualização de Hélices
 Grupo: Curso: Turma: Data: Visualização de Hélices Objetivos Visualizar a estrutura tridimensional de hélices presentes na estrutura de proteínas e peptídeos, usandose recursos computacionais. Analisar
Grupo: Curso: Turma: Data: Visualização de Hélices Objetivos Visualizar a estrutura tridimensional de hélices presentes na estrutura de proteínas e peptídeos, usandose recursos computacionais. Analisar
Catalizadores biológicos - Aceleram reações químicas específicas sem a formação de produtos colaterais
 O que são enzimas? Catalizadores biológicos - Aceleram reações químicas específicas sem a formação de produtos colaterais Reagentes = substratos Local onde a reação ocorre = sítio ou centro ativo S + E
O que são enzimas? Catalizadores biológicos - Aceleram reações químicas específicas sem a formação de produtos colaterais Reagentes = substratos Local onde a reação ocorre = sítio ou centro ativo S + E
Algumas considerações da aula anterior e Interações moleculares
 Algumas considerações da aula anterior e Interações moleculares From: lbe et al, at Rev Drug Discovery 2:132, 2003 Effect of route of administration on plasma-concentration-response relationships based
Algumas considerações da aula anterior e Interações moleculares From: lbe et al, at Rev Drug Discovery 2:132, 2003 Effect of route of administration on plasma-concentration-response relationships based
Catalizadores biológicos - Aceleram reações químicas específicas sem a formação de produtos colaterais
 O que são enzimas? Catalizadores biológicos - Aceleram reações químicas específicas sem a formação de produtos colaterais Reagentes = substratos Local onde a reação ocorre = sitio ou centro ativo S + E
O que são enzimas? Catalizadores biológicos - Aceleram reações químicas específicas sem a formação de produtos colaterais Reagentes = substratos Local onde a reação ocorre = sitio ou centro ativo S + E
Aspectos moleculares
 FARMACOLOGIA I DOCENTE: Msc. ROSALINA COELHO JÁCOME Aspectos moleculares FARMACOLOGIA O que o organismo faz com o fármaco? O que o fármaco faz no organismo? FARMACOCINÉTICA FARMACODINÂMICA CORRELAÇÃO FARMACOCINÉTICA/FARMACODINÂMICA
FARMACOLOGIA I DOCENTE: Msc. ROSALINA COELHO JÁCOME Aspectos moleculares FARMACOLOGIA O que o organismo faz com o fármaco? O que o fármaco faz no organismo? FARMACOCINÉTICA FARMACODINÂMICA CORRELAÇÃO FARMACOCINÉTICA/FARMACODINÂMICA
Atracamento molecular (Docking)
 Atracamento molecular (Docking) O atracamento molecular O que é? Método para achar o melhor encaixe entre duas moléculas O atracamento molecular O que é? Porquê? Método para achar o melhor encaixe entre
Atracamento molecular (Docking) O atracamento molecular O que é? Método para achar o melhor encaixe entre duas moléculas O atracamento molecular O que é? Porquê? Método para achar o melhor encaixe entre
Estrutura de um anticorpo
 Estrutura de um anticorpo Imunoglobulina anticorpo Molécula proteica produzida pelos linfócitos B Apenas um tipo de anticorpo produzido por cada célula B Liga-se a um antigénio (Ag) específico Específico
Estrutura de um anticorpo Imunoglobulina anticorpo Molécula proteica produzida pelos linfócitos B Apenas um tipo de anticorpo produzido por cada célula B Liga-se a um antigénio (Ag) específico Específico
Microscopia de Força Atômica (AFM)
 Microscopia de Força Atômica (AFM) Microscopia (AFM) 7.2.5.1. Introdução Figura.7.36. Modelo de microscópio de força atômica (AFM). Microscopia (AFM) Figura.7.36a. Diagrama representativo de funcionamento
Microscopia de Força Atômica (AFM) Microscopia (AFM) 7.2.5.1. Introdução Figura.7.36. Modelo de microscópio de força atômica (AFM). Microscopia (AFM) Figura.7.36a. Diagrama representativo de funcionamento
Descritores moleculares para aprendizagem automática ( Machine learning ) João Aires de Sousa
 Descritores moleculares para aprendizagem automática ( Machine learning ) 1 Pode um computador aprender Química? 2 Aprender o quê? Por ex., aprender a prever propriedades a partir da estrutura molecular
Descritores moleculares para aprendizagem automática ( Machine learning ) 1 Pode um computador aprender Química? 2 Aprender o quê? Por ex., aprender a prever propriedades a partir da estrutura molecular
Interacções anticorpo-antigénio
 Interacções anticorpo-antigénio Imunização indução voluntária de respostas imunes a antigénios Antigénio é qualquer substância capaz de se ligar a uma receptor dos linfócitos B (imunoglobulinas) ou dos
Interacções anticorpo-antigénio Imunização indução voluntária de respostas imunes a antigénios Antigénio é qualquer substância capaz de se ligar a uma receptor dos linfócitos B (imunoglobulinas) ou dos
Inibidores Enzimáticos
 Inibidores Enzimáticos BIOQUÍMICA - INIBIÇÃO ENZIMÁTICA NOÇÕES BÁSICAS SOBRE ENZIMAS CONCEITO As enzimas são proteínas especializadas na catálise de reações biológicas MECANISMO DE AÇÃO As enzimas aceleram
Inibidores Enzimáticos BIOQUÍMICA - INIBIÇÃO ENZIMÁTICA NOÇÕES BÁSICAS SOBRE ENZIMAS CONCEITO As enzimas são proteínas especializadas na catálise de reações biológicas MECANISMO DE AÇÃO As enzimas aceleram
SEQÜÊNCIA ACONSELHADA DISCIPLINAS POR SEMESTRE
 DISCIPLINAS POR SEMESTRE 1 o SEMESTRE N Código Nome da Disciplina N Tipo* (T P) CHS 01 CSETL4004 Cálculo A N OBR (6-0) 90 02 CSETL4001 Desenho Técnico I N OBR (1-2) 45 03 CSETL4006 Introdução à Engenharia
DISCIPLINAS POR SEMESTRE 1 o SEMESTRE N Código Nome da Disciplina N Tipo* (T P) CHS 01 CSETL4004 Cálculo A N OBR (6-0) 90 02 CSETL4001 Desenho Técnico I N OBR (1-2) 45 03 CSETL4006 Introdução à Engenharia
CARACTERIZAÇÃO DE BENZOFENONAS NA INIBIÇÃO DE CISTEÍNO PROTEASES DE Leishmania mexicana CPB2.8 E SUAS ISOFORMAS
 CARACTERIZAÇÃO DE BENZOFENONAS NA INIBIÇÃO DE CISTEÍNO PROTEASES DE Leishmania mexicana CPB2.8 E SUAS ISOFORMAS Gabriel Garcia Okuda 1 ; Marcelo Henrique dos Santos 2 ; Luiz Juliano 3 ; Wagner Alves de
CARACTERIZAÇÃO DE BENZOFENONAS NA INIBIÇÃO DE CISTEÍNO PROTEASES DE Leishmania mexicana CPB2.8 E SUAS ISOFORMAS Gabriel Garcia Okuda 1 ; Marcelo Henrique dos Santos 2 ; Luiz Juliano 3 ; Wagner Alves de
CURSO DE CIÊNCIAS EXATAS HABILITAÇÃO: BACHARELADO EM CIÊNCIAS EXATAS INGRESSANTES 2009
 CURSO DE CIÊNCIAS EXATAS HABILITAÇÃO: BACHARELADO EM CIÊNCIAS EXATAS INGRESSANTES 2009 Período Atividade Acadêmica Caráter Cr CH Pré-requisito Código Denominação 1º MAT154 Cálculo I Disciplina de Formação
CURSO DE CIÊNCIAS EXATAS HABILITAÇÃO: BACHARELADO EM CIÊNCIAS EXATAS INGRESSANTES 2009 Período Atividade Acadêmica Caráter Cr CH Pré-requisito Código Denominação 1º MAT154 Cálculo I Disciplina de Formação
O FUTURO DAS CHALCONAS COM ATIVIDADE ANTICÂNCER. Prof. Dr. Rosendo Augusto Yunes Prof. Voluntário Univali (Nigfar) e Departamento de Química UFSC
 O FUTURO DAS CHALCONAS COM ATIVIDADE ANTICÂNCER Prof. Dr. Rosendo Augusto Yunes Prof. Voluntário Univali (Nigfar) e Departamento de Química UFSC Chalconas Chalconas são cetonas α,β-insaturada; Constituem
O FUTURO DAS CHALCONAS COM ATIVIDADE ANTICÂNCER Prof. Dr. Rosendo Augusto Yunes Prof. Voluntário Univali (Nigfar) e Departamento de Química UFSC Chalconas Chalconas são cetonas α,β-insaturada; Constituem
Enzimologia Aula 2. Leitura sugerida. Biochemistry Voet & Voet 3ª edição Capítulo 10 parte 1Bb (página 323), parte 4A, 4B e 4C (páginas )
 Enzimologia Aula 2 Leitura sugerida Biochemistry Voet & Voet 3ª edição Capítulo 10 parte 1Bb (página 323), parte 4A, 4B e 4C (páginas 346-350) Structure and Mechanism in Protein Science Alan Fersht 1999
Enzimologia Aula 2 Leitura sugerida Biochemistry Voet & Voet 3ª edição Capítulo 10 parte 1Bb (página 323), parte 4A, 4B e 4C (páginas 346-350) Structure and Mechanism in Protein Science Alan Fersht 1999
8/30/2010. Aula 4 Interações fracas. Introdução a Bioquímica: Biomoléculas. Intermolecular Intramolecular
 Introdução a Bioquímica: Biomoléculas Intermolecular Intramolecular Aula 4 Interações fracas Forças Intermoleculares são forças de atração entre moléculas. 41 kj para vaporizar 1 mol of água (inter) Forças
Introdução a Bioquímica: Biomoléculas Intermolecular Intramolecular Aula 4 Interações fracas Forças Intermoleculares são forças de atração entre moléculas. 41 kj para vaporizar 1 mol of água (inter) Forças
CRISTALOGRAFIA DE PROTEÍNAS Crescimento de cristais
 Crescimento de cristais Referências: Crystallization of Nucleic Acids and Proteins. A Practical Approach. Second Edition. Edited by A.Ducruix e R.Giegé.Oxford University Press. 1999. Protein Crystallization:
Crescimento de cristais Referências: Crystallization of Nucleic Acids and Proteins. A Practical Approach. Second Edition. Edited by A.Ducruix e R.Giegé.Oxford University Press. 1999. Protein Crystallization:
Tutorial: QUÍMICA COMPUTACIONAL E MODELAGEM MOLECULAR. Profa. Nelilma Correia Romeiro
 Tutorial: QUÍMICA COMPUTACIONAL E MODELAGEM MOLECULAR Profa. Nelilma Correia Romeiro Fevereiro de 2008 1 MODELAGEM MOLECULAR Modelagem molecular, segundo a IUPAC, é a investigação das estruturas e das
Tutorial: QUÍMICA COMPUTACIONAL E MODELAGEM MOLECULAR Profa. Nelilma Correia Romeiro Fevereiro de 2008 1 MODELAGEM MOLECULAR Modelagem molecular, segundo a IUPAC, é a investigação das estruturas e das
Structure versus Ligand-Based Drug Design
 Structure versus Ligand-Based Drug Design Known Ligands Unknown Ligands Know protein structure Unknown protein structure Structure-based drug design (SBDD) Protein modelling Docking-guided Chemical optimization
Structure versus Ligand-Based Drug Design Known Ligands Unknown Ligands Know protein structure Unknown protein structure Structure-based drug design (SBDD) Protein modelling Docking-guided Chemical optimization
OBJETIVOS PLANEJAMENTO DE FÁRMACOS MÉTODOS EM QUÍMICA MEDICINAL FFI0763. Propriedades
 MÉTODOS EM QUÍMICA MEDICINAL FFI0763 aandrico@ifsc.usp.br PLANEJAMENTO DE FÁRMACOS OBJETIVOS 1. Potência, Afinidade, Seletividade 2. Absorção, Permeabilidade Propriedades Relações entre a Estrutura e Atividade
MÉTODOS EM QUÍMICA MEDICINAL FFI0763 aandrico@ifsc.usp.br PLANEJAMENTO DE FÁRMACOS OBJETIVOS 1. Potência, Afinidade, Seletividade 2. Absorção, Permeabilidade Propriedades Relações entre a Estrutura e Atividade
OBJETIVOS PLANEJAMENTO DE FÁRMACOS MÉTODOS EM QUÍMICA MEDICINAL FFI0763. Propriedades
 MÉTODOS EM QUÍMICA MEDICINAL FFI0763 aandrico@ifsc.usp.br PLANEJAMENTO DE FÁRMACOS OBJETIVOS 1. Potência, Afinidade, Seletividade 2. Absorção, Permeabilidade Propriedades Relações entre a Estrutura e Atividade
MÉTODOS EM QUÍMICA MEDICINAL FFI0763 aandrico@ifsc.usp.br PLANEJAMENTO DE FÁRMACOS OBJETIVOS 1. Potência, Afinidade, Seletividade 2. Absorção, Permeabilidade Propriedades Relações entre a Estrutura e Atividade
Característica gerais dos vírus e Replicação viral
 Característica gerais dos vírus e Replicação viral O que são os vírus? São agentes infecciosos acelulares; São replicados por uma célula hospedeira (não possuem metabolismo, são parasitas moleculares);
Característica gerais dos vírus e Replicação viral O que são os vírus? São agentes infecciosos acelulares; São replicados por uma célula hospedeira (não possuem metabolismo, são parasitas moleculares);
Enzimas. Bianca Zingales IQ - USP
 Enzimas Bianca Zingales IQ - USP Enzimas As enzimas são catalisadores biológicos extremamente eficientes que aceleram 10 9 a 10 12 vezes (em média) a velocidade da reação. As enzimas chegam a transformar
Enzimas Bianca Zingales IQ - USP Enzimas As enzimas são catalisadores biológicos extremamente eficientes que aceleram 10 9 a 10 12 vezes (em média) a velocidade da reação. As enzimas chegam a transformar
Aula 4: Enzimas Cinética e Regulação
 Disciplina de Engenharia de Proteínas Curso de Ciências Biológicas Aula 4: Enzimas Cinética e Regulação Prof. Marcos Túlio de Oliveira mtoliveira@fcav.unesp.br Faculdade de Ciências Agrárias e Veterinárias
Disciplina de Engenharia de Proteínas Curso de Ciências Biológicas Aula 4: Enzimas Cinética e Regulação Prof. Marcos Túlio de Oliveira mtoliveira@fcav.unesp.br Faculdade de Ciências Agrárias e Veterinárias
QUÍMICA MEDICINAL. Em temos etimológicos pode considerar-se um ramo da farmacologia (de pharmakon + logos = estudo dos fármacos).
 QUÍMICA MEDICINAL Sentido prospectivo envolve o planeamento e produção de compostos que podem ser usados em medicina para a prevenção, tratamento e/ou cura de doenças humanas ou de animais. Em temos etimológicos
QUÍMICA MEDICINAL Sentido prospectivo envolve o planeamento e produção de compostos que podem ser usados em medicina para a prevenção, tratamento e/ou cura de doenças humanas ou de animais. Em temos etimológicos
Setor Sul do Campus Universitário Manaus, AM. Fone/Fax: (092) /4028 PLANO DE ENSINO. Oliveira Cavalcante
 UNIVERSIDADE DO AMAZONAS INSTITUTO DE CIÊNCIAS EXATAS DEPARTAMENTO DE QUÍMICA Setor Sul do Campus Universitário - Bloco H, Av. Gal. Rodrigo Octávio Jordão Ramos, 3000 Coroado 69077-000 Manaus, AM. Fone/Fax:
UNIVERSIDADE DO AMAZONAS INSTITUTO DE CIÊNCIAS EXATAS DEPARTAMENTO DE QUÍMICA Setor Sul do Campus Universitário - Bloco H, Av. Gal. Rodrigo Octávio Jordão Ramos, 3000 Coroado 69077-000 Manaus, AM. Fone/Fax:
Catalizadores biológicos - Aceleram reações químicas específicas sem a formação de produtos colaterais
 O que são enzimas? Catalizadores biológicos - Aceleram reações químicas específicas sem a formação de produtos colaterais Reagentes = substratos Local onde a reação ocorre = sitio ou centro ativo S + E
O que são enzimas? Catalizadores biológicos - Aceleram reações químicas específicas sem a formação de produtos colaterais Reagentes = substratos Local onde a reação ocorre = sitio ou centro ativo S + E
Aula de Bioquímica I. Tema: Enzimas. Prof. Dr. Júlio César Borges
 Aula de Bioquímica I Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: borgesjc@iqsc.usp.br
Aula de Bioquímica I Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: borgesjc@iqsc.usp.br
Biologia Molecular (Parte I)
 Biologia Molecular (Parte I) Introdução 1. Substâncias Inorgânicas 1.1. Água A água faz pontes de hidrogênio Polaridade Propriedades da água Solvente Universal Participa de reações químicas vitais Adesão
Biologia Molecular (Parte I) Introdução 1. Substâncias Inorgânicas 1.1. Água A água faz pontes de hidrogênio Polaridade Propriedades da água Solvente Universal Participa de reações químicas vitais Adesão
MÉTODOS DE MULTI-DOCKING GENERALIZADO
 MÉTODOS DE MULTI-DOCKING GENERALIZADO Aluno: Gabriel Coutinho de Paula Orientador: Bruno Araujo Cautiero Horta Introdução Metodologias computacionais de docking receptor-ligante são ferramentas de grande
MÉTODOS DE MULTI-DOCKING GENERALIZADO Aluno: Gabriel Coutinho de Paula Orientador: Bruno Araujo Cautiero Horta Introdução Metodologias computacionais de docking receptor-ligante são ferramentas de grande
Disciplina Biologia Celular. Profª Cristina Lacerda Soares Petrarolha Silva Curso de Agronomia FISMA / FEA
 Disciplina Biologia Celular Profª Cristina Lacerda Soares Petrarolha Silva Curso de Agronomia FISMA / FEA Aula 4: Bases Macromoleculares da Constituição Celular Bio Cel Profª Cristina Introdução Células
Disciplina Biologia Celular Profª Cristina Lacerda Soares Petrarolha Silva Curso de Agronomia FISMA / FEA Aula 4: Bases Macromoleculares da Constituição Celular Bio Cel Profª Cristina Introdução Células
Proteínas II. (Enzimas) Bioquímica Prof. Dr. Marcelo Soares
 Proteínas II (Enzimas) Conceitos Gerais e Funções As enzimas são proteínas especializadas na catálise de reações biológicas Consideradas as biomoléculas mais notáveis devido a sua extraordinária especificidade
Proteínas II (Enzimas) Conceitos Gerais e Funções As enzimas são proteínas especializadas na catálise de reações biológicas Consideradas as biomoléculas mais notáveis devido a sua extraordinária especificidade
Interação Antígeno Anticorpo. Profª Heide Baida
 Interação Antígeno Anticorpo Profª Heide Baida Introdução T CD4+ memória MØ Resposta imune Ag Linfócito T CD4+ T CD4+ efetor * * * * * * * * * citocinas * * Linfócito B anticorpos B memória B Efetor (plasmócito)
Interação Antígeno Anticorpo Profª Heide Baida Introdução T CD4+ memória MØ Resposta imune Ag Linfócito T CD4+ T CD4+ efetor * * * * * * * * * citocinas * * Linfócito B anticorpos B memória B Efetor (plasmócito)
Antígenos Recombinantes e suas aplicações em Imunologia
 UNIVERSIDADE ESTADUAL PAULISTA - UNESP FACULDADE DE CIÊNCIAS AGRÁRIAS E VETERINÁRIAS FCAV CAMPUS DE JABOTICABAL Antígenos Recombinantes e suas aplicações em Imunologia Bióloga Mariana Monezi Borzi Doutoranda
UNIVERSIDADE ESTADUAL PAULISTA - UNESP FACULDADE DE CIÊNCIAS AGRÁRIAS E VETERINÁRIAS FCAV CAMPUS DE JABOTICABAL Antígenos Recombinantes e suas aplicações em Imunologia Bióloga Mariana Monezi Borzi Doutoranda
ENGENHARIA DE BIOPROCESSOS E BIOTECNOLOGIA MATRIZ CURRICULAR
 ENGENHARIA DE BIOPROCESSOS E BIOTECNOLOGIA MATRIZ CURRICULAR 1º SEMESTRE Cálculo I Sem pré-requisitos Álgebra Linear e Geometria Analítica Sem pré-requisitos Química Geral Sem pré-requisitos Desenho Técnico
ENGENHARIA DE BIOPROCESSOS E BIOTECNOLOGIA MATRIZ CURRICULAR 1º SEMESTRE Cálculo I Sem pré-requisitos Álgebra Linear e Geometria Analítica Sem pré-requisitos Química Geral Sem pré-requisitos Desenho Técnico
UNIVERSIDADE FEDERAL DO CEARÁ CENTRO DE CIÊNCIAS DEPARTAMENTO DE QUÍMICA ORGÂNICA E INORGÂNICA PROGRAMA DE PÓS-GRADUAÇÃO EM QUÍMICA
 UNIVERSIDADE FEDERAL DO CEARÁ CENTRO DE CIÊNCIAS DEPARTAMENTO DE QUÍMICA ORGÂNICA E INORGÂNICA PROGRAMA DE PÓS-GRADUAÇÃO EM QUÍMICA SÉRGIO XAVIER BARBOSA ARAÚJO VIRTUAL SCREENING DE POSSÍVEIS INIBIDORES
UNIVERSIDADE FEDERAL DO CEARÁ CENTRO DE CIÊNCIAS DEPARTAMENTO DE QUÍMICA ORGÂNICA E INORGÂNICA PROGRAMA DE PÓS-GRADUAÇÃO EM QUÍMICA SÉRGIO XAVIER BARBOSA ARAÚJO VIRTUAL SCREENING DE POSSÍVEIS INIBIDORES
Programa Analítico de Disciplina BQI460 Bioinformática
 0 Programa Analítico de Disciplina Departamento de Bioquímica e Biologia Molecular - Centro de Ciências Biológicas e da Saúde Número de créditos: Teóricas Práticas Total Duração em semanas: 15 Carga horária
0 Programa Analítico de Disciplina Departamento de Bioquímica e Biologia Molecular - Centro de Ciências Biológicas e da Saúde Número de créditos: Teóricas Práticas Total Duração em semanas: 15 Carga horária
BIOLOGIA Biologia Molecular 1ª parte
 BIOLOGIA Biologia Molecular 1ª parte Professora: Brenda Braga 2015 Substâncias Inorgânicas Água Participa de reações químicas A água faz ligações de hidrogênio. Dissolve substâncias (hidrofílicas). Sua
BIOLOGIA Biologia Molecular 1ª parte Professora: Brenda Braga 2015 Substâncias Inorgânicas Água Participa de reações químicas A água faz ligações de hidrogênio. Dissolve substâncias (hidrofílicas). Sua
OTIMIZAÇÃO IN SILICO DO FÁRMACO ANTICANCERÍGENO L-ASPARAGINASE
 OTIMIZAÇÃO IN SILICO DO FÁRMACO ANTICANCERÍGENO L-ASPARAGINASE Ronaldo Correia da SILVA SILVA, Ronaldo Correia da. Otimização in silicodo fármaco anticancerígeno L-Asparaginase. Projeto de investigação
OTIMIZAÇÃO IN SILICO DO FÁRMACO ANTICANCERÍGENO L-ASPARAGINASE Ronaldo Correia da SILVA SILVA, Ronaldo Correia da. Otimização in silicodo fármaco anticancerígeno L-Asparaginase. Projeto de investigação
Desenvolvimento de um filtro de descritores moleculares geométricos para gerar um ranqueamento em Banco de Dados de ligantes
 PONTIFÍCIA UNIVERSIDADE CATÓLICA DO RIO GRANDE DO SUL FACULDADE DE INFORMÁTICA PROGRAMA DE PÓS-GRADUAÇÃO EM CIÊNCIA DA COMPUTAÇÃO Desenvolvimento de um filtro de descritores moleculares geométricos para
PONTIFÍCIA UNIVERSIDADE CATÓLICA DO RIO GRANDE DO SUL FACULDADE DE INFORMÁTICA PROGRAMA DE PÓS-GRADUAÇÃO EM CIÊNCIA DA COMPUTAÇÃO Desenvolvimento de um filtro de descritores moleculares geométricos para
