Comunicado Técnico ISSN
|
|
|
- Alícia Raminhos Araújo
- 7 Há anos
- Visualizações:
Transcrição
1 Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, Campinas, SP ISSN Curvatura da Superfície de Proteínas no Java Protein Dossier Paula Kuser Falcão 1 Christian Baudet 2 Roberto Hiroshi Higa 3 Goran Neshich 4 Um aspecto elementar da biologia envolve o reconhecimento entre moléculas. Grande parte das informações estruturais farmacologicamente importantes residem na superfície das proteínas. As interações entre proteínas e entre proteínas e peptídios, ácidos nucléicos ou ligantes têm um papel vital em todos os processos biológicos. Além da necessidade de serem energeticamente favoráveis, estas interações dependem fortemente das características da propriedade das superfícies que interagem. Uma ligação perfeita implica na complementaridade das superfícies. As funções das proteínas tais como catálise ou reconhecimento molecular ocorrem predominantemente na superfície da proteína ou próximo dela (Fersht, 1999; Lesk, 2001). A informação sobre a superfície também pode fornecer detalhes sobre a estabilidade e solubilidade das proteínas, já que estas propriedades dependem de como os elementos da superfície da macromolécula interagem com o solvente e pequenos solutos presentes na solução. Técnicas estruturais modernas como cristalografia de raios-x e ressonância nuclear magnética produzem estruturas moleculares de alta resolução. Para estudar o funcionamento das proteínas, além de utilizar as informações de estrutura, faz-se necessário ter também cálculos analíticos de parâmetros moleculares. No entanto, um grande volume de trabalho é necessário para realizar a análise de várias estruturas, comparálas e extrair a informação desejada. A explosão de técnicas recentes de modelagem de estruturas de proteínas causou um enorme interesse em métodos para modelar a interação de ligantes com os receptores. O primeiro obstáculo que deve ser eliminado, no entanto, é a localização do sítio ativo, o local onde o ligante se posiciona. Este é o tipo de problema que se pretende ajudar a resolver mapeando parâmetros nas estruturas de proteínas. O trabalho desenvolvido no Núcleo de BioInformática Estrutural (NBI), da Embrapa Informática Agropecuária, visa desenvolver ferramentas para a análise estrutural de moléculas biológicas. Uma das ferramentas em 1 Ph.D. em Física Aplicada, Cristalografia de Proteínas, Pesquisadora da Embrapa Informática Agropecuária, Caixa Postal 6041, Barão Geraldo Campinas, SP. ( paula@cnptia.embrapa.br) 2 Estudante de Engenharia da Computação, Estagiário da Embrapa Informática Agropecuária, Caixa Postal 6041, Barão Geraldo Campinas, SP. ( christian@cnptia.embrapa.br) 3 M.Sc. em Engenharia Elétrica, Pesquisador da Embrapa Informática Agropecuária, Caixa Postal 6041, Barão Geraldo Campinas, SP. ( roberto@cnptia.embrapa.br) 4 Ph.D. em Biofísica, Pesquisador da Embrapa Informática Agropecuária, Caixa Postal 6041, Barão Geraldo Campinas, SP. ( neshich@cnptia.embrapa.br)
2 2 Curvatura da Superfície de Proteínas no Java Protein Dossier desenvolvimento é o módulo Java Protein Dossier (JPD) do Sting Millennium Suíte (SMS). O JPD oferece um tipo de visualização através de cores que leva a identificação de possíveis sítios de ligação na superfície dos alvos biológicos. Uma das propriedades que oferece indícios para identificar um possível sítio ativo é a curvatura local da superfície, que deve ser visualizada juntamente com outras propriedades como hidrofobicidade e potencial eletrostático, também mapeadas no JPD. O objetivo deste trabalho é gerar valores de curvatura para os resíduos de todas as proteínas existentes no Protein Data Bank (PDB), depositório mundial de proteínas (Berman et al., 2000), para que estes valores possam ser incorporados no módulo JPD. Existem atualmente aproximadamente vinte mil estruturas no PDB. Gera-se todos esses valores em larga escala (highthroughput) através da utilização do programa SurfRace (Tsodikov et al., 2002) e com a construção de um script que possibilite acessar todo o banco de dados de proteínas e criar um novo banco de dados com os valores de curvatura para os átomos. esfera teste, obtém-se a superfície acessível ao solvente. O valor do raio da esfera teste utilizado geralmente é o raio de uma molécula de água Å (Leach, 2001). A superfície molecular (Richards, 1977; Conolly, 2003) é composta pelos dois tipos de superfície anteriormente descritos: a parte da superfície de van der Waals de cada átomo que é acessível à esfera teste, correspondendo à superfície de contato, e a face interna da esfera teste quando está, simultaneamente, em contato com mais do que um átomo (a superfície reentrante). Estes conceitos ficam mais claros quando ilustrados na Fig. 1. A Fig. 2 representa a superfície molecular de um aminoácido para mostrar as regiões de curvatura côncavas ou convexas. Definição de Superfície No estudo das interações entre moléculas é necessário examinar suas superfícies. A característica de curvatura que se quer quantificar é a curvatura da superfície da molécula. Para entender como é definida esta superfície, três tipos de superfícies serão brevemente explicadas aqui para melhor entendimento do texto: a superfície de van der Waals, a superfície acessível ao solvente e a superfície molecular. A superfície de van der Waals é construída a partir das esferas de van der Waals dos átomos. Estudos mostram que os átomos ficam a uma determinada distância (distância intermolecular) uns dos outros nas moléculas, sugerindo que eles devem ocupar um volume definido. As distâncias intermoleculares é interpretada visualizando os átomos como esferas. O raio dessas esferas é chamado de raio de van der Waals. A superfície de van der Waals corresponde ao envelope molecular contendo as esferas atômicas de raio igual ao raio de van der Waals. Alguns exemplos de valores de raios de van der Waals são: Carbono = 1.70Å, Cl = 1.75Å, Cu = 1.40Å, H = 1.20Å, He = 1Å, N = 1.55Å, O = 1.52Å, Pb = 2.02Å. A superfície de van der Waals de uma molécula não é muito relevante quimicamente falando porque contém muitos vales e depressões entre átomos, que não podem ser acessados por outros átomos. Um conceito mais prático de superfície é a superfície acessível a solvente, introduzida por Lee & Richards (1971). Esta superfície, traçada em torno de uma molécula, é descrita pelo centro de uma esfera teste (probe sphere) rolando em torno da proteína. Aumentando o raio de van der Waals de cada átomo com o valor do raio da Fig. 1. Superfície de Van der Waals (vermelha), é a superfície relacionada com o raio de van der Waals dos átomos; a superfície acessível ao solvente (azul), que requer a rolagem de uma esfera imaginária de raio igual a 1.4 Å; e a superfície molecular (verde), que é composta por partes das duas outras superfícies. Fig. 2. Representação gráfica da superfície molecular do aminoácido triptofano, mostrando a curvatura da superfície, com regiões côncavas e convexas (Extraído de molecular/surfaces_1.7.gif).
3 Curvatura da Superfície de Proteínas no Java Protein Dossier 3 Cálculo dos Valores de Curvatura com SurfRace O programa SurfRace, desenvolvido por Tsodikov et al. (2002), é baseado no teorema de Gauss-Bonnet que relaciona a geometria de uma superfície com a sua topologia. SurfRace utiliza a idéia de correspondência entre a superfície acessível ao solvente e a superfície molecular. O programa utiliza os arquivos do banco de dados de proteínas (PDB) como arquivo de entrada. Este arquivo de entrada contém os nomes de todos os átomos que compõem a proteína, com suas respectivas coordenadas (x, y, z). O arquivo de saída do programa SurfRace contém, além das coordenadas de todos os átomos no formato original, quatro colunas extras que se referem a: raio de van der Walls de cada átomo, área da superfície acessível, área da superfície molecular e curvatura da superfície molecular de cada átomo (Tsodikov et al., 2002). O programa tem algumas opções de entrada: conjunto dos raios de Van der Waals que será utilizado no cálculo; nome do arquivo com código pdb; raio da esfera de teste em Angstrons; tipo de cálculo que se quer executar: área da superfície acessível a solvente, área das superfícies acessível e molecular, área das superfícies acessível e molecular e curvatura média da superfície molecular. Utilizou-se o programa SurfRace para obter os valores de curvatura para todos os átomos do arquivo de coordenadas das proteínas. Para fazer o cálculo do valor de curvatura para todos os arquivos de estruturas disponíveis no PDB ( estruturas) o programa SurfRace rodou através de um script em Perl (Fig. 3). Este script lê os arquivos pdb um a um, cria um arquivo texto com todas as opções de entrada que o programa precisa para cada arquivo pdb e chama o programa. O programa é executado e gera o arquivo de saída com as informações de curvatura para cada arquivo pdb. Estes arquivos são colocados em um banco de dados que será consultado pelo módulo JPD para geração do sumário com as informações das proteínas que este produz. Um exemplo de um arquivo de saída é apresentado na Tabela 1.!/usr/sbin/perl surfrace.pl Chama e executa o surfrace:./surface 1acb.pdb Para cada entrada dos arquivos *.pdb O executavel deve estar no mesmo diretorio do pdb Paula Kuser = `ls -c1 *.pdb`; for ($i=0;$i<=$files;$i++) { $pdb=$files[$i]; open (INPUT,">input.txt") die ("Nao foi possivel abrir o arquiv o"); print INPUT "1\n"; print INPUT "$pdb\n"; print INPUT "1.45\n"; print INPUT "3\n"; print INPUT "\n"; print INPUT "\n"; system ("echo./surfrace < input.txt"); } Fig. 3. Script para executar o programa SurfRace para as estruturas de proteínas do PDB. Tabela 1. Exemplo de arquivo de saída do programa SurfRace onde a última coluna corresponde ao valor de curvatura do átomo. Valores menores que zero correspondem a regiões convexas, iguais a zero correspondem a regiões que não estão na superfície e valores maiores que zero correspondem a regiões côncavas. aa x y z curv ATOM 442 OG1 THR E ATOM 443 CG2 THR E ATOM 449 OG SER E ATOM 456 OD1 ASP E ATOM 457 OD2 ASP E ATOM 463 CG1 VAL E ATOM 464 CG2 VAL E ATOM 470 CG1 VAL E ATOM 471 CG2 VAL E ATOM 477 CG1 VAL E ATOM 478 CG2 VAL E ATOM 483 CB ALA E
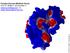
4 4 Curvatura da Superfície de Proteínas no Java Protein Dossier As informações geradas com o cálculo de curvatura estão sendo incorporadas à versão 3.0 do aplicativo Java Protein Dossier do SMS, que está d i s p o n í v e l n a servidora beta do NBI ( beta.cbi.cnptia.embrapa.br/sms). A Fig. 4 mostra os resultados obtidos para uma proteína teste. O parâmetro é mapeado no JPD em tonalidades que vão da cor cinza até o verde, dependendo do valor da curvatura. Os aminoácidos em regiões côncavas estão pintados com a cor cinza e os aminoácidos em regiões convexas estão pintados de verde. Aqueles com valor de curvatura zero, ou seja, que estão em regiões planas da superfície da molécula, aparecem em branco. Um excelente uso da propriedade de curvatura é para o cálculo do docking de duas moléculas. Docking é o processo de encaixar duas moléculas graficamente em três dimensões. Quando se faz o docking de duas estruturas de macromoléculas utilizando o parâmetro curvatura, é necessário ter superfícies geometricamente complementares que são iguais em magnitude, mas de sinais opostos. Este critério de curvatura pode ser usado como condição necessária (mas não suficiente) de complementariedade, permitindo eliminar uma série de arranjos não complementares. Um exemplo de utilização da informação de complementariedade de superfícies pode ser visto na Fig. 5, que mostra o ligante benzamidina dentro do sítio ativo da enzima beta-tripsina (Morris et al.,1996). A posição do ligante foi determinada após vários ciclos de docking, até encontrar o encaixe perfeito na cavidade da superfície do sítio ativo da enzima. Fig. 5. Molécula benzamidina posicionada no sítio ativo da proteína beta-tripsina através da técnica de docking. Conclusões A análise obtida com o uso do JPD dá informações sobre as regiões funcionalmente importantes da proteína muito rapidamente. Com as informações iniciais de curvatura, juntamente com outras propriedades mapeadas no JPD, como por exemplo acessibilidade e entropia, já é possível ter idéias sobre os possíveis ligantes, sobre experimentos de mutação que podem ser feitos em laboratório e sobre interações com outras estruturas. O valor de curvatura das regiões também pode ajudar a identificar regiões de interesse para o docking, que são as cavidades e protrusões. O programa SMS, desenvolvido no Núcleo de Bioinformática Estrutural (NBI), da Embrapa Informática Agropecuária, pode ser utilizado por qualquer pessoa Fig. 4. Java Protein Dossier, com informações de curvatura incorporada.informação contida na última linha (Curvature).
5 Curvatura da Superfície de Proteínas no Java Protein Dossier 5 através do site A versão atual disponível no site é a versão 2.2; a nova versão que inclui o resultado exposto neste trabalho está disponível no site beta do NBI e será instalada para acesso externo no primeiro trimestre de Referências Bibliográficas BERMAN, H. M.; WESTBROOK, J.; FENG, Z.; GILLILAND, G.; BHAT, T. N.; WEISSIG, H.; SHINDYALOV, I. N.; BOURNE, P. E. The Protein Data Bank. Nucleic Acids Research, v. 28, p , CONNOLLY, M. L. Molecular surface: a review. Disponível em: < Compchem/feature14.html>. Acesso em: fev FERSHT, A. Structure and mechanism in protein science: a guide to enzyme catalysis and protein folding. 3 rd ed. New York: W.H. Freeman, p. LEACH, A. R. Molecular modelling: principles and applications. Upper Saddle River: Prentice Hall, p. LEE, B.; RICHARDS, F. M. The interpretation of protein structures: estimation of static accessibility. J. Mol. Biology, v. 55, p , LESK, A. M. Introduction to protein architecture: the structural biology of proteins. New York: Oxford University Press, p. MORRIS, G. M.; GOODSELL, D. S.; HUEY, R.; OLSON, A. J. Distributed automated docking of flexible ligands to proteins: parallel applications of AutoDock 2.4. J. Computer-Aided Molecular Design, v. 10, p , RICHARDS, F. M. Areas, volumes, packing and protein structure. Annu. Rev. Biophysics. Bioeng., v. 6, p , TSODIKOV, O. V.; RECORD JUNIOR, M. T.; SERGEEV, Y. V. A novel computer program for fast exact calculation of accessible and molecular surface areas and average surface curvature. J. Comput. Chem., v. 23, p , Comunicado Técnico, 38 Embrapa Informática Agropecuária Área de Comunicação e Negócios (ACN) Av. André Tosello, 209 Cidade Universitária - Zeferino Vaz Barão Geraldo - Caixa Postal Campinas, SP Telefone (19) Fax (19) sac@cnptia.embrapa.br 1 a edição on-line Todos os direitos reservados Comitê de Publicacões Expediente Presidente: José Ruy Porto de Carvalho Membros efetivos: Amarindo Fausto Soares, Ivanilde Dispato, Luciana Alvim Santos Romani, Marcia Izabel Fugisawa Souza, Suzilei Almeida Carneiro Suplentes: Adriana Delfino dos Santos, Fábio Cesar da Silva, João Francisco Gonçalves Antunes, Maria Angélica de Andrade Leite, Moacir Pedroso Júnior Supervisor editorial: Ivanilde Dispato Normalização bibliográfica: Marcia Izabel Fugisawa Souza Capa: Intermídia Publicações Científicas Editoração Eletrônica: Intermídia Publicações Científicas
Comunicado Técnico ISSN
 Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 34 2002 Campinas, SP ISSN 1677-8464 Incorporação das Propriedades Rotâmeros e Ocupância em Métodos de Análise Estrutural
Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 34 2002 Campinas, SP ISSN 1677-8464 Incorporação das Propriedades Rotâmeros e Ocupância em Métodos de Análise Estrutural
Comunicado Técnico ISSN
 Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 40 2002 Campinas, SP ISSN 1677-8464 Java Protein Dossier Apresentação Gráfica de Parâmetros Protéicos Utilizando o Java
Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 40 2002 Campinas, SP ISSN 1677-8464 Java Protein Dossier Apresentação Gráfica de Parâmetros Protéicos Utilizando o Java
Comunicado Técnico ISSN
 Comunicado Técnico Novembro, 4 2001 Campinas, SP ISSN 1677-8464 Utilização de Interpoladores na Geração de Grades do Spring para Elaboração de Modelos Numéricos de Terreno Utilizando Dados de Fertilidade
Comunicado Técnico Novembro, 4 2001 Campinas, SP ISSN 1677-8464 Utilização de Interpoladores na Geração de Grades do Spring para Elaboração de Modelos Numéricos de Terreno Utilizando Dados de Fertilidade
Modelagem Comparativa de Proteínas
 Modelagem Comparativa de Proteínas Bioinformática Estrutural Aula 3 3 de Junho de 2013 Paula Kuser Falcão Laboratório de Bioinformática Aplicada Embrapa Informática Agropecuária Por que predizer a estrutura?
Modelagem Comparativa de Proteínas Bioinformática Estrutural Aula 3 3 de Junho de 2013 Paula Kuser Falcão Laboratório de Bioinformática Aplicada Embrapa Informática Agropecuária Por que predizer a estrutura?
Comunicado Técnico ISSN 1677-8464
 Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Novembro, 24 2002 Campinas, SP ISSN 1677-8464 Utilização do Software GRASP para gerar Arquivo de Coordenadas com Valores de Potencial
Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Novembro, 24 2002 Campinas, SP ISSN 1677-8464 Utilização do Software GRASP para gerar Arquivo de Coordenadas com Valores de Potencial
Comunicado Técnico ISSN 1677-8464
 Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 37 2002 Campinas, SP ISSN 1677-8464 Análise do Grau de Conservação de Resíduos em Proteínas com Estrutura 3D Resolvida Utilizando
Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 37 2002 Campinas, SP ISSN 1677-8464 Análise do Grau de Conservação de Resíduos em Proteínas com Estrutura 3D Resolvida Utilizando
Interações de van der Waals. Interações de van der Waals. Interações de van der Waals.
 Interações de van der Waals aandrico@if.sc.usp.br Também conhecidas como forças de dispersão de London, caracterizam-se pelo momento de dipolo induzido e ocorrem entre todos os átomos. Apesar de moléculas
Interações de van der Waals aandrico@if.sc.usp.br Também conhecidas como forças de dispersão de London, caracterizam-se pelo momento de dipolo induzido e ocorrem entre todos os átomos. Apesar de moléculas
Primeiro Curso STING Millennium Suite Chemogenomics: Ferramentas para Analisar Macromoleculares e Aplicações em Chemogenomics
 Primeiro Curso STING Millennium Suite Chemogenomics: Ferramentas para Analisar Macromoleculares e Aplicações em Chemogenomics Paula Kuser, Jair De Siqueira Neto, Jorge Fernandez, Roberto Higa, Christian
Primeiro Curso STING Millennium Suite Chemogenomics: Ferramentas para Analisar Macromoleculares e Aplicações em Chemogenomics Paula Kuser, Jair De Siqueira Neto, Jorge Fernandez, Roberto Higa, Christian
Docking (ou atracamento) Molecular. Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia 9 de outubro de 2014
 Docking (ou atracamento) Molecular Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia rafaelasf@gmail.com 9 de outubro de 2014 O ATRACAMENTO MOLECULAR PERMITE ESTIMAR COMO DUAS MOLÉCULAS INTERAGEM
Docking (ou atracamento) Molecular Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia rafaelasf@gmail.com 9 de outubro de 2014 O ATRACAMENTO MOLECULAR PERMITE ESTIMAR COMO DUAS MOLÉCULAS INTERAGEM
Visualização de Hélices
 Grupo: Curso: Turma: Data: Visualização de Hélices Objetivos Visualizar a estrutura tridimensional de hélices presentes na estrutura de proteínas e peptídeos, usandose recursos computacionais. Analisar
Grupo: Curso: Turma: Data: Visualização de Hélices Objetivos Visualizar a estrutura tridimensional de hélices presentes na estrutura de proteínas e peptídeos, usandose recursos computacionais. Analisar
Comunicado Técnico ISSN
 Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 42 2002 Campinas, SP ISSN 1677-8464 Estudo da Influência de Seqüências Polipeptídicas e de Códons na Determinação da Estrutura
Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 42 2002 Campinas, SP ISSN 1677-8464 Estudo da Influência de Seqüências Polipeptídicas e de Códons na Determinação da Estrutura
Documentos Dezembro, 2004
 Documentos Dezembro, 2004 46 ISSN 1677-9274 Um Modelo Orientado a Objetos para o Cálculo da Estimativa da Área Acessível a Solvente República Federativa do Brasil Luiz Inácio Lula da Silva Presidente Ministério
Documentos Dezembro, 2004 46 ISSN 1677-9274 Um Modelo Orientado a Objetos para o Cálculo da Estimativa da Área Acessível a Solvente República Federativa do Brasil Luiz Inácio Lula da Silva Presidente Ministério
2018 Dr. Walter F. de Azevedo Jr. Biofísica. Prof. Dr. Walter F. de Azevedo Jr.
 2018 Dr. Walter F. de Azevedo Jr. Biofísica Prof. Dr. Walter F. de Azevedo Jr. 1 Ao lado temos a estrutura de um peptídeo formado pelos aminoácidos Arginina - Prolina - Alanina - Tirosina - Serina, coloridos
2018 Dr. Walter F. de Azevedo Jr. Biofísica Prof. Dr. Walter F. de Azevedo Jr. 1 Ao lado temos a estrutura de um peptídeo formado pelos aminoácidos Arginina - Prolina - Alanina - Tirosina - Serina, coloridos
Mecanismo de Inibição de Enzimas Preparação de Micro e Macromoléculas Docagem Molecular Exemplo de Aplicação
 bjetivos FFI0776 Modelagem e Engenharia de Proteínas Mecanismo de Inibição de Enzimas Preparação de Micro e Macromoléculas M l Docagem Molecular Exemplo de Aplicação Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br
bjetivos FFI0776 Modelagem e Engenharia de Proteínas Mecanismo de Inibição de Enzimas Preparação de Micro e Macromoléculas M l Docagem Molecular Exemplo de Aplicação Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br
2018 Dr. Walter F. de Azevedo Jr.
 2018 Dr. Walter F. de Azevedo Jr. 000000000000111111111110001100000000000 000000000001111111111111111111000000001 000000000111111111111111111111111000000 000000000111111111111111111111111000000 000000000011111111111111111111100000000
2018 Dr. Walter F. de Azevedo Jr. 000000000000111111111110001100000000000 000000000001111111111111111111000000001 000000000111111111111111111111111000000 000000000111111111111111111111111000000 000000000011111111111111111111100000000
Documentos. Avaliação da Aplicação do II Curso de Uso e Manejo de Irrigação Via Web ISSN Dezembro, 2001
 Documentos Dezembro, 2001 ISSN 1677-9274 Avaliação da Aplicação do II Curso de Uso e Manejo de Irrigação Via Web 8 República Federativa do Brasil Fernando Henrique Cardoso Presidente Ministério da Agricultura,
Documentos Dezembro, 2001 ISSN 1677-9274 Avaliação da Aplicação do II Curso de Uso e Manejo de Irrigação Via Web 8 República Federativa do Brasil Fernando Henrique Cardoso Presidente Ministério da Agricultura,
OBJETIVOS INTERAÇÕES INTERMOLECULARES INTERAÇÕES INTERMOLECULARES.
 OBJETIVOS aandrico@if.sc.usp.br Interações Intermoleculares Mecanismo de Ação Modo de Ligação Complexos Recetor-Ligante Exemplos e Exercícios INTERAÇÕES INTERMOLECULARES INTERAÇÕES INTERMOLECULARES O processo
OBJETIVOS aandrico@if.sc.usp.br Interações Intermoleculares Mecanismo de Ação Modo de Ligação Complexos Recetor-Ligante Exemplos e Exercícios INTERAÇÕES INTERMOLECULARES INTERAÇÕES INTERMOLECULARES O processo
Biologia Estrutural. Qualidade de modelos estruturais Prof. Dr. Walter F. de Azevedo Jr. wfdaj.sites.uol.com.br Dr. Walter F. de Azevedo Jr.
 Biologia Estrutural Qualidade de modelos estruturais Prof. Dr. Walter F. de Azevedo Jr. Biologia Estrutural Resumo SCOP Modelagem molecular SCOP A primeira versão do SCOP foi liberada em 29 de outubro
Biologia Estrutural Qualidade de modelos estruturais Prof. Dr. Walter F. de Azevedo Jr. Biologia Estrutural Resumo SCOP Modelagem molecular SCOP A primeira versão do SCOP foi liberada em 29 de outubro
Modelação Molecular no Desenho de Fármacos 2018/2019
 Modelação Molecular no Desenho de Fármacos 2018/2019 Docente Paulo Martel Gabinete: FCT, Edifício C8, 3.12 Email: pmartel@ualg.pt Homepage: http://w3.ualg.pt/~pmartel Funcionamento da Cadeira Aulas teóricas
Modelação Molecular no Desenho de Fármacos 2018/2019 Docente Paulo Martel Gabinete: FCT, Edifício C8, 3.12 Email: pmartel@ualg.pt Homepage: http://w3.ualg.pt/~pmartel Funcionamento da Cadeira Aulas teóricas
Comunicado Técnico ISSN
 Comunicado Técnico Novembro, 2 2001 Campinas, SP Foto: Arquivo do Ministério da Agricultura, Pecuária e Abastecimento ISSN 1677-8464 Análise de Comércio Exterior de Frutas a partir do Armazém de Dados
Comunicado Técnico Novembro, 2 2001 Campinas, SP Foto: Arquivo do Ministério da Agricultura, Pecuária e Abastecimento ISSN 1677-8464 Análise de Comércio Exterior de Frutas a partir do Armazém de Dados
Documentos. Sistema de Monitoramento de Pragas de Frutas. Projeto CNPq /01-8. Ministério da Agricultura, Pecuária e Abastecimento.
 Ministério da Agricultura, Pecuária e Abastecimento Documentos Agosto, 2002 12 ISSN 1677-9274 Sistema de Monitoramento de Pragas de Frutas República Federativa do Brasil Fernando Henrique Cardoso Presidente
Ministério da Agricultura, Pecuária e Abastecimento Documentos Agosto, 2002 12 ISSN 1677-9274 Sistema de Monitoramento de Pragas de Frutas República Federativa do Brasil Fernando Henrique Cardoso Presidente
QSAR 3D Planejamento de NCEs QSAR 3D. O processo de reconhecimento molecular é um processo tridimensional. Conformação bioativa.
 QSAR 3D Interação Fármaco-Receptor AULA 5 a maioria dos casos, a ação dos fármacos está ligada a interação fármaco-receptor, receptor, através de uma associação do tipo reversível e não- covalente Agonistas
QSAR 3D Interação Fármaco-Receptor AULA 5 a maioria dos casos, a ação dos fármacos está ligada a interação fármaco-receptor, receptor, através de uma associação do tipo reversível e não- covalente Agonistas
Referência: Primeira parte Docking nativo do composto co-cristalizado
 Tutorial Docking utilizando AUTODOCK Vina Profa. Rafaela Salgado Ferreira Departamento de Bioquímica e Imunologia - Universidade Federal de Minas Gerais Referência: AutoDockVina - Trott O, Olson AJ. AutoDock
Tutorial Docking utilizando AUTODOCK Vina Profa. Rafaela Salgado Ferreira Departamento de Bioquímica e Imunologia - Universidade Federal de Minas Gerais Referência: AutoDockVina - Trott O, Olson AJ. AutoDock
BOTUCATU, SP - RUBIÃO JUNIOR Fone (0xx14) fax
 Universidade Estadual Paulista Instituto de Biociências Seção de Pós-Graduação BOTUCATU, SP - RUBIÃO JUNIOR - 18618-000 - Fone (0xx14) 68026148 - fax 68023744 e-mail:posgraduacao@ibb.unesp.br Curso de
Universidade Estadual Paulista Instituto de Biociências Seção de Pós-Graduação BOTUCATU, SP - RUBIÃO JUNIOR - 18618-000 - Fone (0xx14) 68026148 - fax 68023744 e-mail:posgraduacao@ibb.unesp.br Curso de
Mecânica Molecular. Dinâmica Molecular. Exemplos de aplicação. é um método relativamente. energia e conformação de micro ou macromoléculas
 Objetivos FFI0776 Modelagem e Engenharia de Proteínas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 04 Mecânica Molecular Campo de força Exemplos de Campo de Força Dinâmica Molecular Etapas envolvidas
Objetivos FFI0776 Modelagem e Engenharia de Proteínas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 04 Mecânica Molecular Campo de força Exemplos de Campo de Força Dinâmica Molecular Etapas envolvidas
Comunicado Técnico ISSN 1677-8464
 Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 39 2002 Campinas, SP ISSN 1677-8464 SMSLib Biblioteca C++ do Sting Millennium Suite Roberto Hiroshi Higa 1 Christian Baudet
Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 39 2002 Campinas, SP ISSN 1677-8464 SMSLib Biblioteca C++ do Sting Millennium Suite Roberto Hiroshi Higa 1 Christian Baudet
MANUAL DE INSTALAÇÃO E TUTORIAL BÁSICO DE UTILIZAÇÃO DO PROGRAMA YASARA VIEW
 MANUAL DE INSTALAÇÃO E BÁSICO DE UTILIZAÇÃO DO PROGRAMA 1 Neste tutorial será apresentada uma ferramenta informática intuitiva e de acesso livre YASARA View que pode ser usada na sala de aula para que
MANUAL DE INSTALAÇÃO E BÁSICO DE UTILIZAÇÃO DO PROGRAMA 1 Neste tutorial será apresentada uma ferramenta informática intuitiva e de acesso livre YASARA View que pode ser usada na sala de aula para que
CRISTALOGRAFIA DE PROTEÍNAS Crescimento de cristais
 Crescimento de cristais Referências: Crystallization of Nucleic Acids and Proteins. A Practical Approach. Second Edition. Edited by A.Ducruix e R.Giegé.Oxford University Press. 1999. Protein Crystallization:
Crescimento de cristais Referências: Crystallization of Nucleic Acids and Proteins. A Practical Approach. Second Edition. Edited by A.Ducruix e R.Giegé.Oxford University Press. 1999. Protein Crystallization:
Interacções em moléculas biológicas
 Interacções em moléculas biológicas Interacções intramoleculares Ligações covalentes (manutenção da estrutura covalente das moléculas Interacções não-covalentes (conformções, folding, estrutura secundária)
Interacções em moléculas biológicas Interacções intramoleculares Ligações covalentes (manutenção da estrutura covalente das moléculas Interacções não-covalentes (conformções, folding, estrutura secundária)
Comunicado Técnico. Análise Preliminar de um Processo para Identificação e Alinhamento de Seqüências Homólogas para Proteínas com Estrutura Resolvida
 Comunicado Técnico Setembro, 48 2003 Campinas, SP ISSN 1677-8464 Análise Preliminar de um Processo para Identificação e Alinhamento de Seqüências Homólogas para Proteínas com Roberto Hiroshi Higa 1 Paula
Comunicado Técnico Setembro, 48 2003 Campinas, SP ISSN 1677-8464 Análise Preliminar de um Processo para Identificação e Alinhamento de Seqüências Homólogas para Proteínas com Roberto Hiroshi Higa 1 Paula
Comunicado Técnico ISSN
 Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Novembro, 23 2002 Campinas, SP ISSN 1677-8464 Modelagem Numérica de Algumas Variáveis de Clima do Estado de São Paulo Amarindo Fausto
Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Novembro, 23 2002 Campinas, SP ISSN 1677-8464 Modelagem Numérica de Algumas Variáveis de Clima do Estado de São Paulo Amarindo Fausto
Programa Analítico de Disciplina BQI460 Bioinformática
 0 Programa Analítico de Disciplina Departamento de Bioquímica e Biologia Molecular - Centro de Ciências Biológicas e da Saúde Número de créditos: Teóricas Práticas Total Duração em semanas: 15 Carga horária
0 Programa Analítico de Disciplina Departamento de Bioquímica e Biologia Molecular - Centro de Ciências Biológicas e da Saúde Número de créditos: Teóricas Práticas Total Duração em semanas: 15 Carga horária
Empresa Brasileira de Pesquisa Agropecuária. Embrapa Informática Agropecuária. Ministério da Agricultura, Pecuária e Abastecimento.
 ISSN 1677-9274 Dezembro, 2010 Empresa Brasileira de Pesquisa Agropecuária Embrapa Informática Agropecuária Ministério da Agricultura, Pecuária e Abastecimento Documentos 106 Eutils-search - Manual do usuário
ISSN 1677-9274 Dezembro, 2010 Empresa Brasileira de Pesquisa Agropecuária Embrapa Informática Agropecuária Ministério da Agricultura, Pecuária e Abastecimento Documentos 106 Eutils-search - Manual do usuário
ISSN 1677-8464. Goran Neshich
 Comunicado Técnico 59 Dezembro, 2003 Campinas, SP ISSN 1677-8464 Cálculo de Possíveis Contatos Atômicos Internos a uma Proteína ou entre Proteínas no Software SMS 1 Adauto Luiz Mancini 2 Roberto Hiroshi
Comunicado Técnico 59 Dezembro, 2003 Campinas, SP ISSN 1677-8464 Cálculo de Possíveis Contatos Atômicos Internos a uma Proteína ou entre Proteínas no Software SMS 1 Adauto Luiz Mancini 2 Roberto Hiroshi
FFI0750 Biologia Molecular Estrutural
 Objetivos FFI0750 Biologia Molecular Estrutural Visualização de estruturas de macromoléculas Representação de estruturas de macromoléculas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 02 Bacharelado
Objetivos FFI0750 Biologia Molecular Estrutural Visualização de estruturas de macromoléculas Representação de estruturas de macromoléculas Prof. Rafael V. C. Guido rvcguido@ifsc.usp.br Aula 02 Bacharelado
Química 2º Ano. Professora Cristina Lorenski Ferreira
 Química 2º Ano Professora Cristina Lorenski Ferreira 2016 1 GEOMETRIA MOLECULAR POLARIDADE DAS MOLÉCULAS INTERAÇÕES INTERMOLECULARES PROFESSORA CRISTINA LORENSKI FERREIRA 2 ALGUNS QUESTIONAMENTOS Como
Química 2º Ano Professora Cristina Lorenski Ferreira 2016 1 GEOMETRIA MOLECULAR POLARIDADE DAS MOLÉCULAS INTERAÇÕES INTERMOLECULARES PROFESSORA CRISTINA LORENSKI FERREIRA 2 ALGUNS QUESTIONAMENTOS Como
Comunicado Técnico ISSN
 Comunicado Técnico Dezembro, ISSN 1677-8464 10 2001 Campinas, SP Uso de Algoritmos Genéticos em Problemas de Localização Capacitada para Alocação de Recursos no Campo e na Cidade Luiz Antônio Nogueira
Comunicado Técnico Dezembro, ISSN 1677-8464 10 2001 Campinas, SP Uso de Algoritmos Genéticos em Problemas de Localização Capacitada para Alocação de Recursos no Campo e na Cidade Luiz Antônio Nogueira
As letras ASHLC correspondem a Actions, Show, Hide, Label e Color, respectivamente.
 Tutorial Visualização Gráfica com Pymol Profa. Rafaela Salgado Ferreira Departamento de Bioquímica e Imunologia - Universidade Federal de Minas Gerais Objetivos do tutorial: Preparação de uma figura, análise
Tutorial Visualização Gráfica com Pymol Profa. Rafaela Salgado Ferreira Departamento de Bioquímica e Imunologia - Universidade Federal de Minas Gerais Objetivos do tutorial: Preparação de uma figura, análise
ESCOLA SECUNDÁRIA PINHAL DO REI FICHA FORMATIVA 2ºTESTE
 Ano Letivo 2016/2017 ESCOLA SECUNDÁRIA PINHAL DO REI FICHA FORMATIVA 2ºTESTE Física e Química A 10ºAno 1. A energia dos eletrões nos átomos inclui: (A) apenas o efeito das atrações entre os eletrões e
Ano Letivo 2016/2017 ESCOLA SECUNDÁRIA PINHAL DO REI FICHA FORMATIVA 2ºTESTE Física e Química A 10ºAno 1. A energia dos eletrões nos átomos inclui: (A) apenas o efeito das atrações entre os eletrões e
Propriedades Físicas e Químicas dos Compostos Orgânicos
 Aumenta Propriedades das Moléculas Orgânicas Propriedades Físicas e Químicas dos Compostos Orgânicos A partir das ligações químicas que unem os átomos de suas moléculas, e das forças que agem entre elas
Aumenta Propriedades das Moléculas Orgânicas Propriedades Físicas e Químicas dos Compostos Orgânicos A partir das ligações químicas que unem os átomos de suas moléculas, e das forças que agem entre elas
Comunicado Técnico. Geração on-line de Mapas Agrometeorológicos
 Comunicado Técnico Setembro, 47 2003 Campinas, SP ISSN 1677-8464 Geração on-line de Mapas Agrometeorológicos Luciana Alvim Santos Romani 1 Silvio Roberto Medeiros Evangelista 2 Jurandir Zullo Júnior 3
Comunicado Técnico Setembro, 47 2003 Campinas, SP ISSN 1677-8464 Geração on-line de Mapas Agrometeorológicos Luciana Alvim Santos Romani 1 Silvio Roberto Medeiros Evangelista 2 Jurandir Zullo Júnior 3
INTRODUÇÃO Á BIOQUÍMICA
 INTRODUÇÃO Á BIOQUÍMICA BIOQUÍMICA ENFERMAGEM FIO Faculdades Integradas de Ourinhos. Prof. Esp. Roberto Venerando Fundação Educacional Miguel Mofarrej. FIO robertovenerando@fio.edu.br 1 - Introdução à
INTRODUÇÃO Á BIOQUÍMICA BIOQUÍMICA ENFERMAGEM FIO Faculdades Integradas de Ourinhos. Prof. Esp. Roberto Venerando Fundação Educacional Miguel Mofarrej. FIO robertovenerando@fio.edu.br 1 - Introdução à
CÁLCULO ESTRUTURAL DE PROTEÍNAS
 CÁLCULO ESTRUTURAL DE PROTEÍNAS Ana Maria Lemes de Lima (PIC) Unespar/Campus de Paranavaí, anamary_lemes@hotmail.com Valter Soares de Camargo (Orientador) Unespar/Campus de Paranavaí, vsc.unespar@gmail.com
CÁLCULO ESTRUTURAL DE PROTEÍNAS Ana Maria Lemes de Lima (PIC) Unespar/Campus de Paranavaí, anamary_lemes@hotmail.com Valter Soares de Camargo (Orientador) Unespar/Campus de Paranavaí, vsc.unespar@gmail.com
Estrutura Molecular, Ligações Químicas e Propriedades dos Compostos Orgânicos
 Universidade Federal de Campina Grande Centro de Ciências e Tecnologia Agroalimentar Profa. Roberlucia A. Candeia Disciplina: Química Orgânica Estrutura Molecular, Ligações Químicas e Propriedades dos
Universidade Federal de Campina Grande Centro de Ciências e Tecnologia Agroalimentar Profa. Roberlucia A. Candeia Disciplina: Química Orgânica Estrutura Molecular, Ligações Químicas e Propriedades dos
Dados Internacionais de Catalogação na Publicação - CIP Embrapa Informática Agropecuária
 Exemplares desta publicação podem ser adquiridos na: Embrapa Informática Agropecuária Av. André Tosello, 209, Caixa Postal 6041, Barão Geraldo - 13083-970 - Campinas, SP Telefone (19) 3211-5700 Fax (19)
Exemplares desta publicação podem ser adquiridos na: Embrapa Informática Agropecuária Av. André Tosello, 209, Caixa Postal 6041, Barão Geraldo - 13083-970 - Campinas, SP Telefone (19) 3211-5700 Fax (19)
Comunicado Técnico. Modelagem molecular da proteína small heat shock de Xylella fastidiosa
 Comunicado Técnico 6 Dezembro, 200 Campinas, SP ISSN 1677-86 Modelagem molecular da proteína small heat shock de Xylella fastidiosa Paula Regina Kuser Falcão¹ Susely Ferraz de Siqueira Tada² Anete Pereira
Comunicado Técnico 6 Dezembro, 200 Campinas, SP ISSN 1677-86 Modelagem molecular da proteína small heat shock de Xylella fastidiosa Paula Regina Kuser Falcão¹ Susely Ferraz de Siqueira Tada² Anete Pereira
Documentos. Organização e Armazenamento de Arquivos de Back up de Banco de Dados. Novembro, 2003 ISSN
 Documentos Novembro, 2003 33 ISSN 1677-9274 Organização e Armazenamento de Arquivos de Back up de Banco de Dados República Federativa do Brasil Luiz Inácio Lula da Silva Presidente Ministério da Agricultura,
Documentos Novembro, 2003 33 ISSN 1677-9274 Organização e Armazenamento de Arquivos de Back up de Banco de Dados República Federativa do Brasil Luiz Inácio Lula da Silva Presidente Ministério da Agricultura,
TÍTULO: ANÁLISE DA SEMELHANÇA ESTRUTURAL ENTRE PROTEÍNAS ATRAVÉS DE MÉTODOS MATEMÁTICOS
 Anais do Conic-Semesp. Volume 1, 2013 - Faculdade Anhanguera de Campinas - Unidade 3. ISSN 2357-8904 TÍTULO: ANÁLISE DA SEMELHANÇA ESTRUTURAL ENTRE PROTEÍNAS ATRAVÉS DE MÉTODOS MATEMÁTICOS CATEGORIA: CONCLUÍDO
Anais do Conic-Semesp. Volume 1, 2013 - Faculdade Anhanguera de Campinas - Unidade 3. ISSN 2357-8904 TÍTULO: ANÁLISE DA SEMELHANÇA ESTRUTURAL ENTRE PROTEÍNAS ATRAVÉS DE MÉTODOS MATEMÁTICOS CATEGORIA: CONCLUÍDO
Aula 05 Forças intermoleculares
 Universidade Tecnológica Federal do Paraná Departamento Acadêmico de Química e Biologia Aula 05 Dr. Tiago P. Camargo Forças entre moléculas Forças entre moléculas Como moléculas podem interagir entre elas
Universidade Tecnológica Federal do Paraná Departamento Acadêmico de Química e Biologia Aula 05 Dr. Tiago P. Camargo Forças entre moléculas Forças entre moléculas Como moléculas podem interagir entre elas
Química Orgânica I. Formas de representação de moléculas orgânicas e interações intermoleculares Aula 3
 Química rgânica I Formas de representação de moléculas orgânicas e interações intermoleculares Aula 3 Profa. Alceni Augusta Werle ProfaTânia Márcia Sacramento Melo 2- Formas de representação de moléculas
Química rgânica I Formas de representação de moléculas orgânicas e interações intermoleculares Aula 3 Profa. Alceni Augusta Werle ProfaTânia Márcia Sacramento Melo 2- Formas de representação de moléculas
Empresa Brasileira de Pesquisa Agropecuária. Embrapa Informática Agropecuária. Ministério da Agricultura, Pecuária e Abastecimento.
 ISSN 1677-9274 Dezembro, 2011 Empresa Brasileira de Pesquisa Agropecuária Embrapa Informática Agropecuária Ministério da Agricultura, Pecuária e Abastecimento Documentos 114 Sistema de Informação da Rede
ISSN 1677-9274 Dezembro, 2011 Empresa Brasileira de Pesquisa Agropecuária Embrapa Informática Agropecuária Ministério da Agricultura, Pecuária e Abastecimento Documentos 114 Sistema de Informação da Rede
Forças Intermoleculares
 Forças Intermoleculares Você já se perguntou por que a água forma gotas ou como os insetos conseguem caminhar sobre a água? Gota d'água caindo sobre a superfície da água. Inseto pousado sobre a superfície
Forças Intermoleculares Você já se perguntou por que a água forma gotas ou como os insetos conseguem caminhar sobre a água? Gota d'água caindo sobre a superfície da água. Inseto pousado sobre a superfície
ESCLEROSE LATERAL AMIOTRÓFICA ANÁLISES IN SILICO DAS MUTAÇÕES A4V E A4F DA PROTEÍNA SOD1
 ESCLEROSE LATERAL AMIOTRÓFICA ANÁLISES IN SILICO DAS MUTAÇÕES A4V E A4F DA PROTEÍNA SOD1 Aloma Nogueira Rebello da Silva Bióloga (UNIRIO) Programa de Pós-Graduação em Biologia Molecular e Celular aloma.nogueira@gmail.com
ESCLEROSE LATERAL AMIOTRÓFICA ANÁLISES IN SILICO DAS MUTAÇÕES A4V E A4F DA PROTEÍNA SOD1 Aloma Nogueira Rebello da Silva Bióloga (UNIRIO) Programa de Pós-Graduação em Biologia Molecular e Celular aloma.nogueira@gmail.com
Ressonância, Formas de respresentação de moléculas orgânicas, Forças intermoleculares. Aula 3
 Universidade Federal de uro Preto Ressonância, Formas de respresentação de moléculas orgânicas, Forças intermoleculares Aula 3 Flaviane Francisco ilário 1 1 Ressonância ESTRUTURA DE LEWIS Explica de maneira
Universidade Federal de uro Preto Ressonância, Formas de respresentação de moléculas orgânicas, Forças intermoleculares Aula 3 Flaviane Francisco ilário 1 1 Ressonância ESTRUTURA DE LEWIS Explica de maneira
Estrutura de Lewis, Formas de representação e Interações intermoleculares. Aula 2
 Universidade Federal de Ouro Preto Estrutura de Lewis, Formas de representação e Interações intermoleculares Aula 2 Flaviane Francisco ilário 1 1 Estrutura de Lewis Um símbolo de Lewis é um símbolo no
Universidade Federal de Ouro Preto Estrutura de Lewis, Formas de representação e Interações intermoleculares Aula 2 Flaviane Francisco ilário 1 1 Estrutura de Lewis Um símbolo de Lewis é um símbolo no
Funções Escores (MolDock Score) Prof. Dr. Walter F. de Azevedo Jr. ou
 205 Dr. Walter F. de zevedo Jr. Funções Escores (MolDock Score) Prof. Dr. Walter F. de zevedo Jr. walter.junior@pucrs.br ou walter.filgueira@hotmail.com Função MolDock Score função ajuste ou escore, usada
205 Dr. Walter F. de zevedo Jr. Funções Escores (MolDock Score) Prof. Dr. Walter F. de zevedo Jr. walter.junior@pucrs.br ou walter.filgueira@hotmail.com Função MolDock Score função ajuste ou escore, usada
Maxwell Severo da COSTA; Freddy Fernandes GUIMARÃES
 Comparação entre a aproximação Z+1 e o cálculo de buraco de camada real no estudo da dinâmica nuclear dos isômeros do dicloroetileno induzida pela foto-ionização dos elétrons da camada K do cloro (ClK)
Comparação entre a aproximação Z+1 e o cálculo de buraco de camada real no estudo da dinâmica nuclear dos isômeros do dicloroetileno induzida pela foto-ionização dos elétrons da camada K do cloro (ClK)
Determinação da Estrutura de Proteínas
 Centro Brasileiro-Argentino de Biotecnologia Introdução à Biologia Computacional Determinação da Estrutura de Proteínas Paulo enrique C. Godoi Bioinformática objetivo principal é determinar a função de
Centro Brasileiro-Argentino de Biotecnologia Introdução à Biologia Computacional Determinação da Estrutura de Proteínas Paulo enrique C. Godoi Bioinformática objetivo principal é determinar a função de
Documentos. Espacialização Tridimensional de Variáveis de Clima através do Surfer 8. Dezembro, 2003 ISSN
 Documentos Dezembro, 2003 34 ISSN 1677-9274 Espacialização Tridimensional de Variáveis de Clima através do Surfer 8 República Federativa do Brasil Luiz Inácio Lula da Silva Presidente Ministério da Agricultura,
Documentos Dezembro, 2003 34 ISSN 1677-9274 Espacialização Tridimensional de Variáveis de Clima através do Surfer 8 República Federativa do Brasil Luiz Inácio Lula da Silva Presidente Ministério da Agricultura,
Documentos. Manual de Instalação, Configuração e Desinstalação do Siger Versão Ministério da Agricultura, Pecuária e Abastecimento
 Ministério da Agricultura, Pecuária e Abastecimento Documentos Dezembro, 2002 23 ISSN 1677-9274 Manual de Instalação, Configuração e Desinstalação do Siger Versão 1.3.1 República Federativa do Brasil Fernando
Ministério da Agricultura, Pecuária e Abastecimento Documentos Dezembro, 2002 23 ISSN 1677-9274 Manual de Instalação, Configuração e Desinstalação do Siger Versão 1.3.1 República Federativa do Brasil Fernando
Comunicado Técnico ISSN
 Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 26 2002 Campinas, SP ISSN 1677-8464 Utilizando a Vermont para Automação de Testes Funcionais no SIGI João Francisco Gonçalves
Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 26 2002 Campinas, SP ISSN 1677-8464 Utilizando a Vermont para Automação de Testes Funcionais no SIGI João Francisco Gonçalves
Biologia Molecular (Parte I)
 Biologia Molecular (Parte I) Introdução 1. Substâncias Inorgânicas 1.1. Água A água faz pontes de hidrogênio Polaridade Propriedades da água Solvente Universal Participa de reações químicas vitais Adesão
Biologia Molecular (Parte I) Introdução 1. Substâncias Inorgânicas 1.1. Água A água faz pontes de hidrogênio Polaridade Propriedades da água Solvente Universal Participa de reações químicas vitais Adesão
Proteínas São macromoléculas complexas, compostas de aminoácidos, e necessárias para os processos químicos que ocorrem nos organismos vivos
 Proteínas São macromoléculas complexas, compostas de aminoácidos, e necessárias para os processos químicos que ocorrem nos organismos vivos São os constituintes básicos da vida: tanto que seu nome deriva
Proteínas São macromoléculas complexas, compostas de aminoácidos, e necessárias para os processos químicos que ocorrem nos organismos vivos São os constituintes básicos da vida: tanto que seu nome deriva
Tutorial Visualização Gráfica com Pymol
 Sobre o Pymol Tutorial Visualização Gráfica com Pymol Aula Prática 21/06/2018 PyMOL é um software de visualização molecular criado por Warren Lyford DeLano. É um programa open source, lançado sob a licença
Sobre o Pymol Tutorial Visualização Gráfica com Pymol Aula Prática 21/06/2018 PyMOL é um software de visualização molecular criado por Warren Lyford DeLano. É um programa open source, lançado sob a licença
Comunicado Técnico ISSN
 Comunicado Técnico Dezembro, 15 2001 Campinas, SP ISSN 1677-8464 Um Algoritmo para Geração de Caminhos em Grafos a Partir de um Vértice Adauto Luiz Mancini 1 Este trabalho apresenta um algoritmo para gerar
Comunicado Técnico Dezembro, 15 2001 Campinas, SP ISSN 1677-8464 Um Algoritmo para Geração de Caminhos em Grafos a Partir de um Vértice Adauto Luiz Mancini 1 Este trabalho apresenta um algoritmo para gerar
Forças intermoleculares. Formação de fases condensadas Forças íon-dipolo Forças dipolo-dipolo Forças de London Ligação de hidrogênio
 Forças intermoleculares Formação de fases condensadas Forças íon-dipolo Forças dipolo-dipolo Forças de London Ligação de hidrogênio Estado gasoso O estado da matéria mais simples é o gás. Descrevemos esse
Forças intermoleculares Formação de fases condensadas Forças íon-dipolo Forças dipolo-dipolo Forças de London Ligação de hidrogênio Estado gasoso O estado da matéria mais simples é o gás. Descrevemos esse
Aula 1. Referência. Bancos de Dados. Linguagem x Informação. Introdução a Bioquímica: Biomoléculas. Introdução ao Curso: Aminoácidos.
 Introdução a Bioquímica: Biomoléculas Aula 1 Introdução ao urso: Aminoácidos eferência Autores: Ignez aracelli e Julio Zukerman-Schpector Editora: EdUFSar Ignez aracelli BioMat DF UNESP/Bauru Julio Zukerman
Introdução a Bioquímica: Biomoléculas Aula 1 Introdução ao urso: Aminoácidos eferência Autores: Ignez aracelli e Julio Zukerman-Schpector Editora: EdUFSar Ignez aracelli BioMat DF UNESP/Bauru Julio Zukerman
As aventuras de Aram e Abaré na floresta
 Empresa Brasileira de Pesquisa Agropecuária Embrapa Informática Agropecuária Ministério da Agricultura, Pecuária e Abastecimento As aventuras de Aram e Abaré na floresta Luciana Alvim Santos Romani ilustrações
Empresa Brasileira de Pesquisa Agropecuária Embrapa Informática Agropecuária Ministério da Agricultura, Pecuária e Abastecimento As aventuras de Aram e Abaré na floresta Luciana Alvim Santos Romani ilustrações
Identificação de Padrões em Proteínas Utilizando a Ferramenta de Bioinformática CD- Search
 4ª Jornada Científica e Tecnológica e 1º Simpósio de Pós-Graduação do IFSULDEMINAS 16, 17 e 18 de outubro de 2012, Muzambinho MG Identificação de Padrões em Proteínas Utilizando a Ferramenta de Bioinformática
4ª Jornada Científica e Tecnológica e 1º Simpósio de Pós-Graduação do IFSULDEMINAS 16, 17 e 18 de outubro de 2012, Muzambinho MG Identificação de Padrões em Proteínas Utilizando a Ferramenta de Bioinformática
Soluções para Conjunto de Problemas 1
 Soluções para 7.012 Conjunto de Problemas 1 Pergunta 1 a) Quais são os quatro principais tipos de moléculas biológicas discutidas na palestra? Cite uma função importante para cada tipo de molécula biológica
Soluções para 7.012 Conjunto de Problemas 1 Pergunta 1 a) Quais são os quatro principais tipos de moléculas biológicas discutidas na palestra? Cite uma função importante para cada tipo de molécula biológica
Documentos. Primeiro Curso STING Millennium Suite Chemogenomics: Ferramentas para Analisar Macromoleculares e Aplicações em Chemogenomics
 Ministério da Agricultura, Pecuária e Abastecimento Documentos Dezembro, 2002 26 ISSN 1677-9274 Primeiro Curso STING Millennium Suite Chemogenomics: Ferramentas para Analisar Macromoleculares e Aplicações
Ministério da Agricultura, Pecuária e Abastecimento Documentos Dezembro, 2002 26 ISSN 1677-9274 Primeiro Curso STING Millennium Suite Chemogenomics: Ferramentas para Analisar Macromoleculares e Aplicações
Campus de Botucatu PLANO DE ENSINO
 PLANO DE ENSINO I - IDENTIFICAÇÃO CURSO: Física Médica MODALIDADE: Bacharelado DISCIPLINA: Biofísica Molecular (X) OBRIGATÓRIA ( ) OPTATIVA DEPARTAMENTO: Física e Biofísica DOCENTE RESPONSÁVEL: Prof. Dr.
PLANO DE ENSINO I - IDENTIFICAÇÃO CURSO: Física Médica MODALIDADE: Bacharelado DISCIPLINA: Biofísica Molecular (X) OBRIGATÓRIA ( ) OPTATIVA DEPARTAMENTO: Física e Biofísica DOCENTE RESPONSÁVEL: Prof. Dr.
Métodos de Química Computacional
 Universidade Federal de Ouro Preto Instituto de Ciências Exatas e Biológicas Departamento de Química Métodos de Química Computacional Professora: Melissa Soares Caetano Mecânica Molecular Mecânica Molecular
Universidade Federal de Ouro Preto Instituto de Ciências Exatas e Biológicas Departamento de Química Métodos de Química Computacional Professora: Melissa Soares Caetano Mecânica Molecular Mecânica Molecular
4. CARACTERIZAÇÃO TOPOLÓGICA DAS CONFIGURAÇÕES CSA
 4. CARACTERIZAÇÃO TOPOLÓGICA DAS 51.704 CONFIGURAÇÕES CSA As conformações protéicas mostram regularidades que são descritas por meio de diferentes níveis de padrões estruturais. Algumas delas são mais
4. CARACTERIZAÇÃO TOPOLÓGICA DAS 51.704 CONFIGURAÇÕES CSA As conformações protéicas mostram regularidades que são descritas por meio de diferentes níveis de padrões estruturais. Algumas delas são mais
Microscopia de Força Atômica (AFM)
 Microscopia de Força Atômica (AFM) Microscopia (AFM) Modelos AFM Center of Nanoscience, Nanotechnology and Innovation CeNano 2 I Microscopia (AFM) Figura.7.36a. Diagrama representativo de funcionamento
Microscopia de Força Atômica (AFM) Microscopia (AFM) Modelos AFM Center of Nanoscience, Nanotechnology and Innovation CeNano 2 I Microscopia (AFM) Figura.7.36a. Diagrama representativo de funcionamento
Comunicado Técnico ISSN
 Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Outubro, 18 2002 Campinas, SP ISSN 1677-8464 Análise da Produção Brasileira de Frutas a partir do Armazém de Dados da Fruticultura
Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Outubro, 18 2002 Campinas, SP ISSN 1677-8464 Análise da Produção Brasileira de Frutas a partir do Armazém de Dados da Fruticultura
Bioinformática Estrutural Aula 1
 Bioinformática Estrutural Aula 1 03 de Junho de 2013 Paula Kuser-Falcão Laboratório de Bioinformática Aplicada Embrapa Informática Agropecuária Paula.kuser-falcao@embrapa.br Pratique Atividade Física Paula
Bioinformática Estrutural Aula 1 03 de Junho de 2013 Paula Kuser-Falcão Laboratório de Bioinformática Aplicada Embrapa Informática Agropecuária Paula.kuser-falcao@embrapa.br Pratique Atividade Física Paula
Os efeitos do paralelismo e relações de thesaurus em uma ferramenta de busca em bases textuais
 72 Resumos Expandidos: XII Mostra de Estagiários e Bolsistas... Os efeitos do paralelismo e relações de thesaurus em uma ferramenta de busca em bases textuais Renan Gomes Pereira¹ Maria Fernanda Moura²
72 Resumos Expandidos: XII Mostra de Estagiários e Bolsistas... Os efeitos do paralelismo e relações de thesaurus em uma ferramenta de busca em bases textuais Renan Gomes Pereira¹ Maria Fernanda Moura²
Caracterização estrutural de proteínas por métricas de alta e baixa resolução
 6ª Jornada Científica e Tecnológica e 3º Simpósio de Pós-Graduação do IFSULDEMINAS 04 e 05 de novembro de 2014, Pouso Alegre/MG Caracterização estrutural de proteínas por métricas de alta e baixa resolução
6ª Jornada Científica e Tecnológica e 3º Simpósio de Pós-Graduação do IFSULDEMINAS 04 e 05 de novembro de 2014, Pouso Alegre/MG Caracterização estrutural de proteínas por métricas de alta e baixa resolução
Estrutura Molecular, Ligações Químicas e Propriedades dos Compostos Orgânicos
 Universidade Federal de Campina Grande Centro de Ciências e Tecnologia Agroalimentar Profa. Roberlucia A. Candeia Disciplina: Química Orgânica Estrutura Molecular, Ligações Químicas e Propriedades dos
Universidade Federal de Campina Grande Centro de Ciências e Tecnologia Agroalimentar Profa. Roberlucia A. Candeia Disciplina: Química Orgânica Estrutura Molecular, Ligações Químicas e Propriedades dos
Aminoácidos. Prof. Dr. Walter F. de Azevedo Jr. Laboratório de Sistemas BioMoleculares. Departamento de Física. UNESP São José do Rio Preto. SP.
 Aminoácidos Prof. Dr. Walter F. de Azevedo Jr. Laboratório de Sistemas BioMoleculares. Departamento de Física. UNESP São José do Rio Preto. SP. Resumo Introdução Quiralidade Ligação peptídica Cadeia peptídica
Aminoácidos Prof. Dr. Walter F. de Azevedo Jr. Laboratório de Sistemas BioMoleculares. Departamento de Física. UNESP São José do Rio Preto. SP. Resumo Introdução Quiralidade Ligação peptídica Cadeia peptídica
Empresa Brasileira de Pesquisa Agropecuária. Embrapa Informática Agropecuária. Ministério da Agricultura, Pecuária e Abastecimento.
 ISSN 1677-9274 Dezembro, 2010 Empresa Brasileira de Pesquisa Agropecuária Embrapa Informática Agropecuária Ministério da Agricultura, Pecuária e Abastecimento Documentos 107 Estrutura básica do MicroArray
ISSN 1677-9274 Dezembro, 2010 Empresa Brasileira de Pesquisa Agropecuária Embrapa Informática Agropecuária Ministério da Agricultura, Pecuária e Abastecimento Documentos 107 Estrutura básica do MicroArray
Bioquímica. Prof. Dr. Walter F. de Azevedo Jr Dr. Walter F. de Azevedo Jr.
 2018 Dr. Walter F. de Azevedo Jr. Bioquímica Prof. Dr. Walter F. de Azevedo Jr. E-mail: walter@azevedolab.net 1 As proteínas que tiveram sua estrutura tridimensional determinadas estão disponíveis no site
2018 Dr. Walter F. de Azevedo Jr. Bioquímica Prof. Dr. Walter F. de Azevedo Jr. E-mail: walter@azevedolab.net 1 As proteínas que tiveram sua estrutura tridimensional determinadas estão disponíveis no site
TITULO: Implementação do alinhamento de proteínas em GPU utilizando OpenCL PROPOSTA DE TRABALHO DE GRADUAÇÃO
 1 U NIVERSIDADE FEDERAL DE PERNAMBUCO GRADUAÇÃO EM ENGENHARIA DA COMPUTAÇÃO CENTRO DE INFORMÁTICA 2 0 1 6. 1 TITULO: Implementação do alinhamento de proteínas em GPU utilizando OpenCL PROPOSTA DE TRABALHO
1 U NIVERSIDADE FEDERAL DE PERNAMBUCO GRADUAÇÃO EM ENGENHARIA DA COMPUTAÇÃO CENTRO DE INFORMÁTICA 2 0 1 6. 1 TITULO: Implementação do alinhamento de proteínas em GPU utilizando OpenCL PROPOSTA DE TRABALHO
OBJETIVOS AULA 10 DESENVOLVIMENTO DESCOBERTA. ¾ Otimização de Moléculas Bioativas. ¾ Integração com o processo de HTS
 AULA 10 2 DESCOBERTA DESENVOLVIMENTO Pesquisa Básica (Pré-clínica) (Fases Clínicas I IV) Identificação do alvo molecular Triagens clínicas conduzidas em humanos: avaliação da segurança, impacto no estado
AULA 10 2 DESCOBERTA DESENVOLVIMENTO Pesquisa Básica (Pré-clínica) (Fases Clínicas I IV) Identificação do alvo molecular Triagens clínicas conduzidas em humanos: avaliação da segurança, impacto no estado
DESENVOLVIMENTO DE UM SOFTWARE DE GERAÇÃO E VISUALIZAÇÃO DE NANOESTRUTURAS
 DESENVOLVIMENTO DE UM SOFTWARE DE GERAÇÃO E VISUALIZAÇÃO DE NANOESTRUTURAS Aluno: Marcos Paulo Moraes Orientador: André Silva Pimentel Introdução A nanotecnologia está associada a diversas áreas de pesquisa
DESENVOLVIMENTO DE UM SOFTWARE DE GERAÇÃO E VISUALIZAÇÃO DE NANOESTRUTURAS Aluno: Marcos Paulo Moraes Orientador: André Silva Pimentel Introdução A nanotecnologia está associada a diversas áreas de pesquisa
Tipos de Dados Biológicos e Multimídia
 Tipos de Dados Biológicos e Multimídia Arthur Emanuel de O. Carosia Felipe Alves da Louza Luana Peixoto Annibal 1 Dados Biológicos São dados ou medidas coletadas a partir de fontes biológicas São geralmente
Tipos de Dados Biológicos e Multimídia Arthur Emanuel de O. Carosia Felipe Alves da Louza Luana Peixoto Annibal 1 Dados Biológicos São dados ou medidas coletadas a partir de fontes biológicas São geralmente
FFI0750 BIOLOGIA MOLECULAR ESTRUTURAL
 AULA PRÁTICA 1 VISUALIZAÇÃO E REPRESENTAÇÃO MOLECULAR Os programas disponíveis para representação molecular variam em função da finalidade desejada. Por exemplo, as ferramentas necessárias para estudos
AULA PRÁTICA 1 VISUALIZAÇÃO E REPRESENTAÇÃO MOLECULAR Os programas disponíveis para representação molecular variam em função da finalidade desejada. Por exemplo, as ferramentas necessárias para estudos
Comunicado Técnico ISSN 1677-8464
 Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 25 2002 Campinas, SP ISSN 1677-8464 Cobertura de Testes Unitários no SIGI João Francisco Gonçalves Antunes 1 Moacir Pedroso
Ministério da Agricultura, Pecuária e Abastecimento Comunicado Técnico Dezembro, 25 2002 Campinas, SP ISSN 1677-8464 Cobertura de Testes Unitários no SIGI João Francisco Gonçalves Antunes 1 Moacir Pedroso
PMT-3131 Química dos Materiais Aplicada à Engenharia Elétrica. TURMA 3 AULA 1 Augusto Neiva
 PMT-3131 Química dos Materiais Aplicada à Engenharia Elétrica TURMA 3 AULA 1 Augusto Neiva APOSTILA 2017 PARTE 1 - LIGAÇÕES QUÍMICAS PMT-3131 Química dos Materiais Aplicada à Engenharia Elétrica PQI-3110
PMT-3131 Química dos Materiais Aplicada à Engenharia Elétrica TURMA 3 AULA 1 Augusto Neiva APOSTILA 2017 PARTE 1 - LIGAÇÕES QUÍMICAS PMT-3131 Química dos Materiais Aplicada à Engenharia Elétrica PQI-3110
AULA 5 Adsorção, isotermas e filmes monomoleculares. Prof a Elenice Schons
 AULA 5 Adsorção, isotermas e filmes monomoleculares Prof a Elenice Schons ADSORÇÃO É um processo de acumulação e concentração seletiva de um ou mais constituintes contidos num gás ou líquido sobre superfícies
AULA 5 Adsorção, isotermas e filmes monomoleculares Prof a Elenice Schons ADSORÇÃO É um processo de acumulação e concentração seletiva de um ou mais constituintes contidos num gás ou líquido sobre superfícies
AULA 7. Cálculo das energias de interação estereoquímicas e eletrostáticas entre as moléculas do conjunto de
 Análise Comparativa dos Campos Moleculares AULA 7 Análise Comparativa dos Campos Moleculares A contribuição devido às forças de dispersão entre moléculas é descrita pelo potencial de Lennard-Jones e as
Análise Comparativa dos Campos Moleculares AULA 7 Análise Comparativa dos Campos Moleculares A contribuição devido às forças de dispersão entre moléculas é descrita pelo potencial de Lennard-Jones e as
Empresa Brasileira de Pesquisa Agropecuária Embrapa Agroenergia Ministério da Agricultura, Pecuária e Abastecimento Análise Química da Biomassa
 Empresa Brasileira de Pesquisa Agropecuária Embrapa Agroenergia Ministério da Agricultura, Pecuária e Abastecimento Análise Química da Biomassa Sílvio Vaz Júnior Embrapa Brasília, DF 2015 Exemplares desta
Empresa Brasileira de Pesquisa Agropecuária Embrapa Agroenergia Ministério da Agricultura, Pecuária e Abastecimento Análise Química da Biomassa Sílvio Vaz Júnior Embrapa Brasília, DF 2015 Exemplares desta
Simulação da dinâmica de íons em canais transmembranares. Franco Valduga de Almeida Camargo Yan Levin Alexandre Diehl
 Simulação da dinâmica de íons em canais transmembranares Franco Valduga de Almeida Camargo Yan Levin Alexandre Diehl O que são canais iônicos? São proteínas, encontradas na membrana de praticamente todas
Simulação da dinâmica de íons em canais transmembranares Franco Valduga de Almeida Camargo Yan Levin Alexandre Diehl O que são canais iônicos? São proteínas, encontradas na membrana de praticamente todas
Introdução à Bioinformática e Aplicações
 Laboratório de Bioinformática, Modelagem e Simulação de Bi Introdução à Bioinformática e Aplicações Osmar Norberto de Souza osmar.norberto@pucrs.br Porto Alegre, Células Tecidos Tecidos Órgãos Sistemas
Laboratório de Bioinformática, Modelagem e Simulação de Bi Introdução à Bioinformática e Aplicações Osmar Norberto de Souza osmar.norberto@pucrs.br Porto Alegre, Células Tecidos Tecidos Órgãos Sistemas
Ressonância Magnética Nuclear
 Ressonância Magnética Nuclear Bibliografia: Pavia, D.L. et al., Introdução à Espectroscopia, Ed. Cengage Learning, 2010. Bruice, P.Y. et al., Química Orgânica, Ed. Prendice Hall, 2004. Raios-X são as radiações
Ressonância Magnética Nuclear Bibliografia: Pavia, D.L. et al., Introdução à Espectroscopia, Ed. Cengage Learning, 2010. Bruice, P.Y. et al., Química Orgânica, Ed. Prendice Hall, 2004. Raios-X são as radiações
Ácidos nucleicos (DNA e RNA) e os genes
 Disciplina: Biologia Humana Profa. Me. Vivian C. Langiano Ácidos nucleicos (DNA e RNA) e os genes De Robertis, E. Bases da Biologia Celular e Molecular. Rio de Janeiro, Guanabara Koogan, 4 ed. 2006. cap
Disciplina: Biologia Humana Profa. Me. Vivian C. Langiano Ácidos nucleicos (DNA e RNA) e os genes De Robertis, E. Bases da Biologia Celular e Molecular. Rio de Janeiro, Guanabara Koogan, 4 ed. 2006. cap
2015 Dr. Walter F. de Azevedo Jr.
 2015 Dr. Walter F. de Azevedo Jr. 000000000000000000000000000000000000000 000000000000000000000000000000000000000 000000000000111111111110001100000000000 000000000001111111111111111111000000001 000000000111111111111111111111111000000
2015 Dr. Walter F. de Azevedo Jr. 000000000000000000000000000000000000000 000000000000000000000000000000000000000 000000000000111111111110001100000000000 000000000001111111111111111111000000001 000000000111111111111111111111111000000
QUÍMICA ORGÂNICA I. INTRODUÇÃO À QUÍMICA ORGÂNICA (Parte II)
 QUÍMICA RGÂNICA I INTRDUÇÃ À QUÍMICA RGÂNICA (Parte II) CURS FARMÁCIA SEMESTRE 2016/2 Professoras: Alceni Augusta Werle Tânia Márcia Sacramento Melo 1 1 Ressonância ESTRUTURA DE LEWIS Explica de maneira
QUÍMICA RGÂNICA I INTRDUÇÃ À QUÍMICA RGÂNICA (Parte II) CURS FARMÁCIA SEMESTRE 2016/2 Professoras: Alceni Augusta Werle Tânia Márcia Sacramento Melo 1 1 Ressonância ESTRUTURA DE LEWIS Explica de maneira
ESCOLA SECUNDÁRIA PINHAL DO REI FICHA FORMATIVA 2ºTESTE
 Ano Letivo 2016/2017 ESOLA SEUNDÁRIA PINAL DO REI FIA FORMATIVA 2ºTESTE Física e Química A 10ºAno 1. A energia dos eletrões nos átomos inclui: (A) apenas o efeito das atrações entre os eletrões e o núcleo.
Ano Letivo 2016/2017 ESOLA SEUNDÁRIA PINAL DO REI FIA FORMATIVA 2ºTESTE Física e Química A 10ºAno 1. A energia dos eletrões nos átomos inclui: (A) apenas o efeito das atrações entre os eletrões e o núcleo.
