4. MATERIAL E MÉTODOS
|
|
|
- Rachel Santiago Coradelli
- 8 Há anos
- Visualizações:
Transcrição
1 25 4. MATERIAL E MÉTODOS Material Foram utilizados 128 blocos contendo fragmentos de pele de 128 pacientes com diagnóstico de hanseníase, arquivados no Laboratório do Serviço de Anatomia Patológica da Universidade Federal Fluminense - RJ, no período de 1993 a Os cortes histológicos foram previamente analisados pelas técnicas de coloração de HE e Wade (Michalany, 1940). (Anexo página 78). O material para o estudo foi composto de quatro grupos: Grupo de estudo PB. Dos 128 casos, 73 eram da forma PB classificados em 13 casos de HI, 18 de HT e 42 de HDT. Grupo de estudo MB. Entre os 128 casos estudados, 55 foram da forma MB, e classificados em 5 HDT, 2 HDD, 15 HDV e 33 HV. Controle negativo (CN) e controle positivo (CP). Esses controles foram obtidos de fragmento de pele de pacientes do Hospital Escola da Faculdade de Medicina de Valença - RJ. Como controle positivo, utilizou-se fragmento de pele de paciente com diagnóstico de HV. Como controles negativos utilizou-se pele normal, obtida de cirurgia plástica. DNA genômico(dna-h) Como controle de possíveis inibidores foi utilizado o DNA genômico humano extraído de leucócitos de sangue periférico. Este material foi cedido pelo Laboratório de Biologia Molecular (Biomol) - SP.
2 26 Em todas as reações, utilizou-se o controle de reagentes (CR), contendo todos os componentes exceto o DNA a ser amplificado Métodos O processamento do CP, CN e a microtomia dos materiais para a PCR foram realizados no Laboratório de Anatomia Patológica do Hospital Escola da Faculdade de Medicina de Valença, RJ. A extração do DNA, a PCR e a documentação fotográfica foram realizadas no Laboratório de Biologia Molecular Aplicada ao Diagnóstico, da Faculdade de Ciências Farmacêuticas da Universidade de São Paulo (SP). Considerando-se que os materiais utilizados já estavam emblocados em parafina, foi necessário adequar a metodologia para a PCR. Inicialmente, procurouse padronizar uma técnica de otimização capaz de fornecer resultados fidedignos, mesmo utilizando material com possibilidade de conter baixa qualidade e quantidade de DNA do M. leprae, contaminação de DNA exógeno ou mesmo presença de inibidores para a PCR. A otimização foi realizada desde a coleta das amostras para os controles. As amostras foram preparadas em local isolado de outras atividades. Procurou-se manter a área a ser biopsiada e o local de sua realização isento de qualquer componente genético estranho como parasitas ou substâncias estranhas ás amostras. O instrumental utilizado no ato da biópsia foi novo e estéril, quando impossível, o instrumental foi submerso em água oxigenada a 20 volumes, lavado com água Milli Q. e autoclavado. O material foi fixado, desidratado, diafanizado, submetido a banhos de parafina, separadamente entre si e as soluções não foram reaproveitadas Preparo dos controles para emblocamento em parafina O material foi preparado para emblocamento em parafina após centrifugação, semelhante ao que se faz como "cell block" (Takahashi, 1971), para precipitar o material no fundo do tubo de ensaio. Após solidificação fragmentou-se o tubo para liberar o material sem o contato manual, procurando assim, diminuir o unto quanto possível a contaminação exógena.
3 Utilizou-se 10 vezes mais o volume do liquido em relação ao volume do material nos procedimentos de fixação, desidratação, diafanização e no banho de parafina. 2 - Centrifugou-se a rpm durante 1 minuto. 3 - Fixou-se o material em formol tamponado a 10% (BNF) durante 12 a 24 horas, em temperatura ambiente (TA). 4 - Desidratou-se com etanol em concentrações crescentes de 80%, 90% e 95% e mais duas vezes em etanol PA, durante 60 minutos em cada procedimento, em TA e desprezou-se o líquido por inversão. 5 - Diafanizou-se por três vezes em banhos de xilol PA durante 60 minutos em cada banho, em TA e desprezou-se o líquido por inversão. 6 - Impregnou-se o material em três banhos de parafina líquida a 57 C, durante 60 minutos cada banho. Solidificou-se no terceiro banho. Fragmentou-se o tubo para liberar o material emblocado Preparo dos materiais e dos controles (CP e CN) para a PCR A partir deste momento o protocolo de Cook et al. (1994), (Anexo Página 86), com várias modificações, começa a ser utilizado. 1 - Obteve-se cortes histológicos com 10 µm de espessura. Colocou-se cinco fragmentos em cada tubo de Eppendorf de 1,5mL. 2 - Desparafinou-se com 1,0 ml de xilol PA a 95 C, agitou-se leve e - periodicamente durante 10 minutos. Centrifugou-se a rpm durante 5 minutos e desprezou-se o solvente por inversão. 3 - Adicionou-se 1,0 ml de xilol PA a 57 C, agitou-se leve e periodicamente durante 10 minutos. Centrifugou-se a rpm durante 5 minutos e desprezou-se o solvente por inversão. Repetiu- se, esta operação, uma vez. 4 - Removeu-se o solvente com 1,0 ml de álcool PA, agitou-se leve e periodicamente durante 5 minutos. Centrifugou-se durante 5 minutos. Desprezou-se o álcool por inversão. Repetiu-se por duas vezes. 5 - Evaporou-se o álcool residual deixando a tampa do tubo aberta protegida com gaze, em TA.
4 Aplicou-se o choque térmico, aquecendo em banho de água a 98 C, durante 5 minutos e, logo a seguir, submergiu-se em nitrogênio líquido durante 1 minuto. Repetiu-se por mais uma vez. 7 - Procedeu-se a digestão do material com 20µL (400µg/mL) de PK e solução tampão com 480 µl de "BD9", na proporção de 1:24, incubou-se aquecendo em banho de água a 37 C durante 12 horas. Inativou-se a PK em banho de água a 98 C durante 10 minutos e submergiu-se imediatamente em nitrogênio líquido durante 1 minuto. Deixou-se o material repousando durante 20 minutos, em banho de gelo a 4 C. 8 - Extraiu e purificou-se o DNA com 1,0 ml da mistura de fenol:clorofórmio: álcool isoamílico na proporção de 25:24:1; agitou-se em vórtex durante 15 segundos. Centrifugou-se a rpm durante 15 minutos. Repetiuse por mais uma vez. 9 - Adicionou-se 1.0 ml da solução de clorofórmio:álcool isoamílico na proporção de 24:1, agitou-se em vórtex durante 15 segundos. Centrifugou-se a rpm durante 15 minutos e o sobrenadante foi tranferido para outro tubo de Eppendorf Adicionou-se 1.0 ml da solução contendo acetato de amónia a 8 M e isopropanol PA, ambos a -20 C e glicogênio 20 µl a 4 C na proporção de 24:75:1. Homogeinizou-se por inversão várias vezes. Incubou-se a 20 C durante 12 horas. Centrifugou-se a rpm durante 20 minutos, desprezou-se o líquido com pipeta, lavou-se com 1,0 ml de isopropanol a 70% e a -20 C. Repetiu-se a centrifugação e desprezouse o líquido cuidadosamente com pipeta O tubo permaneceu aberto em câmara asséptica protegido com papel até a evaporação total da solução Ressuspendeu-se o DNA em 50 µl de TE e incubou-se a 57 C durante 60 minutos.
5 Quantificação dos ácidos nucléicos Quantificou-se o DNA em espectrofotômetro medindo-se a absorvência da amostra a 260 e 280nm. Considerou-se a relação absortividade molar segundo Sanbrook et al., 1989 (1 DO = 50µml) Teste de inibidores dos controles. Testou-se a presença de possíveis inibidores no DNA do CP e CN, pela amplificação da β-actina humana. A tabela 1 demonstra esquematicamente as etapas realizadas. 1 - Adicionou-se 5,0µL de DNA dos controles e 511L de DNA-H em 40µL de MIX1 (tampão PCR 1X; 1,5 mm de MgCl 2 : 200 mm de cada dntps; 2,0 U de Taq. DNA polimerase; 10 pm de β -actina 1; 10 pm de β -actina 2, e H 2 0 Milli Q. q.s.p. 50µL); 2 - Programou-se o termociclador PTC1 (1 ciclo de 4 minutos a 94 C; seguido de 40 ciclos: cada ciclo de 94 C, 1 minuto; 57 C, 1 minuto e 72 C, 1 minuto e um ciclo de 72 C durante 10 minutos e finalizar com esfriamento de 4 C); 3 - Utilizou-se PGA1,5 (dissolveu-se 1,5% de gel de agarose em TBE 1X, adicionou-se brometo de etídio a 0.3% mg/ml; solidificou-se em cuba de eletroforese em TA, submergiu-se em TBE 1X; utilizou-se 0,5µL de marcador de peso molecular de 100 pb; 2,0 µl de tampão de corrida; 8,0 µl do DNA. Ligou-se a fonte de eletroforese a 110V e 60mA, durante 40,0 minutos. Visualizou-se em UV e documentou-se em câmera Polaroid modelo DS34, com filme 667 de 3000 ASA).
6 PCR para amplificação do gênero Mycobacterium. Os materiais foram submetidos a PCR em duas etapas. Primeira etapa da PCR Conforme demonstrado na tabela 2, adicionou-se 10 µl de DNA das amostras em 40 µl de MIX2 (tampão PCR 1X; 1,5 mm de MgC1 2 ; 200 mm de cada dntps; 2,5 U de Taq. DNA polimerase; 380 nm de cada iniciador T 1 U; T 2 U 2 ; T 1 D) H 2 0 Milli Q. q.s.p. 50 µl e programou-se o termociclador PTC2 (40 ciclos a 94 C durante 1 minuto; 57 C durante 2 minutos; 72 C durante 2 minutos. Extensão final de 72 C durante 10 minutos e esfriamento a 4 C). Segunda etapa da PCR "Nested-PCR" Conforme demonstrado na tabela 3, adicionou-se 5.0 µl do produto da primeira etapa da PCR em 45 µl de MIX3 (tampão PCR 1X; 1,5 mm de MgCl2; 200 mm de cada dntps; 2,5 U de Taq. DNA polimerase; 380 nm de cada iniciador T2U; T2D) H20 Milli Q. q.s.p. 50 µl. Programou-se o termociclador PTC2 conforme a primeira etapa. Digestão pela endonuclease de restrição Alu1 para a espécie leprae. Após a segunda etapa da PCR, as amostras foram submetidas a digestão pela Alu1, especifica para espécie leprae demonstrado na Tabela 4. Adicionou-se 104 de MIX4 (enzima de restrição Alui, 0,5 µl de tampão digestão) H20 Milli Q. q.s.p. 10µL e 10 µl do DNA do produto da segunda etapa da PCR. Incubou-se em banho de água a 37 C, durante quatro horas e preparou-se PGA-2 (2% de gel
7 31 de agarose dissolvido em TBE 1X, adicionou-se em brometo de etídio a 0,3% mg/ml; solidificou-se em cuba de eletroforese em TA, submergiu-se em TBE 1X; adicionou-se 0,5 µl de marcador de peso molecular de 100 pb; 2,0 µl de tampão de corrida; 8,0 µl do DNA. Ligou-se a fonte de eletroforese a 110V e 60mA, durante 40,0 minutos. Visualizou-se em UV e documentou-se em câmera Polaroid modelo DS34, com filme 667 de 3000 ASA). Tabela 4: Digestão pela endonuclease de restrição Alu1 para M. leprae. Volume final 20 µl Teste de sensibilidade Testou-se a sensibilidade do DNA dos controles e de 10 amostras com PCR positiva de PB, (1 a 4) e seis amostras de MB, (5 a10) e em seis materiais MB com PCR negativa (1 a 6), escolhidas aleatoriamente, com diluições sucessivas de 1/10, 1/100 e 1/1000 com água Milli Q. estéril. Primeira etapa da PCR 1 - adicionou-se 10µL de DNA em 40,0 µl de MIX2; 2 - programou-se o termociclador PTC2 conforme procedimento anterior. Tabela 5.
8 32 Segunda etapa da PCR 1 - adicionou-se 5,0µL do produto da primeira etapa da PCR em 45,01.L de MIX3; 2 - programou-se o termociclador PTC2 conforme procedimento anterior. Tabela 6: Segunda etapa da PCR no teste de sensibilidade nas amostras com PCR positiva nas forma PB e MB. Amostras 1 a 4 PB e 5 a 10 MB. Volume final 50.0 µl. Digestão pela endonuclease de restrição Alu1 1 - adicionou-se 10,0 µl do produto da segunda etapa da PCR em 10,0µL de MIX4; 2 - incubou-se a 37 C em banho de água durante quatro horas; 3 - Preparou-se PGA2, conforme prodecimento anterior. Tabela 7 Tabela 7: Digestão pela endonuclease de restrição Alui nas amostras PCR positiva: amostras (1 a 4) PB (5 a 10) MB. Volume final 20,0 µl
9 33 Teste dos controles e das amostras com PCR negativa. Testou-se a sensibilidade de seis amostras de MB com PCR negativa. Primeira etapa da PCR 1 - adicionou-se 10,0 µl de DNA em 40,0 µl de MIX2; 2 - programou-se o termociclador PTC2, conforme procedimento anterior. Tabela 8. Tabela 8: Primeira etapa da PCR no teste de sensibilidade nas amostras com PCR negativa nas forma MB. Volume final 50.0uL. Segunda etapa da PCR. 1 - adicionou-se 5,0 µl do produto da primeira etapa da PCR em 45,0 µl de MIX3; 2 - programou-se termociclador PTC2, conforme procedimento anterior. Tabela 9. Tabela 9: Segunda etapa da PCR no teste de sensibilidade nas amostras com PCR negativa em MB. Volume final 50.0 µl
10 34 Digestão pela endonuclease de restrição Alu adicionou-se 10 µl do produto da segunda etapa da PCR em 10,0 µl de MIX4; 2 - incubou-se em banho de água a 37 C, durante 4 horas; 3 - utilizouse PGA2, conforme procedimento anterior. Tabela 10. Tabela 10: Digestão pela endonuclease de restrição no teste de sensibilidade nas amostras com PCR negativa em MB. Volume final 20.0 µl Teste de inibidores Realizou-se o teste de inibidores de seis amostras com PCR positiva das formas PB (1 a 3) e de MB (4 a 6), escolhidas aleatoriamente. Tabela adicionou-se 5,0 µl de DNA do bacilo e 5,0 µl de DNA-H em 40,0 µl de MIX1; 2- programou-se o termociclador PTC1; 3 - utilizou-se PGA 1.5 (Pág. 95). Tabela 11. Tabela 11: Teste de inibidores nas amostras com PCR positiva. Amostras (1 a 3) PB e (4 a 6) MR Volume final: 50,0 µl Da mesma forma, realizou-se o teste de inibidores em seis amostras de MB com PCR negativa (1 a 6), escolhidas aleatoriamente. 1 - adicionou-se 5,0 µl de DNA e 5,0 µl de DNA-H em 40,0 µl de MIX1; 2- programou-se o termociclador PTC1; 3 - utilizou-se PGA 1,5, conforme procedimentos anteriores. Tabela 4.
11 35 Tabela 12: Teste de inibidores das amostras MB com PCR negativa.volume final: 50,0 µl Análise estatística Utilizou-se o método do x 2 para a avaliação da frequência de casos com resultado de PCR positivo e negativo, considerado significativo ao nível de P< 0,05.
Estudo de um Polimorfismo no Gene da Cadeia Pesada β da Miosina (CPβM)
 Estudo de um Polimorfismo no Gene da Cadeia Pesada β da Miosina (CPβM) Ana Luísa Carvalho Departamento de Zoologia, Universidade de Coimbra Introdução: Neste trabalho pretende-se analisar um polimorfismo
Estudo de um Polimorfismo no Gene da Cadeia Pesada β da Miosina (CPβM) Ana Luísa Carvalho Departamento de Zoologia, Universidade de Coimbra Introdução: Neste trabalho pretende-se analisar um polimorfismo
Gráfico 1: Frequência das formas clínico-histopatológicas da hanseníase, representada em porcentagem de casos.
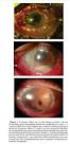 37 5-RESULTADOS Do total de 128 amostras estudadas, obtidos de 128 pacientes, 66 casos (51,56%) foram do sexo masculino e 62 casos (48,48%) do sexo feminino. A idade dos pacientes variou de 03 anos a 88
37 5-RESULTADOS Do total de 128 amostras estudadas, obtidos de 128 pacientes, 66 casos (51,56%) foram do sexo masculino e 62 casos (48,48%) do sexo feminino. A idade dos pacientes variou de 03 anos a 88
Declaração de Conflito de Interesse. Adriana da Silva Santos Duarte Sem conflitos de interesse a declarar
 Declaração de Conflito de Interesse Adriana da Silva Santos Duarte Sem conflitos de interesse a declarar Banco de DNA, RNA e Células Como Arquivar Adriana da Silva Santos Duarte Bióloga- Hemocentro/Unicamp
Declaração de Conflito de Interesse Adriana da Silva Santos Duarte Sem conflitos de interesse a declarar Banco de DNA, RNA e Células Como Arquivar Adriana da Silva Santos Duarte Bióloga- Hemocentro/Unicamp
Apostila de aula prática REAÇÃO EM CADEIA PELA POLIMERASE (PCR)
 1 Universidade Federal Fluminense Instituto Biomédico Departamento de Microbiologia e Parasitologia Curso: Medicina Veterinária Disciplina: Virologia III (MIP00071) Apostila de aula prática REAÇÃO EM CADEIA
1 Universidade Federal Fluminense Instituto Biomédico Departamento de Microbiologia e Parasitologia Curso: Medicina Veterinária Disciplina: Virologia III (MIP00071) Apostila de aula prática REAÇÃO EM CADEIA
Extracção de ADN de mancha de sangue por Chelex 100. Protocolo experimental:
 Extracção de ADN de mancha de sangue por Chelex 100 1. Num tubo eppendorf misturar 1ml de água desionizada estéril com uma mancha de sangue com aproximadamente 3mm²; 2. Incubar à temperatura ambiente no
Extracção de ADN de mancha de sangue por Chelex 100 1. Num tubo eppendorf misturar 1ml de água desionizada estéril com uma mancha de sangue com aproximadamente 3mm²; 2. Incubar à temperatura ambiente no
Para 1L de meio triptona ou peptona 16g (1,6%) extrato de levedura 10g (1%) NaCl 5g (0,5%)
 Preparação de meio líquido - triptona ou peptona - extrato de levedura 1º Dissolver a triptona e o extrato; 2º Acrescentar o cloreto de sódio e acertar o volume; 3º Após tudo dissolvido e com volume correto,
Preparação de meio líquido - triptona ou peptona - extrato de levedura 1º Dissolver a triptona e o extrato; 2º Acrescentar o cloreto de sódio e acertar o volume; 3º Após tudo dissolvido e com volume correto,
Comparação entre Protocolos de Extração de DNA de Algodão para Emprego em Ensaios com Marcadores Moleculares
 ISSN 000-6460 Comparação entre Protocolos de Extração de DNA de Algodão para Emprego em Ensaios com Marcadores Moleculares 74 Circular Técnica Novembro, 2003 O isolamento de DNA de plantas, sejam elas
ISSN 000-6460 Comparação entre Protocolos de Extração de DNA de Algodão para Emprego em Ensaios com Marcadores Moleculares 74 Circular Técnica Novembro, 2003 O isolamento de DNA de plantas, sejam elas
4 O anticoagulante mais utilizado na coleta de sangue para a extração de DNA é:
 CONCURSO PARA VAGA DE TÉCNICO DE LABORATÓRIO PROVA ESPECÍFICA 1ª FASE NOME: RG: DATA: 1 A extração de DNA é possível na seguinte condição: 2 - Um rastro fragmentado de DNA em gel de agarose indica: 3 A
CONCURSO PARA VAGA DE TÉCNICO DE LABORATÓRIO PROVA ESPECÍFICA 1ª FASE NOME: RG: DATA: 1 A extração de DNA é possível na seguinte condição: 2 - Um rastro fragmentado de DNA em gel de agarose indica: 3 A
Departamento de Anatomia Patológica Laboratório de Multiusuário em Pesquisa UNIFESP
 VANTAGENS DO USO DA AGAROSE NAS TÉCNICAS DE PROCESSAMENTO DE CELL BLOCK NA CITOLOGIA ONCÓTICA DE LÍQUIDOS Joaquim Soares de Almeida. Departamento de Anatomia Patológica Laboratório de Multiusuário em Pesquisa
VANTAGENS DO USO DA AGAROSE NAS TÉCNICAS DE PROCESSAMENTO DE CELL BLOCK NA CITOLOGIA ONCÓTICA DE LÍQUIDOS Joaquim Soares de Almeida. Departamento de Anatomia Patológica Laboratório de Multiusuário em Pesquisa
EXTRAÇÃO DE DNA DE SANGUE (LEUCÓCITOS)
 EXTRAÇÃO DE DNA DE SANGUE (LEUCÓCITOS) A) Obtenção de Leucócitos 1. Coletar 5mL de sangue em tubos contendo EDTA potássio (50uL de EDTA (k 3) a 15%). O EDTA é uma substância anticoagulante. Existem outras
EXTRAÇÃO DE DNA DE SANGUE (LEUCÓCITOS) A) Obtenção de Leucócitos 1. Coletar 5mL de sangue em tubos contendo EDTA potássio (50uL de EDTA (k 3) a 15%). O EDTA é uma substância anticoagulante. Existem outras
PCR Prof. Dr. Fábio Gregori
 PCR Prof. Dr. Fábio Gregori Laboratório de Biologia Molecular Aplicada e Sorologia VPS-FMVZ-USP 1 Reação em Cadeia pela Polimerase Amplificação in vitro de DNA BANDA DNA (amplificado) DNA Agente infeccioso
PCR Prof. Dr. Fábio Gregori Laboratório de Biologia Molecular Aplicada e Sorologia VPS-FMVZ-USP 1 Reação em Cadeia pela Polimerase Amplificação in vitro de DNA BANDA DNA (amplificado) DNA Agente infeccioso
Protocolo de extração de DNA de tecido vegetal: (Doyle & Doyle, 1987)
 Protocolo de extração de DNA de tecido vegetal: (Doyle & Doyle, 1987) PROCEDIMENTOS 1. Preparo do Material» Primeiro verifique se todas as soluções estão preparadas;» Ligue o banho-maria a 65ºC;» Prepare
Protocolo de extração de DNA de tecido vegetal: (Doyle & Doyle, 1987) PROCEDIMENTOS 1. Preparo do Material» Primeiro verifique se todas as soluções estão preparadas;» Ligue o banho-maria a 65ºC;» Prepare
Identificação de sementes de soja geneticamente modificadas utilizando a técnica de PCR convencional
 Identificação de sementes de soja geneticamente modificadas utilizando a técnica de PCR convencional HONNA,P.T. 1 ; GIROTTO, L. 2 ; SOLDERA, M.C.A. 2 ; KANAMORI, N. 3 ;MARCELINO-GUIMARAES, F. C. 4 ; YAMAGUCHI-SHINOZAKI,
Identificação de sementes de soja geneticamente modificadas utilizando a técnica de PCR convencional HONNA,P.T. 1 ; GIROTTO, L. 2 ; SOLDERA, M.C.A. 2 ; KANAMORI, N. 3 ;MARCELINO-GUIMARAES, F. C. 4 ; YAMAGUCHI-SHINOZAKI,
PCR Reação de Polimerase em Cadeia. Termociclador
 PCR Reação de Polimerase em Cadeia Termociclador REAÇÃO EM CADEIA DA POLIMERASE (PCR) Técnica que permite a amplificação da quantidade de DNA específico utilizando a enzima Taq DNA polimerase, sequências
PCR Reação de Polimerase em Cadeia Termociclador REAÇÃO EM CADEIA DA POLIMERASE (PCR) Técnica que permite a amplificação da quantidade de DNA específico utilizando a enzima Taq DNA polimerase, sequências
mundo inteiro com uma variedade de aplicações como clonagem, genotipagem e sequenciamento.
 mundo inteiro com uma variedade de aplicações como clonagem, genotipagem e sequenciamento. necessária para que você possa alcançar o melhor desempenho nesta técnica. AGAROSE A agarose é um polissacarídeo
mundo inteiro com uma variedade de aplicações como clonagem, genotipagem e sequenciamento. necessária para que você possa alcançar o melhor desempenho nesta técnica. AGAROSE A agarose é um polissacarídeo
agentes infecciosos (vírus, bactérias, parasitas), na detecção de locos de resistência a antibióticos, no diagnóstico de doenças genéticas para
 58 6-DISCUSSÃO É interessante observar que ao longo do tempo, o diagnóstico da hanseníase permanece como um verdadeiro desafio tanto no diagnóstico clinico, laboratorial e mesmo ao nível da pesquisa básica
58 6-DISCUSSÃO É interessante observar que ao longo do tempo, o diagnóstico da hanseníase permanece como um verdadeiro desafio tanto no diagnóstico clinico, laboratorial e mesmo ao nível da pesquisa básica
Eficiência da PCR convencional na detecção de Leishmania spp em sangue, pele e tecidos linfoides
 Eficiência da PCR convencional na detecção de Leishmania spp em sangue, pele e tecidos linfoides Aluna: Carina de Mattos Soares Orientadora: Dra Cídia Vasconcellos Supervisora: Dra Vânia Lucia Ribeiro
Eficiência da PCR convencional na detecção de Leishmania spp em sangue, pele e tecidos linfoides Aluna: Carina de Mattos Soares Orientadora: Dra Cídia Vasconcellos Supervisora: Dra Vânia Lucia Ribeiro
TRANSFERIBILIDADE DE MARCADORES MICROSSATÉLITES DE MELÃO PARA MELANCIA
 TRANSFERIBILIDADE DE MARCADORES MICROSSATÉLITES DE MELÃO PARA MELANCIA Maia, A. K. S (1) ; Albuquerque, L. B. (1) ; Antonio, R. P. (2) ; Silveira, L. M. (3) ; Nunes, G. H. S (1) ; Silva, A. E. A (1) ;
TRANSFERIBILIDADE DE MARCADORES MICROSSATÉLITES DE MELÃO PARA MELANCIA Maia, A. K. S (1) ; Albuquerque, L. B. (1) ; Antonio, R. P. (2) ; Silveira, L. M. (3) ; Nunes, G. H. S (1) ; Silva, A. E. A (1) ;
GENÉTICA HUMANA LICENCIATURA EM CIÊNCIAS DA SAÚDE
 GENÉTICA HUMANA LICENCIATURA EM CIÊNCIAS DA SAÚDE PROTOCOLOS LABORATORIAIS 3º Ano - 1º Semestre 2013 / 2014 1 EXTRACÇÃO DE DNA GENÓMICO ESFREGAÇO BUCAL Citogene Buccal Kit Esfregar 10 vezes a mucosa bucal
GENÉTICA HUMANA LICENCIATURA EM CIÊNCIAS DA SAÚDE PROTOCOLOS LABORATORIAIS 3º Ano - 1º Semestre 2013 / 2014 1 EXTRACÇÃO DE DNA GENÓMICO ESFREGAÇO BUCAL Citogene Buccal Kit Esfregar 10 vezes a mucosa bucal
Diagnóstico Virológico
 Diagnóstico Virológico Para que serve? Importância do Diagnóstico Laboratorial Diferenciação de agentes que causam a mesma síndrome clínica Identificação de patógenos novos Diferenciação de fases de doença
Diagnóstico Virológico Para que serve? Importância do Diagnóstico Laboratorial Diferenciação de agentes que causam a mesma síndrome clínica Identificação de patógenos novos Diferenciação de fases de doença
CATÁLOGO DE KITS DE EXTRAÇÃO
 CATÁLOGO DE KITS DE EXTRAÇÃO KITS DE EXTRAÇÃO BIOPUR A extração de DNA é o primeiro passo para diferentes procedimentos na Biologia Molecular. Este processo é parte fundamental para se obter alta eficiência
CATÁLOGO DE KITS DE EXTRAÇÃO KITS DE EXTRAÇÃO BIOPUR A extração de DNA é o primeiro passo para diferentes procedimentos na Biologia Molecular. Este processo é parte fundamental para se obter alta eficiência
Exercício 1. Calcule a concentração dos reagentes listados abaixo em mol L -1 Tabela 1. Propriedades de ácidos inorgânicos e hidróxido de amônio.
 ATIVIDADE 2 - CÁLCULO DE CONCENTRAÇÃO Exercício 1. Calcule a concentração dos reagentes listados abaixo em mol L -1 Tabela 1. Propriedades de ácidos inorgânicos e hidróxido de amônio. Exercício 2. Calcule
ATIVIDADE 2 - CÁLCULO DE CONCENTRAÇÃO Exercício 1. Calcule a concentração dos reagentes listados abaixo em mol L -1 Tabela 1. Propriedades de ácidos inorgânicos e hidróxido de amônio. Exercício 2. Calcule
Catálogo de Kits de Extração
 Catálogo de Kits de Extração Kits de Extração Biopur A extração de DNA é o primeiro passo para diferentes procedimentos na Biologia Molecular. Este processo é parte fundamental para se obter alta eficiência
Catálogo de Kits de Extração Kits de Extração Biopur A extração de DNA é o primeiro passo para diferentes procedimentos na Biologia Molecular. Este processo é parte fundamental para se obter alta eficiência
Apostila de aula prática REAÇÃO EM CADEIA PELA POLIMERASE (PCR)
 1 Universidade Federal Fluminense Instituto Biomédico Departamento de Microbiologia e Parasitologia Disciplina: Virologia Apostila de aula prática REAÇÃO EM CADEIA PELA POLIMERASE (PCR) A técnica de reação
1 Universidade Federal Fluminense Instituto Biomédico Departamento de Microbiologia e Parasitologia Disciplina: Virologia Apostila de aula prática REAÇÃO EM CADEIA PELA POLIMERASE (PCR) A técnica de reação
Conceitos Básico sobre Biologia molecular
 Conceitos Básico sobre Biologia molecular UFMS Mestre: Paula Cristhina Niz Xavier INTRODUÇÃO A biologia molecular tem aplicação expressiva na pesquisa de marcadores genéticos úteis no diagnóstico laboratorial.
Conceitos Básico sobre Biologia molecular UFMS Mestre: Paula Cristhina Niz Xavier INTRODUÇÃO A biologia molecular tem aplicação expressiva na pesquisa de marcadores genéticos úteis no diagnóstico laboratorial.
Em nossos experimento serão utilizadas células SH SY5Y, uma sublinhagem de células de neuroblastoma SK-N-SH, figura 1.
 Procedimentos Em nossos experimento serão utilizadas células SH SY5Y, uma sublinhagem de células de neuroblastoma SK-N-SH, figura 1. As células serão submetidas a estresse oxidativo por meio do tratamento
Procedimentos Em nossos experimento serão utilizadas células SH SY5Y, uma sublinhagem de células de neuroblastoma SK-N-SH, figura 1. As células serão submetidas a estresse oxidativo por meio do tratamento
CONSTRUÇÃO DE BACTÉRIAS VERDES FLUORESCENTES PARA USO DIDÁTICO
 UNIVERSIDADE FEDERAL DE MINAS GERAIS INSTITUTO DE CIENCIAS BIOLOGICAS PROJETO DE BIOLOGIA MOLECULAR CONSTRUÇÃO DE BACTÉRIAS VERDES FLUORESCENTES PARA USO DIDÁTICO Débora do Vale Gabriela Modenesi Gabriela
UNIVERSIDADE FEDERAL DE MINAS GERAIS INSTITUTO DE CIENCIAS BIOLOGICAS PROJETO DE BIOLOGIA MOLECULAR CONSTRUÇÃO DE BACTÉRIAS VERDES FLUORESCENTES PARA USO DIDÁTICO Débora do Vale Gabriela Modenesi Gabriela
Protocolo. Extração de Proteínas Totais de Planta. Método Fenol Modificado de:
 Protocolo Extração de Proteínas Totais de Planta Método Fenol Modificado de: Hurkman W. J. and Tanaka C. K. (1986). Solubilization of Plant Membrane Proteins for Analysis by Two-Dimensional Gel Electrophoresis.
Protocolo Extração de Proteínas Totais de Planta Método Fenol Modificado de: Hurkman W. J. and Tanaka C. K. (1986). Solubilization of Plant Membrane Proteins for Analysis by Two-Dimensional Gel Electrophoresis.
NextGeneration ECO One-Step RT-qPCR Kit
 DNA EXPRESS BIOTECNOLOGIA NextGeneration ECO One-Step RT-qPCR Kit Kit para uso em RT-PCR em tempo real quantitativo (RT-qPCR) em único tubo contendo NextGeneration Transcriptase Reversa M-MLV RNAse Minus
DNA EXPRESS BIOTECNOLOGIA NextGeneration ECO One-Step RT-qPCR Kit Kit para uso em RT-PCR em tempo real quantitativo (RT-qPCR) em único tubo contendo NextGeneration Transcriptase Reversa M-MLV RNAse Minus
PADRONIZAÇÃO DE MÉTODO IN HOUSE PARA EXTRAÇÃO DE DNA DE STAPHYLOCOCCUS AUREUS DIRETAMENTE DE AMOSTRAS DE URINA 1
 PADRONIZAÇÃO DE MÉTODO IN HOUSE PARA EXTRAÇÃO DE DNA DE STAPHYLOCOCCUS AUREUS DIRETAMENTE DE AMOSTRAS DE URINA 1 Katianne Wolf Krawczak 2, Bruno Vizzotto 3, Bruna Schultz Bandeira 4, Luciana Mendes Machado
PADRONIZAÇÃO DE MÉTODO IN HOUSE PARA EXTRAÇÃO DE DNA DE STAPHYLOCOCCUS AUREUS DIRETAMENTE DE AMOSTRAS DE URINA 1 Katianne Wolf Krawczak 2, Bruno Vizzotto 3, Bruna Schultz Bandeira 4, Luciana Mendes Machado
Circular Técnica. Protocolos para extração de DNA genômico de amostras de pêlo de bovinos. Introdução. Autores
 ISSN 0103-9334 Protocolos para extração de DNA genômico de amostras de pêlo de bovinos 87 Circular Técnica Porto Velho, RO Setembro, 2006 Autores Ana Karina Dias Salman Zootecnista, D.Sc., Embrapa Rondônia,
ISSN 0103-9334 Protocolos para extração de DNA genômico de amostras de pêlo de bovinos 87 Circular Técnica Porto Velho, RO Setembro, 2006 Autores Ana Karina Dias Salman Zootecnista, D.Sc., Embrapa Rondônia,
Comparação de três métodos de extração de DNA genômico para análises moleculares em Stylosanthes guianensis
 ISSN 1983-9723 36 Comparação de três métodos de extração de DNA genômico para análises moleculares em Stylosanthes guianensis Introdução A extração de DNA puro, de boa qualidade, é pré-requisito para qualquer
ISSN 1983-9723 36 Comparação de três métodos de extração de DNA genômico para análises moleculares em Stylosanthes guianensis Introdução A extração de DNA puro, de boa qualidade, é pré-requisito para qualquer
Extração de DNA e Amplificação por PCR
 Universidade Federal de São Carlos Departamento de Genética e Evolução Disciplina Práticas de Genética Extração de DNA e Amplificação por PCR Érique de Castro 405523, Victor Martyn 405612, Wilson Lau Júnior
Universidade Federal de São Carlos Departamento de Genética e Evolução Disciplina Práticas de Genética Extração de DNA e Amplificação por PCR Érique de Castro 405523, Victor Martyn 405612, Wilson Lau Júnior
Princípios e Aplicações da Técnica de PCR
 Universidade Federal de Santa Catarina Centro de Ciências Biológicas XVIII Semana Acadêmica da Biologia- UFSC Curso teórico-prático Princípios e Aplicações da Técnica de PCR Prof. Dr. Rafael D Rosa Departamento
Universidade Federal de Santa Catarina Centro de Ciências Biológicas XVIII Semana Acadêmica da Biologia- UFSC Curso teórico-prático Princípios e Aplicações da Técnica de PCR Prof. Dr. Rafael D Rosa Departamento
Procedimento Operacional Padrão - POP
 Página 1 de 12 Biobanco Procedimento Operacional Padrão para: Processamento de Sangue POP: V. 1.0 Nome: Extração de DNA em sangue total Efetiva: dezembro, 22 autora: Erika Regina Manuli Aprovação Profa.
Página 1 de 12 Biobanco Procedimento Operacional Padrão para: Processamento de Sangue POP: V. 1.0 Nome: Extração de DNA em sangue total Efetiva: dezembro, 22 autora: Erika Regina Manuli Aprovação Profa.
PCR (Polymerase chain reaction) Reação em cadeia da DNA polimerase. e suas aplicações
 PCR (Polymerase chain reaction) Reação em cadeia da DNA polimerase e suas aplicações Bianca Zingales [email protected] PCR é uma Técnica - Desenvolvida por Kary Mullis e colaboradores em 1983 - É um método
PCR (Polymerase chain reaction) Reação em cadeia da DNA polimerase e suas aplicações Bianca Zingales [email protected] PCR é uma Técnica - Desenvolvida por Kary Mullis e colaboradores em 1983 - É um método
Produtos não passíveis de regulamentação na ANVISA.
 Produtos para PCR PCR A PCR - Reação em Cadeia da Polimerase - é uma técnica de biologia molecular que permite a replicação in vitro do DNA de maneira eficiente, utilizando amostras que podem ser amplificadas
Produtos para PCR PCR A PCR - Reação em Cadeia da Polimerase - é uma técnica de biologia molecular que permite a replicação in vitro do DNA de maneira eficiente, utilizando amostras que podem ser amplificadas
Wipe Test. Instruções de utilização electrónica ver Controlo de contaminação
 PT Instruções de utilização Wipe Test Instruções de utilização electrónica ver www.bag-healthcare.com Controlo de contaminação Kit de teste para a deteção de contaminação numa base genética molecular REF
PT Instruções de utilização Wipe Test Instruções de utilização electrónica ver www.bag-healthcare.com Controlo de contaminação Kit de teste para a deteção de contaminação numa base genética molecular REF
Estagiária da Embrapa Amazônia Oriental, Laboratório de Fitopatologia,
 PROTOCOLO MODIFICADO PARA EXTRAÇÃO DE DNA DO GÊNERO Pestalotiopsis Joyce Solange Ferreira de Oliveira 1, Kenny Bonfim de Arruda Carvalho 2, Eudes de Arruda Carvalho 2 1 Estagiária da Embrapa Amazônia Oriental,
PROTOCOLO MODIFICADO PARA EXTRAÇÃO DE DNA DO GÊNERO Pestalotiopsis Joyce Solange Ferreira de Oliveira 1, Kenny Bonfim de Arruda Carvalho 2, Eudes de Arruda Carvalho 2 1 Estagiária da Embrapa Amazônia Oriental,
PLANO DE MINICURSO TÍTULO DO MINICURSO: 60 ANOS DO DNA E OS AVANÇOS DA PRODUÇÃO AGROPECUÁRIA
 PLANO DE MINICURSO TÍTULO DO MINICURSO: 60 ANOS DO DNA E OS AVANÇOS DA PRODUÇÃO AGROPECUÁRIA OBJETIVO: Proporcionar aos participantes uma maior compreensão dos avanços que a descoberta da estrutura da
PLANO DE MINICURSO TÍTULO DO MINICURSO: 60 ANOS DO DNA E OS AVANÇOS DA PRODUÇÃO AGROPECUÁRIA OBJETIVO: Proporcionar aos participantes uma maior compreensão dos avanços que a descoberta da estrutura da
Procedimento Operacional Padrão - POP
 Página 1 de 10 IMT-POP-BB-0 Biobanco Procedimento Operacional Padrão para: Extração de DNA de sangue total POP: V. 1.0 Nome: Extração de DNA em sangue total Efetiva: dezembro, 22 autora: Erika Regina Manuli
Página 1 de 10 IMT-POP-BB-0 Biobanco Procedimento Operacional Padrão para: Extração de DNA de sangue total POP: V. 1.0 Nome: Extração de DNA em sangue total Efetiva: dezembro, 22 autora: Erika Regina Manuli
Metodologia de Extração de DNA para Análise Genética de Populações de Pupunha (Bactris gasipaes Kunth.) 1
 Metodologia de Extração de DNA para Análise Genética de Populações de Pupunha (Bactris gasipaes Kunth.) 1 Ahmad Abdul Latif Hamze 2 Antonio Nascim Kalil Filho 3 Valderês Aparecida de Sousa 4 Álvaro Figueredo
Metodologia de Extração de DNA para Análise Genética de Populações de Pupunha (Bactris gasipaes Kunth.) 1 Ahmad Abdul Latif Hamze 2 Antonio Nascim Kalil Filho 3 Valderês Aparecida de Sousa 4 Álvaro Figueredo
Eletroforese de DNA. Gabriel M. Matos Nicolas Conceição
 Eletroforese de DNA Gabriel M. Matos Nicolas Conceição Eletroforese Usada para separar, identificar e purificar fragmentos de DNA; Bastante sensível, capaz de detectar até 20 pg de DNA; Permite a recuperação
Eletroforese de DNA Gabriel M. Matos Nicolas Conceição Eletroforese Usada para separar, identificar e purificar fragmentos de DNA; Bastante sensível, capaz de detectar até 20 pg de DNA; Permite a recuperação
A Prevenção do retardo mental na Síndrome do X Frágil
 LOGO A Prevenção do retardo mental na Síndrome do X Frágil Renata Ríspoli Gatti, Msc. Laboratório de Genética Humana Classificação > 200 CGG ~55 200 CGG Afetados Pré mutação 40 ~55 CGG Zona Gray 6 - ~40
LOGO A Prevenção do retardo mental na Síndrome do X Frágil Renata Ríspoli Gatti, Msc. Laboratório de Genética Humana Classificação > 200 CGG ~55 200 CGG Afetados Pré mutação 40 ~55 CGG Zona Gray 6 - ~40
TÉCNICA EM LABORATÓRIO / ANATOMIA PATOLÓGICA
 UFF UNIVERSIDADE FEDERAL FLUMINENSE CCM CENTRO DE CIÊNCIAS MÉDICAS HUAP HOSPITAL UNIVERSITÁRIO ANTONIO PEDRO TÉCNICA EM LABORATÓRIO / ANATOMIA PATOLÓGICA Parte I: MÚLTIPLA ESCOLHA 01 Assinale a opção cuja
UFF UNIVERSIDADE FEDERAL FLUMINENSE CCM CENTRO DE CIÊNCIAS MÉDICAS HUAP HOSPITAL UNIVERSITÁRIO ANTONIO PEDRO TÉCNICA EM LABORATÓRIO / ANATOMIA PATOLÓGICA Parte I: MÚLTIPLA ESCOLHA 01 Assinale a opção cuja
RELATÓRIO DE AULA PRÁTICA
 RELATÓRIO DE AULA PRÁTICA Universidade Federal de Minas Gerais Instituto de Ciências Biológicas Departamento de Bioquímica e Imunologia Professor: Miguel Alunos: Gustavo Bastos, Hugo Rezende, Monica Maertens,
RELATÓRIO DE AULA PRÁTICA Universidade Federal de Minas Gerais Instituto de Ciências Biológicas Departamento de Bioquímica e Imunologia Professor: Miguel Alunos: Gustavo Bastos, Hugo Rezende, Monica Maertens,
Federal de Alagoas. Universidade PROVA PRÁTICA 02. TÉCNICO DE LABORATÓRIO/ BIOLOGIA. (Editais nº 31 e 81/2016) UNIVERSIDADE FEDERAL DE ALAGOAS
 Pró-reitoria de Gestão de Pessoas e do Trabalho CONCURSO PÚBLICO PARA TÉCNICO-ADMINISTRATIVO EM EDUCAÇÃO PROVA TIPO Cargo (Nível Médio NM): 0. TÉCNICO DE LABORATÓRIO/ BIOLOGIA CADERNO DE QUESTÕES PROVA
Pró-reitoria de Gestão de Pessoas e do Trabalho CONCURSO PÚBLICO PARA TÉCNICO-ADMINISTRATIVO EM EDUCAÇÃO PROVA TIPO Cargo (Nível Médio NM): 0. TÉCNICO DE LABORATÓRIO/ BIOLOGIA CADERNO DE QUESTÕES PROVA
Transiluminador. Características
 Produtos para PCR pcr A PCR - Reação em Cadeia da Polimerase - é uma técnica de biologia molecular que permite a replicação in vitro do DNA de maneira eficiente, utilizando amostras que podem ser amplificadas
Produtos para PCR pcr A PCR - Reação em Cadeia da Polimerase - é uma técnica de biologia molecular que permite a replicação in vitro do DNA de maneira eficiente, utilizando amostras que podem ser amplificadas
Hibridação in situ por fluorescência FISH
 Universidade Estadual de Londrina Departamento de Biologia Geral Laboratório de Citogenética Animal - LACA Hibridação in situ por fluorescência FISH O protocolo descrito a seguir foi baseado nos procedimentos
Universidade Estadual de Londrina Departamento de Biologia Geral Laboratório de Citogenética Animal - LACA Hibridação in situ por fluorescência FISH O protocolo descrito a seguir foi baseado nos procedimentos
Alunos: Carlos Guilherme Reis, Roberta Silveira Professora: Fabiana Seixas Disciplina: Biologia Molecular
 Alunos: Carlos Guilherme Reis, Roberta Silveira Professora: Fabiana Seixas Disciplina: Biologia Molecular O que é PCR? Aplicações Técnicas: -Nested-PCR e artigos relacionados -PCR-Elisa e artigos relacionados
Alunos: Carlos Guilherme Reis, Roberta Silveira Professora: Fabiana Seixas Disciplina: Biologia Molecular O que é PCR? Aplicações Técnicas: -Nested-PCR e artigos relacionados -PCR-Elisa e artigos relacionados
25 a 28 de Outubro de 2011 ISBN
 25 a 28 de Outubro de 2011 ISBN 978-85-8084-055-1 AMPLIFICAÇÃO DE REGIÕES DE MICROSSATÉLITES DO DNA DE DUAS ESPÉCIES DE AVES DA FAUNA BRASILEIRA: Oryzoborus angolensis e Oryzoborus maximiliani (Passeriformes)
25 a 28 de Outubro de 2011 ISBN 978-85-8084-055-1 AMPLIFICAÇÃO DE REGIÕES DE MICROSSATÉLITES DO DNA DE DUAS ESPÉCIES DE AVES DA FAUNA BRASILEIRA: Oryzoborus angolensis e Oryzoborus maximiliani (Passeriformes)
Mariana Fronza Maurício Tamborindeguy. Prof. Fabiana Seixas
 Mariana Fronza Maurício Tamborindeguy Prof. Fabiana Seixas Introdução ao PCR PCR RAPD PCR Multiplex Alu PCR Referências Reação em cadeia da polimerase Técnica pela qual moléculas de DNA são amplificadas
Mariana Fronza Maurício Tamborindeguy Prof. Fabiana Seixas Introdução ao PCR PCR RAPD PCR Multiplex Alu PCR Referências Reação em cadeia da polimerase Técnica pela qual moléculas de DNA são amplificadas
Procedimento Operacional Padrão - POP
 Página 1 de 10 Biobanco Procedimento Operacional Padrão para: Extração de RNA total de sangue POP: V. 1.0 Nome: Extração de RNA total de sangue Efetiva: dezembro, 22 autora: Erika Regina Manuli Aprovação
Página 1 de 10 Biobanco Procedimento Operacional Padrão para: Extração de RNA total de sangue POP: V. 1.0 Nome: Extração de RNA total de sangue Efetiva: dezembro, 22 autora: Erika Regina Manuli Aprovação
2016. Março. Versão 9
 2016. Março. Versão 9 Inovação que gera resultados. Esse é o nosso compromisso com você! A KASVI é uma empresa brasileira que trabalha pela vida. Nosso atendimento exclusivo a distribuidores proporciona
2016. Março. Versão 9 Inovação que gera resultados. Esse é o nosso compromisso com você! A KASVI é uma empresa brasileira que trabalha pela vida. Nosso atendimento exclusivo a distribuidores proporciona
Extração de DNA genômico de sementes de alface (Lactuca sativa L.) para análises AFLP.
 Sousa, C.S.; Pereira, C.D.; Bonetti, A.M.; Goulart, L.R. e Kerr, W.R. Extração de DNA genômico de sementes de alface (Lactuca sativa L.) para análises AFLP. Horticultura Brasileira, v.20,n.2, julho 2002.
Sousa, C.S.; Pereira, C.D.; Bonetti, A.M.; Goulart, L.R. e Kerr, W.R. Extração de DNA genômico de sementes de alface (Lactuca sativa L.) para análises AFLP. Horticultura Brasileira, v.20,n.2, julho 2002.
Antes de iniciar o procedimento, preparar o Tampão de Lise: adicionar 1 ml da solução MI2 ao tubo com Lisozima e agitar brevemente.
 90043-50 Kit de Extração EliGene MTB Instruções de Uso USO PRETENDIDO O «Kit de Extração EliGene MTB» é destinado ao isolamento do DNA de espécies de Mycobacterium e eventualmente de outros organismos
90043-50 Kit de Extração EliGene MTB Instruções de Uso USO PRETENDIDO O «Kit de Extração EliGene MTB» é destinado ao isolamento do DNA de espécies de Mycobacterium e eventualmente de outros organismos
VARIABILIDADE GENÉTICA DE POPULAÇÕES DE Oryzoborus angolensis E Oryzoborus maximiliani CRIADAS EM CATIVEIRO, NO MUNICÍPIO DE MARINGÁ, PR
 25 a 28 de Outubro de 2011 ISBN 978-85-8084-055-1 VARIABILIDADE GENÉTICA DE POPULAÇÕES DE Oryzoborus angolensis E Oryzoborus maximiliani CRIADAS EM CATIVEIRO, NO MUNICÍPIO DE MARINGÁ, PR Jessica Francis
25 a 28 de Outubro de 2011 ISBN 978-85-8084-055-1 VARIABILIDADE GENÉTICA DE POPULAÇÕES DE Oryzoborus angolensis E Oryzoborus maximiliani CRIADAS EM CATIVEIRO, NO MUNICÍPIO DE MARINGÁ, PR Jessica Francis
WHO GLOBAL SALM-SURV NÍVEL III
 WHO GLOBAL SALM-SURV NÍVEL III CAMPYLOBACTER spp. Multiplex PCR para detecção de C. jejuni e C. coli Grace Theophilo LRNCEB IOC/FIOCRUZ [email protected] Diagnóstico molecular para Campylobacter spp.
WHO GLOBAL SALM-SURV NÍVEL III CAMPYLOBACTER spp. Multiplex PCR para detecção de C. jejuni e C. coli Grace Theophilo LRNCEB IOC/FIOCRUZ [email protected] Diagnóstico molecular para Campylobacter spp.
CYCLER CHECK. Kit de teste para a validação da uniformidade da temperatura em termocicladores. pronto a usar, pré-aliquotado. REF 71044 (4 testes)
 PT Instruções de utilização CYCLER CHECK Kit de teste para a validação da uniformidade da temperatura em termocicladores pronto a usar, pré-aliquotado REF 7104 (10 testes) REF 71044 (4 testes) Índice 1.
PT Instruções de utilização CYCLER CHECK Kit de teste para a validação da uniformidade da temperatura em termocicladores pronto a usar, pré-aliquotado REF 7104 (10 testes) REF 71044 (4 testes) Índice 1.
MÉTODO PARA ISOLAMENTO DE DNA DE TECIDO FOLIAR DE MAMONA (RICINUS COMMUNIS L.) *
 MÉTODO PARA ISOLAMENTO DE DNA DE TECIDO FOLIAR DE MAMONA (RICINUS COMMUNIS L.) * Muciana Aracely da Silva Cunha, Janice Silva Sales, Thelmo de Albuquerque Morais, Cícero Eduardo Ramalho Neto Universidade
MÉTODO PARA ISOLAMENTO DE DNA DE TECIDO FOLIAR DE MAMONA (RICINUS COMMUNIS L.) * Muciana Aracely da Silva Cunha, Janice Silva Sales, Thelmo de Albuquerque Morais, Cícero Eduardo Ramalho Neto Universidade
Kit de Clonagem Flex-C
 Kit de Clonagem Flex-C Instruções de Uso DESCRIÇÃO O Kit de Clonagem Flex-C é altamente eficiente, rápido e de fácil uso para clonagem por PCR. A enzima Flex-C permite a clonagem direta de qualquer fragmento
Kit de Clonagem Flex-C Instruções de Uso DESCRIÇÃO O Kit de Clonagem Flex-C é altamente eficiente, rápido e de fácil uso para clonagem por PCR. A enzima Flex-C permite a clonagem direta de qualquer fragmento
Drielly Cristina Braite Gabriella Borba Lívia B. Eslabão Luiza P. Rodrigues Tatiane Casarin
 Drielly Cristina Braite Gabriella Borba Lívia B. Eslabão Luiza P. Rodrigues Tatiane Casarin Ferramentas mais rápidas e mais sensíveis, de base molecular, são de grande valor. A extração e a purificação
Drielly Cristina Braite Gabriella Borba Lívia B. Eslabão Luiza P. Rodrigues Tatiane Casarin Ferramentas mais rápidas e mais sensíveis, de base molecular, são de grande valor. A extração e a purificação
Polimerase Chain Reaction PCR
 Polimerase Chain Reaction PCR Reação em cadeia da polimerase Técnica in vitro utilizada para sintetizar muitas cópias de DNA Amplificar uma seqüência alvo específica Termociclador DNA molde dntp DNA polimerase
Polimerase Chain Reaction PCR Reação em cadeia da polimerase Técnica in vitro utilizada para sintetizar muitas cópias de DNA Amplificar uma seqüência alvo específica Termociclador DNA molde dntp DNA polimerase
MANUAL. Contexto do Processo: Macroprocesso Geral. Fase Pré Analítica Geral. RRA s ; Responsável: Disponibilização:
 1/11 Contexto do Processo: Macroprocesso Geral Processo Atividade Fase Pré Analítica Geral RRA s 10.000; 10.002 Responsável: Elaboração Validação Verificação Aprovação Controle Médico Patologista Qualidade
1/11 Contexto do Processo: Macroprocesso Geral Processo Atividade Fase Pré Analítica Geral RRA s 10.000; 10.002 Responsável: Elaboração Validação Verificação Aprovação Controle Médico Patologista Qualidade
TÉCNICAS EM BIOLOGIA MOLECULAR
 TÉCNICAS EM BIOLOGIA MOLECULAR Lívia Ferreira S. Verzola 2016 2 TÉCNICAS EM BIOLOGIA MOLECULAR Mais do que um complexo conjunto de técnicas que geram conflitos intelectuais, sociais e religiosos, a manipulação
TÉCNICAS EM BIOLOGIA MOLECULAR Lívia Ferreira S. Verzola 2016 2 TÉCNICAS EM BIOLOGIA MOLECULAR Mais do que um complexo conjunto de técnicas que geram conflitos intelectuais, sociais e religiosos, a manipulação
MARCADORES MOLECULARES: AFLP E RFLP
 Universidade Federal de Pelotas Programa de Pós Graduação em Agronomia Disciplina de Biotecnologia Aplicada ao Melhoramento MARCADORES MOLECULARES: AFLP E RFLP Prof. PhD. Antonio Costa de Oliveira Gabriela
Universidade Federal de Pelotas Programa de Pós Graduação em Agronomia Disciplina de Biotecnologia Aplicada ao Melhoramento MARCADORES MOLECULARES: AFLP E RFLP Prof. PhD. Antonio Costa de Oliveira Gabriela
Departamento de Zoologia da Universidade de Coimbra
 Departamento de Zoologia da Universidade de Coimbra Ana Luísa Carvalho Amplificação de um fragmento de DNA por PCR Numa reacção em cadeia catalizada pela DNA polimerase (Polymerase Chain Reaction - PCR),
Departamento de Zoologia da Universidade de Coimbra Ana Luísa Carvalho Amplificação de um fragmento de DNA por PCR Numa reacção em cadeia catalizada pela DNA polimerase (Polymerase Chain Reaction - PCR),
EXTRAÇÃO DE DNA E ELETROFORESE
 EXTRAÇÃO DE DNA E ELETROFORESE Isolamento de ácidos nucléicos de células e tecidos Extração de ácidos nucléicos Obtenção do material: Vírus Bactérias; fungos Célula vegetal / célula animal Extração de
EXTRAÇÃO DE DNA E ELETROFORESE Isolamento de ácidos nucléicos de células e tecidos Extração de ácidos nucléicos Obtenção do material: Vírus Bactérias; fungos Célula vegetal / célula animal Extração de
Características de desempenho
 Características de desempenho Kit QIAamp DSP DNA FFPE Tissue, Versão 1 60404 Gestão de versão Este documento é designado de Características de desempenho do Kit QIAamp DSP DNA FFPE Tissue, versão 1, R3.
Características de desempenho Kit QIAamp DSP DNA FFPE Tissue, Versão 1 60404 Gestão de versão Este documento é designado de Características de desempenho do Kit QIAamp DSP DNA FFPE Tissue, versão 1, R3.
Guia Rápido de Bioinformática. Antônio Augusto Fonseca Júnior
 Guia Rápido de Bioinformática Antônio Augusto Fonseca Júnior 1 Sobre o autor Antônio Augusto Fonseca Júnior é farmacêutico formado pela Universidade Federal de Minas Gerais, especialista em Bioética e
Guia Rápido de Bioinformática Antônio Augusto Fonseca Júnior 1 Sobre o autor Antônio Augusto Fonseca Júnior é farmacêutico formado pela Universidade Federal de Minas Gerais, especialista em Bioética e
KITS DE EXTRAÇÃO DNA E RNA
 ACERTE COM PRECISÃO KITS DE EXTRAÇÃO DNA E RNA A Linha Biopur para extração e purificação de DNA e RNA possui kits variados com tecnologia para procedimentos manual (Mini Spin e Mini Cent) e para automação
ACERTE COM PRECISÃO KITS DE EXTRAÇÃO DNA E RNA A Linha Biopur para extração e purificação de DNA e RNA possui kits variados com tecnologia para procedimentos manual (Mini Spin e Mini Cent) e para automação
Faculdade de Medicina da Universidade de Coimbra Ano Lectivo 2011/2012. Unidade Curricular de BIOQUÍMICA I Mestrado Integrado em MEDICINA 1º Ano
 Faculdade de Medicina da Universidade de Coimbra Ano Lectivo 2011/2012 Unidade Curricular de BIOQUÍMICA I Mestrado Integrado em MEDICINA 1º Ano ENSINO PRÁTICO E TEORICO-PRÁTICO 8ª AULA PRÁTICA EXTRACÇÃO
Faculdade de Medicina da Universidade de Coimbra Ano Lectivo 2011/2012 Unidade Curricular de BIOQUÍMICA I Mestrado Integrado em MEDICINA 1º Ano ENSINO PRÁTICO E TEORICO-PRÁTICO 8ª AULA PRÁTICA EXTRACÇÃO
