ATRACAMENTO MOLECULAR
|
|
|
- Zaira de Oliveira
- 7 Há anos
- Visualizações:
Transcrição
1 UNIVERSIDADE FEDERAL DO ESPÍRITO SANTO CENTRO DE CIÊNCIAS DA SAÚDE PROGRAMA DE PÓS-GRADUAÇÃO EM BIOTECNOLOGIA BIOINFORMÁTICA ATRACAMENTO MOLECULAR VITÓRIA 2018 Ivana Alece Arantes Moreno Júlia de Assis Pinheiro Pablo Viana Oliveira Tamires dos Santos Vieira
2 Interação entre macromoléculas Atracamento Molecular Macromolécula e pequena molécula ligante agonista/antagonista ou substrato/inibidor Estimar como duas moléculas interagem A afinidade dessa ligação depende de uma função de avaliação e dos métodos computacionais aplicados [Guedes et al. 2013].
3 Atracamento molecular(molecular Docking) Atracamento Molecular Técnica computacional dedicada à previsão do modo de ligação e dos detalhes do reconhecimento molecular proteína-proteína e receptor-ligante. Pesquisas associadas à saúde e à biotecnologia.
4 Reconhecimento Molecular Metodologias computacionais baseadas no modelo chave-fechadura. Tanto o ligante quanto a proteína são flexíveis, podendo modificar a sua conformação durante o processo de formação do complexo receptorligante(ajuste induzido).
5 Reconhecimento Molecular catálise de reações enzimáticas Flexibilidade da Proteína transdução de sinais transporte através de proteínas de membrana mudanças conformacionais associadas a formas ativas e não ativas de proteínas
6 Reconhecimento Molecular Atracamento proteína-ligante: modelos de encaixe induzido e seleção conformacional; direcionar as metodologias para fornecer um tratamento adequado; Reconhecimento desafio das metodologias de atracamento. molecular físico-químicas estruturais características físicoquímicas interações de van der Waals ligações de hidrogênio interações provenientes do efeito hidrofóbico interações eletrostáticas ligações covalentes características estruturais variações na orientação posicionamento espacial rotações de ligações químicas
7 Características físico-químicas: definem o grau de afinidade e de especificidade do ligante pela proteína relacionadas com as interações intermoleculares existentes no complexo; Características estruturais: associadas aos arranjos espaciais moleculares. Ligantes e proteínas com alta afinidade Reconhecimento Molecular Alto nível de complementaridade estérica, proteína e ligante alta porcentagem de superfícies de Alta complementaridade de propriedades associadas às superfícies de contato moleculares (tanto eletrostática (polaridade) O ligante geralmente se liga em uma conformação energeticamente favorável. Interações repulsivas entre ligante e proteínas são minimizadas. contato moleculares, definidas quanto relacionada à pelos raios de van der Waals complementaridade de regiões atômicos, em contato próximo. hidrofóbicas).
8 Métodos de Atracamento Problema de atracamento i) investigação e predição da conformação e orientação de uma molécula ligante no seu sítio de complexação; ii) predição da afinidade em um complexo receptor-ligante. Scoring
9 Programas Métodos de Atracamento
10 Métodos de Atracamento Preparação do sistema OBTENÇÃO DAS COORDENADAS DAS ESTRUTURAS TRIDIMENSIONAIS;
11 Métodos de Atracamento Preparação do sistema FONTE:
12 Métodos de Atracamento Preparação do sistema CORINA CONCORD OMEGA Balloon Multiconf-DOCK.
13 Métodos de Atracamento Preparação do sistema Prever os sítios de ligação: análises GEOGRÁFICAS e VOLUMÉTRICAS; Cavidades(FINDSITE, SURFNET e LIGSITE); Energias de interação(q-sitefinder e GRID); Uso de propriedades p/ busca de padrões(webpdbinder); Procura de erros: WHAT_IF, MOLPROBITY e PROCHECK.
14 Métodos de Atracamento Preparação do sistema Possíveis erros: ausência de átomos e/ou resíduos; mau posicionamento de cadeias laterais; presença de duas ou mais conformações para um resíduo ou conjunto; conformações não nativas.
15 Métodos de Atracamento Preparação do sistema Estado de protonação; Isomeria; LIGPREP ehits Tautomeria.
16 Métodos de Atracamento Preparação do sistema Graus de liberdade
17 Métodos de Atracamento Preparação do sistema Esboço do processo de acoplamento molecular FONTE: Ferreira et al. Molecular Docking and Structure-Based Drug Design Strategies. Molecules. 20, , doi: /molecules
18 Métodos de busca Método de busca Sistemática Determinística Função Um conjunto de valores é estabelecido para cada grau de liberdade. O objetivo é explorar de forma combinatória todos os graus de liberdade da molécula durante a busca. Dado um mesmo estado inicial de entrada, é obtido sempre o mesmo resultado de saída. Métodos de simulação por dinâmica molecular e métodos clássicos de minimização de energia são exemplos. Estocástica O processo de otimização envolve movimentos aleatórios associados aos graus de liberdade. Este fato implica na possibilidade de se obter diferentes resultados como saída para um mesmo estado inicial de entrada.
19 FUNÇÕES DE AVALIAÇÃO Funções de busca Várias conformações FUNÇÕES DE AVALIAÇÃO Avaliar a qualidade e verificar a afinidade com o receptor. Precisa ser capaz de ordenar ligantes: Previsão do modo de ligação Triagem virtual C c Predição deafinidade MELHOR C CONFORMAÇÃO
20 FUNÇÕES DE AVALIAÇÃO Estas funções são modelos matemáticos geralmente lineares, propriedades físico-químicas Relação de molécula ligante + receptor. Variam: Númeroetipodetermos Complexidade matemática Forma de parametrização Tipo de função: Simples Complexa Custo computacional
21 FUNÇÕES DE AVALIAÇÃO DE ATRACAMENTO MOLECULAR RECEPTOR- LIGANTE Podem ser classificadas em três tipos: Campo de força, Empíricas Conhecimento
22 CAMPOS DE FORÇA Utilizam modelos físicos Somadasenergiasdeinteraçãoentreosliganteseaproteína. Ostermosdeenergiasãodivididosemtermos: Não-ligados associados a interações de van der Waals, eletrostáticas e ligações de hidrogênio. Ligados representando normalmente a energia associada à torção de ligações químicas.
23 FUNÇÕES EMPÍRICAS Complexos receptor-ligante com estruturas tridimensionais e afinidades conhecidas. Ajuste para maior acurácia. Diferenciação Número de termos utilizados para modelar as equações ChemScore X-Score GlideScore
24 BASEADAS EM CONHECIMENTO Estas funções são construídas a partir de análises estatísticas ÁTOMOS RECEPTOR-LIGANTE EXPERIMENTAL Potenciais deforça média (potentialsofmeanforce,pmf) Termos derivados de interações específicas pré-definidas. Com isto, as funções baseadas em conhecimento tendem a capturar efeitos de interações mais específicas e de modelagem mais complexa.
25 BASEADAS EM CONHECIMENTO DESVANTAGEM Dependem de um conjunto de treinamento bastante amplo para a parametrização. Interações podem estar mal representadas VANTAGEM Simplicidade de seus termos Rápidas comparadas as funções empíricas. Uso destas funções restrito. Ex.: DrugScore, RF-Score e PMF.
26 FUNÇÃO AVALIAÇÃO Não existe um função de avaliação universal Para obter maior eficiência e confiabilidade: Utilizar a função de avaliação que mais se adequa ao problema a ser pesquisado. Redocking Análisequalitativas Detecçãodefalsos-positivos
27 FLEXIBILIDADE DA PROTEÍNA Desafio Atracamentomolecular Impulsão de desenvolvimento de novas metodologias: Importância no estudo de fármacos: Receptor +Ligante Algoritmos computacionais: Maior possibilidade.
28 FLEXIBILIDADE DA PROTEÍNA Movimentos locais cadeias laterais de resíduos de aminoácidos Movimentos de média escala rearranjo de alças ou reposicionamento de hélices Movimentos de grande escala Domínios da proteína. Figura 3-9: Graus de flexibilidade do receptor: (A)mobilidade do esqueleto peptídico da enzima protease do HIV-1, (B) diversas conformações de alça no sítio de ligação do ATP à enzima MAP cinase p38, e (C) mudança conformacional da cadeia lateral de resíduo na enzima cinase JNK3, influenciada por diferentes inibidores.
29 FLEXIBILIDADE DA PROTEÍNA Tipo de movimento determina a metodologia empregada. i. Métodos associados ao mecanismo de encaixe induzido ii. Métodos associados ao mecanismo de conjunto de conformações (ensemble docking, em inglês) iii. Métodos híbridos, que levam os dois tipos de mecanismos e procuram considerar um amplo espectro de movimentos da proteína.
30 MÉTODOS ASSOCIADOS AO MECANISMO DE ENCAIXE INDUZIDO Algoritmo de otimização local é utilizado para introduzir certa acomodação proteína-ligante no processo de atracamento Baseadosnaminimizaçãodogradiente MonteCarlo Reinvestigaras configurações ligante-proteína geradas durante o processo de busca.
31 PROGRAMA Prodock ICM/IFREDA AutoDock4 e GOLD MÉTODOS ASSOCIADOS AO MECANISMO DE ENCAIXE INDUZIDO CARACTERÍSTICAS utiliza a minimização por gradiente durante o processo de busca para incorporar a flexibilidade em regiões da cadeia principal da proteína. utiliza o método de Monte Carlo seguido de minimização de energia para otimizar cadeias laterais e/ou partes flexíveis do esqueleto peptídico. utilizam algoritmos genéticos para introduzir flexibilidade nas cadeias laterais de resíduos. ROSETTALIGAND utiliza o método de Monte Carlo para explorar simultaneamente os graus de liberdade associados ao ligante, às cadeias laterais dos resíduos e ao esqueleto peptídico da proteína.
32 MÉTODOS ASSOCIADOS AO MECANISMO DE CONJUNTO DE CONFORMAÇÕES São considerados movimentos de grande e larga escala; Usam um número discreto de conformações representativas da flexibilidade da proteína. Podem ser obtidas utilizando as técnicas de: Difraçãoderaios-Xe/ouRMN. Utilizar modelos gerados por técnicas de predição de estruturas de proteínas Simulações de DM ou utilizando a técnica de modos normais.
33 FLEXIBILIDADE DA PROTEÍNA Há evidências significativas que associam o uso de MÚLTIPLAS CONFORMAÇÕESao aumento significativo da probabilidade de obter SUCESSO em estudos de ATRACAMENTO MOLECULAR. Figura 7-9: Atracamento molecular utilizando conjunto de conformações (adaptado de Guedes e colaboradores, 2013).
34 DIFERENCIAÇÃO DOS MÉTODOS Três questões importantes que se colocam a respeito destas abordagens e que diferenciam os diversos métodos descritos na literatura: i. como utilizar as diversas conformações da proteína; ii. como gerar e selecionar as conformações da proteína; iii. como ordenar os compostos considerando os atracamentos dos ligantes nas diversas conformações da proteína.
35 i. UTILIZAÇÃO DAS CONFORMAÇÕES Considerar cada conformação da proteína como rígida Agrupamento por semelhança ou construção de clusters: Grades de energia combinadas.
36 GRADES DE ENERGIA Figura 8-9: Representação de uma grade de energia cúbica centrada no sítio de ligação do inibidor indinavir da protease do HIV-1,comas dimensões de cadaeixo (dx,dy edz).
37 GRADES DE ENERGIA DOCK FlexE PROGRAMA OBSERVAÇÕES Primeiro a implementar conjuntos de grades de energia para a inclusão da flexibilidade da molécula receptora. Cada ligante é atracado em cada uma das conformações representativas da flexibilidade da proteína. OUTROS PROGRAMAS QUE USAM GRADE DE ENERGIA GOLD, Glide, AutoDock Vina e DockThor
38 ii. GERAÇÃO DE CONFORMAÇÕES DA PROTEÍNA: Flexibilidade local de um receptor Movimentos de mais larga escala Modos de ligação podem ser obtidos resultados experimentais ou de simulações de atracamento molecular.
39 iii. ORDENAÇÃO DOS COMPOSTOS Nãoétarefafácil Grandedesafio Utilizar a média das energias dos ligantes com relação às múltiplas conformações da proteína. Considerar a melhor/menor energia obtida por um ligante ao interagir comdeterminadaconformação Possibilidade denovosfármacos.
40 TRIAGEM VIRTUAL (virtual screening) Metodologia de atracamento molecular em larga escala, através da qual muitos ligantes são avaliados no sítio de ligação de um receptor; Busca de moléculas candidatas a novos fármacos; rápidas, eficazes e de baixo custo. Complementar os resultados obtidos pela triagem experimental(high-throughput screening); Bancos: ZINC, BindingDB, PubChem, SuperNatural e ChEMBL. Fonte:
41 Fonte: Fonte:
42 Como escolher os ligantes? Propriedades físico-químicas definidas pelo usuário; Ex.: número de ligações rotacionáveis e logp ou, em alguns deles, desenhar o fragmento desejável na estrutura dos ligantes; objetivo de reduzir o número de compostos a serem analisados pela triagem virtual, especificando o perfil desejado para estes ligantes. Geralmente o banco fornece uma tabela com as principais propriedades químicas dos compostos; Construção de uma biblioteca de ligantes própria- FAF-Drugs.
43 Metodologias Baseadas na estrutura do Receptor (structure-based) Com base na estrutura tridimensional do ligante; Mais utilizado quando a estrutura tridimensional da molécula receptora está disponível com boa qualidade; Baseadas na estrutura do Ligante (ligand-based) Quando não é possível obter a estrutura tridimensional do receptor; Esta abordagem consiste na análise de similaridade de propriedades estruturais e físico-químicas de compostos ativos e inativos. estudo da relação estrutura-atividade (SAR, structure activity relationship ou QSAR, quantitative structure activity relationship) e a modelagem farmacofórica.
44 Validação do Protocolo Avaliar se o método de busca e a função de avaliação escolhidos são capazes de reproduzir o modo de ligação experimental de compostos originalmente complexados com o receptor alvo. Análise que deve ser feita é a capacidade de o protocolo diferenciar as moléculas ativas das inativas, conhecidas como casos falsopositivos
45
46 CONSIDERAÇÕES FINAIS A descoberta e planejamento de novos fármacos é um processo muito caro e muito demorado. novo fármaco ao mercado são necessários de 10 a 20 anos e o custo estimadoédecercade800milhõesdedólares. Abordagens in silico que possam reduzir estes custos e acelerar o processo de descoberta e planejamento de novos fármacos; moléculas que foram descobertas/otimizadas utilizando técnicas computacionais e que estão na fase de ensaios clínicos ou que já foram aprovadas para uso terapêutico.
47 CONSIDERAÇÕES FINAIS É possível prever que, no futuro, metodologias computacionais mais sofisticadas terão um papel cada vez mais destacado em estratégias de planejamento racional de fármacos. Avanços teórico/metodológicos para que se consiga obter uma melhor previsão das constantes de afinidade receptor-ligante.
Docking (ou atracamento) Molecular. Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia 9 de outubro de 2014
 Docking (ou atracamento) Molecular Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia [email protected] 9 de outubro de 2014 O ATRACAMENTO MOLECULAR PERMITE ESTIMAR COMO DUAS MOLÉCULAS INTERAGEM
Docking (ou atracamento) Molecular Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia [email protected] 9 de outubro de 2014 O ATRACAMENTO MOLECULAR PERMITE ESTIMAR COMO DUAS MOLÉCULAS INTERAGEM
Mecanismo de Inibição de Enzimas Preparação de Micro e Macromoléculas Docagem Molecular Exemplo de Aplicação
 bjetivos FFI0776 Modelagem e Engenharia de Proteínas Mecanismo de Inibição de Enzimas Preparação de Micro e Macromoléculas M l Docagem Molecular Exemplo de Aplicação Prof. Rafael V. C. Guido [email protected]
bjetivos FFI0776 Modelagem e Engenharia de Proteínas Mecanismo de Inibição de Enzimas Preparação de Micro e Macromoléculas M l Docagem Molecular Exemplo de Aplicação Prof. Rafael V. C. Guido [email protected]
Triagem Virtual em Larga Escala. Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia 10 de outubro de 2014
 Triagem Virtual em Larga Escala Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia [email protected] 10 de outubro de 2014 1 O que é triagem virtual? Grande conjunto de compostos Estratégia
Triagem Virtual em Larga Escala Profa. Dra. Rafaela Ferreira Dept. de Bioquímica e Imunologia [email protected] 10 de outubro de 2014 1 O que é triagem virtual? Grande conjunto de compostos Estratégia
Métodos de Química Computacional
 Universidade Federal de Ouro Preto Instituto de Ciências Exatas e Biológicas Departamento de Química Métodos de Química Computacional Professora: Melissa Soares Caetano Mecânica Molecular Mecânica Molecular
Universidade Federal de Ouro Preto Instituto de Ciências Exatas e Biológicas Departamento de Química Métodos de Química Computacional Professora: Melissa Soares Caetano Mecânica Molecular Mecânica Molecular
Quiminformática e o planejamento de fármacos
 Quiminformática e o planejamento de fármacos Banco de Dados Otimização do Matriz Análise e Modelagem Estatística Quiminformática Carlos Montanari NEQUIMED/DQFM/IQSC/USP [email protected] Evolução do
Quiminformática e o planejamento de fármacos Banco de Dados Otimização do Matriz Análise e Modelagem Estatística Quiminformática Carlos Montanari NEQUIMED/DQFM/IQSC/USP [email protected] Evolução do
QSAR 3D Planejamento de NCEs QSAR 3D. O processo de reconhecimento molecular é um processo tridimensional. Conformação bioativa.
 QSAR 3D Interação Fármaco-Receptor AULA 5 a maioria dos casos, a ação dos fármacos está ligada a interação fármaco-receptor, receptor, através de uma associação do tipo reversível e não- covalente Agonistas
QSAR 3D Interação Fármaco-Receptor AULA 5 a maioria dos casos, a ação dos fármacos está ligada a interação fármaco-receptor, receptor, através de uma associação do tipo reversível e não- covalente Agonistas
Estrutura e Função de Proteínas O NMR tem a vantagem de puder apresentar mais do que uma estrura possivel
 Vamos trabalhar com a neurominidase. A m-glutinina liga o virs à celula. A neurominidasez o contrario e permite que o virus de despegue dessa celula e consegue ir infetar mais virus. O centro ativo mantem
Vamos trabalhar com a neurominidase. A m-glutinina liga o virs à celula. A neurominidasez o contrario e permite que o virus de despegue dessa celula e consegue ir infetar mais virus. O centro ativo mantem
Interações de van der Waals. Interações de van der Waals. Interações de van der Waals.
 Interações de van der Waals [email protected] Também conhecidas como forças de dispersão de London, caracterizam-se pelo momento de dipolo induzido e ocorrem entre todos os átomos. Apesar de moléculas
Interações de van der Waals [email protected] Também conhecidas como forças de dispersão de London, caracterizam-se pelo momento de dipolo induzido e ocorrem entre todos os átomos. Apesar de moléculas
Princípios básicos da modelagem molecular e sua aplicação no desenvolvimento de novos fármacos
 II JRADA DE IVER DA QUÍMICA Princípios básicos da modelagem molecular e sua aplicação no desenvolvimento de novos fármacos Ana Carolina de liveira Introdução MDELAGEM MLECULAR DEFIIÇÃ: Trata da investigação
II JRADA DE IVER DA QUÍMICA Princípios básicos da modelagem molecular e sua aplicação no desenvolvimento de novos fármacos Ana Carolina de liveira Introdução MDELAGEM MLECULAR DEFIIÇÃ: Trata da investigação
INTRODUÇÃO Á BIOQUÍMICA
 INTRODUÇÃO Á BIOQUÍMICA BIOQUÍMICA ENFERMAGEM FIO Faculdades Integradas de Ourinhos. Prof. Esp. Roberto Venerando Fundação Educacional Miguel Mofarrej. FIO [email protected] 1 - Introdução à
INTRODUÇÃO Á BIOQUÍMICA BIOQUÍMICA ENFERMAGEM FIO Faculdades Integradas de Ourinhos. Prof. Esp. Roberto Venerando Fundação Educacional Miguel Mofarrej. FIO [email protected] 1 - Introdução à
AULA 7. Cálculo das energias de interação estereoquímicas e eletrostáticas entre as moléculas do conjunto de
 Análise Comparativa dos Campos Moleculares AULA 7 Análise Comparativa dos Campos Moleculares A contribuição devido às forças de dispersão entre moléculas é descrita pelo potencial de Lennard-Jones e as
Análise Comparativa dos Campos Moleculares AULA 7 Análise Comparativa dos Campos Moleculares A contribuição devido às forças de dispersão entre moléculas é descrita pelo potencial de Lennard-Jones e as
RELAÇÕES ENTRE A ESTRUTURA E ATIVIDADE. Relações entre a estrutura e atividade (SAR) Requerimentos para estudos de QSAR
 BJETIVS AULA 3 Relações entre a estrutura e atividade (SAR) Requerimentos para estudos de QSAR Propriedade biológica Descritores moleculares Conjunto de dados Parâmetros estatísticos RELAÇÕES ETRE A ESTRUTURA
BJETIVS AULA 3 Relações entre a estrutura e atividade (SAR) Requerimentos para estudos de QSAR Propriedade biológica Descritores moleculares Conjunto de dados Parâmetros estatísticos RELAÇÕES ETRE A ESTRUTURA
FUNDAÇÃO CARMELITANA MÁRIO PALMÉRIO FACIHUS - FACULDADE DE CIÊNCIAS HUMANAS E SOCIAIS. Enzimas. Prof. Me. Cássio Resende de Morais
 FUNDAÇÃO CARMELITANA MÁRIO PALMÉRIO FACIHUS - FACULDADE DE CIÊNCIAS HUMANAS E SOCIAIS Enzimas Prof. Me. Cássio Resende de Morais Enzimas Catalisadores biológicos: substâncias de origem biológica que aceleram
FUNDAÇÃO CARMELITANA MÁRIO PALMÉRIO FACIHUS - FACULDADE DE CIÊNCIAS HUMANAS E SOCIAIS Enzimas Prof. Me. Cássio Resende de Morais Enzimas Catalisadores biológicos: substâncias de origem biológica que aceleram
Funções Escores (MolDock Score) Prof. Dr. Walter F. de Azevedo Jr. ou
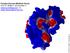 205 Dr. Walter F. de zevedo Jr. Funções Escores (MolDock Score) Prof. Dr. Walter F. de zevedo Jr. [email protected] ou [email protected] Função MolDock Score função ajuste ou escore, usada
205 Dr. Walter F. de zevedo Jr. Funções Escores (MolDock Score) Prof. Dr. Walter F. de zevedo Jr. [email protected] ou [email protected] Função MolDock Score função ajuste ou escore, usada
O QUE É UMA PROTEÍNA?
 PROTEÍNAS O QUE É UMA PROTEÍNA? Macromoléculas que agem em processos biológicos como: Mediação por catálise proteica, transporte de outras moléculas, controle de condições intra/extra celulares e transporte
PROTEÍNAS O QUE É UMA PROTEÍNA? Macromoléculas que agem em processos biológicos como: Mediação por catálise proteica, transporte de outras moléculas, controle de condições intra/extra celulares e transporte
Aula de Bioquímica I. Tema: Enzimas. Prof. Dr. Júlio César Borges
 Aula de Bioquímica I Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: [email protected]
Aula de Bioquímica I Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: [email protected]
ENSAIO VIRTUAL E A IDENTIFICAÇÃO DE MOLÉCULAS BIOATIVAS
 ENSAIO VIRTUAL E A IDENTIFICAÇÃO DE MOLÉCULAS BIOATIVAS 1. Introdução A fantástica evolução da Química Medicinal nas últimas décadas foi acompanhada por avanços científicos significativos que levaram a
ENSAIO VIRTUAL E A IDENTIFICAÇÃO DE MOLÉCULAS BIOATIVAS 1. Introdução A fantástica evolução da Química Medicinal nas últimas décadas foi acompanhada por avanços científicos significativos que levaram a
Modelagem Comparativa de Proteínas
 Modelagem Comparativa de Proteínas Bioinformática Estrutural Aula 3 3 de Junho de 2013 Paula Kuser Falcão Laboratório de Bioinformática Aplicada Embrapa Informática Agropecuária Por que predizer a estrutura?
Modelagem Comparativa de Proteínas Bioinformática Estrutural Aula 3 3 de Junho de 2013 Paula Kuser Falcão Laboratório de Bioinformática Aplicada Embrapa Informática Agropecuária Por que predizer a estrutura?
Métodos de Química Computacional
 Universidade Federal de Ouro Preto Instituto de Ciências Exatas e Biológicas Departamento de Química Métodos de Química Computacional Professora: Melissa Soares Caetano Química Medicinal Matemática Química
Universidade Federal de Ouro Preto Instituto de Ciências Exatas e Biológicas Departamento de Química Métodos de Química Computacional Professora: Melissa Soares Caetano Química Medicinal Matemática Química
Aula de Bioquímica Avançada. Tema: Enzimas. Prof. Dr. Júlio César Borges
 Aula de Bioquímica Avançada Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: [email protected]
Aula de Bioquímica Avançada Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: [email protected]
Função proteica envolve a ligação reversível com outras moléculas O ligante se liga na proteína e um sítio específico, chamado SÍTIO DE LIGAÇÃO.
 Estrutura Função 1. Função proteica envolve a ligação reversível com outras moléculas. A molécula que se liga reversivelmente à proteina LIGANTE 2. O ligante se liga na proteína e um sítio específico,
Estrutura Função 1. Função proteica envolve a ligação reversível com outras moléculas. A molécula que se liga reversivelmente à proteina LIGANTE 2. O ligante se liga na proteína e um sítio específico,
Fundamentos da modelagem Molecular - 1
 Fundamentos da modelagem Molecular - 1 Departamento de Física UFPel ufpellogo Introdução Rotas para a pesquisa Conexão entre experimento, simulação e teoria Sistema real Fazer modelos do sistema Fazer
Fundamentos da modelagem Molecular - 1 Departamento de Física UFPel ufpellogo Introdução Rotas para a pesquisa Conexão entre experimento, simulação e teoria Sistema real Fazer modelos do sistema Fazer
Rafael Mesquita. Proteínas. Estrutura
 Proteínas Estrutura Ligação peptídica Ligação peptídica - Rígida e plana - Ligação simples com caráter de dupla ligação Ângulos Φ e Ψ Ligação peptídica limitações estruturais Limitações estruturais impostas
Proteínas Estrutura Ligação peptídica Ligação peptídica - Rígida e plana - Ligação simples com caráter de dupla ligação Ângulos Φ e Ψ Ligação peptídica limitações estruturais Limitações estruturais impostas
Aula 1. Referência. Bancos de Dados. Linguagem x Informação. Introdução a Bioquímica: Biomoléculas. Introdução ao Curso: Aminoácidos.
 Introdução a Bioquímica: Biomoléculas Aula 1 Introdução ao urso: Aminoácidos eferência Autores: Ignez aracelli e Julio Zukerman-Schpector Editora: EdUFSar Ignez aracelli BioMat DF UNESP/Bauru Julio Zukerman
Introdução a Bioquímica: Biomoléculas Aula 1 Introdução ao urso: Aminoácidos eferência Autores: Ignez aracelli e Julio Zukerman-Schpector Editora: EdUFSar Ignez aracelli BioMat DF UNESP/Bauru Julio Zukerman
Atracamento molecular (Docking)
 Atracamento molecular (Docking) O atracamento molecular O que é? Método para achar o melhor encaixe entre duas moléculas O atracamento molecular O que é? Porquê? Método para achar o melhor encaixe entre
Atracamento molecular (Docking) O atracamento molecular O que é? Método para achar o melhor encaixe entre duas moléculas O atracamento molecular O que é? Porquê? Método para achar o melhor encaixe entre
Introdução à Modelagem Molecular
 Introdução à Modelagem Molecular Prof. Alex Fabiano C. Campos, Dr Introdução Métodos teóricos e técnicas computacionais para modelar ou imitar o comportamento de moléculas e sistemas atômicos. Empregados
Introdução à Modelagem Molecular Prof. Alex Fabiano C. Campos, Dr Introdução Métodos teóricos e técnicas computacionais para modelar ou imitar o comportamento de moléculas e sistemas atômicos. Empregados
OBJETIVOS PLANEJAMENTO DE FÁRMACOS MÉTODOS EM QUÍMICA MEDICINAL FFI0763. Propriedades
 MÉTODOS EM QUÍMICA MEDICINAL FFI0763 [email protected] PLANEJAMENTO DE FÁRMACOS OBJETIVOS 1. Potência, Afinidade, Seletividade 2. Absorção, Permeabilidade Propriedades Relações entre a Estrutura e Atividade
MÉTODOS EM QUÍMICA MEDICINAL FFI0763 [email protected] PLANEJAMENTO DE FÁRMACOS OBJETIVOS 1. Potência, Afinidade, Seletividade 2. Absorção, Permeabilidade Propriedades Relações entre a Estrutura e Atividade
OBJETIVOS PLANEJAMENTO DE FÁRMACOS MÉTODOS EM QUÍMICA MEDICINAL FFI0763. Propriedades
 MÉTODOS EM QUÍMICA MEDICINAL FFI0763 [email protected] PLANEJAMENTO DE FÁRMACOS OBJETIVOS 1. Potência, Afinidade, Seletividade 2. Absorção, Permeabilidade Propriedades Relações entre a Estrutura e Atividade
MÉTODOS EM QUÍMICA MEDICINAL FFI0763 [email protected] PLANEJAMENTO DE FÁRMACOS OBJETIVOS 1. Potência, Afinidade, Seletividade 2. Absorção, Permeabilidade Propriedades Relações entre a Estrutura e Atividade
Proteínas São macromoléculas complexas, compostas de aminoácidos, e necessárias para os processos químicos que ocorrem nos organismos vivos
 Proteínas São macromoléculas complexas, compostas de aminoácidos, e necessárias para os processos químicos que ocorrem nos organismos vivos São os constituintes básicos da vida: tanto que seu nome deriva
Proteínas São macromoléculas complexas, compostas de aminoácidos, e necessárias para os processos químicos que ocorrem nos organismos vivos São os constituintes básicos da vida: tanto que seu nome deriva
Mecânica Molecular. Dinâmica Molecular. Exemplos de aplicação. é um método relativamente. energia e conformação de micro ou macromoléculas
 Objetivos FFI0776 Modelagem e Engenharia de Proteínas Prof. Rafael V. C. Guido [email protected] Aula 04 Mecânica Molecular Campo de força Exemplos de Campo de Força Dinâmica Molecular Etapas envolvidas
Objetivos FFI0776 Modelagem e Engenharia de Proteínas Prof. Rafael V. C. Guido [email protected] Aula 04 Mecânica Molecular Campo de força Exemplos de Campo de Força Dinâmica Molecular Etapas envolvidas
Características AULA 11. Características e Propriedades. drug-like (fármaco-similar) Bioativo-similar
 AULA 11 rganização e gerenciamento de bases de dados padrões Emprego de pré-filtros: otimização das bases de dados (e.g., seleção por tipo de átomo: C,,,, S, F, Cl, Br, P) Características e Propriedades
AULA 11 rganização e gerenciamento de bases de dados padrões Emprego de pré-filtros: otimização das bases de dados (e.g., seleção por tipo de átomo: C,,,, S, F, Cl, Br, P) Características e Propriedades
04/10/2011 FORÇAS DE INTERAÇÃO MOLECULAR ENTRE LIGANTES E PROTEÍNAS. O que é um medicamento?
 FORÇAS DE INTERAÇÃO MOLECULAR ENTRE LIGANTES E PROTEÍNAS O que é um medicamento? 1 O que é um medicamento? Medicamento (produto final) Excipientes + Principio ativo ( fármaco, droga ) Como atua uma droga?
FORÇAS DE INTERAÇÃO MOLECULAR ENTRE LIGANTES E PROTEÍNAS O que é um medicamento? 1 O que é um medicamento? Medicamento (produto final) Excipientes + Principio ativo ( fármaco, droga ) Como atua uma droga?
FFI0750 Biologia Molecular Estrutural
 Objetivos FFI0750 Biologia Molecular Estrutural Prof. Rafael V. C. Guido [email protected] Estrutura de proteínas Estrutura primária Estrutura secundária Estrutura terciária Estrutura quaternária Aula
Objetivos FFI0750 Biologia Molecular Estrutural Prof. Rafael V. C. Guido [email protected] Estrutura de proteínas Estrutura primária Estrutura secundária Estrutura terciária Estrutura quaternária Aula
BIOQUÍMICA I 1º ano de Medicina Ensino teórico 2010/2011
 BIOQUÍMICA I 1º ano de Medicina Ensino teórico 2010/2011 7ª aula teórica 11 Outubro 2010 Proteínas estruturais e funcionais Organização estrutural das proteínas Estrutura e diferentes funções de proteínas
BIOQUÍMICA I 1º ano de Medicina Ensino teórico 2010/2011 7ª aula teórica 11 Outubro 2010 Proteínas estruturais e funcionais Organização estrutural das proteínas Estrutura e diferentes funções de proteínas
3. Cite e explique cada uma das etapas envolvidas no processo de planejamento e desenvolvimento de fármacos.
 ESTUD DIRIGID 1 o BIMESTRE QUÍMICA FARMACÊUTICA Profa. Andrea e-mail:[email protected] BSERVAÇÃ: estudo dirigido em questão, apresenta a finalidade de AUXILIAR os alunos na organização e estudo
ESTUD DIRIGID 1 o BIMESTRE QUÍMICA FARMACÊUTICA Profa. Andrea e-mail:[email protected] BSERVAÇÃ: estudo dirigido em questão, apresenta a finalidade de AUXILIAR os alunos na organização e estudo
Determinação da Estrutura de Proteínas
 Centro Brasileiro-Argentino de Biotecnologia Introdução à Biologia Computacional Determinação da Estrutura de Proteínas Paulo enrique C. Godoi Bioinformática objetivo principal é determinar a função de
Centro Brasileiro-Argentino de Biotecnologia Introdução à Biologia Computacional Determinação da Estrutura de Proteínas Paulo enrique C. Godoi Bioinformática objetivo principal é determinar a função de
Proteínas. Proteínas são polímeros de aminoácidos
 Proteínas Estrutura & Propriedades Proteínas são polímeros de aminoácidos Existem 20 tipos diferentes de aminoácidos Aminoácidos são ácidos fracos A carga elétrica do aminoácido varia de acordo com o ph
Proteínas Estrutura & Propriedades Proteínas são polímeros de aminoácidos Existem 20 tipos diferentes de aminoácidos Aminoácidos são ácidos fracos A carga elétrica do aminoácido varia de acordo com o ph
Proteínas II. (Enzimas) Bioquímica Prof. Dr. Marcelo Soares
 Proteínas II (Enzimas) Conceitos Gerais e Funções As enzimas são proteínas especializadas na catálise de reações biológicas Consideradas as biomoléculas mais notáveis devido a sua extraordinária especificidade
Proteínas II (Enzimas) Conceitos Gerais e Funções As enzimas são proteínas especializadas na catálise de reações biológicas Consideradas as biomoléculas mais notáveis devido a sua extraordinária especificidade
Peptídeos e Proteínas: Estrutura de Proteínas
 Peptídeos e Proteínas: Estrutura de Proteínas QFL0343 - REATIVIDADE DE COMPOSTOS ORGÂNICOS II E BIOMOLÉCULAS Adriana Uehara 9820384 Janaína Novais 9819722 Aminoácidos Estruturas carbônicas que possuem
Peptídeos e Proteínas: Estrutura de Proteínas QFL0343 - REATIVIDADE DE COMPOSTOS ORGÂNICOS II E BIOMOLÉCULAS Adriana Uehara 9820384 Janaína Novais 9819722 Aminoácidos Estruturas carbônicas que possuem
Proteínas. Profa. Alana Cecília
 Proteínas Profa. Alana Cecília Proteínas Aminoácidos ligados formam uma cadeia proteica (polipeptídica). As unidades de repetição são planos de amida que contêm ligações peptídicas. Esses planos de amida
Proteínas Profa. Alana Cecília Proteínas Aminoácidos ligados formam uma cadeia proteica (polipeptídica). As unidades de repetição são planos de amida que contêm ligações peptídicas. Esses planos de amida
Estudo da velocidade da reação enzimática e como ela se altera em função de diferentes parâmetros
 Estudo da velocidade da reação enzimática e como ela se altera em função de diferentes parâmetros Importante abordagem para o entendimento do mecanismo de ação de uma enzima. Vários fatores afetam a atividade
Estudo da velocidade da reação enzimática e como ela se altera em função de diferentes parâmetros Importante abordagem para o entendimento do mecanismo de ação de uma enzima. Vários fatores afetam a atividade
Universidade Salgado de Oliveira Disciplina de Bioquímica Básica Proteínas
 Universidade Salgado de Oliveira Disciplina de Bioquímica Básica Proteínas Profª Larissa dos Santos Introdução As proteínas (ou também conhecidas como polipeptídeos) são as macromoléculas mais abundantes
Universidade Salgado de Oliveira Disciplina de Bioquímica Básica Proteínas Profª Larissa dos Santos Introdução As proteínas (ou também conhecidas como polipeptídeos) são as macromoléculas mais abundantes
Fundamentos da modelagem Molecular - 1
 Fundamentos da modelagem Molecular - 1 Departamento de Física UFPel Introdução Rotas para a pesquisa Conexão entre experimento, simulação e teoria Sistema real Fazer modelos do sistema Fazer experimentos
Fundamentos da modelagem Molecular - 1 Departamento de Física UFPel Introdução Rotas para a pesquisa Conexão entre experimento, simulação e teoria Sistema real Fazer modelos do sistema Fazer experimentos
Gabriela Sehnem Heck 1,2, Prof. Dr. Walter F. de Azevedo Jr 2. (orientador)
 Pontifícia Universidade Católica do Rio Grande do Sul Gabriela Sehnem Heck 1,2, Prof. Dr. Walter F. de Azevedo Jr 2. (orientador) 1 Acadêmica de Curso de Ciêncas Biológicas da PUCRS, 2 Laboratório de Bioquímica
Pontifícia Universidade Católica do Rio Grande do Sul Gabriela Sehnem Heck 1,2, Prof. Dr. Walter F. de Azevedo Jr 2. (orientador) 1 Acadêmica de Curso de Ciêncas Biológicas da PUCRS, 2 Laboratório de Bioquímica
Universidade de São Paulo QFL0343: Reações de Compostos Orgânicos II e Biomoléculas Grupo 2: Peptídeos e Proteínas - Estrutura de Proteínas
 Universidade de São Paulo QFL0343: Reações de Compostos Orgânicos II e Biomoléculas - 2016 Grupo 2: Peptídeos e Proteínas - Estrutura de Proteínas Alex Monteiro Magalhães (8020779) Karina Brandt (8566483)
Universidade de São Paulo QFL0343: Reações de Compostos Orgânicos II e Biomoléculas - 2016 Grupo 2: Peptídeos e Proteínas - Estrutura de Proteínas Alex Monteiro Magalhães (8020779) Karina Brandt (8566483)
Disciplina Biologia Celular. Profª Cristina Lacerda Soares Petrarolha Silva Curso de Agronomia FISMA / FEA
 Disciplina Biologia Celular Profª Cristina Lacerda Soares Petrarolha Silva Curso de Agronomia FISMA / FEA Aula 4: Bases Macromoleculares da Constituição Celular Bio Cel Profª Cristina Introdução Células
Disciplina Biologia Celular Profª Cristina Lacerda Soares Petrarolha Silva Curso de Agronomia FISMA / FEA Aula 4: Bases Macromoleculares da Constituição Celular Bio Cel Profª Cristina Introdução Células
Enzimas. As enzimas são proteínas com exceção de um pequeno grupo de moléculas de RNA que tem ação catalítica.
 Enzimas As enzimas são proteínas com exceção de um pequeno grupo de moléculas de RNA que tem ação catalítica. Diferem dos catalisadores comuns em vários aspectos Velocidades de reações catalisadas por
Enzimas As enzimas são proteínas com exceção de um pequeno grupo de moléculas de RNA que tem ação catalítica. Diferem dos catalisadores comuns em vários aspectos Velocidades de reações catalisadas por
Enzimas versus outros catalisadores
 Enzimas versus outros catalisadores Catalisadores proteicos Elevados factores de aceleração das reacções Grande especificidade para os substratos Estereo-especificidade (também absoluta) Reduzido número
Enzimas versus outros catalisadores Catalisadores proteicos Elevados factores de aceleração das reacções Grande especificidade para os substratos Estereo-especificidade (também absoluta) Reduzido número
BIOQUÍMICA PARA ODONTO
 BIOQUÍMICA PARA ODONTO Aula 3: Autoria: Ligação peptídica Proteínas globulares: estrutura primária, secundária e terciária Luiza Higa Programa de Biologia Estrutural Instituto de Bioquímica Médica Universidade
BIOQUÍMICA PARA ODONTO Aula 3: Autoria: Ligação peptídica Proteínas globulares: estrutura primária, secundária e terciária Luiza Higa Programa de Biologia Estrutural Instituto de Bioquímica Médica Universidade
Enzimas - Sítio catalítico
 Enzimas - Sítio catalítico Significado de cofator, grupo prostético e coenzima Enzima holozima Grupo prostético metal cofator coenzima Distinção entre cofator e coenzima depende da força de ligação com
Enzimas - Sítio catalítico Significado de cofator, grupo prostético e coenzima Enzima holozima Grupo prostético metal cofator coenzima Distinção entre cofator e coenzima depende da força de ligação com
Polaridade, Geometria Molecular e Forças Intermoleculares
 Polaridade, Geometria Molecular e Forças Intermoleculares Polaridade das Ligações x Polaridade das Moléculas Polaridade das Ligações Ligações covalentes Apolares: elétrons são compartilhados igualmente
Polaridade, Geometria Molecular e Forças Intermoleculares Polaridade das Ligações x Polaridade das Moléculas Polaridade das Ligações Ligações covalentes Apolares: elétrons são compartilhados igualmente
PROTEÍNAS. A palavra proteína derivada de proteos, (grego = primeira ou a mais importante)
 PROTEÍNAS A palavra proteína derivada de proteos, (grego = primeira ou a mais importante) Macromolécula mais abundante nas células Produto final da informação genética (DNA-RNA-Proteína) Diversidade funcional
PROTEÍNAS A palavra proteína derivada de proteos, (grego = primeira ou a mais importante) Macromolécula mais abundante nas células Produto final da informação genética (DNA-RNA-Proteína) Diversidade funcional
Profº Lásaro Henrique
 Profº Lásaro Henrique Proteínas são macromoléculas complexas, compostas de aminoácidos. São os constituintes básicos da vida e necessárias para os processos químicos que ocorrem nos organismos vivos. Nos
Profº Lásaro Henrique Proteínas são macromoléculas complexas, compostas de aminoácidos. São os constituintes básicos da vida e necessárias para os processos químicos que ocorrem nos organismos vivos. Nos
Referência: Primeira parte Docking nativo do composto co-cristalizado
 Tutorial Docking utilizando AUTODOCK Vina Profa. Rafaela Salgado Ferreira Departamento de Bioquímica e Imunologia - Universidade Federal de Minas Gerais Referência: AutoDockVina - Trott O, Olson AJ. AutoDock
Tutorial Docking utilizando AUTODOCK Vina Profa. Rafaela Salgado Ferreira Departamento de Bioquímica e Imunologia - Universidade Federal de Minas Gerais Referência: AutoDockVina - Trott O, Olson AJ. AutoDock
ENZIMAS ENZIMAS ENZIMAS 19/02/17 DEFINIÇÃO CLASSIFICAÇÃO ESTRUTURAL. ativa. inativa
 DFNÇÃO nzimas são proteínas que atuam como catalisadores biológicos o Aceleram a velocidade das reações químicas o Não alteram os produtos finais das reações o Zimogênio (inativas) / nzima (ativas) Composto
DFNÇÃO nzimas são proteínas que atuam como catalisadores biológicos o Aceleram a velocidade das reações químicas o Não alteram os produtos finais das reações o Zimogênio (inativas) / nzima (ativas) Composto
Estrutura Secundária
 Bioinformática I Estrutura Secundária Profa. Dra. Ignez Caracelli [email protected] Julio Zukerman Schpector 1 Ignez Caracelli aminoácido em sua forma ionizada forma zwitteriônica cadeia lateral amino-terminal
Bioinformática I Estrutura Secundária Profa. Dra. Ignez Caracelli [email protected] Julio Zukerman Schpector 1 Ignez Caracelli aminoácido em sua forma ionizada forma zwitteriônica cadeia lateral amino-terminal
29/08/2015 QUÍMICA DE PROTEÍNAS. Medicina Veterinária IBGM - IBS. Medicina Veterinária IBGM - IBS
 QUÍMICA DE PROTEÍNAS D i s c i p l i n a : b i o q u í m i c a, p r o f. D r. Va g n e O l i v e i ra E-mail: [email protected] Medicina Veterinária IBGM - IBS Medicina Veterinária IBGM -
QUÍMICA DE PROTEÍNAS D i s c i p l i n a : b i o q u í m i c a, p r o f. D r. Va g n e O l i v e i ra E-mail: [email protected] Medicina Veterinária IBGM - IBS Medicina Veterinária IBGM -
Soluções para Conjunto de Problemas 1
 Soluções para 7.012 Conjunto de Problemas 1 Pergunta 1 a) Quais são os quatro principais tipos de moléculas biológicas discutidas na palestra? Cite uma função importante para cada tipo de molécula biológica
Soluções para 7.012 Conjunto de Problemas 1 Pergunta 1 a) Quais são os quatro principais tipos de moléculas biológicas discutidas na palestra? Cite uma função importante para cada tipo de molécula biológica
Componentes Químicos das Células
 Componentes Químicos das Células Os seres vivos são um sistema Fundamentam-se em: químico! compostos de carbono, ou seja, na química orgânica. Dependem de reações químicas que ocorrem em soluções aquosas,
Componentes Químicos das Células Os seres vivos são um sistema Fundamentam-se em: químico! compostos de carbono, ou seja, na química orgânica. Dependem de reações químicas que ocorrem em soluções aquosas,
UNIFESO Engenharia Ambiental Prof.: Edson R. Fernandes dos Santos Aminoácidos
 UNIFESO Engenharia Ambiental Prof.: Edson R. Fernandes dos Santos Aminoácidos Clique para editar o estilo do subtítulo mestre α-aminoácidos Variações possíveis Estrutura básica Amina Ácido Carboxílico
UNIFESO Engenharia Ambiental Prof.: Edson R. Fernandes dos Santos Aminoácidos Clique para editar o estilo do subtítulo mestre α-aminoácidos Variações possíveis Estrutura básica Amina Ácido Carboxílico
Química Orgânica I Profa. Dra. Alceni Augusta Werle Profa. Dra. Tania Márcia do Sacramento Melo
 Química Orgânica I Profa. Dra. Alceni Augusta Werle Profa. Dra. Tania Márcia do Sacramento Melo Formas de representação e interações intermoleculares Aula 3 1- Fórmula química Maneira que os químicos possuem
Química Orgânica I Profa. Dra. Alceni Augusta Werle Profa. Dra. Tania Márcia do Sacramento Melo Formas de representação e interações intermoleculares Aula 3 1- Fórmula química Maneira que os químicos possuem
Aula 2: Estrutura e Função de Proteínas
 Disciplina de Mét. Purif. e Anál. Proteínas Curso de Ciências Biológicas Aula 2: Estrutura e Função de Proteínas Prof. Marcos Túlio de Oliveira [email protected] Faculdade de Ciências Agrárias e
Disciplina de Mét. Purif. e Anál. Proteínas Curso de Ciências Biológicas Aula 2: Estrutura e Função de Proteínas Prof. Marcos Túlio de Oliveira [email protected] Faculdade de Ciências Agrárias e
Biologia Molecular (Parte I)
 Biologia Molecular (Parte I) Introdução 1. Substâncias Inorgânicas 1.1. Água A água faz pontes de hidrogênio Polaridade Propriedades da água Solvente Universal Participa de reações químicas vitais Adesão
Biologia Molecular (Parte I) Introdução 1. Substâncias Inorgânicas 1.1. Água A água faz pontes de hidrogênio Polaridade Propriedades da água Solvente Universal Participa de reações químicas vitais Adesão
ESTABILIDADE DE ENZIMAS
 ESTABILIDADE DE ENZIMAS Estabilidade Enzimática X Atividade Enzimática Atividade Enzimática: É dada pela medição da velocidade inicial da reação sob uma faixa de condições determinadas. Establidade Enzimática:
ESTABILIDADE DE ENZIMAS Estabilidade Enzimática X Atividade Enzimática Atividade Enzimática: É dada pela medição da velocidade inicial da reação sob uma faixa de condições determinadas. Establidade Enzimática:
Ressonância, Formas de respresentação de moléculas orgânicas, Forças intermoleculares. Aula 3
 Universidade Federal de uro Preto Ressonância, Formas de respresentação de moléculas orgânicas, Forças intermoleculares Aula 3 Flaviane Francisco ilário 1 1 Ressonância ESTRUTURA DE LEWIS Explica de maneira
Universidade Federal de uro Preto Ressonância, Formas de respresentação de moléculas orgânicas, Forças intermoleculares Aula 3 Flaviane Francisco ilário 1 1 Ressonância ESTRUTURA DE LEWIS Explica de maneira
Enzimas. Disciplina: Bioquímica Curso: Análises Clínicas 3º. Módulo Docente: Profa. Dra. Marilanda Ferreira Bellini
 Enzimas Disciplina: Bioquímica Curso: Análises Clínicas 3º. Módulo Docente: Profa. Dra. Marilanda Ferreira Bellini Enzimas Proteínas especializadas em catalisar reações biológicas, ou seja aumentam a velocidade
Enzimas Disciplina: Bioquímica Curso: Análises Clínicas 3º. Módulo Docente: Profa. Dra. Marilanda Ferreira Bellini Enzimas Proteínas especializadas em catalisar reações biológicas, ou seja aumentam a velocidade
ALVOS MOLECULARES DA AÇÃO DE FÁRMACOS
 ALVS MLECULARES DA AÇÃ DE FÁRMACS Como os fármacos funcionam? Prof. Msc.: Inácio Lino 1 Quais são os ALVS MLECULARES dos fármacos? carboidratos lipídios receptores enzimas ácidos nucléicos 2 ALVS MLECULARES:
ALVS MLECULARES DA AÇÃ DE FÁRMACS Como os fármacos funcionam? Prof. Msc.: Inácio Lino 1 Quais são os ALVS MLECULARES dos fármacos? carboidratos lipídios receptores enzimas ácidos nucléicos 2 ALVS MLECULARES:
Programa Analítico de Disciplina BQI460 Bioinformática
 0 Programa Analítico de Disciplina Departamento de Bioquímica e Biologia Molecular - Centro de Ciências Biológicas e da Saúde Número de créditos: Teóricas Práticas Total Duração em semanas: 15 Carga horária
0 Programa Analítico de Disciplina Departamento de Bioquímica e Biologia Molecular - Centro de Ciências Biológicas e da Saúde Número de créditos: Teóricas Práticas Total Duração em semanas: 15 Carga horária
Bioinformática Estrutural Aula 1
 Bioinformática Estrutural Aula 1 03 de Junho de 2013 Paula Kuser-Falcão Laboratório de Bioinformática Aplicada Embrapa Informática Agropecuária [email protected] Pratique Atividade Física Paula
Bioinformática Estrutural Aula 1 03 de Junho de 2013 Paula Kuser-Falcão Laboratório de Bioinformática Aplicada Embrapa Informática Agropecuária [email protected] Pratique Atividade Física Paula
LICENCIATURA EM QUÍMICA QUÍMICA ORGÂNICA I SEGUNDO SEMESTRE 2014 PLANO DE CURSO Professora: Ana Júlia Silveira
 LICENCIATURA EM QUÍMICA QUÍMICA ORGÂNICA I SEGUNDO SEMESTRE 2014 PLANO DE CURSO Professora: Ana Júlia Silveira EMENTA QUÍMICA ORGÂNICA I Introdução a química orgânica: teoria estrutural e o átomo de carbono
LICENCIATURA EM QUÍMICA QUÍMICA ORGÂNICA I SEGUNDO SEMESTRE 2014 PLANO DE CURSO Professora: Ana Júlia Silveira EMENTA QUÍMICA ORGÂNICA I Introdução a química orgânica: teoria estrutural e o átomo de carbono
Aula de Bioquímica I. Tema: Enzimas. Prof. Dr. Júlio César Borges
 Aula de Bioquímica I Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: [email protected]
Aula de Bioquímica I Tema: Enzimas Prof. Dr. Júlio César Borges Depto. de Química e Física Molecular DQFM Instituto de Química de São Carlos IQSC Universidade de São Paulo USP E-mail: [email protected]
LIGAÇÃO PEPTÍDICA. ligação peptídica DIPEPTÍDEO AMINOÁCIDOS
 PROTEÍNAS PROTEÍNAS LIGAÇÃO PEPTÍDICA DIPEPTÍDEO AMINOÁCIDOS ligação peptídica PEPTÍDEO Resíduo N-terminal Resíduo C-terminal OLIGOPEPTÍDEOS: 2 a 10 resíduos de aminoácidos. Exemplos: dipeptídio (2 aminoácidos),
PROTEÍNAS PROTEÍNAS LIGAÇÃO PEPTÍDICA DIPEPTÍDEO AMINOÁCIDOS ligação peptídica PEPTÍDEO Resíduo N-terminal Resíduo C-terminal OLIGOPEPTÍDEOS: 2 a 10 resíduos de aminoácidos. Exemplos: dipeptídio (2 aminoácidos),
São macromoléculas formadas pela união de muitos aminoácidos. Esses aminoácidos estão ligados um ao outro por meio de ligações peptídicas.
 São macromoléculas formadas pela união de muitos aminoácidos. Esses aminoácidos estão ligados um ao outro por meio de ligações peptídicas. Proteínas possuem muitas funções dentro do organismo. Aminoácidos
São macromoléculas formadas pela união de muitos aminoácidos. Esses aminoácidos estão ligados um ao outro por meio de ligações peptídicas. Proteínas possuem muitas funções dentro do organismo. Aminoácidos
LIGAÇÕES QUÍMICAS REVISÃO
 LIGAÇÕES QUÍMICAS REVISÃO Ligações químicas e forças atrativas 1- Ligações covalentes Ligação química entre dois átomos na qual elétrons são compartilhados Ligação Forte Energia de ligação é a energia
LIGAÇÕES QUÍMICAS REVISÃO Ligações químicas e forças atrativas 1- Ligações covalentes Ligação química entre dois átomos na qual elétrons são compartilhados Ligação Forte Energia de ligação é a energia
10 FORMAS ESTATÍSTICA MODELAGEM PARA USAR
 10 FORMAS PARA USAR MODELAGEM ESTATÍSTICA Introdução Conheça um pouco mais sobre algumas modelagens estatísticas e como você pode implantar dentro da sua organização A análise preditiva é capaz de descobrir
10 FORMAS PARA USAR MODELAGEM ESTATÍSTICA Introdução Conheça um pouco mais sobre algumas modelagens estatísticas e como você pode implantar dentro da sua organização A análise preditiva é capaz de descobrir
Estrutura de Lewis, Formas de representação e Interações intermoleculares. Aula 2
 Universidade Federal de Ouro Preto Estrutura de Lewis, Formas de representação e Interações intermoleculares Aula 2 Flaviane Francisco ilário 1 1 Estrutura de Lewis Um símbolo de Lewis é um símbolo no
Universidade Federal de Ouro Preto Estrutura de Lewis, Formas de representação e Interações intermoleculares Aula 2 Flaviane Francisco ilário 1 1 Estrutura de Lewis Um símbolo de Lewis é um símbolo no
Dos genes às proteínas
 Dos genes às proteínas - Estrutura e função Bioinformática aula 1 INTRODUÇÃO O Dogma Central O fluxo de informação nos organismos segue uma direção única: do DNA para o RNA, e do RNA para a proteína DNA
Dos genes às proteínas - Estrutura e função Bioinformática aula 1 INTRODUÇÃO O Dogma Central O fluxo de informação nos organismos segue uma direção única: do DNA para o RNA, e do RNA para a proteína DNA
CONFORMAÇÕES DO CICLOEXANO: um modelo de estudo no PCMODEL
 CONFORMAÇÕES DO CICLOEXANO: um modelo de estudo no PCMODEL Anderson Hollerbach Klier 1 RESUMO: O estudo molecular conformacional ainda é visto como um dos entraves para o entendimento de estabilidade molecular
CONFORMAÇÕES DO CICLOEXANO: um modelo de estudo no PCMODEL Anderson Hollerbach Klier 1 RESUMO: O estudo molecular conformacional ainda é visto como um dos entraves para o entendimento de estabilidade molecular
Proteínas. - Revisão - Prof a. Dr a. Elisa d Avila Costa Cavalcanti. Bromatologia EN/UNIRIO
 Proteínas - Revisão - Prof a. Dr a. Elisa d Avila Costa Cavalcanti Bromatologia EN/UNIRIO 2018.2 O que são proteínas? Aminoácidos α 21 tipos Grupos R Tendência de interagir com a água em ph intracelular
Proteínas - Revisão - Prof a. Dr a. Elisa d Avila Costa Cavalcanti Bromatologia EN/UNIRIO 2018.2 O que são proteínas? Aminoácidos α 21 tipos Grupos R Tendência de interagir com a água em ph intracelular
Estrutura Primária de Proteínas: Sequenciamento de Aminoácidos
 UNIVERSIDADE DE SÃO PAULO USP FARMÁCIA BIOQUÍMICA 015N Reatividade de Compostos Orgânicos II Estrutura Primária de Proteínas: Sequenciamento de Aminoácidos Beatriz In Soon Chang (9328183) João Gabriel
UNIVERSIDADE DE SÃO PAULO USP FARMÁCIA BIOQUÍMICA 015N Reatividade de Compostos Orgânicos II Estrutura Primária de Proteínas: Sequenciamento de Aminoácidos Beatriz In Soon Chang (9328183) João Gabriel
